このコンテンツを視聴するには、JoVE 購読が必要です。 サインイン又は無料トライアルを申し込む。
肝脂肪症評価のための3D再構成による蛍光染色された脂肪滴の分析
要約
ここでは、肝臓組織における脂肪滴の特性評価に最適化されたBODIPY 493/503蛍光ベースのプロトコルを示します。直交投影と3D再構成を使用することにより、蛍光色素は微小小胞性脂肪症と大水疱性脂肪症の識別に成功し、肝脂肪症評価のための古典的な組織学的プロトコルへの補完的なアプローチを表す可能性があります。
要約
脂肪滴(LD)は、脂質貯蔵を媒介する特殊な細胞小器官であり、脂肪毒性の抑制や遊離脂肪酸(FA)による機能障害の予防に非常に重要な役割を果たしています。肝臓は、体の脂肪代謝におけるその重要な役割を考えると、小胞性および大小胞性肝脂肪症の両方の形でのLDの細胞内蓄積によって持続的に脅かされています。LDの組織学的特性評価は、通常、オイルレッドO(ORO)染色などの脂溶性ジアゾ色素に基づいていますが、多くの欠点が肝臓標本でのこの分析の使用を一貫して妨げています。最近では、親油性蛍光色素493/503は、中性脂肪滴コアへの迅速な取り込みと蓄積により、LDの可視化と位置特定に一般的になっています。ほとんどのアプリケーションは細胞培養で十分に説明されていますが、組織サンプルにおけるLDイメージングツールとしての親油性蛍光色素プローブの信頼性の高い使用を実証する証拠はほとんどありません。ここでは、最適化されたホウ素ジピロメテン(BODIPY)493/503ベースのプロトコルを提案します 高脂肪食(HFD)誘発肝脂肪症の動物モデルからの肝臓検体中のLDの評価。このプロトコルは、肝臓サンプル調製、組織切片作成、BODIPY 493/503染色、画像取得、およびデータ分析をカバーしています。HFD給餌時の肝LDの数、強度、面積比、および直径の増加を示しています。直交投影と3D再構成を使用して、ほぼ球形の液滴として現れるLDコアの中性脂質の完全な含有量を観察することができました。さらに、蛍光色素BODIPY 493/503では、マイクロベシクル(1 μm < d ≤ 3 μm)、中間小胞(3 μm < d ≤ 9 μm)、マクロベシクル(d > 9 μm)を区別することができ、微小小胞および大小胞脂肪症の識別に成功しました。全体として、このBODIPY 493/503蛍光ベースのプロトコルは、肝臓LDの特性評価のための信頼性が高くシンプルなツールであり、古典的な組織学的プロトコルに対する補完的なアプローチを表す可能性があります。
概要
古典的にエネルギー貯蔵庫と見なされる脂肪滴(LD)は、脂質貯蔵を媒介する特殊な細胞小器官であり、リン脂質単層1,2,3によってカプセル化されたコレステロールエステルおよびトリグリセリド(TG)を主成分とする疎水性の中性脂質コアを含む。
LD生合成は、トリアシルグリセロール(TAG)およびステロールエステルの合成から始めて、小胞体(ER)で起こる。中性脂質は、低濃度では小胞体二重層の小葉の間に拡散しますが、細胞内濃度が増加すると、小胞体膜からほぼ球形の液滴に成長して発芽する油レンズに合体します4。続いて、ER二重層およびサイトゾルからのタンパク質、特にペリリピン(PLIN)タンパク質ファミリーがLDの表面に移行し、出芽を促進します5、6、7、8、9。
新しい脂肪酸合成とLD融合または合体により、LDはさまざまなサイズに成長します。したがって、LDのサイズと数は、細胞タイプによって大きく異なります。初期LD(iLD)として知られる小さな液滴(直径300〜800 nm)は、ほぼすべての細胞によって形成され得る4。LD形成の後半では、ほとんどの細胞はいくつかのiLDをより大きなiLDに変換することができます-より大きな拡張LD(直径>1μmのeLD)。しかし、脂肪細胞や肝細胞などの特定の細胞型だけが、巨大または超大型のLD(直径数十ミクロンまで)を形成する能力を持っています4,10。
LDは、細胞の脂質代謝の調節、脂肪毒性の抑制、小胞体ストレス、ミトコンドリア機能障害、そして最終的には遊離脂肪酸(FA)によって引き起こされる細胞死の予防に非常に重要な役割を果たします11,12,13,14。さらに、LDは、遺伝子発現、ウイルス複製タンパク質隔離、および膜輸送およびシグナル伝達の調節にも関与しています15,16,17。したがって、LD生合成の誤調節は、メタボリックシンドローム、肥満、2型糖尿病(T2DM)、および/または動脈硬化に関連する慢性疾患の特徴であり、ほんの数例を挙げると18,19,20です。
肝臓は、代謝ハブとして、脂質を貯蔵および処理することによって脂質代謝に主に関与しているため、脂肪毒性によって常に脅かされています21。肝脂肪症(HS)は、一連の進行性肝疾患の一般的な特徴であり、細胞質LDの形での過剰な細胞内脂質蓄積を特徴とし、最終的には肝代謝機能障害、炎症、および進行型の非アルコール性脂肪性肝疾患につながる可能性があります22,23,24,25.HSは、超低密度リポタンパク質(VLDL)内の脂肪酸の酸化およびトリグリセリドとしての輸出の速度が、血漿およびde novo脂肪酸合成からの肝脂肪酸の取り込み速度よりも低い場合に発生します26。脂質の肝蓄積は、しばしば2つの形態(微小小胞および大小胞脂肪症)で起こり、これらは明確な細胞アーキテクト学的特徴を示す27。典型的には、微小小胞脂肪症は、核が中央に配置された肝細胞全体に分散した小さなLDの存在によって特徴付けられるのに対し、大小胞脂肪症は、肝細胞の大部分を占める単一の大きなLDの存在によって特徴付けられ、核を末梢に押し出す28,29。.特に、これら2種類の脂肪症はしばしば一緒に発見され、証拠がまだ一貫していないため、これら2つのLDパターンが疾患の病因にどのように影響するかは不明のままです31,32,33,34。しかし、このようなタイプの分析は、LDの動的挙動を理解し、肝脂肪症を特徴付けるための前臨床および臨床試験の「参照標準」としてしばしば採用されます29,34,35,36。
HSの診断と等級付けのゴールドスタンダードである肝生検は、組織学的ヘマトキシリンおよびエオジン(H&E)分析によって日常的に評価され、脂肪滴はH&E染色された肝臓切片の染色されていない液胞として評価されます37。大水疱性脂肪症の評価には許容できるが、このタイプの染色は一般に微小小胞脂肪症の評価を狭める38。Oil Red O(ORO)などの脂溶性ジアゾ色素は、細胞内脂質貯蔵を分析するために古典的に明視野顕微鏡と組み合わされますが、これらには依然として多くの欠点があります:(i)染色プロセスでのエタノールまたはイソプロパノールの使用、これはしばしば天然LDの破壊を引き起こし、細胞が固定されているにもかかわらず時折融合します39;(ii)ORO溶液は貯蔵寿命が限られているため、新鮮な粉末の溶解とろ過が必要なため、時間のかかる性質により、一貫性の低い結果に寄与します。(iii)そして、OROが単なる脂肪滴以上のものを染色し、しばしば肝脂肪症を過大評価するという事実38。
その結果、Nile Redなどの細胞透過性親油性蛍光色素は、前述の制限のいくつかを克服するために、生サンプルまたは固定サンプルのいずれかで使用されてきました。しかし、細胞脂質オルガネラ標識の非特異的な性質は、LD評価を繰り返し狭めます40。さらに、ナイルレッドのスペクトル特性は環境の極性によって変化し、スペクトルシフト41につながることがよくあります。
親油性蛍光プローブである1,3,5,7,8-ペンタメチル-4-ボラ-3a,4ジアザ-s-インダセン(励起波長:480 nm; 発光極大:515 nm;BODIPY 493/503)は、細胞内LDによる迅速な取り込みを可能にする疎水性特性を示し、脂肪滴コアに蓄積し、続いて明るい緑色の蛍光を発する12。ナイルレッドとは異なり、BODIPY 493/503は環境の極性に敏感ではなく、LDイメージング用に高輝度を表示するため、より選択的であることが示されています。中性LDを染色するために、この色素は生細胞または固定細胞で使用でき、他の染色および/または標識法とうまく結合することができます42。色素の別の利点は、溶液に入れるのにほとんど労力を必要とせず、安定であり、したがって、各実験42のためにそれを新たに調製する必要性を排除することである。BODIPY 493/503プローブは、細胞培養におけるLDの局在と動態を可視化するために成功裏に使用されていますが、ヒト外側広筋43、ラットヒラメ筋42、マウス腸44などの組織におけるLDイメージングツールとしてのこの色素の信頼性の高い使用も実証されています。
ここでは、肝脂肪症の動物モデルからの肝臓検体のLD数、面積、および直径を評価するための代替分析アプローチとして、最適化されたBODIPY 493/503ベースのプロトコルを提案します。この手順では、肝臓サンプルの準備、組織切片作成、染色条件、画像取得、およびデータ分析について説明します。
プロトコル
この研究で実施されたすべての動物の手順は、コインブラ臨床生物医学研究所(iCBR)の動物福祉団体(ORBEA、#9/2018)によって承認され、アニマルケア国内および欧州指令およびARRIVEガイドラインに準拠しています。
1. 実験計画
- ペアハウス13週齢のオスのWistarラットを、温度(22°C±1°C)、湿度(50%-60%)、および明るい(12時間の明暗サイクル)の制御された環境条件下で、水道水と標準的なげっ歯類の飼料への 自由 アクセス。
- 2週間の順応期間の後、ラットを任意に2つのグループに割り当てる。
- 対照群(CTRL、n = 6)および高脂肪食群(HFD、n = 6)に、それぞれ標準飼料および高脂肪食(45%kcal /脂肪)を24週間給餌する。
- 毎週体重(BW)を監視します。ケージごとに毎日食べ物と飲み物の消費量を記録します。
2.肝臓サンプル調製
- 肝解離
- 蠕動ポンプの準備:70%エタノールをチューブに通し、27 Gの針をチューブの出口端に接続し、氷冷(4°C)1xリン酸緩衝生理食塩水(PBS、pH~7.4)でチューブをプライミングします(たとえば、内径1.6 mmのシリコンチューブを備えた蠕動ポンプで200 rpm、IVミニドリップセット)。体重に合わせて調整します(たとえば、100〜150 gのラットの場合、約10〜12 mL / minの流量を使用します)。.
- 麻酔プロトコルを使用した腹腔内注射によってラットを麻酔します(ケタミンの最終濃度= 75 mg / kg、およびメデトミジンの最終濃度= 1 mg / kg)。.
注意: つま先のつまみ応答方法を使用して、ラットが完全に麻酔されていることを確認してください。 - ラットを解剖トレイに置きます。
- 毛皮を70%エタノールで完全に消毒し、ペーパータオルで乾かします。
- ハサミを使用して、皮膚を通して「U」字型の切開を行い、横隔膜の下を切り開きます。次に、胸郭の端を吻側に切り、心臓を露出させます。
- 1x PBSが作動している間に、針を左心室を通して上行大動脈に通し、クランプします。次に、灌流が始まったら排水できるように右心房を切断します。
注意: 血液がPBSに置き換えられると、肝臓は白くなり始めるはずです。 - はさみとデュモン鉗子を使用して、肝臓を注意深く取り除き、1x PBSですすいでください。
- 肝臓をペトリ皿に移し、体重を量ります。
- メスを使用して、包埋プロセスのために肝臓の左葉の側面(端から1 cm)から厚さ5 mmの肝組織サンプルを収集します。
注 残りの組織は、長期保存のために-80°Cで保存することができます。
- 肝臓組織埋め込み
- ドライアイス容器を準備し、クライオモールドにサンプルIDと向きを適切にラベル付けします。
- クライオ包埋マトリックスをクライオモールドの中心に数滴置き、最適な切断温度(OCT)にします。
- 組織サンプルが横断面に対して適切に配置されていることを確認してください。
注意: クライオモールドの底に接触する側が最初に切断される側であることを確認してください。 - 完全に覆われるまで、さらにOCTをクライオモルドに慎重に落とします。気泡の形成を避けるようにしてください。必要に応じて、プレーン鉗子を使用して、OCT内の気泡を取り除きます。
- OCTで覆われたサンプルを入れたクライオモールドをドライアイス容器にすばやく入れます。
注:組織は-80°Cで3年間保存できます。
3.凍結組織切片作成
- クライオスタット温度(チャンバー:-21°C、試料:-18°C)を調整し、新しい滅菌ブレードを挿入します。
- 温度が平衡化する前に、サンプルをクライオスタットに30分間入れます。
- 試料ディスク上にOCTの単層を作り、試料を接着できるようにします。OCTを凍結させ、組織サンプルを希望の方向に取り付けます。
注意: 切断面はブレードと平行である必要があります。良好な接着性を維持するには、サンプルの上部に熱抽出器を置きます。前のステップは、ドライアイスの入ったドライアイス容器内でも実行できます。 - サンプルを検体ヘッドに入れ、組織の表面(数個の30 μm組織サンプル切片)をトリミングします。
- 関心領域がセクショニングのためにアクセス可能になったら、厚さ12 μmの切片を切断し、室温(RT)に保たれたラベル付き顕微鏡スライドに置きます。
注意: 切片を収集するには、スライドを組織切片に向かってゆっくりと動かします。各スライドは2つの肝臓切片を集めることができます。 - スライドをRTで10分間乾燥させます。
注意: スライドは、-20°Cで6〜12か月間、または-80°Cで最大3年間保存できます。
4.ボディ染色
- スライド染色システムでスライドをRTで30分間解凍します。
- 1x PBSで洗浄します(各3回5分間)。
- バリアペンを使用して、疎水性層でセクションを丸で囲みます。
- 500 μg/mL ボディピー 493/503 ストック溶液を調製する: 1 mg の BODIPY 493/503 を 2 mL の溶媒 (90% DMSO; 10% 1x PBS) に溶解します。光から保護してください。超音波浴中で37°Cで1時間(9.5-10W)超音波処理する。
注:溶液は-20°Cで少なくとも30日間保存できます。 - 1x PBSの997.9 μLに2 μLのBODIPY 493/503ストック溶液と0.1 μLのDAPIストック溶液(5 mg/mL)を加えて、BODIPY染色液(1 μg/mL)を調製します。
- スライド(75 μL/スライド)をBODIPY 493/503(1 μg/mL)およびDAPI(0.1 μg/mL)とともにRTで40分間インキュベートします。
注意: このステップ以降、スライドを暗闇に保管してください。 - スライドを1x PBSで洗浄します(それぞれ5分間3回)。
- 蛍光封入剤を使用してスライドをカバーガラスで取り付け、30分間乾燥させてから、マニキュアで密封します。
注:スライドは、イメージングまで4°Cで保存できます。
5. 脂質定量
- 血清総コレステロールとTGレベルを、自動で検証済みの方法と機器を使用して測定します。
- 製造元のプロトコルに従って、トリグリセリド比色アッセイキット(材料表)を使用して肝臓TGレベルを測定します。
6. 画像取得
- スライドをレーザー走査型共焦点顕微鏡スライドホルダーに置きます。
- 画像の視覚化と取得には、20倍の対物レンズ(平面アポクロマート:20倍/0.8)を備えた共焦点顕微鏡を使用します。
- BODIPY 493/503とDAPI間のクロストークを回避するには、共焦点ソフトウェアでシーケンシャル(ベスト信号)スキャンモードを使用します。
- 488 nmアルゴンレーザーラインを使用してBODIPY 593/503を励起し、405 nmレーザーラインを使用してDAPIを励起します。発光範囲を BODIPY 493/503 の場合は 493-589 nm、DAPI の場合は 410-464 nm に設定します。
- ピンホール: 1 AU、解像度: 1,024 ピクセル x 1,024 ピクセル、ビット深度: 12、ピクセルサイズ: 0.415 μm、双方向モード、スキャン速度: 7 (20 倍対物レンズの場合は ~1.58 μs/ピクセル)、ライン平均: 2x、デジタルズーム: 1.
注:上記のスキャンパラメータは、使用する共焦点顕微鏡と対物レンズごとに最適化する必要があります。 - ゲインとデジタルゲインを適切に設定して、レンジインジケータで飽和ピクセルが検出されないようにします。
注意: オフセットを調整して、バックグラウンド信号を修正します。 - LDが正しく識別されたら、BODIPYチャネルとDAPIチャネルを使用して画像を集録します。
注意: すべての画像は、各カラーチャンネルで同じ条件(露出と一般設定)で取得する必要があります。 - 広域画像を作成するには(図2)、対物レンズをa10倍対物レンズ(平面図:10倍/0.3)に変更します。
- タイルスキャンモードを選択し、5枚の画像ごとに5枚のモザイクを作成します。
注:この作業では、分析のためにタイルを適切にマージするために、各タイルに10%のオーバーラップがありました。 - 3Dおよび直交ビューを作成するには(図3A)、カバーガラスの上部に液浸オイルを滴下し、対物レンズを40倍対物レンズ(plan-neofluar:40x/1.30オイル)に変更します。
- Z スタック モードを選択し、Z平面を調整して、最適な厚さ(~0.5 μm)の光学スライスを使用して取得する最初と最後の位置を定義し、すべての液滴を確実に捕捉します。
注意: 画像取得を高速化し、漂白を避けるために、光学スライスを最適ではないサイズに調整して、優れた3D再構成のために少なくとも30%のオーバーサンプリングを確保できます。 - [直交]モジュールを選択し、 直交 ビューを作成します。
- 共焦点顕微鏡ソフトウェアで透明レンダリングモードに続いて3Dモジュールを選択して、3D画像を取得します。
7. 画像の解析
- セルプロファイラ(バージョン4.2.5)を使用して、単一平面画像(倍率20倍)を処理および分析します。
注:この作業で使用されたパイプラインは、Adomshickらから採用されました。45。 - CellProfiler ウィンドウの左上隅にある [画像 ] モジュールをクリックし、画像を .tiff ファイルとしてアップロードします。
- NamesAndTypes モジュールを使用して、ファイル名に基づいて BODIPY- (液滴) と DAPI- (核) で染色された画像を並べ替えます。LD解析は、ボディ染色画像のみで行ってください。
- パイプライン構成を開始するには、[ モジュールの調整] をクリックし、モジュール ColorToGray を選択して画像をグレースケール画像に変換します。
注: オブジェクトを識別するには、グレースケール画像が必要です。 - グレースケール画像を使用して IdentifyPrimaryObjects モジュールを使用して液滴を識別します。
注意: このモジュールのパラメータは、LDの識別を適切に行うように調整する必要があります。この作業では、6ピクセルから300ピクセルのサイズと1.0のしきい値補正係数でLDを定義すると、最も正確な識別につながりました。 - 識別された脂肪滴のピクセル強度を測定するには、 MeasureObjectIntensity モジュールを追加します。
- FilterObjectsモジュールを追加して、最も強いシグナルのみが定量され、強度の低いシグナルが最終的な脂肪滴分析から除外されるようにします(最小強度:0.15、最大強度:1任意の単位)。
- 出力データに関連する LD を測定するには、 MeasureObjectSizeShape モジュールを追加します。
- この時点で OverlayOutlines モジュールを追加して、識別された液滴を元の画像にオーバーレイし、未処理の画像でもセグメンテーションが正確に見えるようにします。
注意: これはオプションの(品質管理)ステップです。 - 最後に ExportToSpreadsheet モジュールを追加し、左下隅にある[ 画像の分析 ]ボタンをクリックします。
8.統計分析
- 統計解析ソフトウェアアプリケーションを使用して、結果を平均±平均の標準誤差(S.E.M.)として表します。
注:この研究では、統計分析にGraphPadソフトウェアを使用しました。 - コルモゴロフ-スミルノフ検定を使用して値の分布を分析し、正規性からの有意な偏差を評価します。スチューデントの対応のないt検定を使用してパラメトリックデータを分析します。
注: p <0.05の値は統計的に有意であると考えられた。
結果
この手法の実行に成功すると、LD形態(3D再構成に基づく形状と脂質コア密度)とその空間分布、総面積あたりの数、および平均サイズ(上記のパイプラインで評価、 図1)を同時に特性評価するための明確な脂肪滴染色が得られるはずです。
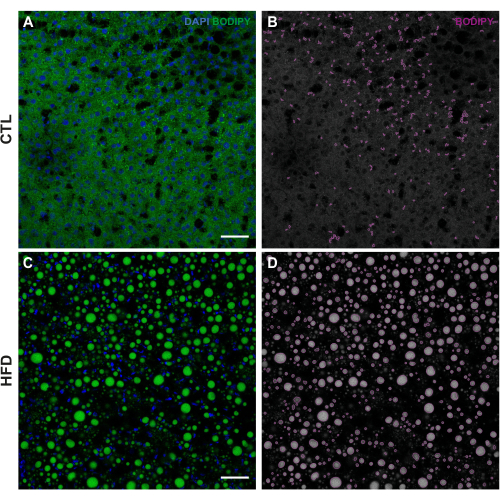
?...
ディスカッション
この BODIPY 493/503 LD評価用蛍光ベースのプロトコルは、肝脂肪症の評価のための新しいイメージングアプローチを開発することを目的としていました。肥満と脂肪肝疾患との強い相関を考慮して、西洋式の高脂肪食を使用して肝脂肪症の動物モデルを確立しました26。肝TG含有量の力強い増加は、定量的トリグリセリド比色アッセイキットによって確認され、HFD給餌動物におけ...
開示事項
著者は開示するものは何もありません。
謝辞
この研究は、ポルトガル科学技術財団(FCT)、欧州地域開発基金(FEDER)、および競争要因プログラム(COMPETE):2020.09481.BD、UIDP/04539/2020(CIBB)、およびPOCI-01-0145-FEDER-007440 を介して 、国内および欧州基金から資金提供を受けました。著者らは、コインブラ大学医学部の施設であり、国家インフラPPBI-ポルトガルバイオイメージングプラットフォーム(POCI-01-0145-FEDER-022122)のメンバーであるiLAB顕微鏡およびバイオイメージングラボのサポート、およびFSE CENTRO-04-3559-FSE-000142のサポートに感謝します。
資料
| Name | Company | Catalog Number | Comments |
| 1.6 mm I.D. silicone tubing, I.V mini drip set | Fisher Scientific | ||
| 4,4-difluoro-1,3,5,7,8-pentametil-4-bora-3a,4a-diaza-s-indaceno (BODIPY 493/503) | Sigma-Aldrich, Lyon, France | D3922 | |
| 4',6-diamidino-2-phenylindole (DAPI) | Molecular Probes Inc, Invitrogen, Eugene, OR | D1306 | |
| 70% ethanol | Honeywell | 10191455 | |
| Adobe Illustrator CC | Adobe Inc. | Used to design the figures | |
| Automatic analyzer Hitachi 717 | Roche Diagnostics Inc., Mannheim, Germany | 8177-30-0010 | |
| Barrier pen (Liquid blocker super pap pen) | Daido Sangyo Co., Ltd, Japon | _ | |
| Blade | Leica | 221052145 | Used in the cryostat |
| Cell Profiler version 4.2.5 | https://cellprofiler.org/releases/ | Used to analyse the acquired images | |
| Coverslips | Menzel-Glaser, Germany | _ | |
| Cryomolds | Tissue-Tek | _ | |
| Cryostat (including specimen disc and heat extractor) CM3050 S | Leica Biosystems | _ | |
| Dimethyl Sulfoxide (DMSO) | Sigma-Aldrich, Lyon, France | D-8418 | Used to dissolve Bodipy for the 5 mg/mL stock solution. CAUTION: Toxic and flammable. Vapors may cause irritation. Manipulate in a fume hood. Avoid direct contact with skin. Wear rubber gloves, protective eye goggles. |
| Dry ice container (styrofoam cooler) | Novolab | A26742 | |
| Dumont forceps | Fine Science Tools, Germany | 11295-10 | |
| Glass Petri dish (H 25 mm, ø 150 mm) | Thermo Scientific | 150318 | Used to weigh the liver after dissection |
| Glycergel | DAKO Omnis | S303023 | |
| GraphPad Prism software, version 9.3.1 | GraphPad Software, Inc., La Jolla, CA, USA | ||
| High-fat diet | Envigo, Barcelona, Spain | MD.08811 | |
| Ketamine (Nimatek 100 mg/mL) | Dechra | 791/01/14DFVPT | Used at a final concentration of 75 mg/kg |
| Laser scanning confocal microscope (QUASAR detection unit; ) | Carl Zeiss, germany | LSM 710 Axio Observer Z1 microscope | |
| Medetomidine (Sedator 1 mg/mL) | Dechra | 1838 ESP / 020/01/07RFVPT | Used at a final concentration of 1 mg/kg |
| Needle | BD microlance | 300635 | |
| No 15 Sterile carbon steel scalpel Blade | Swann-Morton | 205 | |
| Objectives 10x (Plan-Neofluar 10x/0.3), 20x (Plan-Apochromat 20x/0.8) and 40x (Plan-Neofluar 40x/1.30 Oil) | Carl Zeiss, Germany | ||
| Paint brushes | Van Bleiswijck Amazon B07W7KJQ2X | Used to handle cryosections | |
| Peristaltic pump (Minipuls 3) | Gilson | 1004170 | |
| Phosphate-buffered saline (PBS, pH ~ 7.4) | Sigma-Aldrich, Lyon, France | P3813 | |
| Scalpel handle, 125 mm (5"), No. 3 | Swann-Morton | 0208 | |
| Slide staining system StainTray | Simport Scientific | M920 | |
| Standard diet | Mucedola | 4RF21 | |
| Superfrost Plus microscope slides | Menzel-Glaser, Germany | J1800AMNZ | |
| Tissue-Tek OCT mounting media | VWR CHEMICALS | 361603E | |
| Triglycerides colorimetric assay kit | Cayman Chemical | 10010303 | |
| Ultrasonic bath | Bandelin Sonorex | TK 52 | |
| Vannas spring scissors - 3 mm cutting edge | Fine Science Tools, Germany | 15000-00 | |
| ZEN Black software | Zeiss |
参考文献
- Klemm, R. W., Ikonen, E. The cell biology of lipid droplets: More than just a phase. Seminars in Cell & Developmental Biology. 108, 1-3 (2020).
- Martin, S., Parton, R. G. Lipid droplets: A unified view of a dynamic organelle. Nature Reviews Molecular Cell Biology. 7 (5), 373-378 (2006).
- Thiele, C., Penno, A., Bradshaw, R. A., Stahl, P. D. Lipid droplets. Encyclopedia of Cell Biology. , 273-278 (2016).
- Gluchowski, N. L., Becuwe, M., Walther, T. C., Farese, R. V. Lipid droplets and liver disease: From basic biology to clinical implications. Nature Reviews Gastroenterology & Hepatology. 14 (6), 343-355 (2017).
- Bickel, P. E., Tansey, J. T., Welte, M. A. PAT proteins, an ancient family of lipid droplet proteins that regulate cellular lipid stores. Biochimica et Biophysica Acta. 1791 (6), 419-440 (2009).
- Olzmann, J. A., Carvalho, P. Dynamics and functions of lipid droplets. Nature Reviews. Molecular Cell Biology. 20 (3), 137-155 (2019).
- Wang, L., Liu, J., Miao, Z., Pan, Q., Cao, W. Lipid droplets and their interactions with other organelles in liver diseases. The International Journal of Biochemistry & Cell Biology. 133, 105937 (2021).
- Carr, R. M., Ahima, R. S. Pathophysiology of lipid droplet proteins in liver diseases. Experimental Cell Research. 340 (2), 187-192 (2016).
- Jackson, C. L. Lipid droplet biogenesis. Current Opinion in Cell Biology. 59, 88-96 (2019).
- Onal, G., Kutlu, O., Gozuacik, D., Dokmeci Emre, S. Lipid droplets in health and disease. Lipids in Health and Disease. 16 (1), 128 (2017).
- Wang, H., Quiroga, A. D., Lehner, R., Yang, H., Li, P. Lipid Droplets. Methods in Cell Biology. , 107-127 (2013).
- Listenberger, L. L., Brown, D. A. Fluorescent detection of lipid droplets and associated proteins. Current Protocols in Cell Biology. , (2007).
- Welte, M. A., Gould, A. P. Lipid droplet functions beyond energy storage. Biochimica et Biophysica Acta. Molecular and Cell Biology of Lipids. 1862 (10), 1260-1272 (2017).
- Roberts, M. A., Olzmann, J. A. Protein quality control and lipid droplet metabolism). Annual Review of Cell and Developmental Biology. 36, 115-139 (2020).
- Filali-Mouncef, Y., et al. The ménage à trois of autophagy, lipid droplets and liver disease. Autophagy. 18 (1), 50-72 (2022).
- Bandyopadhyay, D., et al. Lipid droplets promote phase separation of Ago2 to accelerate Dicer1 loss and decelerate miRNA activity in lipid exposed hepatic cells. bioRxiv. , (2020).
- Farías, M. A., Diethelm-Varela, B., Navarro, A. J., Kalergis, A. M., González, P. A. Interplay between lipid metabolism, lipid droplets, and DNA virus infections. Cells. 11 (14), 2224 (2022).
- Krahmer, N., Farese, R. V., Walther, T. C. Balancing the fat: Lipid droplets and human disease. EMBO Molecular Medicine. 5 (7), 973-983 (2013).
- Greenberg, A. S., et al. The role of lipid droplets in metabolic disease in rodents and humans. The Journal of Clinical Investigation. 121 (6), 2102-2110 (2011).
- Xu, S., Zhang, X., Liu, P. Lipid droplet proteins and metabolic diseases. Biochimica et Biophysica Acta. Molecular Basis of Disease. 1864 (5), 1968-1983 (2018).
- Herms, A., et al. Cell-to-cell heterogeneity in lipid droplets suggests a mechanism to reduce lipotoxicity. Current Biology. 23 (15), 1489-1496 (2013).
- Hooper, A. J., Adams, L. A., Burnett, J. R. Genetic determinants of hepatic steatosis in man. Journal of Lipid Research. 52 (4), 593-617 (2011).
- Parafati, M., Kirby, R. J., Khorasanizadeh, S., Rastinejad, F., Malany, S. A nonalcoholic fatty liver disease model in human induced pluripotent stem cell-derived hepatocytes, created by endoplasmic reticulum stress-induced steatosis. Disease Models & Mechanisms. 11 (9), (2018).
- Nassir, F., Rector, R. S., Hammoud, G. M., Ibdah, J. A. Pathogenesis and prevention of hepatic steatosis. Gastroenterology & Hepatology. 11 (3), 167-175 (2015).
- Starekova, J., Reeder, S. B. Liver fat quantification: Where do we stand. Abdominal Radiology. 45 (11), 3386-3399 (2020).
- Fabbrini, E., Sullivan, S., Klein, S. Obesity and nonalcoholic fatty liver disease: Biochemical, metabolic, and clinical implications. Hepatology. 51 (2), 679-689 (2010).
- Kristiansen, M. N. B., Veidal, S. S., Christoffersen, C., Jelsing, J., Rigbolt, K. T. G. Molecular characterization of microvesicular and macrovesicular steatosis shows widespread differences in metabolic pathways. Lipids. 54 (1), 109-115 (2019).
- Tsutsumi, V., Nakamura, T., Ueno, T., Torimura, T., Aguirre-García, J., Muriel, P. Chapter 2: Structure and ultrastructure of the normal and diseased liver. Liver Pathophysiology. , 23-44 (2017).
- Tandra, S., et al. Presence and significance of microvesicular steatosis in nonalcoholic fatty liver disease. Journal of Hepatology. 55 (3), 654-659 (2011).
- Nascimbeni, F., et al. Clinical relevance of liver histopathology and different histological classifications of NASH in adults. Expert Review of Gastroenterology & Hepatology. 12 (4), 351-367 (2018).
- Yerian, L. Histopathological evaluation of fatty and alcoholic liver diseases. Journal of Digestive Diseases. 12 (1), 17-24 (2011).
- Stöppeler, S., et al. Gender and strain-specific differences in the development of steatosis in rats. Laboratory Animals. 47 (1), 43-52 (2013).
- Hübscher, S. G., Saxena, R. Alcohol-induced liver disease. Practical Hepatic Pathology: A Diagnostic Approach (Second Edition). , 371-390 (2018).
- Sethunath, D., et al. Automated assessment of steatosis in murine fatty liver. PLoS One. 13 (5), e0197242 (2018).
- Sinton, M. C., et al. Macrovesicular steatosis in nonalcoholic fatty liver disease is a consequence of purine nucleotide cycle driven fumarate accumulation. bioRxiv. , (2020).
- de Conti, A., et al. Characterization of the variability in the extent of nonalcoholic fatty liver induced by a high-fat diet in the genetically diverse collaborative cross mouse model. The FASEB Journal. 34 (6), 7773-7785 (2020).
- Virarkar, M., Szklaruk, J., Jensen, C. T., Taggart, M. W., Bhosale, P. What's new in hepatic steatosis. Seminars in Ultrasound, CT and MRI. 42 (4), 405-415 (2021).
- Le, T. T., Ziemba, A., Urasaki, Y., Brotman, S., Pizzorno, G. Label-free evaluation of hepatic microvesicular steatosis with multimodal coherent anti-Stokes Raman scattering microscopy. PLoS One. 7 (11), e51092 (2012).
- Fam, T. K., Klymchenko, A. S., Collot, M. Recent advances in fluorescent probes for lipid droplets. Materials. 11 (9), 1768 (2018).
- Rumin, J., et al. The use of fluorescent Nile red and BODIPY for lipid measurement in microalgae. Biotechnology for Biofuels. 8 (1), 42 (2015).
- Daemen, S., van Zandvoort, M. A. M. J., Parekh, S. H., Hesselink, M. K. C. Microscopy tools for the investigation of intracellular lipid storage and dynamics. Molecular Metabolism. 5 (3), 153-163 (2015).
- Spangenburg, E. E., Pratt, S. J. P., Wohlers, L. M., Lovering, R. M. Use of BODIPY (493/503) to visualize intramuscular lipid droplets in skeletal muscle. Journal of Biomedicine & Biotechnology. 2011, 598358 (2011).
- Prats, C., et al. An optimized histochemical method to assess skeletal muscle glycogen and lipid stores reveals two metabolically distinct populations of type I muscle fibers. PLoS One. 8 (10), e77774 (2013).
- Nakano, T., et al. Ezetimibe impairs transcellular lipid trafficking and induces large lipid droplet formation in intestinal absorptive epithelial cells. Biochimica et Biophysica Acta - Molecular and Cell Biology of Lipids. 1865 (12), 158808 (2020).
- Adomshick, V., Pu, Y., Veiga-Lopez, A. Automated lipid droplet quantification system for phenotypic analysis of adipocytes using CellProfiler. Toxicology Mechanisms and Methods. 30 (5), 378-387 (2020).
- Moon, J., et al. Intravital longitudinal imaging of hepatic lipid droplet accumulation in a murine model for nonalcoholic fatty liver disease. Biomedical Optics Express. 11 (9), 5132-5146 (2020).
- Martinez-Lopez, N., Singh, R. Autophagy and lipid droplets in the liver. Annual Review of Nutrition. 35, 215-237 (2015).
- Collot, M., et al. Ultrabright and fluorogenic probes for multicolor imaging and tracking of lipid droplets in cells and tissues. Journal of the American Chemical Society. 140 (16), 5401-5411 (2018).
- Selvais, C. M., De Cock, L. L., Brichard, S. M., Davis-Lopez de Carrizosa, M. A. Fiber type and subcellular-specific analysis of lipid droplet content in skeletal muscle. Journal of Visualized Experiments: Jove. (184), e63718 (2022).
- Zhuang, H., et al. Long-term high-fat diet consumption by mice throughout adulthood induces neurobehavioral alterations and hippocampal neuronal remodeling accompanied by augmented microglial lipid accumulation. Brain, Behavior, and Immunity. 100, 155-171 (2022).
- Chen, J., Yue, F., Kuang, S. Labeling and analyzing lipid droplets in mouse muscle stem cells. STAR Protocols. 3 (4), 101849 (2022).
転載および許可
このJoVE論文のテキスト又は図を再利用するための許可を申請します
許可を申請さらに記事を探す
This article has been published
Video Coming Soon
Copyright © 2023 MyJoVE Corporation. All rights reserved