Un abonnement à JoVE est nécessaire pour voir ce contenu. Connectez-vous ou commencez votre essai gratuit.
Method Article
Les analyses microscopiques de Criblage à haut débit des facteurs de l'hôte impliqués dans
* Ces auteurs ont contribué à parts égales
Dans cet article
Résumé
Two assays for microscopy-based high-throughput screening of host factors involved in Brucella infection are described. The entry assay detects host factors required for Brucella entry and the endpoint assay those required for intracellular replication. While applicable for alternative approaches, siRNA screening in HeLa cells is used to illustrate the protocols.
Résumé
Espèces de Brucella sont des agents pathogènes intracellulaires facultatifs qui infectent les animaux comme leurs hôtes naturels. La transmission aux humains est le plus souvent causée par un contact direct avec des animaux infectés ou par ingestion d'aliments contaminés et peut conduire à des infections chroniques graves.
Brucella peut envahir les cellules phagocytaires professionnels et non-professionnels et réplique au sein du réticulum endoplasmique (RE) de vacuoles -derived. Les facteurs de l' hôte requis pour l' entrée Brucella dans des cellules hôtes, éviter la dégradation lysosomale, et la réplication dans le compartiment ER-like demeurent largement inconnus. Nous décrivons ici deux essais pour identifier les facteurs de l' hôte impliqués dans Brucella l' entrée et la réplication dans les cellules HeLa. Les protocoles décrivent l'utilisation de l'interférence ARN, alors que les méthodes de criblage alternatives pourraient être appliquées. Les essais sont basés sur la détection de bactéries marquées par fluorescence dans les cellules hôtes marquées par fluorescence en utilisant automatiséla microscopie à champ large. Les images fluorescentes sont analysées à l'aide d'un pipeline d'analyse d'image normalisée dans CellProfiler qui permet l'infection par simple pointage à base de cellules.
Dans l'essai de point final, la réplication intracellulaire est mesurée deux jours après l'infection. Cela permet aux bactéries de trafic vers leur niche réplicative où la prolifération est lancé autour de 12 heures après l' entrée bactérienne. Brucella qui ont établi avec succès une niche intracellulaire aura ainsi fortement proliféré à l' intérieur des cellules hôtes. Comme les bactéries intracellulaires grandement plus nombreux que les bactéries non réplicatifs extracellulaires ou intracellulaires individuels, une souche exprimant constitutivement GFP peut être utilisé. Le signal de la GFP solide est ensuite utilisé pour identifier les cellules infectées.
En revanche, pour le dosage d'entrée, il est essentiel de faire la distinction entre les bactéries intracellulaires et extracellulaires. Ici, un codage de déformation pour une GFP inductible par la tétracycline est utilisée. Inductionde la GFP avec l'inactivation simultanée des bactéries extracellulaires par la gentamicine permet la différenciation entre intracellulaire et extracellulaire des bactéries en fonction du signal de la GFP, seules les bactéries intracellulaires étant capable d'exprimer la GFP. Ceci permet la détection des bactéries intracellulaires robuste unique avant la prolifération intracellulaire est initiée.
Introduction
Espèces de Brucella sont, les agents pathogènes intracellulaires facultatifs Gram négatif appartenant à la classe des α-protéobactéries. Ils provoquent des avortements et l'infertilité chez leurs hôtes naturels tels que les bovins, les chèvres, les moutons ou entraînant des pertes économiques sévères dans les zones endémiques. La brucellose est l' une des maladies zoonotiques les plus importants dans le monde entier causant plus d' un demi - million de nouvelles infections humaines par an 1. La transmission à l'homme est le plus souvent causée par un contact direct avec des animaux infectés ou par ingestion d'aliments contaminés tels que le lait non pasteurisé. Les symptômes de la maladie fébrile sont non spécifiques, ce qui provoque des difficultés pour le diagnostic de la brucellose. Si non traitée, les patients peuvent développer une infection chronique avec des symptômes plus graves tels que l' arthrite, l' endocardite et la neuropathie 2.
Au niveau cellulaire Brucella est capable d'envahir les cellules phagocytaires et non phagocytaires et reproduit dans un intracellulairecompartiment connu sous le nom de la vacuole Brucella (BCV). Internalisation des bactéries nécessite des réarrangements du cytosquelette d'actine par Rac, Rho, et l' activation directe de Cdc42 3. A l' intérieur de la cellule hôte eucaryote, la BCV trafique le long de la voie endocytique et en dépit de l'interaction avec les lysosomes, les bactéries parviennent à éviter une dégradation 4. L' acidification de la BCV par le vésiculaire ATPase est nécessaire pour induire l'expression du système IV de sécrétion de type bactérien (T4SS) 5. On croit que les effecteurs bactériennes sécrétées par le T4SS sont essentiels pour Brucella pour établir son créneau réplicative, depuis la suppression de la T4SS 6 ou l' inhibition de l'ATPase plomb vésiculaire à des défauts dans la mise en place de la niche intracellulaire 7. Les bactéries ne se répliquent pas pendant la phase de la traite jusqu'à ce qu'ils parvenir à un compartiment vacuolaire ER dérivé 8. Une fois la prolifération intracellulaire se produit, la BCV se trouve dans classociation OSE avec des marqueurs tels que l' ER calnexine et le glucose-6-phosphatase 6.
Les mécanismes moléculaires par lesquels Brucella pénètre dans les cellules, évite la dégradation lysosomale, et enfin se réplique dans un compartiment ER-like demeurent largement inconnus. Les facteurs de l' hôte impliqués dans différentes étapes de l' infection ont principalement été identifiés par des approches ciblées ou un écran à petite échelle petits ARN interférents (siRNA) effectuée dans les cellules de drosophile 9. Ceux - ci ont mis en lumière la contribution des facteurs d'accueil individuels au cours de l' infection à Brucella , mais nous sommes encore loin d'une compréhension globale de l'ensemble du processus.
Ici, les protocoles qui permettent l'identification des facteurs de l'hôte humain en utilisant à grande échelle l'interférence ARN (ARNi) criblage en combinaison avec automatisée de microscopie par fluorescence à champ large et analyse d'image automatisée sont présentés. La transfection inverse de siRNA de cellules HeLa On procède comme described tôt 10,11 avec des modifications mineures. Le dosage de point final couvre une grande partie du cycle de vie intracellulaire Brucella , sauf la sortie et l'infection des cellules voisines. Pour caractériser davantage les résultats identifiés dans l'essai de point final, un protocole modifié pour identifier les facteurs qui interviennent dans les étapes précoces de l'infection est utilisée.
Une souche de Brucella abortus qui exprime constitutivement la GFP est utilisée pour l'essai de point d' extrémité , où les bactéries sont autorisés à infecter les cellules pendant deux jours. Pendant ce temps, les bactéries pénètrent dans les cellules, le trafic à la niche réplicative dérivés d'ER, et de reproduire dans l'espace péri-nucléaire. Les niveaux élevés de signal GFP peuvent ensuite être utilisés pour détecter de manière fiable les cellules individuelles contiennent des bactéries qui se répliquant.
Pour étudier l' entrée Brucella dans un dosage à haut débit, il est important de pouvoir distinguer entre les bactéries intracellulaires et extracellulaires. La méthode présentée ici circumvents anticorps différentiel coloration des bactéries intracellulaires et extracellulaires. Il est basé sur une souche de Brucella exprimant une GFP inductible par la tetracycline en combinaison avec l' expression constitutive de la DsRed. La présence d'un marqueur DsRed constitutif permet l'identification de toutes les bactéries présentes dans l'échantillon. expression de la GFP est induite par l'addition de tetracycline anhydrotétracycline analogue non toxique (ATC) en même temps que l'inactivation des bactéries extracellulaires par la gentamicine (Gm). Bien que la cellule imperméable aux antibiotiques Gm tue les bactéries extracellulaires, Atc peut entrer dans la cellule hôte et induire l'expression de la GFP sélectivement dans des bactéries intracellulaires. Cette double rapporteur permet la séparation solide des bactéries intracellulaires simples (GFP et DsRed signaux) provenant de bactéries extracellulaires (uniquement de signaux DsRed) en utilisant la microscopie à champ large. Afin d'atteindre l' expression de GFP détectable par intracellulaire Brucella nous avons constaté que 4 heures d'induction par l' ATC se traduit par un relisignal de mesure. Induction des systèmes similaires pour exprimer sélectivement GFP dans des bactéries intracellulaires a été utilisé auparavant pour étudier Shigella intracellulaire 12.
Protocole
Note: Tous les travaux avec en direct des souches de Brucella abortus doit être effectuée à l' intérieur d' un niveau de biosécurité 3 (BSL3) laboratoire compte tenu de tous les règlements nécessaires et les précautions de sécurité.
1. Préparation du dépistage Plaques et culture des bactéries et des cellules
- Préparation de Brucella abortus Cultures de démarrage
- Streak Brucella abortus 2308 (B. abortus) de -80 ° C le lait disponible sur une plaque CASO Agar (TSA) contenant 50 pg / ml de kanamycine (TSA / Km). Incuber la plaque pendant 3-4 jours à 37 ° C. Utilisez la souche Brucella abortus 2308 pJC43 (Apht :: GFP) 13 pour le dosage de point final et la souche Brucella abortus pAC042.08 (aphT :: DsRed, tetO :: tetR-GFP) pour le test d'entrée.
Remarque: Le lipopolysaccharide (LPS) lisse de Brucella abortus est un déterminant important de la virulence mais mutants rugueux peut se produire à des fréquences relativement élevées 14. We recommande donc de tester l'état de la souche de culture avant de commencer l'expérience. - bactéries Restreak sur quatre TSA / Km plaques couvrant la plaque pleine et incuber pendant 2-3 jours à 37 ° C.
- En utilisant une boucle en plastique jetable, le transfert et les bactéries resuspendre des plaques TSA / Km dans 10 ml 10% autoclave du lait écrémé. Assurez-vous que les bactéries sont bien remises en suspension pour assurer des concentrations bactériennes cohérentes dans toutes les cultures de démarrage.
- Aliquoter 250 pi de la suspension bactérienne dans 2 ml à vis des tubes à bouchon et congeler à -80 ° C.
- Décongeler une aliquote de la culture de départ et de transférer 25 pi, 50 pi et 100 pi de la culture de départ bactérienne pour séparer 250 ml à vis des bouteilles à bouchon avec 50 ml de bouillon de soja tryptique (TSB) contenant 50 pg / ml de kanamycine (TSB / km) . Sceller les bouteilles avec Parafilm.
- Incuber les bouteilles pendant une nuit sur un agitateur orbital à 100 tpm et 37 ° C.
- Mesurer la densité optique à 600 nm (OD 600) pour déterminer le volume de culture de départ nécessaire pour atteindre une DO600 = 0,8-1,1 après culture de la nuit.
- Streak Brucella abortus 2308 (B. abortus) de -80 ° C le lait disponible sur une plaque CASO Agar (TSA) contenant 50 pg / ml de kanamycine (TSA / Km). Incuber la plaque pendant 3-4 jours à 37 ° C. Utilisez la souche Brucella abortus 2308 pJC43 (Apht :: GFP) 13 pour le dosage de point final et la souche Brucella abortus pAC042.08 (aphT :: DsRed, tetO :: tetR-GFP) pour le test d'entrée.
- Préparation des cellules HeLa
- Faire croître des cellules HeLa dans Dulbecco Modified Eagle Medium (DMEM) supplémenté avec 10% de sérum de foetus de veau (FCS) (DMEM / 10% FCS) dans un incubateur à 37 ° C humide avec 5% de CO 2 croître des cellules jusqu'à 80% de confluence.
- Préparer la projection des plaques avec des ARNsi.
- Diluer ARNsi dans l'eau sans RNase à une concentration finale de 0,32 uM. Transfert 5 pl / puits sur des plaques à 384 puits noir clair et à fond plat.
- Utilisez les colonnes 1, 2, 23 et 24 pour les contrôles standard. Pour les contrôles négatifs, utiliser non-ciblage siRNA (brouillés) et simulacres puits sans siRNA (réactif de transfection seulement). Pour les contrôles de transfection, utiliser un siRNA qui induit la mort cellulaire (KIF11), ainsi que des contrôles positifs de facteurs de l' hôte connus impliqués dans l' infection à Brucella (par exemple, ARPC3,un composant du complexe Arp2 / 3 impliquée dans la polymérisation de l'actine). Transfert disponible dans le commerce des bibliothèques siARN ou personnalisés siRNA dans les puits restants.
- plaques d'étanchéité avec des feuilles d'aluminium pelables. plaques de conserver à -20 ° C.
Remarque: Les plaques peuvent être conservés à -20 ° C pendant au moins 6 mois et jusqu'à ans, selon les recommandations du fabricant.
- Diluer ARNsi dans l'eau sans RNase à une concentration finale de 0,32 uM. Transfert 5 pl / puits sur des plaques à 384 puits noir clair et à fond plat.
2. Inverse siRNA Transfection
- Décongeler une plaque 384 puits noire par centrifugation à 300 xg pendant 20 min à température ambiante.
Remarque: Cela fera descendre tout le liquide qui pourrait adhérer au couvercle ou du côté des puits. - Préparer le milieu de transfection par dilution du réactif de transfection 1: 200 dans du DMEM sans SVF à température ambiante. Préparer le milieu de transfection a pas plus de 20 minutes avant l'utilisation. Mélanger soigneusement la solution avant utilisation.
- Ajouter 25 ul de milieu de transfection à chaque puits en utilisant un distributeur de réactifet mélanger les solutions en déplaçant la plaque avant et en arrière.
- Incuber la plaque pendant 1 heure à la température ambiante pour permettre ARNsi / transfection formation du complexe réactif.
- Dans l'intervalle, la préparation des cellules HeLa par lavage des cellules sous-confluentes un flacon de 75 cm2 une fois avec 2,5 ml de 0,05% de trypsine-EDTA dans du PBS (trypsine).
- Ajouter 1,5 ml de trypsine fraîche et transférer le ballon à 37 ° C pendant 2-3 minutes jusqu'à ce que les cellules arrondies vers le haut.
- Resuspendre les cellules dans 10 ml de pré-chauffé DMEM / 16% de FCS.
- Compter les cellules en utilisant un compteur de cellules automatisé et à préparer une suspension de cellules de 10.000 cellules / ml dans DMEM / 16% de FCS.
- Ajouter 50 ul de suspension cellulaire à chaque puits en utilisant un distributeur de réactif résultant dans 500 cellules / puits.
- Déplacer la plaque avant et en arrière pour obtenir une répartition uniforme des cellules. Laissez la plaque à température ambiante pendant 5-10 minutes pour permettre aux cellules de s'installer.
- Sceller la plaque avec du Parafilm et incuber pendant 72 heures sur un aluminium préchaufféla plaque dans un incubateur à 37 ° C humide avec 5% de CO 2.
Remarque: La plaque d'aluminium préchauffé permet la distribution de température égale tout au long de toute la plaque de 384 puits.
3. Infection et fixation
- Un jour avant l'infection, inoculer le montant déterminé en 1.1.7 de B. abortus culture starter dans 50 ml TSB / Km moyenne de 250 ml bouchon à vis bouteille. Sceller la bouteille avec du Parafilm et faire croître les bactéries pendant une nuit à 37 ° C et 100 rpm sur un agitateur orbital à OD 600 = 0,8-1,1.
- Mesurer la DO600 de la culture bactérienne et de préparer le milieu d'infection par dilution de la culture bactérienne dans un milieu DMEM / 10% de FCS pour atteindre la multiplicité désirée de l' infection (MOI).
Remarque: Pour obtenir un taux de 5-10% dans les cellules HeLa d'infection, une MOI de 10.000 est utilisé. Une courbe de titrage MOI doit être effectué pour chaque type de cellule pour obtenir des taux d'infection optimaux. - Remplacez le milieu de transfection de la plaque 384 puitsavec 50 ul de milieu d'infection en utilisant un laveur de plaque automatisé.
- Centrifuger la plaque 384 puits à 400 g et 4 ° C pendant 20 min.
Note: Ceci permet de synchroniser le processus d'infection. - Sceller la plaque avec du Parafilm et on incube sur une plaque d'aluminium préchauffé dans un incubateur à 37 ° C humide avec 5% de CO 2 pendant 4 heures.
- Laver les cellules avec du DMEM / 10% de FCS contenant 100 ug / ml Gm pour inactiver les bactéries extracellulaires utilisant le laveur de plaques automatique (utiliser 200 pl / lavage et débordement).
Remarque: Lors d'un lavage de trop-plein, la machine à laver automatique de plaques distribue et aspire à moyen simultanément. - Pour le test d'entrée, laver les cellules une seconde fois avec DMEM / 10% de FCS contenant 100 ug / ml Gm et 100 ng / ml Atc en utilisant la machine à laver automatique de plaques (utiliser 200 pl / lavage et débordement).
- Sceller la plaque avec du Parafilm et le retourner à une plaque d'aluminium préchauffé dans le 37 ° C incubateur humide avec 5% de CO 2 pour un autre40 h ou 4 h, pour le dosage de point d'extrémité et le test d'entrée, respectivement.
- Pour la fixation, laver les puits avec du PBS en utilisant la machine à laver automatique de plaques (utiliser 200 pl / lavage et débordement).
- Échange PBS avec 50 ul de 3,7% de paraformaldehyde dans 0,2 M HEPES à pH 7,4 (PFA) en utilisant le laveur de plaques automatique.
Remarque: Attention: PFA est toxique par inhalation, par contact avec la peau et par ingestion. - Incuber pendant 20 min à température ambiante.
- Remplacez le milieu de fixation avec 50 ul de PBS en utilisant le laveur de plaques automatique. Remarque: Les échantillons sont maintenant prêts à être prises à partir du BSL3 si nécessaire.
Attention: Suppression d'un échantillon provenant d'une installation de BSL3 est soumis à une évaluation des risques et la validation de la procédure et dépend de la réglementation applicable en matière de biosécurité.
4. coloration
- Laver les cellules deux fois avec 50 ul de PBS.
- Perméabiliser les cellules dans 50 ul de 0,1% de Triton-X-100 dans du PBS pendant 10 min.
- Wcellules de cendres trois fois avec PBS. Ajouter 20 pi de PBS contenant 1 pg / ml de DAPI (4 ', 6-diamidino-2-phénylindole) et incuber pendant 30 min à température ambiante.
- Laver les cellules trois fois dans du PBS et protéger la coloration de la lumière avec une feuille d'aluminium.
5. Imaging
- Mettre en place le microscope à champ large automatisé pour l'acquisition d'images.
Remarque: Les paramètres d'un microscope ImageXpress Device moléculaire en utilisant un logiciel MetaXpress sont décrits ci-dessous. dispositifs de microscopie alternatifs 2D grand champ avec les spécifications matérielles appropriées et des logiciels d'imagerie peuvent être utilisés (voir le tableau des matières / équipement pour plus de détails).- Sélectionnez objectif 10X, caméra binning = 1, le gain = 1.
- Sélectionnez le format de plaque correspondant à la plaque de 384 puits.
- Acquérir 9 sites par puits.
- Utilisez "Activer laser basé focus" et "Focus sur la plaque et bien inférieure".
- Set "First bien" que le bien initialtrouver l'échantillon et «Tous les sites" pour le site autofocus.
- Utilisez le canal DAPI pour définir manuellement Z-Offset de mise au point.
- sélectionner manuellement le Z-Offset de DAPI pour tous les autres canaux.
- Manuellement corriger le temps d'exposition pour tous les canaux pour assurer une large plage dynamique avec une faible surexposition.
- Acquérir une image d'un site représentatif en utilisant la fonction d'exposition automatique. Utilisez ce temps d'exposition à l'image 3-5 sites à travers la plaque et ajuster le temps d'exposition manuellement jusqu'à ce que les pixels les plus brillants atteignent ~ 80% de la luminosité maximale sur tous les sites.
- Image la plaque complète en utilisant les canaux DAPI et GFP pour le test final. Pour le test d'entrée sélectionner le canal DP en plus.
6. Analyse d'image automatisé
Note: CellProfiler 2 15 est utilisé en tant que logiciel d'analyse d'image pour segmenter cellulaire et objets bactériens et effectuer mesur automatiséements dans les objets identifiés. Le logiciel fournit des images des algorithmes d'analyse dans les modules individuels, qui peuvent être combinés dans un pipeline qui exécutera les modules consécutivement sur toutes les images, pour effectuer automatiquement une tâche spécifique d'analyse d'image. Pour suivre le protocole, installez CellProfiler 2.1.1 ou une version plus récente. Ensuite, chargez le pipeline fourni et suivez les instructions ci-dessous pour régler les paramètres requis dans les modules. Une description des modules individuels de tous les pipelines peuvent être trouvées dans les fichiers supplémentaires.
Note: Les deux canalisations séparées sont utilisées pour chaque essai. Le premier pipeline calcule un modèle d'ombrage, qui est utilisé par la seconde canalisation pour corriger les images avant l'analyse. Correction d'ombrage est appliqué sur les images pour réduire les effets d'un chemin de lumière inhomogène du microscope. Le calcul du modèle d'ombrage dans le premier pipeline est un processus long, mais les résultats seront d'une plus grande précision.
- Endpoint Assay
- Calculer le modèle d'ombrage
- Allez dans le menu "Fichier", sélectionnez "Importer" → "Pipeline à partir du fichier ..." et sélectionnez le pipeline fourni "BrucellaShadingCorrectionPart1-Ver007". Lorsqu'on lui a demandé si vous souhaitez convertir le pipeline existant, répondre "Ne pas convertir".
- Aller à la "production" → "Afficher les paramètres de sortie" et sélectionnez un dossier d'entrée avec les images et un dossier de sortie pour les modèles d'ombrage résultant.
- Dans le module (1) "loadImages", régler le nom du "texte que ces images ont en commun" pour faire correspondre les noms d'image.
- Assurez-vous qu'aucun des modules montrent leur affichage avant d'exécuter l'analyse complète en décochant tous les symboles de l'oeil à côté des modules. Note: Ceci diminue considérablement les ressources informatiques nécessaires lors du traitement du pipeline.
- Appuyez sur "l'analyse des images" pour démarrer le calcul du modèle d'ombrage.
- Analyse d'image Exécuter
- Allez dans le menu "Fichier", sélectionnez "Importer" → "Pipeline à partir du fichier ..." et sélectionnez le pipeline fourni "BrucellaEndpointWithShadingCorrectionPart2-Ver007". Lorsqu'on lui a demandé si vous souhaitez convertir le pipeline existant, répondre "Ne pas convertir".
- Aller à la "production" → "Afficher les paramètres de sortie" et sélectionnez un dossier d'entrée avec les images et un dossier de sortie pour la feuille de calcul résultant.
- Dans le module (1) "loadImages", régler le nom du "texte que ces images ont en commun" pour faire correspondre les noms d'image.
- Dans le module (2) "LoadSingleImage", charger les modèles d'ombrage calculés sous 6.1.1 en sélectionnant l'emplacement et les noms de fichiers des deux modèles d'ombrage.
- Dans les modules (4) - (5) "ImageMath", régler le paramètre "Multiplier la première image en" correspondant à la profondeur de bits de la caméra du microscope. Pour 8 et 16 bitsimages régler le paramètre "1.0", pour 12 images de bits régler le paramètre à "16,0".
- Dans le module (9) "ImageMath" régler le paramètre "Multipliez la seconde image par" à une valeur ( en commençant par 0,25) qui supprimera le signal Brucella dans la coloration DAPI sans supprimer l'Nuclei.
- Cliquez sur "Mode Test Démarrer", puis activer le symbole de pause et la fonction d'affichage pour le module (9) en cliquant sur les icônes correspondantes du module.
Remarque: Le symbole de pause apparaît en jaune, tandis que le symbole de l'oeil montrera un oeil ouvert si elle est activée. - Cliquez sur "Exécuter" pour lancer l'analyse jusqu'au module (9) avec le symbole de pause active. Pour tester les valeurs pour le module, appuyez sur "Step".
- Cliquez droit sur l'image nouvellement ouvert et réglez "contraste de l'image" à "Log normalisée". À plusieurs reprises remonter au module (9), régler le paramètre "Multipliez la seconde image par", et l'étape sur til Module de nouveau, jusqu'à ce que le signal est complètement supprimé Brucella tandis que dans les mêmes zones noires de temps qui indiquent au- dessus de soustraction sont réduites au minimum dans l'image résultante.
- Cliquez sur "Mode Test Démarrer", puis activer le symbole de pause et la fonction d'affichage pour le module (9) en cliquant sur les icônes correspondantes du module.
- Dans le module (10) "IdentifyPrimaryObjects", régler le paramètre "Borne inférieure sur le seuil" assez élevé (en commençant par zéro), de sorte que les noyaux sont segmentés et le fond est ignoré.
- Pour identifier une bonne valeur pour le module (10), étape sur le module et afficher l'image d'entrée comme expliqué dans les étapes 6.1.2.6.1 et 6.1.2.6.2.
- Cliquez droit sur l'image d'entrée et afficher l'histogramme.
Remarque: Le pic de l'histogramme indique généralement fond. - A partir de l'intensité d'arrière-plan augmenter le paramètre jusqu'à ce qu'une bonne segmentation des noyaux est réalisé comme indiqué dans l'image de sortie.
Remarque: Réglage du seuil plus élevé que l'intensité de fond est particulièrement important pour les sites vides.
- Module (15)4; FilterObjects ", régler le paramètre" Valeur minimale " de sorte que les cellules avec clairement visibles Brucella dans le noyau sont conservés, et tous les autres sont filtrés loin Dans cette étape, ignorer Brucella en dehors du noyau..
- Pour identifier une bonne valeur, étape sur le module et afficher l'image de sortie, comme expliqué dans les étapes 6.1.2.6.1 et 6.1.2.6.2. À partir de zéro, ce qui identifie toutes les cellules comme infectés, et d' augmenter la valeur par de petites étapes jusqu'à ce que seules les cellules avec clairement visibles Brucella au noyau sont conservés.
- Dans le module (16) "FilterObjects", régler le paramètre "Valeur minimale" de sorte que les cellules avec clairement visibles Brucella aux périnoyau sont conservés, et toutes les autres cellules sont filtrées loin. Utiliser une approche similaire à celle dans le module précédent.
- Dans le module (17) "FilterObjects", régler le paramètre "Valeur minimale" de sorte que les cellules avec clairement visibles Brucella au Vorcorps cellulaire onoi sont conservés, et toutes les autres cellules sont filtrées loin. Utiliser une approche similaire à celle dans le module précédent.
Remarque: Le corps de la cellule de Voronoï est une extension radiale du noyau de 25 pixels sans chevauchement avec les corps cellulaires Voronoï voisins. - Quittez le mode de test et assurez-vous qu'aucun des modules montrent leur affichage avant d'exécuter l'analyse complète en décochant tous les symboles de l'oeil à côté des modules.
Note: Ceci diminue considérablement les ressources informatiques nécessaires lors du traitement du pipeline. - Appuyez sur "l'analyse des images" pour lancer l'analyse.
- Lorsque l'analyse est terminée, inspecter les images résultantes PNG, ainsi que la feuille CSV pour faire en sorte que l'analyse a fonctionné de manière fiable tout au long de la plaque.
- Calculer le modèle d'ombrage
- Entrée Assay
- Calculer le modèle d'ombrage
- Allez dans le menu "Fichier", sélectionnez "Importer" → "Pipeline à partir du fichier ...", et sélectionnez le fournird pipeline »BrucellaShadingCorrectionPart1-Ver007». Lorsqu'on lui a demandé si vous souhaitez convertir le pipeline existant, répondre "Ne pas convertir".
- Aller à la "production" → "Afficher les paramètres de sortie" et sélectionnez un dossier d'entrée avec les images et un dossier de sortie pour les modèles d'ombrage résultant.
- Dans le module (1) "loadImages", régler le nom du "texte que ces images ont en commun" pour faire correspondre les noms d'image.
- Assurez-vous qu'aucun des modules montrent leur affichage avant d'exécuter l'analyse complète en décochant tous les symboles de l'oeil à côté des modules.
Note: Ceci diminue considérablement les ressources informatiques nécessaires lors du traitement du pipeline. - Appuyez sur "l'analyse des images" pour démarrer le calcul du modèle d'ombrage.
- Analyse d'image Exécuter
- Allez dans le menu "Fichier", sélectionnez "Importer" → "Pipeline à partir du fichier ...", et sélectionnez le provided pipeline "BrucellaEntryWithShadingCorrectionPart2-Ver007". Lorsqu'on lui a demandé si vous souhaitez convertir le pipeline existant, répondre "Ne pas convertir".
- Aller à la "production" → "Afficher les paramètres de sortie" et sélectionnez un dossier d'entrée avec les images et un dossier de sortie pour la feuille de calcul résultant.
- Dans le module (1) "loadImages", régler le nom du "texte que ces images ont en commun" pour faire correspondre les noms d'image.
- Dans le module (2) "LoadSingleImage", charger les modèles d'ombrage calculés sous 6.2.1 en sélectionnant l'emplacement et les noms de fichiers des deux modèles d'ombrage.
- Dans les modules (4) - (5) "ImageMath", régler le paramètre "Multiplier la première image en" correspondant à la profondeur de bits de la caméra du microscope. Pour 8 et 16 images de bits régler le paramètre "1.0", pour 12 images de bits régler le paramètre sur "16.0".
- Dans le module (6) "IdentifyPrimaryObjects", régler le paramètre "Lower lié sur le seuil "suffisamment élevé pour que seuls les noyaux sont segmentés et le fond est ignoré.
- Pour identifier une bonne valeur pour le module (6), étape sur le module et afficher l'image d'entrée comme expliqué dans les étapes 6.1.2.6.1 et 6.1.2.6.2.
- Cliquez droit sur l'image d'entrée et afficher l'histogramme.
Remarque: Le pic de l'histogramme indique généralement fond. - A partir de l'intensité d'arrière-plan augmenter le paramètre jusqu'à ce qu'une bonne segmentation des noyaux est réalisé comme indiqué dans l'image de sortie.
Remarque: Régler le seuil au-dessus de fond est important pour les sites vides.
- Dans le module (8) "IdentifyPrimaryObjects", régler le paramètre "Borne inférieure sur le seuil" assez élevé qui ne Brucella sont segmentés et arrière - plan est ignoré.
- Pour identifier une bonne valeur pour le module (8), étape sur le module et afficher l'image d'entrée comme expliqué dans les étapes 6.1.2.6.1 et 6.1.2.6.2.
- Cliquez droit sur l'image d'entrée et afficher l'histogramme.
Remarque: Le pic de l'histogramme indique généralement fond. - A partir de l' intensité de fond augmenter le paramètre jusqu'à ce que la bonne segmentation de Brucella tel qu'il apparaît dans l'image de sortie est atteint.
Remarque: Régler le seuil au-dessus de fond est important pour les sites vides.
- Dans le module (11) "FilterObjects", régler le paramètre "Valeur minimale" de telle sorte que de fond et des objets sont filtrés loin, et seules les colonies de Brucella sont conservés.
- Pour identifier une bonne valeur, étape sur le module et afficher l'image de sortie, comme expliqué dans les étapes 6.1.2.6.1 et 6.1.2.6.2. Commencez par la valeur sélectionnée dans 6.2.2.7 et progressivement augmenter jusqu'à ce que les objets Brucella seulement sont conservés.
- Quittez le mode de test et assurez-vous qu'aucun des modules montrent leur affichage avant d'exécuter l'analyse complète par UNCHEcking tous les symboles de l'oeil à côté des modules.
Note: Ceci diminue considérablement les ressources informatiques nécessaires lors du traitement du pipeline. - Appuyez sur "l'analyse des images" pour lancer l'analyse.
- Lorsque l'analyse est terminée, inspecter les images résultantes PNG ainsi que la feuille CSV pour veiller à ce que l'analyse a bien fonctionné tout au long de la plaque.
- Calculer le modèle d'ombrage
7. Infection Scoring
Note: siRNA qui ont un impact significatif sur la viabilité des cellules doivent être considérées avec prudence, car cela peut favoriser des découvertes faux positifs. Un nombre de cellules altérées affecte la réelle MOI et le ciblage de gènes essentiels peut avoir des effets pléiotropiques sur l'infection par des agents pathogènes. Alors que l'épuisement incomplète par ARNsi permet l'étude des gènes essentiels, ces objectifs doivent être validés par des méthodes alternatives (par exemple, l' interférence pharmaceutique) pour corroborer leur rôle en tant que facteurs de l' hôtelors de l'infection.
- Endpoint Assay
- Ouvrez la feuille CSV généré à l'étape 6.1.2.12 et calculer un taux par infection et en divisant le nombre de cellules infectées (CellProfiler lecture: "Count_InfectedCells") par le nombre total de cellules (CellProfiler de lecture: "CountNuclei"). Si plusieurs sites par puits ont été imagé, d'abord de résumer tous les sites pour chaque puits, de construire un nombre par puits de cellules infectées et un nombre bien par-total de cellules.
- Effectuer Z score de normalisation pour tenir compte des variations de plaque à plaque si les plaques contiennent suffisamment ARNsi non-hit. Supposons un nombre suffisant d'ARNsi non touchées par plaque si les bibliothèques complètes sont projetés.
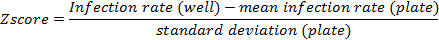
- Entrée Assay
- Ouvrez la feuille CSV généré à l'étape 6.2.2.10 et calculer un taux par infection et en divisant le nombre de cellules infectées (CellProfiler lecture: "Count_InfectedCells ") par le nombre total de cellules (CellProfiler lecture:". CountNuclei ") Si plusieurs sites par puits ont été imagé, d'abord résumer tous les sites pour chaque puits, de construire un nombre par puits de cellules infectées et d'un puits par- nombre total de cellules.
- Pour quantifier la charge bactérienne des cellules infectées, estimer la superficie moyenne occupée par des bactéries intracellulaires par cellule infectée. À cette fin, diviser la zone intégrée de toutes les bactéries intracellulaires qui se chevauchent avec des cellules (CellProfiler de lecture: "AreaOccupied_AreaOccupied_TrueIntPathogenInCells") par le nombre de cellules infectées dans ce site. Pour tenir compte des objets, utiliser la médiane de tous les sites de cette lecture que la lecture du puits.
Remarque: Si ce test est utilisé comme un test de suivi contenant un grand nombre de gènes impliqués dans l' infection à Brucella, ne pas appliquer Z résultat normalisation. Au lieu de cela, effectuez la normalisation en utilisant des puits simulés comme une référence pour tenir compte de la variation de plaque à plaque.
Résultats
La figure 1A représente un exemple d'analyse d'image utilisé pour identifier automatiquement les cellules infectées dans l'essai de point final. Les noyaux des cellules HeLa colorées avec du DAPI ont été identifiées, une péri-noyau d'une largeur de 8 pixels entourant le noyau et un corps de cellule de Voronoi par extension du noyau par 25 pixels ont été calculés. Etant donné que les bactéries prolifèrent principalement dans l'espace pér...
Discussion
Bacterial pathogens have evolved numerous strategies to manipulate eukaryotic host cells to their benefit. Pathogens causing acute infections often show rapid proliferation which is accompanied by significant alarming of the immune system and loss of viability of infected cells. In contrast, Brucella and other pathogens that cause chronic infections manage to establish long-lasting interactions within host cells. Therefore, bacteria need to fine tune host cell functions to their benefit without disrupting cellul...
Déclarations de divulgation
The authors declare no conflicts of interest.
Remerciements
This work was supported by grants 51RT 0_126008 and 51RTP0_151029 for the Research and Technology Development (RTD) project InfectX and TargetInfectX, respectively, in the frame of SystemsX.ch, the Swiss Initiative for Systems Biology. We acknowledge grant 310030B_149886 from the Swiss National Science Foundation (SNSF). Work of S.H.L and A.C. was supported by the International PhD Program "Fellowships for Excellence" of the Biozentrum. Simone Muntwiler is acknowledged for technical assistance. We would like to thank Dirk Bumann for providing pNF106 and Jean Celli for pJC43 and pJC44.
matériels
| Name | Company | Catalog Number | Comments |
| Tryptic Soy Agar (TSA) | BD | 236950 | |
| Tryptic Soy Broth (TSB) | Fluka | 22092 | |
| Kanamycin sulfate | Sigma-Aldrich | 60615 | |
| Skim milk | |||
| 250 ml screw cap bottle | Corning | 8396 | |
| DMEM | Sigma-Aldrich | D5796 | |
| Fetal Calf Serum (FCS) | Gibco | 10270 | Heat-inactivated |
| Trypsin-EDTA (0.5%) | Gibco | 15400-054 | 10x stock solution, dilute 1:10 in PBS |
| Scepte 2.0 Cell Counter | Merck Milipore | PHCC20060 | Alternative cell counting devices can be used |
| Greiner CELLSTAR 384-well plate | Sigma-Aldrich | M2062 | |
| Peelable aluminum foil | Costar | 6570 | |
| Reagent dispenser: "Multidrop 384 Reagent Dispenser" | Thermo Scientific | 5840150 | Alternative reagent dispenser can be used. |
| Transfection reagent: "Lipofectamine RNAiMAX | Invitrogen | 13778-150 | |
| Automated plate washer: "Plate washer ELx50-16" | BioTek | ELX5016 | This plate washer contains a 16-channel manifold suitable for 384-well plates. It fits into a biosafety cabinet and has a lid covering the plate during washing which reduces the risk of aerosol production. Alternative plate washers with similar features could be used. |
| Gentamicin | Sigma-Aldrich | G1397 | |
| Anhydrotetracycline hydrochloride | Sigma-Aldrich | 37919 | 100 μg/ml solution in 100% ethanol is kept at -20 °C protected from light in aluminum-foil |
| PBS | Gibco | 20012 | |
| Paraformaldehyde | Sigma-Aldrich | P6148 | Dissolve in 0.2 M HEPES buffer, pH 7.4. Store at -20 °C and thaw freshly the day before use. Caution, PFA is toxic by inhalation, in contact with skin and if swallowed. |
| HEPES | Sigma-Aldrich | H3375 | |
| Triton X-100 | Sigma-Aldrich | T9284 | |
| DAPI | Roche | 10236276001 | |
| Scrambled siRNA | Dharmacon | D-001810-10 | |
| Kif11 siRNA | Dharmacon | L-003317-00 | |
| ARPC3 siRNA | Dharmacon | L-005284-00 | |
| Brucella abortus 2308 | |||
| pJC43 (apHT::GFP) | Celli et al.12 | ||
| pAC042.08 (apht::dsRed, tetO::tetR-GFP) | Construction: pJC44 4 was digested with EcoRI followed by generation of blunt ends with Klenov enzyme and subsequent digestion with SalI. TetR-GFP was amplified from pNF106 using primer prAC090 and prAC092. Following digestion with SalI, the TetR-GFP product was ligated to the digested pJC44 vector. | ||
| Primer prAC090 | Sigma-Aldrich | TTT TTG AAT TCT GGC AAT TCC GAC GTC TAA GAA ACC | |
| Primer prAC092 | Sigma-Aldrich | TTT TTG TCG ACT TTG TCC TAC TCA GGA GAG CGT TC | |
| HeLa CCL-2 | ATCC | CCL-2 | |
| ImageXpress Micro | Molecular Devices | IXM IMAGING MSCOPE | Automated cellular imaging microscope equipped with a precision motorized Z-stage. Alternative systems for automated microscopy and alternative components for hard- and software specified below can be employed. |
| High-Speed Laser Auto-Focus | Molecular Devices | 1-2300-1037 | |
| CFI Super Fluor 10X objective | Nikon | MRF00100 | N.A 0.50, W.D 1.20 mm, DIC Prism: 10X, Spring loaded |
| Photometrics CoolSNAP HQ Monochrome CCD Camera | Molecular Devices | 1-2300-1060 | 1,392 x 1,040 imaging pixels, 6.45 x 6.45 µm pixels, 12 bits digitization |
| MetaXpress software | Molecular Devices | 9500-0100 | |
| LUI-Spectra-X-7 | Lumencor | SPECTRA X V-XXX-YZ | Light engine. The following light sources are used: violet (DAPI), cyan (GFP), green/yellow (RFP) |
| Single Band Exciter for DAPI | Semrock | FF01-377/50-25 | |
| Single Band Emitter for DAPI | Semrock | FF02-447/60-25 | |
| Single Band Dichroic for DAPI | Semrock | FF409-Di03-25x36 | |
| Single Band Exciter for GFP | Semrock | FF02-472/30-25 | |
| Single Band Emitter for GFP | Semrock | FF01-520/35-25 | |
| Single Band Dichroic for GFP | Semrock | FF495-Di03-25x36 | |
| Single Band Exciter for RFP | Semrock | FF01-562/40-25 | |
| Single Band Emitter for RFP | Semrock | FF01-624/40-25 | |
| Single Band Dichroic for RFP | Semrock | FF593-Di03-25x36 |
Références
- Pappas, G., Papadimitriou, P., Akritidis, N., Christou, L., Tsianos, E. V. The new global map of human brucellosis. Lancet Infect Dis. 6, 91-99 (2006).
- Atluri, V. L., Xavier, M. N., de Jong, M. F., den Hartigh, A. B., Tsolis, R. E. Interactions of the human pathogenic Brucella species with their hosts. Annu Rev Microbiol. 65, 523-541 (2011).
- Guzman-Verri, C., et al. GTPases of the Rho subfamily are required for Brucella abortus internalization in nonprofessional phagocytes: direct activation of Cdc42. J Biol Chem. 276, 44435-44443 (2001).
- Starr, T., Ng, T. W., Wehrly, T. D., Knodler, L. A., Celli, J. Brucella intracellular replication requires trafficking through the late endosomal/lysosomal compartment. Traffic. 9, 678-694 (2008).
- Boschiroli, M. L., et al. The Brucella suis virB operon is induced intracellularly in macrophages. Proc Natl Acad Sci U S A. 99, 1544-1549 (2002).
- Celli, J., et al. Brucella evades macrophage killing via VirB-dependent sustained interactions with the endoplasmic reticulum. J Exp Med. 198, 545-556 (2003).
- Porte, F., Liautard, J. P., Kohler, S. Early acidification of phagosomes containing Brucella suis is essential for intracellular survival in murine macrophages. Infect Immun. 67, 4041-4047 (1999).
- Anderson, T. D., Cheville, N. F. Ultrastructural morphometric analysis of Brucella abortus-infected trophoblasts in experimental placentitis. Bacterial replication occurs in rough endoplasmic reticulum. Am J Pathol. 124, 226-237 (1986).
- Qin, Q. M., et al. RNAi screen of endoplasmic reticulum-associated host factors reveals a role for IRE1alpha in supporting Brucella replication. PLoS Pathog. 4, e1000110 (2008).
- Ramo, P., et al. Simultaneous analysis of large-scale RNAi screens for pathogen entry. BMC genomics. 15, 1162 (2014).
- Kuhbacher, A., Gouin, E., Cossart, P., Pizarro-Cerda, J. Imaging InlC secretion to investigate cellular infection by the bacterial pathogen Listeria monocytogenes. J Vis Exp. , e51043 (2013).
- Kentner, D., et al. Shigella reroutes host cell central metabolism to obtain high-flux nutrient supply for vigorous intracellular growth. Proc Natl Acad Sci U S A. 111, 9929-9934 (2014).
- Celli, J., Salcedo, S. P., Gorvel, J. P. Brucella coopts the small GTPase Sar1 for intracellular replication. Proc Natl Acad Sci U S A. 102, 1673-1678 (2005).
- von Bargen, K., Gorvel, J. P., Salcedo, S. P. Internal affairs: investigating the Brucella intracellular lifestyle. FEMS microbiology reviews. 36, 533-562 (2012).
- Kamentsky, L., et al. Improved structure, function and compatibility for CellProfiler: modular high-throughput image analysis software. Bioinformatics. 27, 1179-1180 (2011).
Réimpressions et Autorisations
Demande d’autorisation pour utiliser le texte ou les figures de cet article JoVE
Demande d’autorisationExplorer plus d’articles
This article has been published
Video Coming Soon