Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Genoom-brede analyse met behulp van chip Isoform-specifieke Gene targets te identificeren
Hier presenteren we een chromatine immunoprecipitatie (ChIP) procedure voor genoom-brede locatie analyse van eiwit-isovormen die verschillen in een histon-bindend domein. We zijn toe te passen op ChIP-Seq analyse om de doelstellingen van het KDM5A/JARID1A/RBP2 histon demethylase te identificeren.
Werving van transcriptionele en epigenetische factoren om hun doelstellingen is een belangrijke stap in hun regelgeving. Prominent in werving zijn het eiwit domeinen die binden aan specifieke histon modificaties. Een voorbeeld van zo'n domein is de plant homeodomein (PHD), gevonden in verschillende chromatine-eiwitten. De epigenetische factor RBP2 heeft meerdere PHD domeinen, maar ze hebben verschillende functies (figuur 4). Met name de C-terminale PHD domein, gevonden in een RBP2 oncogeen fusie in de menselijke leukemie, bindt aan trimethylated lysine 4 in histon H3 (H3K4me3) 1. Het transcript die overeenkomt met de RBP2 isovorm met de C-terminale PHD accumuleert tijdens de differentiatie van promonocytic, lymfoom-afgeleide, U937 cellen in monocyten 2. In overeenstemming met beide sets van gegevens, genoom-brede analyse toonde aan dat in gedifferentieerde U937-cellen, de RBP2 eiwit wordt gelokaliseerd genomische regio's hoogverrijkt voor H3K4me3 3. Lokalisatie van RBP2 om haar doelstellingen correleert met een afname van de H3K4me3 te wijten aan RBP2 histon demethylase activiteit en een afname van de transcriptionele activiteit. In tegenstelling tot twee andere PHDs van RBP2 zijn niet in staat om H3K4me3 te binden. Met name de C-terminale domein van PHD RBP2 afwezig is in de kleinere RBP2 isovorm 4. Het is denkbaar dat de kleine isovorm van RBP2, die de interactie ontbreekt met H3K4me3, verschilt van de grotere isovorm in genomische locatie. Het verschil in genomische locatie van RBP2 isovormen rekening kan worden gehouden voor de waargenomen diversiteit in RBP2 functie. In het bijzonder, RBP2 is een cruciale speler in cellulaire differentiatie gemedieerd door de retinoblastoma eiwit (PRB). In overeenstemming met deze gegevens, vorige genome-wide analyse, zonder onderscheid te maken tussen isovormen, geïdentificeerd twee verschillende groepen van RBP2 doelwitgenen: 1) genen die gebonden zijn door RBP2 op een manier die onafhankelijk is van differentiatie, 2) genen die gebonden zijn door RBP2 in een differentiatie- afhankelijke manier.
Het identificeren van de verschillen in lokalisatie tussen de isovormen voerden wij genoom-brede locatie analyse door ChIP-Seq. Met behulp van antilichamen die zowel RBP2 isovormen hebben we verspreid RBP2 doelen op te sporen. Daarnaast hebben we antistoffen die alleen binden groot, en geen kleine RBP2 isoform (figuur 4). Na het identificeren van de grote isovorm doelstellingen, kan men dan aftrekken hen van alle RBP2 doelstellingen om de doelstellingen van de kleine isovorm onthullen. Deze gegevens geven de bijdrage van chromatine-interagerende domein in eiwit rekrutering van de bindingsplaatsen in het genoom.
Het protocol werd oorspronkelijk aangepast van B. Ren, 2001. Het is een lichte wijziging van het protocol door Odom et al.. 5 die gevonden kunnen worden op http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pre-blok en binding van antilichaam aan magnetische beads (dient te worden uitgevoerd in de nacht voor de volgende stap)
- Was de 100 pi van Dynabeads Protein G (per IP, combineren voor meerdere IP's) in 1 ml vers BSA / PBS-oplossing (50 mg BSA in 10 ml PBS-Deze oplossing zal duren voor een week).
- Verzamel de kralen met behulp van een magnetische voet en herhaal het wassen procedure nog twee keer.
- Voeg vervolgens 10 ug van antilichaam aan 250 ul van de kralen slurry in PBS / BSA-oplossing (per IP) en incubeer overnacht op een draaiend platform bij 4 ° C.
- Na voltooiing, was de kralen drie keer in 1 ml van het PBS / BSA-oplossing en vervolgens opnieuw in suspensie in 10 ul van de PBS / BSA-oplossing (per IP).
2. Cel cross-linking
- Om te beginnen deze procedure, te groeien ongeveer 10 8 cellen voor elk immunoprecipitatie of IP. Hier worden diffuus histiocytische lymfoom U937 cellen die worden gebruikt en geïnduceerde voor monocytische differentiatie met TPA voor 96 uur.
- Naar aanleiding van de celgroei, direct toe te voegen formaldehyde-oplossing aan de media tot een uiteindelijke concentratie van 1%. Dan, laat wervelen de kolven kort en hen om op kamertemperatuur te zitten voor 10 minuten. Dan, aspireren de media en spoel de cellen met 15 ml ijskoud PBS. Herhaal deze te wassen.
- Voeg vervolgens 6 mL van Lysis Buffer 1 (50 mM HEPES-KOH, pH 7,5, 140 mM NaCl, 1 mM EDTA, 10% glycerol, 0,5% NP-40, 0,25% Triton X-100, met protease-remmers) aan elke van de kolven op het ijs. Dan, rock de kolven gedurende 20 minuten bij 4 ° C.
- Tot slot, de oogst van de cellen met behulp van een cel schraper en overbrengen naar 15 ml conische buizen. Op dit punt van de cellen kan worden opgeslagen bij -80 ° C.
3. Cel Ultrasoonbehandeling
- Als de cellen werden bevroren, ontdooien ze uit. Eenmaal ontdooid, draai de cellen neer op 3000 rpm gedurende 10 minuten bij 4 ° C en gooi het supernatant. Dan, resuspendeer de cellen in 6 ml van Lysis Buffer 2 (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, met protease-remmers). Schud de buizen bij kamertemperatuur gedurende 10 minuten.
- Herhaal het centrifugeren en resuspendeer de cellen in 2,5 ml lysis buffer 3 (10 mM Tris-HCl, pH 8,0, 100 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, 0,1% natriumdeoxycholaat, 0,5% N-lauroylsarcosine, met protease-remmers) .
- Vervolgens de voorbereiding van de suspensie voor ultrasoonapparaat door het plaatsen in een bekerglas van ijzige water met de microtip van een Branson 450 Sonifier ingesteld tussen de 50 en 60% amplitude.
- Sonificeer de oplossing voor een 30 seconden constant barsten en koel op ijs gedurende 1 minuut. Herhaal deze pulsen 10 tot 15 keer. Dan, pipet de inhoud van de buis op en neer en overbrengen naar een nieuwe buis. Blijf puls en de oplossing afkoelen een extra 5 keer.
- Na sonicatie, voeg 10% Triton X-100 tot 1 / 10 van de oplossing volume. Breng de lysaten tot 1,5 ml centrifuge buizen, en spin het puin in een microcentrifuge. Vervolgens overbrengen van de cellysaat naar een nieuwe buis.
4. Chromatine Immunoprecipitatie
- Voorafgaand aan chromatine immunoprecipitatie, of chip, op te slaan 50 ul van de cel lysaat als de input monster. Dan combineer de gewist cellysaat met Dynabeads pre-gebonden antilichaam dat eerder bereid zoals hierboven beschreven. Rock the mix, in aanvulling op de 50 uL ingang monster bij 4 ° C gedurende de nacht.
- Was de kralen met 1 ml van de Wash Buffer (50 mM HEPES-KOH, pH 7,6, 0,5 M LiCl, 1 mM EDTA, 0,7% natriumdeoxycholaat, 1% NP-40). Gebruik vervolgens een magnetische staan om de kralen te verzamelen en de supernatant te verwijderen. Herhaal deze wassen 6 tot 8 keer.
- Voer een laatste wassen met 1 ml TE-plus-50 mM NaCl (10 mM Tris-HCl, pH 8,0, 50 mM NaCl, 1 mM EDTA). Spin de kralen in een microcentrifuge bij 3.000 tpm gedurende 2 minuten bij 4 ° C. Na centrifugatie, aspiratie eventueel resterende TE-buffer.
- Dan, voeg 100 ul van elutiebuffer (50 mM Tris-HCl, pH 8,0, 10 mM EDTA, 1% SDS) om de monsters. Onmiddellijk na, incubeer de monsters bij 65 ° C gedurende 10 tot 15 minuten. Scratch de buizen tegen een 1,5 mL buis rek elke 2 minuten om de kralen te houden in de suspensie.
- Verzamel de kralen met behulp van centrifugatie en de magnetische staan, en breng de supernatant om een PCR-buis. Vervolgens halen de eerder opgeslagen ingang monster en voeg drie volumes van de elutiebuffer.
- Ten slotte is het IP en de input samples 's nachts plaats in de thermische cycler bij 65 ° C totomgekeerde van de cross-banden.
- De volgende dag, voeg een volume van TE-buffer om de monsters. Vervolgens voegt u RNase A tot een uiteindelijke concentratie van 0,2 ug / ul. Incubeer de monsters in het PCR-apparaat voor 1 tot 2 uur bij 37 ° C.
- Na de incubatie toe te voegen proteinase K tot een uiteindelijke concentratie van 0,2 ug / ul. Dan, incubeer monsters in het PCR-apparaat bij 55 ° C gedurende 2 uur.
- Vervolgens een keer extract van de monsters met een volume van fenol. Pak de samples een tweede keer met een volume van fenol: chloroform: isoamylalcohol. Tot slot, extract van de monsters opnieuw met een volume van chloroform: isoamylalcohol.
- Voeg dan 30 ug van glycogeen aan elk monster. Ook, voeg NaCl tot een uiteindelijke concentratie van 0,2 Molar en twee volumes ethanol aan de monsters. Incubeer ze gedurende 30 minuten bij -80 ° C. Na incubatie, draai de monsters en decanteer het supernatant. Was de pellets met 500 pl van 75% ethanol. Dan, droog de pellets en deze opnieuw te schorten in 40 ul van water.
- Om te controleren of de grootte van de DNA-fragmenten door de sonicatie procedure, belasting 5 ug van het gezuiverde ingang monster in een 1,8% agarosegel en voer de gel. De ultrasoonapparaat procedure moet produceren van fragmenten in de range van 150 tot 350 basenparen. Echter, als de fragmenten vallen niet in dit bereik, moet de sonicatie procedure worden aangepast door het variëren van het aantal barst en de amplitude.
- Om robuustheid en specificiteit van ChIP controleren, de verrijking in control binding regio's door het uitvoeren van gen-specifieke PCR met 1 pl van de IP-monsters en een verdunningsreeks van de input monster. Twee tot drie "gebonden" regio's en een ongebonden controle regio moeten worden geselecteerd om de kwaliteit van IP-en input monsters te testen.
5. Amplificatie van genomisch DNA
- Te beginnen met 34 ul van de IP-monster of 200 ng van de input monster, uit te voeren end reparatie, 'A' staart optellen en ligatie van adapters om DNA-fragmenten met behulp van Genomic DNA-monster Prep Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc, San Diego, CA).
- Zuiveren het DNA met behulp van een PCR Purification Kit MinElute en dan is het elueren in buffer EB (10 mM Tris Cl, pH 8,5) dat is voorverwarmd tot 50 ° C. Gebruik bijvoorbeeld 23 pL en 46 ul voor de finale elutie van IP en input DNA-monsters, respectievelijk.
- Maak de PCR-reactie met behulp van 23 pi van het DNA met adapters, en 25 uL Phusion DNA-polymerase uit de kit, 1 ul van 20 uM Sol_PCR_1, en 1 ul van 20 uM Sol_PCR_2. Lopen de PCR-reactie als volgt: 1) 30 seconden bij 98 ° C; 2) 10 seconden bij 98 ° C, 3) 30 seconden bij 65 ° C; 4) 30 seconden bij 72 ° C; herhalen de stappen stappen 2-4 18 keer en dan 5 minuten bij 72 ° C, uiteindelijk houden bij 4 ° C.
- Na de PCR-amplificatie, zuiveren het DNA met de QIAGEN MinElute PCR Purification Kit. Pre-warm 15 ul buffer EB tot 50 ° C en elueer het DNA. Verdun 0,5 pi van het monster 1:04 en het uitvoeren van een Nanodrop lezen.
6. Gel zuivering van geamplificeerde producten
- Te zuiveren van de geamplificeerde producten, bereiden een 1,8% agarose gel van 50 ml met behulp van HPLC-kwaliteit water. Voeg TAE-en ethidiumbromide na de agarose is gesmolten. Dan giet de gel. Laad de gel na toevoeging van 4 pi van laadbuffer aan de ingang en IP-monsters. Ren dan de gel op 120 volt voor 45 minuten.
- Analyseren van de gel na het lopen. De gel moet uitwijzen dat fragmenten in het bereik tussen 150 en 350 basenparen worden geproduceerd. Zij vertegenwoordigen genomische DNA-fragmenten tussen de 50 en 250 basenparen in lengte en een adapter.
- Accijnzen het gebied van gel met daarin het materiaal in de 150 350 basenparen uit met een scalpel. Neem de zorg om te voorkomen weg te snijden van de adapter-adapter band, die loopt van ongeveer 120 baseparen. Herstellen het DNA met behulp van een QIAquick Gel Extraction Kit volgens de instructies van de fabrikant. In het bijzonder, gebruikt u een kolom uit de QIAquick Gel Extraction Kit voor een gel stukje van 400 mg of minder. Om te beginnen de extractie proces, voeg 3 volumes van QG buffer tot een volume van gel. Voeg een volume van isopropanol en de belasting van het mengsel op de kolom. Gebruik 0,5 ml van QG om de kolom te wassen, gevolgd door de standaard procedure beschreven in de kit handleiding. Gebruik H 2 O voorverwarmd tot 50 ° C om het DNA te elueren. Incubeer de kolom met 30 ul van H 2 O gedurende 5 minuten bij 37 ° C vóór het spinnen naar beneden.
- Droog het monster naar beneden om precies 11 uL in een Speedvac zonder warmte. Verwijder een pi van het monster en meet de DNA-concentratie met behulp van een Nanodrop spectrofotometer.
- Tot slot, te identificeren verrijkte genproducten met de Illumina Genome AnalyzerIIe zoals beschreven op http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Representatieve resultaten
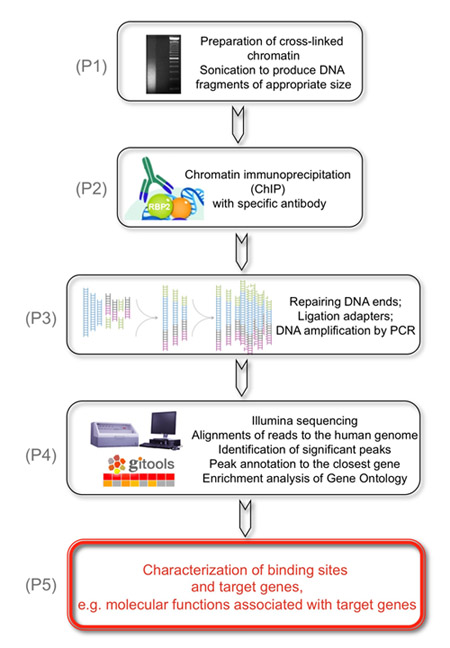
Figuur 1. Het algemene doel van het volgende experiment is het identificeren van genomische doelen van KDM5A/JARID1A/RBP2 histon demethylase.
(P1) Dit wordt bereikt door de voorbereiding van de cross-linked chromatine, dat is gesoniceerd om DNA-fragmenten van de juiste maat te produceren. (P2) Als tweede stap worden RBP2 gebonden DNA-fragmenten immunogeprecipiteerd met RBP2 antilichamen. (P3) Vervolgens worden de herstelde DNA-fragmenten gerepareerd aan de uiteinden en adapters worden geligeerd op de uiteinden van genomische DNA om bibliotheken van genomisch DNA voor te bereiden op analyse van de stroming cellen in de Illumina Cluster Station. De DNA-bibliotheken worden geamplificeerd door PCR met behulp van lage aantal cycli. (P4) Ten slotte, Illumina volgorde kort leest zijn uniek afgestemd op het menselijk genoom, zijn significante pieken geïdentificeerd en geannoteerde naar de dichtstbijzijnde genen om RBP2 verrijkt regio's te identificeren. (P5) de resultaten zijn verkregen die aantonen dat moleculaire functies geassocieerd met RBP2 doelwitgenen op basis van genoom-brede identificatie van RBP2 verrijkt regio's.
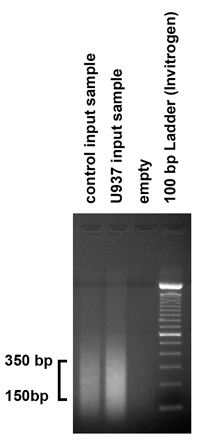
Figuur 2. Het controleren van de resultaten van het chromatine ultrasoonapparaat Om de grootte van de DNA-fragmenten die door de sonicatie procedure te verifiëren, werd 5 pg (1 / 10) van het gezuiverde ingang sample geladen op 1,8% agarose gel. Zoals verwacht, onze sonicatie procedure geproduceerd fragmenten in het bereik van 150-350 bp. Echter, als de fragmenten vallen niet in dit bereik, moet de sonicatie procedure worden aangepast, door het variëren van het aantal barst en de amplitude.
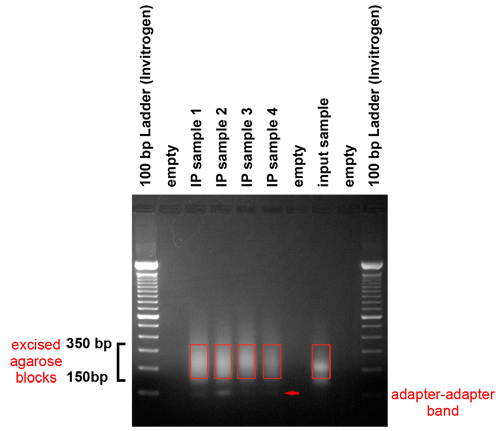
Figuur 3. Gel zuivering van geamplificeerde producten. De PCR-producten worden uitgevoerd op een gel om de adapters te verwijderen en een grootte-range van sjablonen voor de cluster generatie platform te selecteren. Deze gel laat zien dat fragmenten in het bereik tussen 150 en 350 basenparen werden geproduceerd. Zij vertegenwoordigen genomische DNA-fragmenten tussen de 50 en 250 basenparen in lengte en een adapter. We accijnzen het geselecteerde gebied van de gel met een scalpel. Zorg moet worden genomen om de adapter-adapter band, die loopt van ongeveer 120 baseparen te voorkomen.
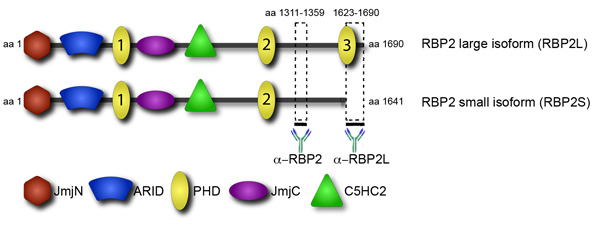
Figuur 4. Isovorm-specifieke antilichaam maakt onderscheid tussen grote en kleine isovormen van RBP2. RBP2 eiwitstructuur wordt gepresenteerd in het domein te bekijken. RBP2 bevat een aantal domeinen: de katalytische histon demethylering JmjC domein en bijbehorende JmjN domein, een ARID domeinnaam in staat is van sequentie-specifieke DNA-binding, een C5HC2 zinkvinger die mogelijk kunnen interageren met DNA of andere eiwitten, en meerdere PHD domeinen. De twee anti-RBP2 antilichamen die het mogelijk maken onderscheid te maken tussen RBP2 isovormen zijn afgeleid ten opzichte van de RBP2 fragmenten aangegeven met dikke lijnen.
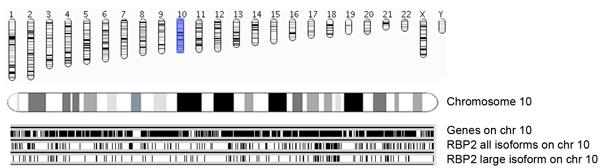
Figuur 5a. Overzicht van de RBP2 binding regio's, samen met chromosoom en Ensembl genen. Genomische coördinaten van de geïdentificeerde verrijkt RBP2 (alle isovormen en grote isovorm) binding regio's worden gepresenteerd chromosoom wijs. Occupances van Ensembl genen (versie 54, hg18) in de chromosomen (chromosoom 10 op deze foto) worden gepresenteerd als zwarte balken (bovenste paneel). Elke RBP2 binding regio wordt voorgesteld als een verticale lijn, waar de middelste paneel toont alle RBP2 isovormen bindend regio's op chromosoom 10, en het onderste paneel toont RBP2 grote isovorm binding regio's. De middelste en onderste panelen geven overzicht van overlappende en specifieke bezetting van RBP2 isovormen op chromosoom 10.
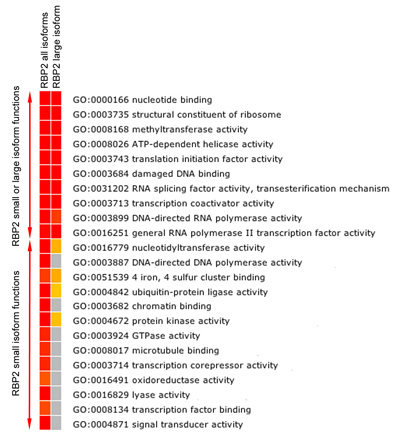
Figuur 5b. Functionele analyse van de verrijking RBP2 doelwitgenen. Temperatuurkaart toont FDR gecorrigeerd significant (p-waarde ≤ 0,05) verrijkt Moleculaire Functie categorieën GO onder de genen gebonden (het dichtst genen om de RBP2 binding regio) door RBP2 (alle grote en isovormen). Kleuren in de richting van rood geven een hoge statistische significantie, geel betekent een lage statistische significantie, en grijs geeft geen statistische significantie. Verrijking analyse toont de overlappende en isovorm specifieke moleculaire functies van RBP2 doelwitgenen.
Functionele verschillen tussen RBP2 isovormen zijn niet vastgesteld. We hebben gebruik gemaakt van een alomvattende aanpak van genomische regio's gebonden RBP2 isovormen te identificeren en de functionele categorieën die deze regio's vertegenwoordigen definiëren. Dit werd bereikt door ChIP-Seq analyse gevolgd door bio-informatica analyse van de verkregen volgorde leest.
RBP2 wijzigt gemethyleerde lysine residuen op histon staarten. Wij vonden dat RBP2 grote isovorm de erkenning module bevat voor gemethyleerd histon-lysine en RBP2 kleine isovorm zonder deze module binden aan verschillende regio's in het menselijke genoom (figuur 5A). Belangrijk is dat isovorm-specifieke regio's en overlappende regio's behoren tot genen met verschillende moleculaire functies (figuur 5B). Bijvoorbeeld, "chromatine binding" en "transcriptiefactor binding" functies kunnen worden toegeschreven aan gen-targets van RBP2 kleine isovorm, maar niet van RBP2 grote isovorm (Figuur 5B). Door het vergelijken van de werkelijke gen sets gegenereerd voor alle isovormen en RBP2 grote isovorm (gegevens niet getoond), hebben we ook kunnen definiëren als de grote isovorm is speciaal aangetrokken om bepaalde genen.
Dit werk werd ondersteund door 115.347-RSG-08-271-01-GMC van ACS, en door CA138631 subsidie van NIH.
Oligonucleotidesequenties 2006 Illumina, Inc All rights reserved.
- Sol_PCR_1
Sequentie 5'-AAT GAT ACG GCG ACC ACC GAG ATC TAC ACT CTT TCC CTA CAC GAC GCT CCG CTT ATC T-3 ' - Sol_PCR_2
Sequentie 5'-CAA GCA GAA GAC GGC ATA CGA CTT GCT CCG ATC T-3 '
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved