Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Analyse du génome entier en utilisant ChIP d'identifier les gènes cibles spécifiques Isoform
Ici, nous présentons une immunoprécipitation de la chromatine (ChIP) procédure pour analyse de la localisation du génome entier d'isoformes de protéines qui diffèrent dans un domaine histone-contraignant. Nous sommes en l'appliquant à ChIP-Seq analyse pour identifier les cibles de la déméthylase KDM5A/JARID1A/RBP2 histones.
Le recrutement de facteurs transcriptionnels et épigénétiques de leurs objectifs est une étape clé dans leur régulation. Place de choix dans le recrutement sont les domaines de protéines qui se lient aux modifications des histones spécifiques. Un domaine est l'homéodomaine plante (PHD), trouvés dans plusieurs chromatine des protéines de liaison. Le facteur de RBP2 épigénétique a de multiples domaines PHD, cependant, ils ont des fonctions différentes (figure 4). En particulier, le C-terminale du domaine PHD, a trouvé dans une fusion RBP2 oncogènes dans la leucémie humaine, se lie à triméthylée lysine 4 de l'histone H3 (H3K4me3) 1. La transcription correspondant à l'isoforme RBP2 contenant le PHD C-terminale s'accumule pendant la différenciation des promonocytaire, lymphomes dérivés, les cellules U937 en monocytes 2. Conformément aux deux ensembles de données, l'analyse du génome entier ont montré que dans les cellules U937 différenciées, la protéine localisée à RBP2 obtient régions génomiques hautement enrichi pour H3K4me3 3. Localisation des RBP2 à ses objectifs en corrélation avec une diminution due à H3K4me3 RBP2 activité déméthylase histone et une diminution de l'activité transcriptionnelle. En revanche, deux doctorats autres RBP2 sont incapables de se lier H3K4me3. Notamment, le domaine C-terminal de doctorat de RBP2 est absent dans la petite RBP2 isoforme 4. Il est concevable que l'isoforme de la petite RBP2, qui manque d'interaction avec les H3K4me3, diffère de la grande isoforme de localisation génomique. La différence de localisation génomique des RBP2 isoformes peuvent rendre compte de la diversité observée dans RBP2 fonction. Plus précisément, RBP2 est un acteur essentiel dans la différenciation cellulaire médiée par la protéine du rétinoblastome (pRB). Conformément à ces données, l'échelle du génome précédente analyse, sans distinction entre les isoformes, a identifié deux groupes distincts de gènes cibles RBP2: 1) les gènes liés par RBP2 d'une manière qui est indépendante de la différenciation, 2) les gènes liés par RBP2 dans une différenciation manière dépendante.
Pour identifier les différences de localisation entre les isoformes nous avons effectué une analyse du génome entier emplacement par ChIP-Seq. En utilisant des anticorps qui permettent de détecter à la fois RBP2 isoformes nous avons localisé l'ensemble RBP2 cibles. En outre, nous avons des anticorps qui se lient seulement grand, et pas de petits RBP2 isoforme (Figure 4). Après l'identification des cibles isoforme grande, on peut alors les soustraire de toutes les cibles RBP2 pour révéler les cibles de l'isoforme de petite taille. Ces données montrent la contribution de la chromatine en interaction de domaine dans le recrutement de protéines pour ses sites de liaison dans le génome.
Le protocole a été adapté de B. Ren, 2001. Il représente une légère modification du protocole par Odom et al. 5, qui se trouve à l' http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pré-bloc et fixation de l'anticorps à des billes magnétiques (doit être effectué la nuit avant l'étape suivante)
- Lavez 100 uL d'Dynabeads protéine G (par IP, se combinent pour plusieurs adresses IP) dans 1 ml de frais de BSA / PBS solution (50 mg de BSA dans 10 ml de PBS-Cette solution va durer une semaine).
- Ramassez les perles en utilisant un support magnétique et répétez la procédure de lavage deux fois plus.
- Ensuite, ajoutez 10 ug d'anticorps à 250 pi de la bouillie de perles dans du PBS / BSA solution (par IP) et incuber pendant la nuit sur une plateforme rotative à 4 ° C.
- À la fin, se laver les perles à trois reprises dans 1 ml de la solution de PBS / BSA et ensuite remettre en suspension dans 10 pl de la solution de PBS / BSA (par IP).
2. Cellule de réticulation
- Pour commencer cette procédure, croître d'environ 10 8 cellules pour chaque immunoprécipitation, ou IP. Ici, diffuse histiocytaire cellules U937 lymphome sont utilisés et induit la différenciation monocytaire avec le TPA pendant 96 heures.
- Suite à la croissance cellulaire, ajouter une solution de formaldéhyde directement aux médias à une concentration finale de 1%. Puis, tourbillon brièvement flacons et de leur permettre de reposer à température ambiante pendant 10 minutes. Ensuite, aspirez les médias et rincer les cellules avec 15 ml de PBS glacé. Répéter ce lavage une fois.
- Ensuite, ajoutez 6 ml d'une mémoire tampon de lyse (50 mM HEPES-KOH, pH 7,5, NaCl 140 mM, EDTA 1 mM, glycérol 10%, 0,5% NP-40, 0,25% de Triton X-100, contenant des inhibiteurs de protéase) pour chaque des flacons sur la glace. Puis, le rock des flacons pendant 20 minutes à 4 ° C.
- Enfin, la récolte des cellules à l'aide d'un grattoir de cellules et de les transférer à 15 ml tubes coniques. À ce stade, les cellules peuvent être stockés à -80 ° C.
3. Sonication cellulaire
- Si les cellules ont été congelées, les dégeler. Une fois décongelé, le spin des cellules vers le bas à 3000 rpm pendant 10 minutes à 4 ° C et jeter le surnageant. Ensuite, remettre en suspension les cellules dans 6 mL de 2 tampon de lyse (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, contenant des inhibiteurs de la protéase). Rock the tubes doucement à température ambiante pendant 10 minutes.
- Répétez la centrifugation et la remettre en suspension les cellules dans 2,5 ml de 3 tampon de lyse (10 mM Tris-HCl, pH 8,0, NaCl 100 mM, EDTA 1 mM, 0,5 mM EGTA, désoxycholate de sodium 0,1%, 0,5% de N-lauroylsarcosine, contenant des inhibiteurs de protéase) .
- Ensuite, préparer la suspension pour une sonication en le plaçant dans un bécher d'eau glacée avec la micropointe d'un Sonifier Branson 450 réglé entre 50 et 60% d'amplitude.
- Soniquer la solution pour un éclat constant 30 secondes et laisser refroidir sur glace pendant 1 minute. Répétez ces impulsions 10 à 15 fois. Puis, une pipette le contenu du tube de haut en bas et de les transférer dans un nouveau tube. Continuer à impulsions et refroidir la solution un supplément de 5 fois.
- Après sonication, ajouter 10% de Triton X-100 à 1 / 10 du volume de solution. Transférer les lysats des tubes de 1,5 ml par centrifugation, et le spin des débris dans une microcentrifugeuse. Puis transférer le lysat cellulaire dans un nouveau tube.
4. Immunoprécipitation de la chromatine
- Avant immunoprécipitation de la chromatine, ou puce, économiser 50 uL du lysat cellulaire que l'échantillon d'entrée. Ensuite, mélanger le lysat cellulaire effacé avec Dynabeads pré-lié à un anticorps qui ont été préalablement préparés comme décrit ci-dessus. Rocher le mélange, en plus de l'échantillon d'entrée 50 uL, à 4 ° C pendant la nuit.
- Laver les billes avec 1 mL de tampon de lavage (50 mM HEPES-KOH pH 7,6, 0,5 M LiCl, 1mM EDTA, le désoxycholate de sodium à 0,7%, 1% NP-40). Ensuite, utilisez un support magnétique pour recueillir les perles et retirer le surnageant. Répéter ce lavage 6 à 8 fois.
- Effectuer un lavage final avec 1 ml de TE-plus-50 mM de NaCl (10 mM Tris-HCI, pH 8,0, NaCl 50 mM, EDTA 1 mM). Faites tourner les perles dans une microcentrifugeuse à 3000 rpm pendant 2 minutes à 4 ° C. Après la centrifugation, aspirer toute tampon résiduel TE.
- Ensuite, ajouter 100 ul de tampon d'élution (50 mM Tris-HCI, pH 8,0, EDTA 10 mM, SDS 1%) pour les échantillons. Immédiatement après, incuber les échantillons à 65 ° C pendant 10 à 15 minutes. Grattez les tubes contre un rack tube de 1,5 ml toutes les 2 minutes pour maintenir les billes en suspension.
- Ramassez les perles en utilisant la centrifugation et le support magnétique, et le transfert du surnageant dans un tube PCR. Ensuite, récupérer l'échantillon d'entrée précédemment enregistrés et ajouter 3 volumes de tampon d'élution.
- Enfin, placez les échantillons IP et d'entrée dans le thermocycleur nuit à 65 ° C àinverser les liens croisés.
- Le lendemain, ajouter 1 volume de tampon TE aux échantillons. Ensuite, ajoutez la RNase A à une concentration finale de 0,2 ug / uL. Incuber les échantillons dans le thermocycleur pour 1 à 2 heures à 37 ° C.
- Après incubation, ajouter la protéinase K à une concentration finale de 0,2 ug / uL. Puis, incuber des échantillons dans le thermocycleur à 55 ° C pendant 2 heures.
- Ensuite, extraire les échantillons une fois avec un volume de phénol. Extraire les échantillons une seconde fois avec un volume de phénol: chloroforme: alcool isoamylique. Enfin, l'extrait les échantillons une fois de plus avec un volume de chloroforme: alcool isoamylique.
- Ensuite, ajoutez 30 g de glycogène à chaque échantillon. En outre, ajouter du NaCl à une concentration finale de 0,2 volumes molaires et deux de l'éthanol pour les échantillons. Laisser incuber pendant 30 minutes à -80 ° C. Après incubation, le spin des échantillons et décanter le surnageant. Lavez les boulettes avec 500 ul d'éthanol à 75%. Ensuite, sécher les boulettes et remettre en suspension eux dans 40 ul d'eau.
- Pour vérifier la taille des fragments d'ADN produites par la procédure sonication, charge 5 pg de l'échantillon d'entrée purifié dans un gel d'agarose 1,8% et exécutez le gel. La procédure sonication devraient produire des fragments de l'ordre de 150 à 350 paires de bases. Cependant, si les fragments ne tombent pas dans cette gamme, la procédure sonication doit être ajustée en faisant varier le nombre de salves et de l'amplitude.
- Pour vérifier la robustesse et la spécificité de puce, l'enrichissement dans les régions de contrôle obligatoires en effectuant spécifiques du gène par PCR avec 1 pl des échantillons IP et une série de dilution de l'échantillon d'entrée. Deux à trois «lié» des régions et une région de contrôle indépendant doivent être sélectionnés en vue de tester la qualité des échantillons IP et d'entrée.
5. Amplification de l'ADN génomique
- A partir de 34 pl de l'échantillon IP ou 200 ng de l'échantillon d'entrée, effectuer la réparation fin, 'A' plus la queue et la ligature des adaptateurs pour utiliser des fragments d'ADN génomique échantillon d'ADN Prep Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc, San Diego, Californie).
- Purifier l'ADN en utilisant un kit de purification MinElute PCR puis éluer de tampon EB (10 mM Tris Cl, pH 8,5) qui a été pré-chauffé à 50 ° C. Par exemple, utiliser 23 uL et 46 uL pour l'élution finale de la PI et des échantillons d'ADN d'entrée, respectivement.
- Faire de la réaction PCR en utilisant 23 uL d'ADN avec des adaptateurs, et 25 uL d'ADN polymérase Phusion du kit, 1 pl de 20 pM Sol_PCR_1, et 1 ul de 20 pM Sol_PCR_2. Exécutez la réaction PCR comme suit: 1) 30 secondes à 98 ° C; 2) 10 secondes à 98 ° C; 3) 30 secondes à 65 ° C; 4) 30 secondes à 72 ° C; on répète les étapes étape 2-4 18 fois, puis 5 minutes à 72 ° C, enfin maintien à 4 ° C.
- Après amplification par PCR, de purifier l'ADN avec le kit QIAGEN MinElute PCR Purification. Préchauffer 15 ul de tampon EB à 50 ° C et éluer l'ADN. Diluer 0,5 uL de l'échantillon et 01h04 effectuer une lecture Nanodrop.
6. Purification sur gel des produits amplifiés
- Pour purifier les produits amplifiés, préparer un gel d'agarose 1,8% de 50 ml en utilisant l'eau de qualité CLHP. Ajouter TAE et le bromure d'éthidium après l'agarose a fondu. Ensuite, versez le gel. Chargez le gel après l'ajout de 4 pi de tampon de chargement à l'entrée et des échantillons de propriété intellectuelle. Ensuite, exécutez le gel à 120 volts pendant 45 minutes.
- Analyser le gel après leur exécution. Le gel doit révéler que des fragments dans la gamme entre 150 et 350 paires de base sont produites. Ils représentent des fragments d'ADN génomique entre 50 et 250 paires de base de longueur et d'un adaptateur.
- Accise de la région du gel contenant le matériau dans la gamme de 150 350 paires de base avec un scalpel. Prenez soin d'éviter l'excision la bande adaptateur adaptateur, qui fonctionne à environ 120 paires de bases. Récupérer l'ADN en utilisant un kit QIAquick Gel Extraction selon les instructions du fabricant. Plus précisément, l'utilisation d'une colonne du kit QIAquick Gel Extraction d'une tranche de gel de 400 mg ou moins. Pour commencer le processus d'extraction, ajouter 3 volumes de tampon QG pour 1 volume de gel. Ajouter 1 volume d'isopropanol et de charger le mélange sur la colonne. Utiliser 0,5 ml de QG pour laver la colonne, suivie par la procédure standard décrite dans le kit manuel. Utilisez H 2 O préchauffée à 50 ° C pour éluer l'ADN. Incuber la colonne avec 30 ul de H 2 O pendant 5 minutes à 37 ° C avant de filer vers le bas.
- Sécher l'échantillon jusqu'à 11 uL précisément dans un Speedvac sans chaleur. Retirer 1 pl de l'échantillon et de mesurer la concentration d'ADN à l'aide d'un spectrophotomètre Nanodrop.
- Enfin, identifier les produits de gènes enrichis utilisant le génome Illumina AnalyzerIIe comme décrit au http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Les résultats représentatifs
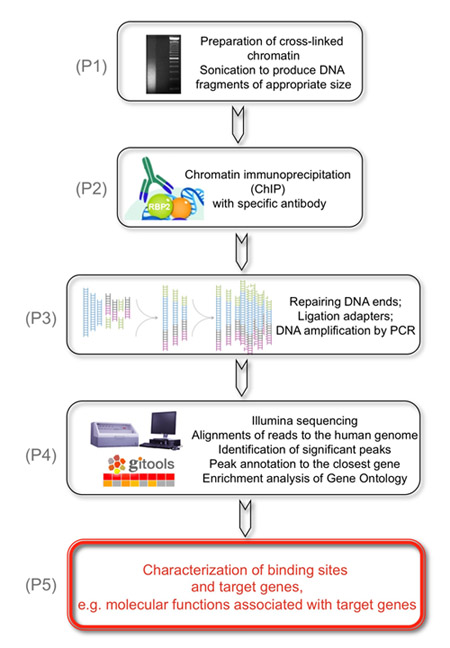
Figure 1. L'objectif global de l'expérience suivante est d'identifier les cibles génomiques de KDM5A/JARID1A/RBP2 déméthylase histones.
(P1) Ce résultat est obtenu par la préparation de la chromatine réticulée qui est soniqué pour produire des fragments d'ADN de taille appropriée. (P2) Dans une deuxième étape, les fragments d'ADN liés RBP2 sont immunoprécipités avec RBP2 anticorps. (P3) Ensuite, les fragments d'ADN récupérés sont réparés aux extrémités et les adaptateurs sont ligaturés sur les extrémités de l'ADN génomique pour préparer des bibliothèques d'ADN génomique pour l'analyse sur les cellules d'écoulement dans la station Pôle Illumina. Les banques d'ADN sont amplifiés par PCR en utilisant le faible nombre de cycles. (P4) Enfin, Illumina séquencé courtes lectures sont alignés de façon unique au génome humain, des pics significatifs sont identifiés et annotés à la plus proche des gènes afin d'identifier les régions RBP2 enrichi. (P5) Les résultats sont obtenus montrent que les fonctions moléculaires associés à RBP2 gènes cibles basées sur l'échelle du génome l'identification des régions enrichi RBP2.
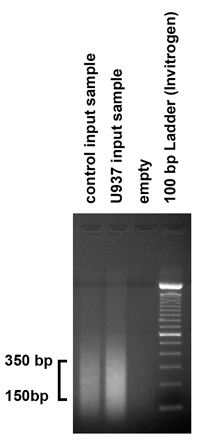
Figure 2. Vérification des résultats de sonication chromatine Pour vérifier la taille des fragments d'ADN produites par la procédure sonication, 5 ug (1 / 10) de l'échantillon d'entrée purifiée a été chargé sur 1,8% gel d'agarose. Comme prévu, notre procédure sonication produit des fragments de l'ordre de 150 à 350 pb. Cependant, si les fragments ne tombent pas dans cette gamme, la procédure sonication doit être ajustée en conséquence, en faisant varier le nombre de salves et de l'amplitude.
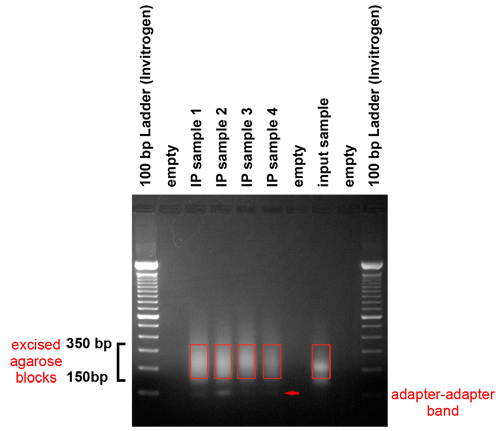
Figure 3. Purification sur gel des produits amplifiés. Les produits de PCR sont exécutées sur un gel pour éliminer les adaptateurs et sélectionnez un format de gamme de modèles pour la génération de plateforme cluster. Ce gel montre que des fragments dans la gamme entre 150 et 350 paires de bases ont été produites. Ils représentent des fragments d'ADN génomique entre 50 et 250 paires de base de longueur et d'un adaptateur. Nous accise de la région sélectionnée de gel avec un scalpel. Des précautions doivent être prises pour éviter la bande adaptateur adaptateur, qui fonctionne à environ 120 paires de bases.
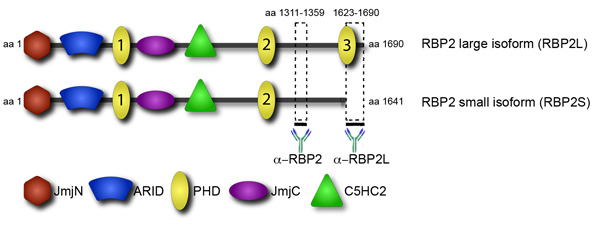
Figure 4. Isoform anticorps spécifiques permet de distinguer entre les grandes et petites isoformes du RBP2. RBP2 la structure des protéines est présenté en vue de domaine. RBP2 contient plusieurs domaines: le catalyseur d'histone déméthylation JmjC domaine et associés JmjN domaine, un domaine ARIDES capable de séquences de liaison spécifique de l'ADN, un doigt de zinc C5HC2 qui peuvent potentiellement interagir avec l'ADN ou d'autres protéines, et de multiples domaines PHD. Les deux anticorps anti-RBP2 qui permettent la distinction entre RBP2 isoformes ont été tirées contre le RBP2 fragments indiqués par des lignes épaisses.
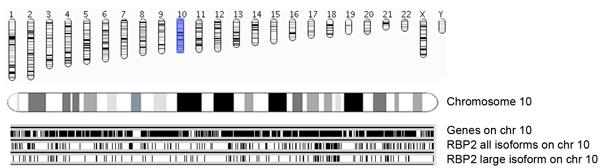
La figure 5a. Vue d'ensemble des régions RBP2 de liaison ainsi que des chromosomes et les gènes Ensembl. Coordonnées génomiques de RBP2 identifié enrichi (toutes les isoformes et de l'isoforme de grande taille) des régions de liaison sont présentés chromosomes sage. Occupances de gènes Ensembl (version 54; hg18) dans les chromosomes (le chromosome 10 dans cette image) sont présentés comme des barres noires (panneau supérieur). Chaque région RBP2 liaison est représentée par une ligne verticale, où le panneau du milieu montre toutes les isoformes RBP2 régions de liaison sur le chromosome 10, et le panneau du bas montre RBP2 régions isoforme grande contraignant. Le milieu et en bas des panneaux donnent aperçu de chevauchement et de l'occupation spécifique de RBP2 isoformes sur le chromosome 10.
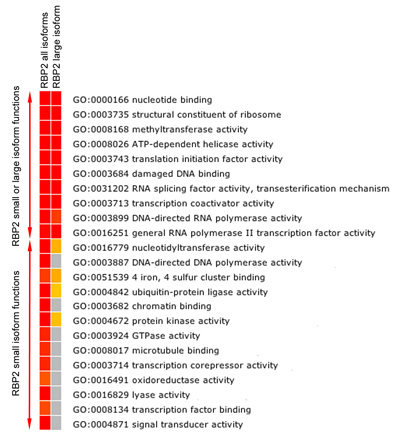
La figure 5b. L'analyse d'enrichissement fonctionnel de RBP2 gènes cibles. Heatmap montrant FDR corrigée de façon significative (valeur p ≤ 0,05) enrichi GO catégories Fonction moléculaire entre les gènes liés (le plus proche des gènes de la région RBP2 contraignante) par RBP2 (isoformes tous et de grande taille). Couleurs vers le rouge indiquent la significativité statistique élevé, jaune indique une signification statistique faible, et le gris indique l'absence de signification statistique. L'analyse d'enrichissement montre les chevauchements et isoforme spécifique des fonctions moléculaires de RBP2 gènes cibles.
Les différences fonctionnelles entre RBP2 isoformes n'ont pas été déterminées. Nous avons utilisé une approche globale pour identifier les régions génomiques liés par RBP2 isoformes et de définir les catégories fonctionnelles que ces régions représentent. Cela a été accompli par ChIP-Seq analyse suivie par l'analyse bioinformatique des séquences obtenues lit.
RBP2 modifie méthylé résidus lysine sur la queue des histones. Nous avons constaté que RBP2 isoforme de grande taille contenant le module de reconnaissance pour méthylé isoforme histone petite lysine et RBP2 dépourvues de ce module pour lier les différentes régions dans le génome humain (figure 5A). Surtout, l'isoforme spécifique des régions et des régions qui se chevauchent appartiennent à des gènes de différentes fonctions moléculaires (figure 5B). Par exemple, «chromatine contraignante" et "facteur de transcription liant« les fonctions peuvent être attribuées à des gènes cibles RBP2 isoforme petit mais pas des RBP2 isoforme de grande taille (figure 5B). En comparant les gènes réels générés pour tous les ensembles et les isoformes RBP2 isoforme de grande taille (données non présentées), on peut aussi définir si l'isoforme grande est spécialement recruté pour certains gènes.
Ce travail a été soutenu par 115 347-RSG-08-271-01-GMC d'ACS, et par CA138631 subventions du NIH.
Séquences oligonucléotidiques 2006 Illumina, Inc Tous droits réservés.
- Sol_PCR_1
Séquence 5'-AAT GCG GAT ACG CAC CAC GAG ATC ATC LOI CTT TCC CTA CAC GAC TGC CTT GCC ATC T-3 ' - Sol_PCR_2
Séquence 5'-CAA GCA GAA GAC GGC CGA ATA GCT ATC CTT GCC T-3 '
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved