Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Genomweite Analyse mittels ChIP zu Isoform-spezifische Gene-Targets zu identifizieren
Hier präsentieren wir eine Chromatin-Immunopräzipitation (ChIP) Verfahren zur genomweiten Ort Analyse von Protein-Isoformen, die in einer Histon-bindende Domäne unterscheiden. Wir wenden es ChIP-Seq-Analyse, um die Ziele des KDM5A/JARID1A/RBP2 Histon-Demethylase zu identifizieren.
Rekrutierung von Transkriptions-und epigenetische Faktoren, um ihre Ziele ist ein wichtiger Schritt in ihrer Regulierung. Prominent in Rekrutierung featured sind die Protein-Domänen, die auf bestimmte Histon-Modifikationen zu binden. Ein solcher Bereich ist die Anlage homeodomain (PHD), in mehreren Chromatin-bindenden Proteinen gefunden. Die epigenetische Faktor RBP2 mehrere PHD-Domänen, jedoch haben sie unterschiedliche Funktionen (Abbildung 4). Insbesondere bindet die C-terminale Domäne PHD, in einem RBP2 onkogenen Fusion in menschlichen Leukämien gefunden, um trimethyliertes Lysin 4 in Histon H3 (H3K4me3) 1. Das Transkript entsprechend der RBP2 Isoform mit dem C-terminalen PHD sammelt während der Differenzierung von promonocytic, Lymphom-derived, U937-Zellen in Monozyten 2. In Übereinstimmung mit beiden Datensätzen zeigte genomweite Analyse, dass in differenzierten U937-Zellen, die RBP2 Protein genomischen Regionen in hohem Grade für H3K4me3 3 angereichert wird lokalisiert. Lokalisierung von RBP2 seine Ziele korreliert mit einer Abnahme der H3K4me3 aufgrund RBP2 Histon-Demethylase-Aktivität und eine Abnahme der transkriptionellen Aktivität. Im Gegensatz dazu sind zwei weitere PHDs von RBP2 nicht H3K4me3 binden. Bemerkenswert ist, dass die C-terminale Domäne von PHD RBP2 in den kleineren RBP2 Isoform 4 fehlen. Es ist denkbar, dass die kleinen Isoform RBP2, die Interaktion fehlt mit H3K4me3, von der größeren Isoform in der genomischen Lage unterscheidet. Der Unterschied in der genomischen Lage des RBP2 Isoformen für die beobachtete Vielfalt in RBP2 Funktion Konto. Insbesondere ist RBP2 eine kritische Spieler in der zellulären Differenzierung durch die Retinoblastomprotein (pRB) vermittelt. In Übereinstimmung mit diesen Daten, frühere genomweite Analyse, ohne Unterscheidung zwischen Isoformen, wurden zwei unterschiedliche Gruppen von RBP2 Zielgene: 1) Gene durch RBP2 in einer Weise, die unabhängig von Differenzierung gebunden ist; 2) Gene durch RBP2 in einer gebundenen Differenzierung- abhängigen Weise.
Zur Identifizierung Unterschiede in der Lokalisation zwischen den Isoformen führten wir genomweite Standortanalyse durch ChIP-Seq. Mit Antikörpern, die sowohl RBP2 Isoformen wir alle RBP2 Ziele gefunden haben zu erkennen. Zusätzlich haben wir Antikörper, binden nur groß und nicht klein RBP2 Isoform (Abbildung 4). Nach der Identifizierung der große Isoform Ziele kann man dann davon subtrahieren alle RBP2 Ziele, um die Ziele von kleinen Isoform offenbaren. Diese Daten zeigen, den Beitrag der Chromatin-Interaktion Domain in Protein Einstellung in ihren Bindungsstellen im Genom.
Das Protokoll wurde ursprünglich von B. Ren, 2001 angepasst. Es stellt eine leichte Modifikation des Protokolls durch Odom et al. 5, die Sie hier finden http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pre-Block und Bindung des Antikörpers an magnetische Kügelchen (Sollte der Nacht vor dem nächsten Schritt ausgeführt werden)
- Wash 100 L Dynabeads Protein G (pro IP, für mehrere IPs kombinieren) in 1 ml frischem BSA / PBS-Lösung (50 mg BSA in 10 mL PBS-Diese Lösung wird für eine Woche reicht).
- Sammeln Sie die Kugeln mit einem Magnetfuß, und wiederholen Sie den Waschvorgang zwei weitere Male.
- Anschließend fügen Sie 10 ug von Antikörpern gegen 250 ul der Perlen Gülle in PBS / BSA-Lösung (pro IP) beimpft und über Nacht auf einer rotierenden Plattform bei 4 ° C.
- Nach der Fertigstellung, waschen Sie die Beads dreimal in 1 ml der PBS / BSA-Lösung und dann in 10 ul PBS / BSA-Lösung (pro IP) resuspendieren.
2. Zell-Vernetzung
- Zu Beginn dieses Verfahrens, wachsen etwa 10 8 Zellen pro Immunpräzipitation oder IP. Hier sind diffuse histiozytisches Lymphom U937-Zellen verwendet und induzierte für monozytären Differenzierung mit TPA für 96 Stunden.
- Nach Zellwachstum, fügen Formaldehyd-Lösung direkt auf die Medien bis zu einer Endkonzentration von 1%. Dann können wirbeln die Flaschen kurz und sie bei Raumtemperatur für 10 Minuten sitzen. Dann saugen die Medien und waschen Sie die Zellen mit 15 ml eiskaltem PBS. Wiederholen Sie diesen waschen einmal.
- Als Nächstes fügen Sie 6 ml Lysispuffer 1 (50 mM HEPES-KOH, pH 7,5, 140 mM NaCl, 1 mM EDTA, 10% Glycerin, 0,5% NP-40, 0,25% Triton X-100, mit Protease-Inhibitoren) in jede der Kolben auf Eis. Dann rocken die Kolben für 20 Minuten bei 4 ° C.
- Schließlich Ernte der Zellen mit einem Zellschaber und übertragen diese auf 15 ml konische Röhrchen. An dieser Stelle können die Zellen bei -80 ° C gelagert werden
3. Zell-Beschallung
- Wenn die Zellen wurden eingefroren, tauen sie aus. Einmal aufgetaut, drehen Sie das Zellen nach unten bei 3.000 rpm für 10 Minuten bei 4 ° C und den Überstand verwerfen. Dann die Zellen in 6 ml Lysepuffer 2 (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, mit Protease-Inhibitoren). Rock the Röhrchen vorsichtig bei Raumtemperatur für 10 Minuten.
- Wiederholen Sie die Zentrifugation und Resuspendieren der Zellen in 2,5 ml Lysispuffer 3 (10 mM Tris-HCl, pH 8,0, 100 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, 0,1% Natriumdeoxycholat, 0,5% N-Lauroylsarcosin, mit Protease-Inhibitoren) .
- Als nächstes bereiten die Aussetzung für Beschallung, indem Sie es in ein Becherglas mit Eiswasser mit der Mikrospitze eines Branson 450 Sonifier auf einen Wert zwischen 50 und 60% Amplitude.
- Mit Ultraschall die Lösung für eine 30 Sekunden konstant platzen und kühlen auf Eis für 1 Minute. Wiederholen Sie diese Impulse von 10 bis 15 mal. Dann Pipette der Inhalt des Röhrchens auf und ab und übertragen Sie sie auf eine neue Röhre. Weiter zu Puls und die Lösung eine zusätzliche 5-mal.
- Nach Beschallung, mit 10% Triton X-100 bis 1 / 10 der Lösung Volumen. Übertragen Sie die Lysate bis 1,5 mL Zentrifugenröhrchen, und drehen Sie die Trümmer in einer Mikrozentrifuge. Übertragen Sie anschließend das Zelllysat in ein neues Röhrchen.
4. Chromatin Immunopräzipitation
- Vor Chromatinimmunpräzipitation oder Chip, sparen Sie 50 ul der Zelllysate wie das Eingangs-Sample. Dann verbinden die gelöscht Zelllysat mit Dynabeads, um Antikörper, die zuvor wie oben beschrieben hergestellt pre-gebunden. Rock the Mischung, zusätzlich zu den 50 ul Eingang Probe bei 4 ° C über Nacht.
- Waschen Sie die Kugeln mit 1 mL der Waschpuffer (50 mM HEPES-KOH, pH 7,6, 0,5 M LiCl, 1mM EDTA, 0,7% Natriumdeoxycholat, 1% NP-40). Verwenden Sie dann ein magnetisches stehen, um die Perlen zu sammeln und entfernen Sie den Überstand. Wiederholen Sie diesen waschen 6 bis 8 mal.
- Führen Sie eine letzte Waschung mit 1 mL TE-plus-50 mM NaCl (10 mM Tris-HCl, pH 8,0, 50 mM NaCl, 1 mM EDTA). Drehen Sie die Perlen in einer Mikrozentrifuge bei 3.000 rpm für 2 Minuten bei 4 ° C. Nach der Zentrifugation absaugen restliche TE-Puffer.
- Dann fügen Sie 100 ul Elutionspuffer (50 mM Tris-HCl, pH 8,0, 10 mM EDTA, 1% SDS) zu den Proben. Unmittelbar nach, inkubieren Sie die Proben bei 65 ° C für 10 bis 15 Minuten. Scratch die Rohre gegen eine 1,5-ml-Tube-Rack alle 2 Minuten, um die Perlen in der Schwebe zu halten.
- Sammeln Sie die Kugeln mittels Zentrifugation und die magnetische stehen, und überweisen Sie den Überstand in ein PCR-Röhrchen. Dann rufen Sie die zuvor gespeicherten Eingangs-Sample, und fügen Sie 3 Bände der Elutionspuffer.
- Schließlich legen Sie die IP-und Input-Proben in den Thermocycler über Nacht bei 65 ° C bisUmkehr der Querverbindungen.
- Am folgenden Tag, fügen Sie 1 Volumen TE-Puffer zu den Proben. Dann fügen RNase A bis zu einer Endkonzentration von 0,2 ug / ul. Inkubieren Sie die Proben in den Thermocycler für 1 bis 2 Stunden bei 37 ° C.
- Nach der Inkubation, fügen Proteinase K in einer Endkonzentration von 0,2 ug / ul. Dann inkubieren Proben im Thermocycler bei 55 ° C für 2 Stunden.
- Anschließend entpacken Sie die Proben einmal mit einem Volumen Phenol. Entpacken Sie die Proben ein zweites Mal mit einem Volumen Phenol: Chloroform: Isoamylalkohol. Schließlich, extrahieren Sie die Proben noch einmal mit einem Volumen Chloroform: Isoamylalkohol.
- Dann fügen Sie 30 g Glykogen zu jeder Probe. Fügen Sie außerdem NaCl auf eine Endkonzentration von 0,2 Molar und zwei Volumina Ethanol zu den Proben. Inkubieren Sie für 30 Minuten bei -80 ° C. Nach der Inkubation, Spin der Proben und Dekantieren des Überstandes. Waschen Sie die Pellets mit 500 ul 75% Ethanol. Dann trocknen die Pellets und resuspendieren Sie in 40 ul Wasser.
- So überprüfen Sie die Größen der DNA-Fragmente durch die Beschallung Verfahren hergestellt, Last 5 ug des gereinigten Eingang Probe in einem 1,8% Agarosegel und führen Sie das Gel. Die Beschallung Verfahren sollte Fragmente im Bereich von 150-350 Basenpaaren zu produzieren. Allerdings, wenn die Fragmente nicht in diesem Bereich fallen, sollte die Beschallung Verfahren durch Variation der Anzahl von Bursts und die Amplitude eingestellt werden.
- Um Robustheit und Spezifität der ChIP überprüfen, die Anreicherung unter Kontrolle bindenden Regionen, indem Gen-spezifischen PCR mit 1 ul der IP-Proben und eine Verdünnungsreihe des Eingangs Probe. Zwei bis drei "gebunden" Regionen und ein ungebundenes Steuerelement Region müssen gewählt, um die Qualität von IP-und Input-Proben zu testen.
5. Amplifikation von genomischer DNA
- Beginnend mit 34 ul der IP Probe oder 200 ng des Eingangs Probe durchführen Ende zu reparieren, 'A' tail hinaus und Ligation von Adaptern, um DNA-Fragmente unter Verwendung von genomischer DNA Sample Prep Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc., San Diego, CA).
- Purify die DNA mit einem MinElute PCR Purification Kit und dann eluieren es in Puffer EB (10 mM Tris Cl, pH 8,5), die wurde auf 50 ° C vorgewärmten Zum Beispiel, Beanspruchungsklasse 23 ul und 46 ul für die endgültige Elution von IP-und Input-DNA Proben.
- Nehmen Sie die PCR-Reaktion unter Verwendung von 23 ul der DNA mit Adaptern und 25 ul Phusion DNA-Polymerase aus dem Kit, 1 ul 20 uM Sol_PCR_1 und 1 ul 20 uM Sol_PCR_2. Führen Sie die PCR-Reaktion wie folgt: 1) 30 Sekunden bei 98 ° C; 2) 10 Sekunden bei 98 ° C; 3) 30 Sekunden bei 65 ° C; 4) 30 Sekunden bei 72 ° C; Wiederholung der Schritte Schritt 2-4 18 mal und dann 5 Minuten bei 72 ° C, schließlich halten bei 4 ° C.
- Nach PCR-Amplifikation, reinigen die DNA mit dem QIAGEN MinElute PCR Purification Kit. Pre-warme 15 ul Puffer EB auf 50 ° C und eluieren DNA. Verdünnen 0,5 ul der Probe 1:4 und führen Sie eine Nanodrop Lesen.
6. Gel Reinigung der amplifizierten Produkte
- Zur Reinigung der amplifizierten Produkte, bereiten ein 1,8% Agarosegel von 50 mL mittels HPLC-grade Wasser. Add TAE und Ethidiumbromid nach dem Agarose geschmolzen ist. Dann gießen Sie das Gel. Legen Sie das Gel nach Zugabe von 4 ul Ladepuffer auf die Eingangs-und IP-Proben. Führen Sie dann das Gel bei 120 Volt für 45 Minuten.
- Analysieren Sie das Gel nach der Ausführung. Das Gel sollte, dass Fragmente im Bereich zwischen 150 und 350 Basenpaaren hergestellt offenbaren. Sie stellen genomische DNA-Fragmente zwischen 50 und 250 Basenpaare lang und einen Adapter.
- Excise der Region Gel mit dem Material in dem 150 350-Basenpaar-Bereich mit einem Skalpell. Achten Sie darauf, um zu vermeiden Auslösen der Adapter-Adapter Band läuft, die bei etwa 120 Basenpaare. Stellen Sie die DNA mit Hilfe eines QIAquick Gel Extraction Kit Anweisungen des Herstellers. Insbesondere verwenden Sie eine Spalte aus dem QIAquick Gel Extraction Kit für ein Gel Stück 400 mg oder weniger. Zu Beginn der Extraktion, fügen Sie 3 Bände von QG Puffer 1 Volumen Gel. Add 1 Volumen Isopropanol und laden Sie die Mischung auf die Säule. Verwenden Sie 0,5 ml QG auf die Säule zu waschen, gefolgt von Standard-Verfahren in Kit beschrieben. Verwenden Sie H 2 O vorgewärmt auf 50 ° C, um die DNA zu eluieren. Inkubieren Sie die Spalte mit 30 ul H 2 O für 5 Minuten bei 37 ° C vor dem Spinnen es nach unten.
- Trocknen Sie die Probe auf genau 11 ul in einem Speedvac ohne Wärme. Nehmen Sie 1 ul der Probe und messen Sie die DNA-Konzentration mit einem Nanodrop Spektralphotometer.
- Schließlich identifizieren bereichert Genprodukte mit dem Illumina Genome AnalyzerIIe, wie dies unter http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Repräsentative Ergebnisse
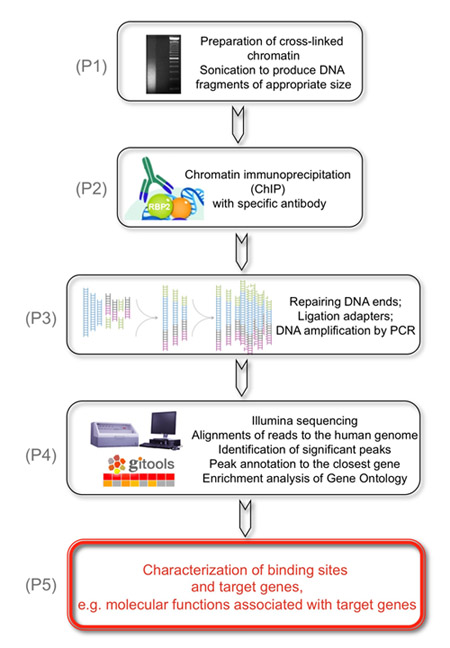
Abbildung 1. Das übergeordnete Ziel der folgenden Experiments ist es, genomische Ziele KDM5A/JARID1A/RBP2 Histon-Demethylase zu identifizieren.
(P1) Dies ist bei der Vorbereitung der vernetzten Chromatin, beschallt, um DNA-Fragmente geeigneter Größe zu produzieren erreicht ist. (P2) In einem zweiten Schritt werden RBP2 gebundenen DNA-Fragmente mit RBP2 Antikörper immunpräzipitiert. (P3) Als nächstes werden die wiederhergestellten DNA-Fragmente an den Enden repariert und Adapter sind an den Enden der genomischen DNA ligiert, um Bibliotheken von genomischer DNA für die Analyse vorzubereiten auf die Strömung Zellen in der Illumina Cluster Station. Die DNA-Bibliotheken sind durch PCR mit geringen Anzahl von Zyklen amplifiziert. (P4) Schließlich liest Illumina sequenziert kurz sind eindeutig auf das menschliche Genom ausgerichtet ist, sind signifikante Peaks identifiziert und mit Anmerkungen versehen, um die nächste Gene, um RBP2 bereichert Regionen zu identifizieren. (P5) Ergebnisse erzielt, die zeigen, molekularen Funktionen mit RBP2 Zielgene auf genomweite Identifizierung RBP2 bereichert Regionen basieren verbunden.
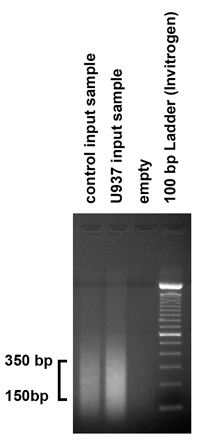
Abbildung 2. Überprüfung der Ergebnisse von Chromatin Beschallung Um die Größe der DNA-Fragmente durch die Beschallung Verfahren hergestellt zu überprüfen, wurde 5 ug (10.1) des gereinigten Eingang Probe auf 1,8% Agarosegel aufgetragen. Wie erwartet, produziert unser Beschallung Verfahren Fragmente im Bereich von 150-350 bp. Allerdings, wenn die Fragmente nicht in diesem Bereich fallen, sollte die Beschallung Verfahren entsprechend angepasst werden, indem die Anzahl der Bursts und die Amplitude.
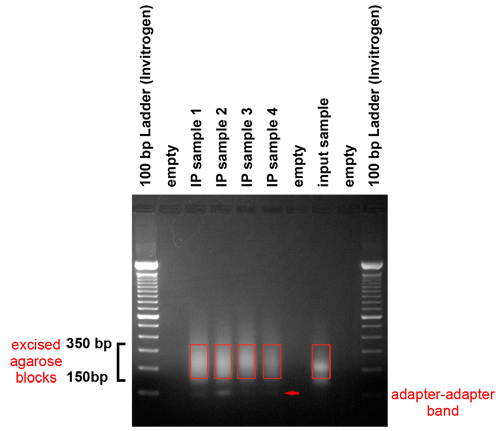
Abbildung 3. Gel Reinigung der amplifizierten Produkte. Die PCR-Produkte werden auf einem Gel laufen, um den Adapter zu entfernen und wählen Sie eine Größe-Reihe von Vorlagen für die Cluster-Generation-Plattform. Dieses Gel zeigt, dass Fragmente im Bereich zwischen 150 und 350 Basenpaaren hergestellt wurden. Sie stellen genomische DNA-Fragmente zwischen 50 und 250 Basenpaare lang und einen Adapter. Wir Verbrauchsteuern der ausgewählten Region des Gels mit einem Skalpell. Es sollte darauf geachtet, um den Adapter-Adapter Band, die bei etwa 120 Basenpaare führt zu vermeiden.
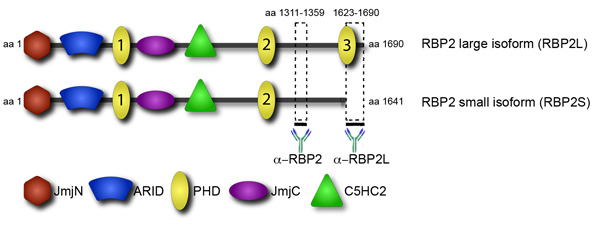
Abbildung 4. Isoform-spezifischen Antikörper ermöglicht die Unterscheidung zwischen großen und kleinen Isoformen RBP2. RBP2 Proteinstruktur in Domain-Ansicht präsentiert. RBP2 enthält mehrere Domänen: die katalytische Histon-Demethylierung JmjC Domain und die damit verbundenen JmjN Domäne, einer trockenen Domain-fähig Sequenz-spezifische DNA-Bindung, eine C5HC2 Zinkfinger, die möglicherweise mit DNA oder anderen Proteinen, und mehrere PHD-Domänen interagieren können. Die beiden anti-RBP2 Antikörper, die zwischen RBP2 Isoformen unterscheiden können gegen die RBP2 Fragmente, die durch dicke Linien angedeutet abgeleitet.
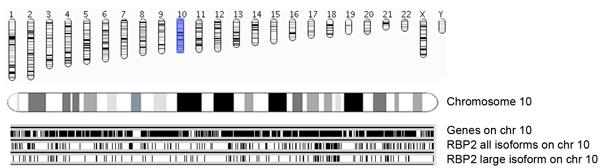
Abbildung 5a. Übersicht der RBP2 bindenden Regionen zusammen mit Chromosom und Ensembl Gene. Genomic Koordinaten identifiziert bereichert RBP2 (alle Isoformen und große Isoform) bindenden Regionen vorgestellt Chromosom weise. Occupances von Ensembl Gene (Version 54; HG18) in den Chromosomen (Chromosom 10 in diesem Bild) sind als schwarze Balken (oben) präsentiert. Jeder RBP2 bindende Region ist als eine vertikale Linie, wo das mittlere Fenster zeigt alle RBP2 Isoformen bindenden Regionen auf Chromosom 10 vertreten, und auf der Unterseite zeigt RBP2 große Isoform bindenden Regionen. Die mittleren und unteren Platten geben Überblick über die Überschneidungen und spezifische Belegung RBP2 Isoformen auf Chromosom 10.
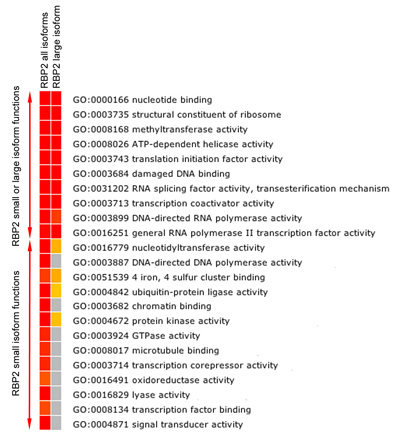
Abbildung 5b. Functional Bereicherung Analyse RBP2 Zielgene. Heatmap zeigt FDR korrigiert signifikant (p-Wert ≤ 0,05) angereichert GO Molecular Function Kategorien unter den Genen gebunden (am nächsten Gene an die RBP2 bindende Region) durch RBP2 (alle Großen und Ganzen Isoformen). Farben nach Rot zeigen eine hohe statistische Signifikanz zeigt gelb geringe statistische Signifikanz und Grau gibt keine statistische Signifikanz. Enrichment-Analyse zeigt die Überlappung und Isoform spezifischen molekularen Funktionen der RBP2 Zielgene.
Funktionelle Unterschiede zwischen RBP2 Isoformen sind nicht bestimmt worden. Wir haben ein umfassendes Konzept zur genomischen Regionen von RBP2 Isoformen gebunden Ermittlung und Festlegung der funktionalen Kategorien, die diese Regionen darstellen. Dies wurde durch ChIP-Seq Analyse durch bioinformatische Analyse der erhaltenen Sequenz liest, erreicht.
RBP2 modifiziert methylierte Lysinreste auf Histone. Wir fanden, dass RBP2 große Isoform die Anerkennung Modul enthält für methylierte Histon-Lysin und RBP2 kleinen Isoform fehlt diesem Modul binden an verschiedene Regionen im menschlichen Genom (Abbildung 5A). Wichtig ist, dass Isoform-spezifischen Regionen und überlappenden Regionen von Genen gehören mit unterschiedlichen molekularen Funktionen (Abbildung 5B). Zum Beispiel, "Chromatin Bindung" und "Transkriptionsfaktorbindungsstellen" Funktionen können auf Gen-Targets von RBP2 kleinen Isoform zugeschrieben werden, aber nicht von RBP2 großen Isoform (Abbildung 5B). Durch den Vergleich der tatsächlichen Gen-Sets generiert für alle Isoformen und RBP2 großen Isoform (Daten nicht gezeigt), können wir auch festlegen, ob die große Isoform ist spezifisch an bestimmte Gene rekrutiert.
Diese Arbeit wurde von 115.347-RSG-08-271 bis 01-GMC von ACS, und durch CA138631 Zuschuss von NIH unterstützt.
Oligonukleotidsequenzen 2006 Illumina, Inc. Alle Rechte vorbehalten.
- Sol_PCR_1
Sequenz 5'-AAT GAT ACG GCG ACC ACC GAG ATC TAC ACT CTT TCC CTA CAC GAC GCT CTT CCG ATC T-3 ' - Sol_PCR_2
Sequenz 5'-CAA GCA GAA GAC GGC ATA CGA GCT CTT CCG ATC T-3 '
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved