Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Análise do genoma usando chip para identificar alvos isoforma específica Gene
Aqui estamos apresentando uma imunoprecipitação da cromatina (CHIP) procedimento para análise do genoma localização das isoformas de proteínas que diferem em um domínio de ligação de histonas. Estamos aplicando-a-CHIP Seq análise para identificar os alvos da demetilase KDM5A/JARID1A/RBP2 histonas.
Recrutamento de fatores de transcrição e epigenéticos para as suas metas é um passo fundamental na sua regulamentação. Em lugar de destaque no recrutamento são os domínios de proteínas que se ligam a determinadas modificações das histonas. Um domínio como é o homeodomínio planta (PHD), encontrado em várias proteínas de ligação da cromatina. O RBP2 fator epigenético tem vários domínios PHD, no entanto, eles têm funções diferentes (Figura 4). Em particular, o C-terminal PHD domínio, encontrado em uma fusão RBP2 oncogênico em leucemia humana, liga-se a lisina trimethylated 4 em H3 histonas (H3K4me3) 1. A transcrição correspondente à isoforma RBP2 contendo o PHD C-terminal se acumula durante a diferenciação de promonocytic, linfoma derivados, U937 células em monócitos 2. Consistente com ambos os conjuntos de dados, análise do genoma mostrou que em células U937 diferenciada, a proteína RBP2 é localizado para regiões genômicas altamente enriquecido para H3K4me3 3. Localização de suas metas para RBP2 correlaciona-se com uma diminuição na H3K4me3 devido à atividade RBP2 demetilase histona e uma diminuição da atividade transcricional. Em contraste, dois outros RBP2 DPSs são incapazes de vincular H3K4me3. Notavelmente, o C-terminal do domínio de PHD RBP2 está ausente no menor RBP2 isoforma 4. É concebível que a isoforma pequeno de RBP2, que carece de interação com H3K4me3, difere da maior isoforma na localização genômica. A diferença na localização genômica de RBP2 isoformas pode explicar a diversidade observada em RBP2 função. Especificamente, RBP2 é um jogador fundamental na diferenciação celular mediada pela proteína retinoblastoma (pRB). Consistente com esses dados, a análise do genoma anterior, sem distinção entre as isoformas, identificou dois grupos distintos de genes RBP2 alvo: 1) genes vinculados por RBP2 de uma forma que é independente de diferenciação; 2) genes vinculados por RBP2 em uma diferenciação forma dependente.
Para identificar diferenças na localização entre as isoformas realizamos genome-wide análise de localização por Chip Seq. Utilizando anticorpos que detectam tanto RBP2 isoformas temos localizado todos os RBP2 alvos. Além disso, temos anticorpos que se ligam apenas grande, e não pequeno RBP2 isoforma (Figura 4). Depois de identificar os alvos isoforma de grande porte, pode-se então subtrair-los de todos os RBP2 alvos para revelar as metas da isoforma de pequeno porte. Esses dados mostram a contribuição de cromatina interagindo domínio no recrutamento de proteínas para seus sítios de ligação no genoma.
O protocolo foi originalmente adaptado do B. Ren, 2001. Ela representa uma ligeira modificação do protocolo por Odom et al. 5 que podem ser encontradas em http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pré-bloco e ligação de anticorpos para esferas magnéticas (Deve ser realizada na noite anterior próximo passo)
- Lave de 100 L de Dynabeads Protein G (por IP, combine para múltiplos IPs) em 1 mL de fresco BSA / PBS solução (50 mg BSA em 10 mL PBS-Esta solução vai durar uma semana).
- Recolher as contas usando um suporte magnético e repita o procedimento de lavagem mais duas vezes.
- Em seguida, adicionar 10 mg de anticorpos para 250 mL da suspensão contas em PBS / BSA solução (por IP) e incubar durante a noite em uma plataforma giratória a 4 ° C.
- Após a conclusão, lavar as contas três vezes em 1 ml da solução de PBS / BSA e ressuspender em 10 ml da solução de PBS / BSA (por IP).
2. Célula cross-linking
- Para iniciar este procedimento, crescer cerca de 10 8 células para cada imunoprecipitação, ou IP. Aqui, difuso de células U937 histiocitária linfoma são usados e induziu a diferenciação monocítica com TPA de 96 horas.
- Após o crescimento celular, adicione solução de formol diretamente para a mídia para uma concentração final de 1%. Então, redemoinho brevemente frascos e permitir-lhes para sentar-se à temperatura ambiente por 10 minutos. Então, aspirar a mídia e lave as células com 15 mL de PBS gelado. Repita este lave uma vez.
- Em seguida, adicionar 6 mL de Tampão de Lise 1 (50 mM HEPES-KOH, pH 7,5, 140 mM NaCl, EDTA 1 mM, glicerol 10%, 0,5% NP-40, 0,25% Triton X-100, contendo inibidores da protease) para cada dos frascos no gelo. Então, rock os frascos durante 20 minutos a 4 ° C.
- Finalmente, a colheita das células usando um raspador celular e transferi-los para 15 mL tubos cônicos. Neste ponto, as células podem ser armazenadas a -80 ° C.
3. Sonication celular
- Se as células foram congeladas, descongele-los. Uma vez descongelado, girar a células para baixo a 3.000 rpm por 10 minutos a 4 ° C e desprezar o sobrenadante. Então, voltar a suspender as células em 6 mL de Tampão de Lise 2 (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1mM EDTA, EGTA 0,5 mM, contendo inibidores da protease). Rock the tubos suavemente em temperatura ambiente por 10 minutos.
- Repetir a centrifugação e ressuspender as células em 2,5 mL de Tampão de Lise 3 (10 mM Tris-HCl, pH 8,0, 100 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, desoxicolato de sódio a 0,1%, 0,5% N-lauroylsarcosine, contendo inibidores da protease) .
- Em seguida, preparar a suspensão por sonicação, colocando-o num copo de água gelada com o MICROTIP de 450 Branson Sonifier definida entre 50 e amplitude de 60%.
- Sonicate a solução para uma explosão 30 segundo constante e frio no gelo por 1 minuto. Repita estes pulsos 10 a 15 vezes. Então, pipetar o conteúdo do tubo de cima a baixo e transferi-los para um novo tubo. Continuar a pulso e esfriar a solução de um adicional de 5 vezes.
- Seguintes sonicação, adicionar 10% Triton X-100 a 1 / 10 do volume de solução. Transferir os lisados para tubos de 1,5 mL de centrífuga, e girar os detritos para fora em uma microcentrífuga. Em seguida, transferir o lisado celular para um novo tubo.
4. Cromatina Imunoprecipitação
- Antes de cromatina imunoprecipitação, ou chip, economizar 50 mL do lisado celular como a amostra de entrada. Então, combinar o lisado celular apuradas com Dynabeads pré-ligado ao anticorpo que tenham sido previamente preparada como descrito acima. Pedra a mistura, além de a amostra de entrada de 50 mL, a 4 ° C durante a noite.
- Lave as contas com 1 mL do tampão de lavagem (50 mM HEPES-KOH, pH 7,6, 0,5 M LiCl, 1mM EDTA, desoxicolato de sódio 0,7%, 1% NP-40). Então, use um suporte magnético para recolher as contas e remover o sobrenadante. Repita esta lavagem de 6 a 8 vezes.
- Realizar uma lavagem final com 1 mL TE-plus-50 mM NaCl (10 mM Tris-HCl, pH 8,0, 50 mM NaCl, 1 mM EDTA). Girar a contas em uma microcentrífuga a 3.000 rpm por 2 minutos a 4 ° C. Após centrifugação, aspirar qualquer tampão TE residual.
- Então, adicionar 100 mL de tampão de eluição (50 mM Tris-HCl, pH 8,0, 10 mM EDTA, 1% SDS) para as amostras. Imediatamente após, incubar as amostras a 65 ° C por 10 a 15 minutos. Zero os tubos contra um suporte para tubos de 1,5 ml a cada 2 minutos para manter as contas na suspensão.
- Recolher as contas usando centrifugação e do suporte magnético, e transferir o sobrenadante para um tubo de PCR. Em seguida, recuperar a amostra de entrada salvo anteriormente e adicionar 3 volumes de tampão de eluição.
- Finalmente, coloque o IP e amostras de entrada para o termociclador durante a noite a 65 ° C parainverter as ligações cruzadas.
- No dia seguinte, adicione um volume de tampão TE para as amostras. Em seguida, adicione RNase A para uma concentração final de 0,2 mg / mL. Incubar as amostras no termociclador por 1 a 2 horas a 37 ° C.
- Após a incubação, adicionar proteinase K para uma concentração final de 0,2 mg / mL. Então, incubar amostras no termociclador a 55 ° C por 2 horas.
- Em seguida, extrair as amostras uma vez com um volume de fenol. Extrair as amostras uma segunda vez com um volume de fenol: clorofórmio: álcool isoamílico. Finalmente, extrair as amostras mais uma vez com um volume de clorofórmio: álcool isoamílico.
- Então, adicionar 30 mg de glicogênio para cada amostra. Além disso, adicionar NaCl para uma concentração final de 0,2 Molar e dois volumes de etanol para as amostras. Incubar por 30 minutos a -80 ° C. Após a incubação, as amostras de spin e decantar o sobrenadante. Lavar as pelotas com 500 mL de etanol 75%. Em seguida, secar o pellets e re-suspendê-las em 40 mL de água.
- Para verificar os tamanhos dos fragmentos de DNA produzidos pelo processo de ultra-som, carga de 5 mg da amostra de entrada purificada em um gel de agarose 1,8% e correr o gel. O procedimento de sonicação deve produzir fragmentos na faixa de 150-350 pares de bases. No entanto, se os fragmentos não se enquadram nesta faixa, o procedimento de sonicação deve ser ajustada pela variação do número de rajadas ea amplitude.
- Para verificar a robustez e especificidade do chip, o enriquecimento em regiões de controle de ligação através da realização de gene específico PCR com 1 ml de amostras de IP e uma série de diluição da amostra de entrada. Duas a três "ligado" regiões e uma região controlo independente precisam ser selecionados, a fim de testar a qualidade das amostras e IP de entrada.
5. Amplificação do DNA genômico
- Começando com 34 mL da amostra IP ou 200 ng da amostra de entrada, realizar o reparo final, 'A' além da cauda e ligadura de adaptadores para fragmentos de DNA genômico utilizando DNA da amostra Prep Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc., San Diego, CA).
- Purificar o DNA através de um Kit de Purificação MinElute PCR e eluir em tampão EB (10 mM Tris Cl, pH 8,5) que tem sido pré-aquecido a 50 ° C. Por exemplo, usar 23 mL e 46 mL para a eluição final do IP e amostras de DNA de entrada, respectivamente.
- Fazer a reação de PCR utilizando 23 mL de DNA com adaptadores, e 25 mL DNA polimerase Phusion do kit, 1 mL de 20 mM Sol_PCR_1, e 1 mL de 20 mM Sol_PCR_2. Executar a reação de PCR da seguinte forma: 1) 30 segundos a 98 ° C, 2) 10 segundos a 98 ° C, 3) 30 segundos a 65 ° C; 4) 30 segundos a 72 ° C; passos repetindo o passo 2-4 18 vezes e depois 5 minutos a 72 ° C, finalmente, segurando a 4 ° C.
- Após amplificação por PCR, purificar o DNA com o Kit de Purificação QIAGEN MinElute PCR. Pré-aquecer mL EB 15 de buffer para 50 ° C e eluir o DNA. Diluir 0,5 mL da amostra 1:04 e realizar uma leitura Nanodrop.
6. Gel de purificação dos produtos amplificados
- Para purificar os produtos amplificados, preparar um gel de agarose 1,8% de 50 mL utilizando HPLC-grade água. Adicionar TAE e brometo de etídio após a agarose derreter. Em seguida, despeje o gel. Carregar o gel após a adição de 4 mL de tampão de carregamento para a entrada e amostras de IP. Em seguida, execute o gel em 120 volts por 45 minutos.
- Analisar o gel depois que ele foi executado. O gel deve revelam que fragmentos na faixa entre 150 e 350 pares de bases são produzidos. Eles representam fragmentos de DNA genômico entre 50 e 250 pares de bases de comprimento e um adaptador.
- Região, o consumo de gel contendo o material na faixa de 150 par 350 de base com um bisturi. Tome cuidado para evitar extirpar a banda adaptador adaptador, que roda a cerca de 120 pares de bases. Recuperar o DNA usando um QIAquick Kit Gel Extraction por instruções do fabricante. Especificamente, use uma coluna do Kit Gel Extraction QIAquick para uma fatia de gel de 400 mg ou menos. Para começar o processo de extração, adicionar 3 volumes de tampão QG para 1 volume de gel. Adicionar um volume de isopropanol e carregar a mistura na coluna. Use 0,5 ml de QG para lavar a coluna, seguido pelo procedimento padrão descrito no kit manual. Use H 2 O pré-aquecido a 50 ° C para eluir o DNA. Incubar a coluna com 30 mL de H 2 O, durante 5 minutos a 37 ° C antes de girar para baixo.
- Secar a amostra até precisamente 11 mL em um Speedvac sem calor. Retire 1 mL da amostra e medir a concentração de DNA usando um espectrofotômetro Nanodrop.
- Finalmente, identificar produtos enriquecidos com o gene AnalyzerIIe Genoma Illumina conforme descrito no http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Resultados representante
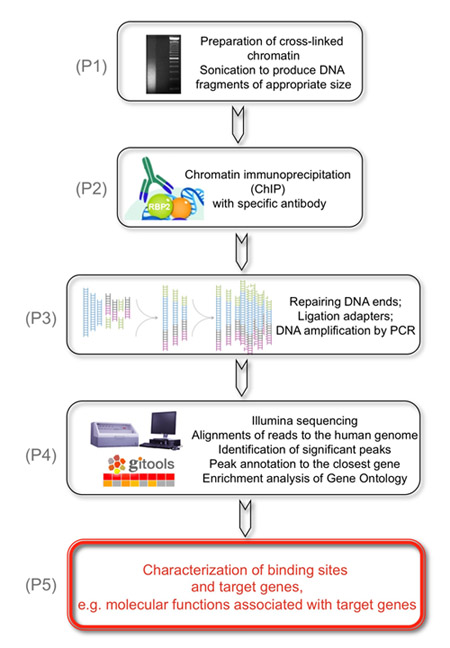
Figura 1. O objetivo geral do experimento seguinte é identificar alvos genoma de KDM5A/JARID1A/RBP2 demetilase histonas.
(P1) Isto é conseguido pela preparação de cross-linked cromatina que é sonicado para produzir fragmentos de DNA de tamanho apropriado. (P2) Como segundo passo, RBP2 fragmentos de DNA ligados são immunoprecipitated com RBP2 anticorpos. (P3) Em seguida, os fragmentos de DNA recuperado são reparados nas extremidades e adaptadores são ligados nas extremidades do DNA genômico para preparar bibliotecas de DNA genômico para análise sobre as células de fluxo na Estação Cluster Illumina. As bibliotecas de DNA são amplificados por PCR usando baixo número de ciclos. (P4) Por fim, Illumina seqüenciados curto lê são exclusivamente alinhados ao genoma humano, picos significativos são identificados e anotados para o próximo genes a fim de identificar RBP2 regiões enriquecido. (P5) Os resultados são obtidos que mostram funções moleculares associados com RBP2 genes alvo com base no genoma de identificação de regiões RBP2 enriquecido.
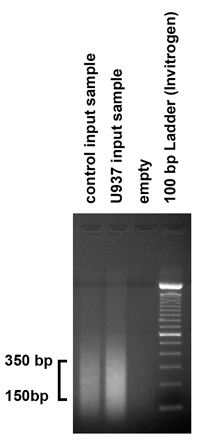
Figura 2. Verificar os resultados de sonicação cromatina Para verificar os tamanhos dos fragmentos de DNA produzidos pelo processo de sonicação, 5 mg (1 / 10) da amostra de entrada purificada foi carregado em 1,8% agarose gel. Como esperado, o nosso procedimento de sonicação produzido fragmentos na faixa de 150-350 bp. No entanto, se os fragmentos não se enquadram nesta faixa, o procedimento de sonicação deve ser ajustada em conformidade, variando o número de rajadas ea amplitude.
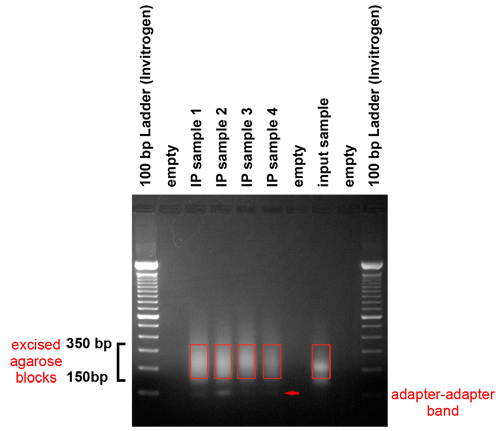
Figura 3. Gel de purificação dos produtos amplificados. Os produtos de PCR são executados em um gel para remover os adaptadores e selecione um tamanho gama de modelos para a plataforma de geração de cluster. Este gel mostra que fragmentos na faixa entre 150 e 350 pares de base foram produzidos. Eles representam fragmentos de DNA genômico entre 50 e 250 pares de bases de comprimento e um adaptador. Nós a região selecionada consumo de gel com um bisturi. Cuidados devem ser tomados para evitar a banda adaptador adaptador, que roda a cerca de 120 pares de bases.
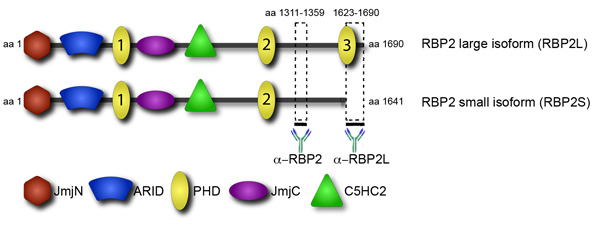
Figura 4. Isoforma específica de anticorpos permite distinguir entre grandes e pequenos isoformas de RBP2. RBP2 estrutura da proteína é apresentado na vista de domínio. RBP2 contém vários domínios: o catalisador da histona desmetilação JmjC domínio e associados JmjN domínio, um domínio ÁRIDO capaz de sequências específicas de DNA de ligação, um dedo de zinco C5HC2 que potencialmente podem interagir com DNA ou outras proteínas, e vários domínios PHD. Os dois anticorpos anti-RBP2 que permitem distinguir entre RBP2 isoformas foram obtidos contra o RBP2 fragmentos indicadas por linhas grossas.
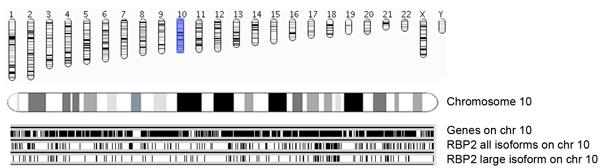
Figura 5a. Visão geral do RBP2 regiões de ligação junto com cromossomos e genes Ensembl. Coordenadas de Genomic identificados enriquecido RBP2 (todas as isoformas e isoforma grande) regiões de ligação são apresentados cromossomo sábio. Occupances de genes Ensembl (versão 54; hg18) nos cromossomos (cromossomo 10 na foto) são apresentados como barras pretas (painel superior). Cada região RBP2 ligação é representada como uma linha vertical, onde o painel do meio mostra todas as isoformas RBP2 regiões de ligação no cromossomo 10, eo painel inferior mostra RBP2 regiões isoforma grande ligação. Meio e painéis de fundo dar visão geral de sobreposição e de ocupação específico de RBP2 isoformas no cromossomo 10.
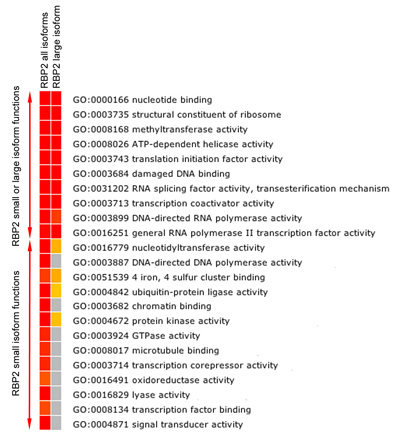
Figura 5b. Análise funcional de enriquecimento RBP2 genes-alvo. Mapa de calor mostrando FDR corrigido significativamente (p ≤ 0,05) enriquecido GO categorias Função Molecular entre os genes ligados (o mais próximo genes para a região RBP2 ligação) por RBP2 (isoformas todos e grande). As cores para vermelho indicam alta significância estatística, amarelo indica significância estatística baixa, e cinza indica que não há significância estatística. Análise de enriquecimento mostra a sobreposição de funções específicas e isoforma molecular dos genes RBP2 alvo.
Diferenças funcionais entre RBP2 isoformas não foram determinadas. Temos usado uma abordagem abrangente para identificar regiões genômicas vinculado por RBP2 isoformas e definir as categorias funcionais que estas regiões representam. Isto foi conseguido por Chip-Seq análise bioinformática seguido por análise de seqüência obtida lê.
RBP2 modifica metilado resíduos de lisina nas caudas das histonas. Descobrimos que RBP2 isoforma grandes contendo o módulo de reconhecimento de metilado isoforma lisina e RBP2 histona pequena sem este módulo para ligar as diferentes regiões do genoma humano (Figura 5A). Importante, isoforma específica regiões e regiões sobrepostas pertencem a genes com funções diferentes molecular (Figura 5B). Por exemplo, "cromatina obrigatório" e "fator de transcrição de ligação" funções podem ser atribuídas a metas de gene da isoforma RBP2 pequeno, mas não de grande RBP2 isoforma (Figura 5B). Comparando gene real conjuntos gerados para todas as isoformas e RBP2 isoforma grande (dados não mostrados), também podemos definir se a isoforma grande é especificamente recrutados para determinados genes.
Este trabalho foi financiado pelo 115.347-RSG-08-271-01-GMC da ACS, e por CA138631 concessão do NIH.
Seqüências de oligonucleotídeos 2006 Illumina, Inc. Todos os direitos reservados.
- Sol_PCR_1
Seqüência 5'-AAT GAT ACG GCG ACC ACC GAG ATC TAC ACT CTT TCC CTA CAC GAC GCT CTT ATC CCG T-3 ' - Sol_PCR_2
Seqüência 5'-CAA GGC GAC GAA GCA ATA CGA GCT CTT ATC CCG T-3 '
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved