Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Análisis de todo el genoma con chip para identificar objetivos específicos para cada isoforma Gene
Aquí estamos presentando una inmunoprecipitación de cromatina (CHIP) Procedimiento para el análisis de localización en todo el genoma de las isoformas de la proteína que se diferencian en un dominio de unión a las histonas. Estamos aplicando a CHIP-Seq análisis para identificar los objetivos de la histona desmetilasa KDM5A/JARID1A/RBP2.
El reclutamiento de factores de transcripción y epigenéticas de sus objetivos es un paso clave en su regulación. Un lugar destacado en la contratación son los dominios de la proteína que se unen a determinadas modificaciones de las histonas. Un dominio, es la planta de homeodominio (PHD), que se encuentra en varias proteínas de unión a la cromatina. El factor de RBP2 epigenética tiene múltiples dominios PHD, sin embargo, tienen funciones diferentes (Figura 4). En particular, el C-terminal de dominio PHD, que se encuentra en una fusión RBP2 oncogénico en la leucemia humana, se une a trimetiladas lisina 4 de la histona H3 (H3K4me3) 1. La transcripción que corresponde a la isoforma RBP2 que contiene el PHD C-terminal se acumula durante la diferenciación de promonocítica, el linfoma de origen, las células U937 en monocitos 2. De acuerdo con ambos conjuntos de datos de todo el genoma análisis mostró que en las células U937 diferenciadas, la proteína RBP2 se localiza en regiones genómicas altamente enriquecido para H3K4me3 3. Localización de RBP2 de sus objetivos se correlaciona con una disminución en H3K4me3, debido a la actividad RBP2 desmetilasa histonas y una disminución en la actividad transcripcional. Por el contrario, otros dos doctorados de RBP2 son incapaces de unirse H3K4me3. Cabe destacar que el dominio C-terminal de la PHD RBP2 está ausente en los más pequeños RBP2 isoforma 4. Es concebible que la isoforma pequeña RBP2, que carece de la interacción con H3K4me3, difiere de la isoforma más grande en la localización genómica. La diferencia en la localización genómica de RBP2 isoformas puede dar cuenta de la diversidad observada en RBP2 función. En concreto, RBP2 es un jugador fundamental en la diferenciación celular mediada por la proteína retinoblastoma (pRB). De acuerdo con estos datos, el análisis anterior, todo el genoma, sin distinción entre las isoformas, se identificaron dos grupos distintos de RBP2 genes diana: 1) los genes vinculados por RBP2 de una manera que es independiente de la diferenciación, 2) los genes vinculados por RBP2 en una diferenciación manera dependiente.
Para identificar las diferencias en la localización entre las isoformas se realizó en todo el genoma análisis de la ubicación por chip-Seq. El uso de anticuerpos que detectan tanto RBP2 isoformas se han localizado todos los RBP2 objetivos. Además tenemos los anticuerpos que se unen sólo grandes y pequeños no RBP2 isoforma (Figura 4). Después de identificar los objetivos de la isoforma grandes, uno se puede quitar de todos los RBP2 objetivos para revelar los objetivos de la isoforma pequeña. Estos datos muestran la contribución de la cromatina, la interacción de dominio en el reclutamiento de proteínas para sus sitios de unión en el genoma.
El protocolo fue adaptado originalmente de B. Ren, 2001. Que representa una ligera modificación del protocolo de Odom et al. 5, que se puede encontrar en http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pre-bloque y la unión del anticuerpo a perlas magnéticas (En caso de llevarse a cabo la noche antes de que el siguiente paso)
- Lavado de 100 L de Dynabeads proteína G (por IP, se combinan para múltiples IPs) en 1 ml de agua dulce BSA / PBS solución (50 mg de BSA en 10 ml de PBS-Esta solución tendrá una duración de una semana).
- Recoge las cuentas con un soporte magnético y repetir el procedimiento de lavado dos veces más.
- A continuación, agregar 10 mg de anticuerpos frente a 250 l de la suspensión de cuentas en PBS / BSA solución (por IP) e incubar durante la noche sobre una plataforma giratoria a 4 ° C.
- Al terminar, lavar las cuentas tres veces en 1 ml de la solución de PBS / BSA y luego volver a suspender en 10 l de la solución de PBS / BSA (por IP).
2. Células de entrecruzamiento
- Para iniciar este procedimiento, creciendo aproximadamente 10 8 células por inmunoprecipitación, o IP. Aquí, difusa histiocitos U937 linfoma se utilizan y se indujo la diferenciación de monocitos con TPA durante 96 horas.
- Siguiendo el crecimiento celular, agregar una solución de formaldehído directamente a los medios de comunicación a una concentración final de 1%. Luego, haga girar la breve frascos y les permitan permanecer a temperatura ambiente durante 10 minutos. A continuación, aspirar los medios de comunicación y aclarar las células con 15 ml de helado de PBS. Repetir este lavado una vez.
- A continuación, añadir 6 mL de tampón de lisis 1 (50 mM HEPES-KOH, pH 7,5, 140 mM NaCl, 1 mM EDTA, 10% de glicerol, 0,5% NP-40, 0,25% de Triton X-100, que contiene inhibidores de la proteasa) para cada uno de los frascos en el hielo. Entonces, el rock los frascos durante 20 minutos a 4 ° C.
- Por último, la cosecha de las células utilizando un rascador de células y transferirlos a tubos cónicos de 15 ml. En este punto, las células pueden ser almacenadas a -80 ° C.
3. Sonicación celular
- Si las células fueron congeladas, a descongelarse. Una vez descongelado, girar las células hacia abajo a 3.000 rpm durante 10 minutos a 4 ° C y descartar el sobrenadante. A continuación, volver a suspender las células en 6 ml de tampón de lisis 2 (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, que contienen inhibidores de la proteasa). Roca de los tubos suavemente a temperatura ambiente durante 10 minutos.
- Repetir la centrifugación y se resuspenden las células en 2,5 ml de tampón de lisis 3 (10 mM Tris-HCl, pH 8,0, 100 mM NaCl, 1 mM EDTA, 0,5 mM EGTA, 0,1% de desoxicolato de sodio, 0,5% de N-lauroylsarcosine, que contienen inhibidores de la proteasa) .
- A continuación, preparar la suspensión de ultrasonidos, colocándolo en un vaso de agua helada con la micropunta de un Sonifier Branson 450 establece que entre el 50 y el 60% de la amplitud.
- Sonicar la solución para un estallido constante de 30 segundos y enfriar en hielo durante 1 minuto. Repita estos pulsos de 10 a 15 veces. Luego, pipeta el contenido del tubo de arriba a abajo y transferirlos a un nuevo tubo. Siguen el pulso y enfriar la solución de un adicional de 5 veces.
- Después de sonicación, añadir 10% de Triton X-100 a 1 / 10 del volumen de la solución. La transferencia de los lisados a tubos de 1,5 ml de centrífuga, y el giro de los escombros en una microcentrífuga. Luego transferir el lisado celular a un tubo nuevo.
4. Inmunoprecipitación de cromatina
- Antes de la inmunoprecipitación de la cromatina, o chip, ahorrar un 50 l del lisado celular como la muestra de entrada. Luego, combine el lisado celular aclarado con Dynabeads pre-unida al anticuerpo que han sido previamente preparado como se describió anteriormente. Roca de la mezcla, además de la muestra de entrada de 50 l, a 4 ° C durante la noche.
- Lavar las perlas con 1 mL del tampón de lavado (50 mM HEPES-KOH, pH 7,6, 0,5 M LiCl, 1 mM EDTA, 0,7% desoxicolato de sodio, 1% NP-40). Luego, utilice un soporte magnético para recoger las cuentas y eliminar el sobrenadante. Repita este lavado de 6 a 8 veces.
- Realizar un lavado final con 1 ml de TE-plus-50 mM de NaCl (10 mM Tris-HCl, pH 8,0, 50 mM NaCl, 1 mM EDTA). Girar las bolas en una microcentrífuga a 3.000 rpm durante 2 minutos a 4 ° C. Después del centrifugado, aspirar cualquier residuo de buffer TE.
- A continuación, añadir 100 ml de tampón de elución (50 mM Tris-HCl, pH 8,0, 10 mM EDTA, 1% SDS) a las muestras. Inmediatamente después, incubar las muestras a 65 ° C durante 10 a 15 minutos. Cero de los tubos contra un soporte de tubos de 1,5 ml cada 2 minutos para mantener las cuentas en la suspensión.
- Recoge las cuentas usando la centrifugación y el soporte magnético, y la transferencia del sobrenadante a un tubo de PCR. A continuación, recuperar la muestra de entrada guardada anteriormente y agregar 3 volúmenes de tampón de elución.
- Por último, coloque las muestras de IP y de entrada en el termociclador durante la noche a 65 ° C arevertir las relaciones cruzadas.
- Al día siguiente, agregue un volumen de buffer TE a las muestras. A continuación, añadir RNasa A a una concentración final de 0,2 mg / mL. Incubar las muestras en el termociclador durante 1 a 2 horas a 37 ° C.
- Después de la incubación, añadir proteinasa K a una concentración final de 0,2 mg / mL. A continuación, se incuban las muestras en el termociclador a 55 ° C durante 2 horas.
- A continuación, el extracto de las muestras una vez con un volumen de fenol. Extraer las muestras por segunda vez con un volumen de fenol: cloroformo: alcohol isoamílico. Finalmente, el extracto de las muestras una vez más, con un volumen de cloroformo: alcohol isoamílico.
- A continuación, añadir 30 g de glucógeno a cada muestra. Además, añade NaCl a una concentración final de 0,2 volúmenes molares y dos de etanol a las muestras. Incubar por 30 minutos a -80 ° C. Después de la incubación, girar las muestras y recoger el sobrenadante. Lavar los pellets con 500 l de etanol al 75%. A continuación, los pellets seco y volver a suspender en 40 ml de agua.
- Para comprobar el tamaño de los fragmentos de ADN producidos por el procedimiento de ultrasonidos, la carga de 5 mg de la muestra de entrada purificado en un 1,8% en gel de agarosa y ejecutar el gel. El procedimiento de ultrasonidos que producen fragmentos en el rango de 150-350 pares de bases. Sin embargo, si los fragmentos no están en este rango, el procedimiento de ultrasonidos debe ser ajustada por la variación del número de explosiones y la amplitud.
- Para comprobar la solidez y la especificidad del chip, el enriquecimiento de las regiones controlan el enlace mediante la realización de los genes específicos de PCR con 1 l de las muestras de IP y una serie de diluciones de la muestra de entrada. Dos o tres "consolidados" las regiones y una región de control independiente deben ser seleccionados con el fin de probar la calidad de las muestras de IP y de entrada.
5. Amplificación de ADN genómico
- A partir de 34 l de la muestra IP o 200 ng de la muestra de entrada, realizar la reparación final, 'A' además de la cola y la ligadura de los adaptadores a los fragmentos de ADN utilizando ADN genómico preparación de muestras Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc., San Diego, CA).
- Purificar el ADN utilizando un kit de PCR Purificación MinElute y luego eluir en tampón EB (10 mM Tris Cl, pH 8,5) que ha sido previamente calentada a 50 ° C. Por ejemplo, utilice 23 ly 46 l para la elución final de la IP y las muestras de ADN de entrada, respectivamente.
- Que la reacción de PCR utilizando 23 L de ADN con los adaptadores, y 25 de la polimerasa de ADN l Phusion del kit, 1 l de 20 mM Sol_PCR_1, y 1 l de 20 mM Sol_PCR_2. Ejecutar la reacción de PCR de la siguiente manera: 1) 30 segundos a 98 ° C, 2) 10 segundos a 98 ° C, 3) 30 segundos a 65 ° C, 4) 30 segundos a 72 ° C, repitiendo los pasos pasos 2-4 18 veces y luego 5 minutos a 72 ° C, finalmente, mantenimiento a 4 ° C.
- Después de la amplificación por PCR, purificar el ADN con el kit de QIAGEN MinElute Purificación de PCR. Pre-caliente 15 l de tampón EB a 50 ° C y eluir el ADN. Diluir 0,5 l de la muestra 1:4 y realizar una lectura Nanodrop.
6. Gel de purificación de los productos amplificados
- Para purificar los productos amplificados, preparar un gel de agarosa al 1,8% de 50 ml con agua grado HPLC. Añadir TAE y bromuro de etidio después de la agarosa se haya derretido. Luego, vierta el gel. Cargar el gel después de añadir 4 l de tampón de carga a la entrada y las muestras de IP. A continuación, ejecute el gel a 120 voltios durante 45 minutos.
- Analizar el gel después de que se ha ejecutado. El gel debe revelar que los fragmentos en el rango entre 150 y 350 pares de bases se producen. Que representan fragmentos de ADN genómico de entre 50 y 250 pares de bases de longitud y un adaptador.
- Impuestos Especiales de la región del gel que contiene el material en el rango de 150 350 pares de bases con un bisturí. Tenga cuidado para evitar la escisión de la banda adaptador adaptador, que se cifra en unas 120 pares de bases. Recuperar el ADN utilizando un kit de extracción de gel QIAquick las instrucciones del fabricante. En concreto, el uso de una columna del kit de extracción QIAquick Gel para una rebanada de gel de 400 mg o menos. Para comenzar el proceso de extracción, agregar 3 volúmenes de buffer QG a un volumen de gel. Añadir 1 volumen de isopropanol y la carga de la mezcla en la columna. Use 0,5 ml de QG para lavar la columna, seguido por el procedimiento estándar descrito en el juego de manual. Use H 2 O pre-calentado a 50 ° C para eluir el ADN. Incubar la columna con 30 l de H 2 O durante 5 minutos a 37 ° C antes de girar hacia abajo.
- Secar la muestra hasta 11 l, precisamente en un Speedvac sin calor. Quitar una L de la muestra y medir la concentración de ADN utilizando un espectrofotómetro Nanodrop.
- Por último, identificar los productos enriquecidos con el gen del genoma Illumina AnalyzerIIe como se describe en http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Resultados representante
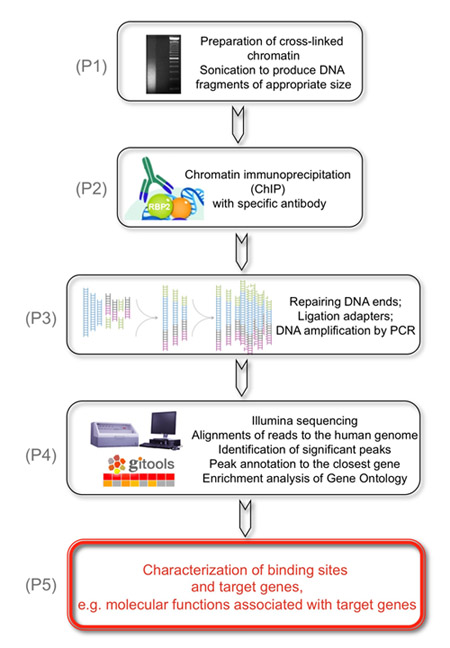
Figura 1. El objetivo general de la siguiente experimento consiste en identificar los objetivos de la genómica KDM5A/JARID1A/RBP2 desmetilasa histonas.
(P1) Esto se logra mediante la preparación de enlaces cruzados de la cromatina que se somete a sonicación para producir fragmentos de ADN de tamaño apropiado. (P2) En un segundo paso, RBP2 fragmentos de ADN están obligados immunoprecipitated con RBP2 anticuerpos. (P3) A continuación, los fragmentos de ADN recuperado se reparan en los extremos y los adaptadores se ligan a los extremos de ADN genómico para preparar las bibliotecas de ADN genómico para el análisis de las células de flujo en la estación de racimo Illumina. Las bibliotecas de ADN amplificado por PCR utilizando bajo número de ciclos. (P4) Por último, Illumina secuencia corta lee son los únicos alineados con el genoma humano, los picos que se detecten y anotadas, en el más genes a fin de identificar RBP2 regiones enriquecidas. (P5) Los resultados se obtienen que muestran las funciones moleculares asociados con RBP2 genes diana sobre la base de todo el genoma de identificación de RBP2 regiones enriquecidas.
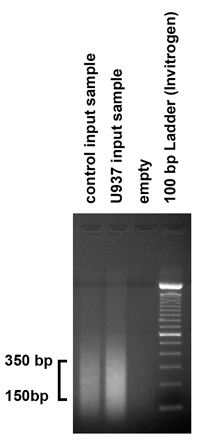
Figura 2. Comprobar los resultados de la cromatina sonicación Para comprobar el tamaño de los fragmentos de ADN producidos por el procedimiento de ultrasonidos, 5 g (1 / 10) de la muestra de entrada purificada fue cargado en un 1,8% en gel de agarosa. Como era de esperar, nuestro proceso de sonicación produjo fragmentos en el rango de 150-350 pb. Sin embargo, si los fragmentos no están en este rango, el procedimiento de ultrasonidos debe ajustarse en consecuencia, variando el número de explosiones y la amplitud.
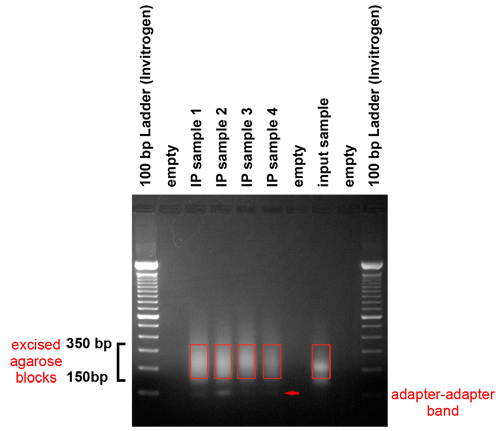
Figura 3. Purificación en gel de los productos amplificados. Los productos de PCR se ejecutan en un gel para eliminar los adaptadores y seleccione un tamaño de gama de plantillas para la generación de plataformas de cluster. Este gel muestra que los fragmentos en el rango entre 150 y 350 pares de bases se produjeron. Que representan fragmentos de ADN genómico de entre 50 y 250 pares de bases de longitud y un adaptador. Estamos sujetos a impuestos especiales de la región seleccionada de gel con un bisturí. Se debe tener cuidado para evitar que la banda adaptador adaptador, que se cifra en unas 120 pares de bases.
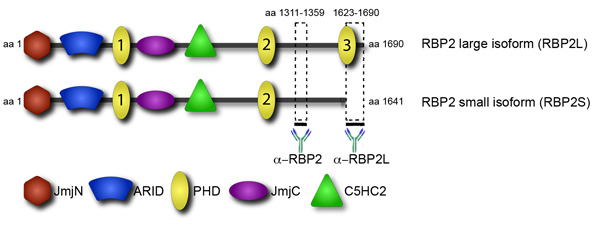
Figura 4. Isoforma de anticuerpos específicos permite distinguir entre las isoformas de grandes y pequeños de RBP2. RBP2 estructura de la proteína se presenta en el punto de vista del dominio. RBP2 contiene varios dominios: el catalizador histona desmetilación JmjC dominio y asociados JmjN de dominio, un dominio de ÁRIDAS capaz de secuencia específica de unión al ADN, un dedo de zinc C5HC2 que potencialmente pueden interactuar con el ADN o las proteínas, y varios dominios PHD. Los dos anticuerpos anti-RBP2 que permiten distinguir entre RBP2 isoformas se obtuvieron en contra de la RBP2 fragmentos indicado por líneas gruesas.
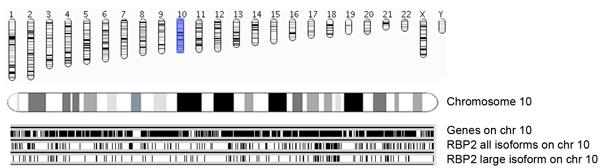
Figura 5a. Resumen de RBP2 regiones de unión a lo largo de los cromosomas y los genes con Ensembl. Coordenadas de Genómica identifica enriquecida RBP2 (todas las isoformas y la isoforma de gran tamaño) se presentan regiones de unión de cromosomas sabio. Occupances de genes Ensembl (versión 54; hg18) en los cromosomas (el cromosoma 10, en esta imagen) se presentan como barras de color negro (arriba). Cada región está representada RBP2 vinculante como una línea vertical, en el panel central muestra todas las isoformas RBP2 regiones de unión en el cromosoma 10, y el panel inferior muestra RBP2 regiones isoforma vinculante grandes. El centro y los paneles inferiores con un resúmen de la superposición y la ocupación específica de RBP2 isoformas en el cromosoma 10.
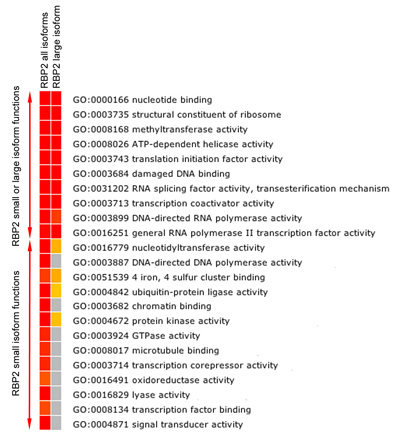
Figura 5b. El análisis de enriquecimiento funcional de los genes diana RBP2. Heatmap mostrando FDR corregida de forma significativa (valor de p ≤ 0,05) enriquecido GO categorías de función molecular entre los genes vinculados (más genes de la región de unión RBP2) por RBP2 (isoformas de todos y de gran tamaño). Colores hacia el rojo indican significación estadística alta, color amarillo indica significación estadística baja, y el gris indica que no hay significación estadística. El análisis de enriquecimiento muestra la superposición de funciones específicas y la isoforma molecular de los genes diana RBP2.
Las diferencias funcionales entre las isoformas RBP2 no se han determinado. Hemos utilizado un enfoque integral para identificar las regiones genómicas obligado por RBP2 isoformas y definir las categorías funcionales que estas regiones representan. Esto se logró por chip-Seq análisis, seguidas de análisis bioinformático de la secuencia obtenida se lee.
RBP2 modifica metilado residuos de lisina en las colas de las histonas. Hemos encontrado que RBP2 isoforma grande que contiene el módulo de reconocimiento de las histonas metiladas isoforma pequeña lisina y RBP2 que carecen de este módulo se unen a las diferentes regiones en el genoma humano (Figura 5). Es importante destacar que la isoforma específica de las regiones y las regiones con áreas pertenecen a los genes con diferentes funciones moleculares (Figura 5). Por ejemplo, "la cromatina vinculante" y "factor de transcripción vinculante" se pueden atribuir a los objetivos del gen de la isoforma RBP2 pequeño, pero no de la isoforma RBP2 grandes (Figura 5). Al comparar los genes reales conjuntos generados para todas las isoformas y RBP2 isoforma de gran tamaño (datos no mostrados), también puede definir si la isoforma grande es contratado específicamente a ciertos genes.
Este trabajo fue apoyado por 115 347-RSG-08-271-01-GMC de ACS, y por CA138631 subvención de los NIH.
Secuencias de ADN de 2006 Illumina, Inc. Todos los derechos reservados.
- Sol_PCR_1
Secuencia 5'-AAT GAT ACG GCG CAC CAC GAG ATC TAC CTT ACT TCC CAC GAC CTA GCT CTT CCG ATC T-3 ' - Sol_PCR_2
Secuencia 5'-CAA GGC GCA GAA GAC ATA CGA GCT CTT CCG ATC T-3 '
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved