Summary
Abstract
Protocol
Discussion
Acknowledgements
Materials
References
Biology
Genomvid Analys med hjälp av chip för att identifiera isoform-specifik gen mål
Här är vi presentera en kromatin immunoprecipitation (chip) Förfarandet för arvsmassan plats för hela analys av protein isoformer som skiljer sig en histon-bindande domän. Vi tillämpar den till chip-Seq analys för att identifiera målen för KDM5A/JARID1A/RBP2 histon demetylas.
Rekrytering av transkription och epigenetiska faktorer för att deras mål är ett viktigt steg i deras reglering. Prominently inom rekrytering är det protein domäner som binder till specifika histon ändringar. En sådan domän är anläggningen homeodomain (PhD), finns i flera kromatin-bindande proteiner. Den epigenetiska faktorn RBP2 har flera PHD domäner, har de dock olika funktioner (Figur 4). Framför allt binder C-terminalen PHD domän, hittades i en RBP2 onkogena fusion i mänskliga leukemi, att trimethylated lysin 4 i histon H3 (H3K4me3) 1. Avskriften motsvarar RBP2 isoformen som innehåller C-terminalen PHD ackumuleras under differentiering av promonocytic, lymfom-derived, U937 celler i monocyter 2. I överensstämmelse med båda uppgifterna, visade genomet hela analysen som i differentierade U937 celler, blir RBP2 proteinet lokaliserad till genomiska regioner höganrikat för H3K4me3 3. Lokalisering av RBP2 sina mål korrelerar med en minskning av H3K4me3 grund RBP2 histon demetylas aktivitet och en minskning i transkriptionell aktivitet. Däremot två andra doktorer i RBP2 inte kan binda H3K4me3. Noterbart är C-terminal domän PHD av RBP2 frånvarande i det mindre RBP2 isoformen 4. Det är tänkbart att de små isoformen av RBP2, som saknar interaktion med H3K4me3, skiljer sig från de större isoformen i genomisk plats. Skillnaden i genomisk plats RBP2 isoformer kan svara för den observerade mångfald i RBP2 funktion. Specifikt är RBP2 en kritisk aktör i cellulär differentiering förmedlas av retinoblastom protein (PRB). I överensstämmelse med dessa uppgifter tidigare genomet hela analysen, utan åtskillnad mellan isoformer, två avgränsade grupper av RBP2 mål gener: 1) gener bunden av RBP2 på ett sätt som är oberoende av differentiering, 2) gener bunden av RBP2 i en differentiering- beroende sätt.
Att hitta skillnader i lokaliseringen mellan isoformerna vi utförde genomet plats för hela analys av Chip-Seq. Använda antikroppar som upptäcker både RBP2 isoformer vi har hittat alla RBP2 mål. Dessutom har vi antikroppar som bara binder stora och inte små RBP2 isoform (Figur 4). Efter att ha identifierat de stora isoformen målen, kan man dra dem sedan från alla RBP2 mål att avslöja att fångas med mindre isoformen. Dessa data visar bidrag kromatin-interagerande domän i proteinet rekryteringen till dess bindningsställen i arvsmassan.
Protokollet var ursprungligen anpassats från B. Ren, 2001. Det representerar en liten ändring av protokollet Odom et al. 5 som finns på http://jura.wi.mit.edu/cgi-bin/young_public/navframe.cgi?s=22&f=appendices_downloads
1. Pre-blocket och bindning av antikroppar till magnetiska kulor (bör göras kvällen innan nästa steg)
- Tvätta 100 mikroliter av Dynabeads Protein G (per IP, kombinera för flera IP-adresser) i 1 ml färsk BSA / PBS-lösning (50 mg BSA i 10 ml PBS-Den här lösningen kommer att pågå i en vecka).
- Samla pärlor med hjälp av en magnetisk stå och tvätta på samma sätt två gånger till.
- Lägg sedan till 10 mikrogram av antikroppar mot 250 ìl av pärlor slam i PBS / BSA-lösning (per IP) och inkubera över natten på en roterande plattform vid 4 ° C.
- Efter avslutad, tvätta pärlor tre gånger i 1 ml PBS / BSA lösning och sedan återsuspendera i 10 ìl av PBS / BSA-lösning (per IP).
2. Cell tvärbindning
- Till att börja den här proceduren, växa ungefär 10 8 celler för varje immunoprecipitation, eller IP. Här är diffusa histiocytära lymfom U937 celler som används och inducerade för monocytic differentiering med tPA i 96 timmar.
- Efter celltillväxt, lägga formaldehyd lösningen direkt till media till en slutlig koncentration av 1%. Sedan snurra flaskor kort stund och låta dem sitta i rumstemperatur i 10 minuter. Sedan aspirera media och skölj celler med 15 ml iskall PBS. Upprepa denna tvätt en gång.
- Lägg sedan till 6 ml lyseringsbuffert 1 (50 mM HEPES-KOH, pH 7,5, 140 mM NaCl, 1 mM EDTA, 10% glycerol, 0,5% NP-40, 0,25% Triton X-100, som innehåller proteashämmare) till varje av kolvarna på is. Sedan, rock kolvarna under 20 minuter vid 4 ° C.
- Slutligen skörda cellerna med hjälp av en cell skrapa och överföra dem till 15 ml koniska rör. Vid denna punkt cellerna kan lagras vid -80 ° C.
3. Cell sonication
- Om cellerna frystes, tina dem. När tinade, snurra celler nedåt vid 3000 rpm i 10 minuter vid 4 ° C och kassera supernatanten. Sedan resuspendera cellerna i 6 ml lyseringsbuffert 2 (10 mM Tris-HCl, pH 8,0, 200 mM NaCl, 1mm EDTA, 0,5 mm EGTA, innehållande proteashämmare). Rock rören försiktigt vid rumstemperatur i 10 minuter.
- Upprepa centrifugeringen och återsuspendera cellerna i 2,5 mL lyseringsbuffert 3 (10 mM Tris-HCl, pH 8,0, 100 mM NaCl, 1 mM EDTA, 0,5 mm EGTA, 0,1% natriumdeoxikolat, 0,5% N-lauroylsarcosine, innehållande proteashämmare) .
- Därefter förbereda suspension sonication genom att placera den i en bägare av iskalla vattnet med microtip en Branson 450 Sonifier satt till mellan 50 och 60% amplitud.
- Sonikera lösningen för en 30 sekunders konstant brast och svalt på is i 1 minut. Upprepa dessa pulser 10 till 15 gånger. Sedan pipett innehållet i röret upp och ner och överföra dem till ett nytt rör. Fortsätt att puls och kyla lösningen ytterligare 5 gånger.
- Efter ultraljudsbehandling, lägga till 10% Triton X-100 till 1 / 10 av lösningen volym. Överför lysates till 1,5 rör ml centrifugering, och snurra skräp i en mikrocentrifug. Sedan överföra cellen lysat till ett nytt rör.
4. Kromatin Immunoprecipitation
- Före kromatin immunoprecipitation eller Chip, spara 50 mikroliter av cellen lysat som ingång prov. Sedan kombinera rensas cellen lysat med Dynabeads före bunden till antikropp som tidigare har upprättats enligt ovan. Rock blandningen, utöver de 50 mikroliter ingång prov, vid 4 ° C över natten.
- Tvätta pärlor med 1 mL av tvättbufferten (50 mm HEPES-KOH, 7,6 pH, 0,5 M LiCl, 1mm EDTA, 0,7% natriumdeoxikolat, 1% NP-40). Använd sedan en magnetisk står för att samla pärlor och avlägsna supernatanten. Upprepa detta tvätta 6 till 8 gånger.
- Gör ett sista tvätten med 1 ml TE-plus-50 mM NaCl (10 mM Tris-HCl, pH 8,0, 50 mM NaCl, 1 mM EDTA). Snurra pärlor i en mikrocentrifug vid 3000 rpm i 2 minuter vid 4 ° C. Efter centrifugering, aspirera någon resterande TE buffert.
- Lägg sedan till 100 mikroliter av Elution Buffer (50 mM Tris-HCl, pH 8,0, 10 mM EDTA, 1% SDS) till proverna. Omedelbart efter, inkubera proverna vid 65 ° C i 10 till 15 minuter. Skrapa rören mot en 1,5 ml provrörsställ varje 2 minuter för att hålla kulorna i suspensionen.
- Samla pärlor med hjälp av centrifugering och den magnetiska står, och överför supernatanten till ett PCR-rör. Sedan hämta tidigare sparade in provet och tillsätt 3 volymer av Elution Buffer.
- Slutligen, placera IP och input prover i värmecykeln över natten vid 65 ° C tillvända den gränsöverskridande kopplingar.
- Följande dag, tillsätt 1 volym av TE buffert för att proverna. Lägg sedan till RNas A till en slutlig koncentration av 0,2 mikrogram / mikroliter. Inkubera proverna i värmecykeln med 1 till 2 timmar vid 37 ° C.
- Efter inkubation, lägga proteinas K till en slutlig koncentration av 0,2 mikrogram / mikroliter. Då, inkubera proven i värmecykeln vid 55 ° C i 2 timmar.
- Nästa, extrahera prover en gång med en volym av fenol. Utdrag proverna en andra gång med en volym av fenol: kloroform: Isoamyl alkohol. Slutligen extrahera prover en gång med en volym av kloroform: Isoamyl alkohol.
- Lägg sedan till 30 mikrogram av glykogen till varje prov. Lägg också till NaCl till en slutlig koncentration av 0,2 Molar och två volymer av etanol till proverna. Inkubera dem i 30 minuter vid -80 ° C. Efter inkubation, snurra prover och dekantera supernatanten. Tvätta pellets med 500 mikroliter av 75% etanol. Sedan torka pellets och återsuspendera dem i 40 mikroliter vatten.
- För att kontrollera storleken på DNA-fragment som produceras av sonication förfarande, belastning 5 mikrogram av det renade in provet i en 1,8% agarosgel och köra gelen. Den sonication förfarande bör ge fragment i intervallet 150-350 baspar. Men om fragmenten inte faller inom detta intervall bör sonication förfarande justeras genom att variera antalet brister och amplitud.
- För att kontrollera robusthet och specificitet chip anrikning i kontrollen bindande regioner genom att utföra genspecifika PCR med 1 ìl av IP-prover och en spädningsserie av den ingående prov. Två till tre "bundna" regioner och en obunden kontroll region måste väljas för att testa kvaliteten på IP och input prover.
5. Amplifiering av genomiska DNA
- Från och med 34 l av IP-prov eller 200 ng av den ingående prov, utföra slutet reparera "A" svans tillägg och ligatur av adaptrar till DNA-fragment med hjälp Genomiskt DNA-prov Prep Kit http://www.illumina.com/systems/ genome_analyzer.ilmn (Illumina, Inc., San Diego, CA).
- Rena DNA med en MinElute PCR Purification Kit och sedan eluera det i buffert EB (10 mM Tris Cl, pH 8,5) som har förvärmas till 50 ° C. Använd till exempel 23 mikroliter och 46 mikroliter för den slutliga eluering av IP och input prov-DNA, respektive.
- Gör PCR-reaktionen med hjälp av 23 mikroliter av DNA med adaptrar och 25 mikroliter Phusion DNA-polymeras från kit, 1 mikroliter av 20 mikroM Sol_PCR_1 och 1 mikroliter av 20 mikroM Sol_PCR_2. Kör PCR-reaktionen som följer: 1) 30 sekunder vid 98 ° C, 2) 10 sekunder vid 98 ° C, 3) 30 sekunder vid 65 ° C, 4) 30 sekunder vid 72 ° C, upprepa steg steg 2-4 18 gånger och sedan 5 minuter vid 72 ° C, håller äntligen vid 4 ° C.
- Efter PCR-amplifiering, rena DNA med QIAGEN MinElute PCR Purification Kit. Förvärma 15 mikroliter av buffert EB till 50 ° C och eluera DNA. Späd 0,5 mikroliter av provet 01:04 och utföra en Nanodrop läsning.
6. Gel rening av förstärkta produkter
- Att rena de förstärkta produkter, förbereda en 1,8% agarosgel på 50 ml med hjälp av HPLC-kvalitet vatten. Lägg TAE och etidiumbromid efter agarosen har smält. Sedan, häll gelen. Ladda gelen efter tillägg 4 mikroliter av buffert till ingången och prover IP. Kör gelen vid 120 volt i 45 minuter.
- Analysera gelen efter det att springa. Gelen visar att fragment i intervallet mellan 150 och 350 baspar produceras. De representerar genomiska DNA-fragment mellan 50 och 250 baspar i längd och en adapter.
- Excise regionen gel som innehåller material i 150 350 baspar utbud med en skalpell. Var noga med att undvika excising adaptern-adaptern bandet, går som på ca 120 baspar. Återställa DNA med hjälp av en QIAquick Kit Gel Extraction per tillverkarens anvisningar. Specifikt använder en kolumn från QIAquick Gel Extraction Kit för en gel skiva 400 mg eller mindre. För att börja utvinningen, tillsätt 3 volymer av QG buffert till en volym av gel. Tillsätt 1 volym av isopropanol och ladda blandningen på kolumnen. Använd 0,5 ml QG att tvätta kolumnen, följt av standard som beskrivs i kit manual. Använd H 2 O förvärmas till 50 ° C för att eluera DNA. Inkubera kolonnen med 30 l H 2 O i 5 minuter vid 37 ° C innan spinningen ner den.
- Torka provet ner till exakt 11 mikroliter i en Speedvac utan värme. Ta bort 1 mikroliter av provet och mät DNA-koncentration med hjälp av en Nanodrop spektrofotometer.
- Slutligen, identifiera berikas genprodukter med Illumina Genome AnalyzerIIe enligt beskrivningen på http://genesdev.cshlp.org/content/suppl/ 2008/12/15/22.24.3403.DC1/GuentherSuppMat.pdf 6.
7. Representativa resultat
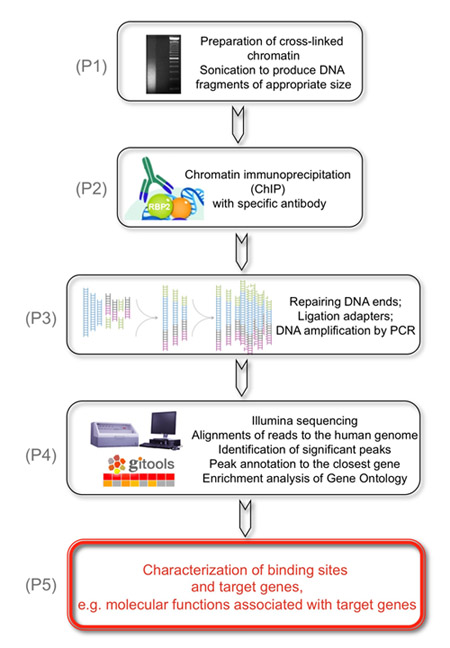
Figur 1. Det övergripande målet för följande experiment är att identifiera genomiska mål KDM5A/JARID1A/RBP2 histon demetylas.
(P1) Detta uppnås genom beredning av tvärbunden kromatin som är sonicated att producera DNA-fragment av lämplig storlek. (P2) Som ett andra steg är RBP2 bundna DNA-fragment immunoprecipitated med RBP2 antikroppar. (P3) Nästa är det återvunna DNA-fragment repareras i ändarna och adaptrar knyts ihop på ändarna av arvsmassans DNA för att förbereda bibliotek av arvsmassans DNA för analys på flödet celler i Illumina Cluster Station. DNA-biblioteken förökas med PCR med lågt antal cykler. (P4) Slutligen, läser belysning sekvenserat korta unikt anpassas till det mänskliga genomet, är betydande toppar identifieras och kommenterade till närmaste gener i syfte att identifiera RBP2 berikad regioner. (P5) Resultat erhålls som visar molekylära funktioner i samband med RBP2 mål gener baserat på genomet hela identifiering av RBP2 berikat regioner.
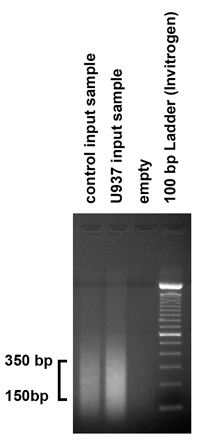
Figur 2. Kontroll av resultaten av kromatin ultraljudsbehandling vill kontrollera storleken på DNA-fragment som produceras av sonication förfarandet var 5 mikrogram (1 / 10) av det renade ingång prov lastas på 1,8% agarosgel. Som väntat producerade våra ultraljudsbehandling förfarande fragment i intervallet 150-350 bp. Men om fragmenten inte faller inom detta intervall bör sonication förfarandet anpassas därefter, genom att variera antalet brister och amplitud.
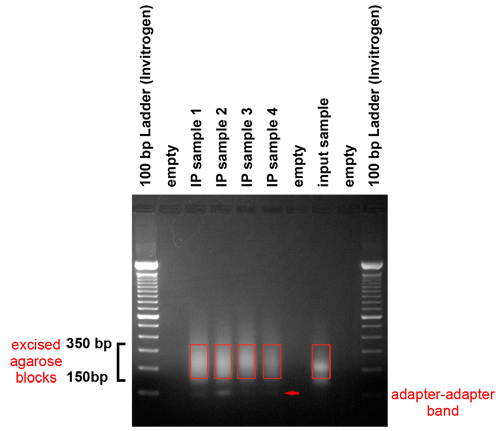
Figur 3. Gel rening av förstärkta produkter. PCR-produkter körs på en gel för att ta bort adaptrar och välj en storlek-antal mallar för klustret generations plattform. Denna gel visar att fragment i intervallet mellan 150 och 350 par bas producerades. De representerar genomiska DNA-fragment mellan 50 och 250 baspar i längd och en adapter. Vi punktskatter det markerade området gel med en skalpell. Försiktighet bör iakttas för att undvika adaptern-adaptern bandet, som uppgår till ca 120 baspar.
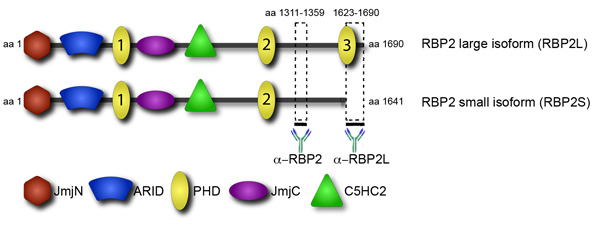
Figur 4. Isoform-specifik antikropp kan skilja mellan stora och små isoformer av RBP2. RBP2 protein struktur presenteras i domän vy. RBP2 innehåller flera områden: den katalytiska histon demetylering JmjC domän och tillhörande JmjN domän, en ofruktbar domän som kan sekvensspecifika DNA-bindande, en C5HC2 zink finger som potentiellt kan interagera med DNA eller andra proteiner, och flera PHD domäner. De två anti-RBP2 antikroppar som gör att skilja mellan RBP2 isoformer härrör mot RBP2 fragmenten visas med tjocka linjer.
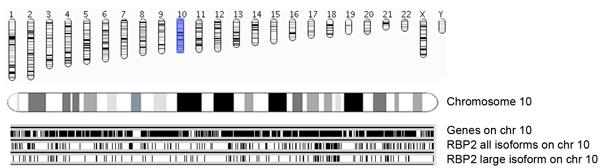
Figur 5a. Översikt över RBP2 bindande regioner längs med kromosom och Ensembl gener. Genomisk koordinater identifierade berikad RBP2 (alla isoformer och stora isoformen) bindande regionerna presenteras kromosom klokt. Occupances av Ensembl gener (version 54, hg18) i kromosomer (kromosom 10 på bilden) presenteras som svarta fält (övre panelen). Varje RBP2 bindande regionen representeras som en vertikal linje, där den mittersta panelen visar alla RBP2 isoformer bindande regioner på kromosom 10, och den nedre panelen visar RBP2 stora isoformen bindande regioner. I mitten och botten paneler ger överblick av överlappande och specifika beläggning av RBP2 isoformer på kromosom 10.
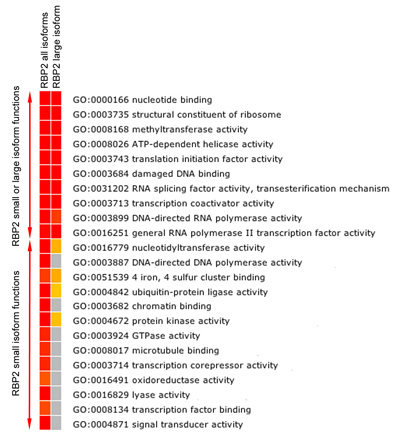
Figur 5b. Funktionell anrikning analys av RBP2 mål gener. Heatmap visar FDR korrigeras signifikant (p-värde ≤ 0,05) berikat GO Molekylär Funktion kategorier bland de gener som är bundna (närmast gener till RBP2 bindande regionen) med RBP2 (alla och stora isoformer). Färgerna mot rött indikerar hög statistik betydelse, visar gul låga statistik betydelse, och grått ingen statistik betydelse. Anrikning analys visar överlappningen och isoformen specifika molekylära funktioner RBP2 mål gener.
Funktionella skillnader mellan RBP2 isoformer har inte fastställts. Vi har använt en övergripande strategi för att identifiera genomiska regioner bunden av RBP2 isoformer och definiera funktionella kategorier som representerar dessa regioner. Detta uppnåddes genom Chip-Seq analys följt av bioinformatik analys av erhållna sekvens läser.
RBP2 ändrar metylerade lysinrester på histon svansar. Vi fann att RBP2 stora isoformen innehåller erkännande modulen för metylerade histon lysin och RBP2 små isoformen saknar denna modul binder till olika regioner i det mänskliga genomet (Figur 5A). Viktigt isoformen-specifika regioner och överlappande regioner tillhör gener med olika molekylära funktioner (Figur 5B). Till exempel kan "kromatin bindande" och "transkriptionsfaktor bindande" funktioner tillskrivas gen mål RBP2 små isoformen men inte RBP2 stora isoform (Figur 5B). Genom att jämföra faktiska genen sätter genereras för alla isoformer och RBP2 stora isoformen (data visas inte), kan vi också definiera om stora isoformen är speciellt rekryteras till vissa gener.
Detta arbete stöddes av 115.347-RSG-08-271-01-GMC från ACS, och genom CA138631 anslag från NIH.
Oligonukleotid sekvenser 2006 Illumina, Inc. Med ensamrätt.
- Sol_PCR_1
Sekvens 5'-AAT GAT ACG GCG ACC ACC GAG ATC TAC ACT CTT TCC CTA CAC GAC GCT CTT CCG ATC T-3 " - Sol_PCR_2
Sekvens 5'-CAA GCA GAA GAC GGC ATA CGA GCT CTT CCG ATC T-3 "
- Wang, G. G. Haematopoietic malignancies caused by dysregulation of a chromatin-binding PHD finger. Nature. 459 (7248), (2009).
- Benevolenskaya, E. V. Binding of pRB to the PHD protein RBP2 promotes cellular differentiation. Mol Cell. 18 (6), 623-623 (2005).
- Lopez-Bigas, N. Genome-wide analysis of the H3K4 histone demethylase RBP2 reveals a transcriptional program controlling differentiation. Mol Cell. 31 (4), 520-520 (2008).
- Benevolenskaya, E. V. Histone H3K4 demethylases are essential in development and differentiation. Biochem Cell Biol. 85 (4), 435-435 (2007).
- Odom, D. T. Control of pancreas and liver gene expression by HNF transcription factors. Science. 303 (5662), 1378-1378 (2004).
- Guenther, M. G. Aberrant chromatin at genes encoding stem cell regulators in human mixed-lineage leukemia. Genes Dev. 22 (24), 3403-3403 (2008).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved