Summary
Abstract
Introduction
Protocol
Representative Results
Discussion
Acknowledgements
Materials
References
Biology
-Faag gemedieerde Levering van gerichte sRNA Constructen voor het neerslaan van Gene Expression
We describe a method to knock down gene expression in a growing population of E. coli cells using sequence-targeted sRNA expression cassettes delivered by an M13 phagemid vector.
-RNA gemedieerde knockdowns worden wijd gebruikt om genexpressie. Deze veelzijdige familie van technieken maakt gebruik van korte RNA (sRNA) die kan worden gesynthetiseerd met willekeurige volgorde en ontworpen om elk gen gericht voor silencing vullen. Omdat sRNA constructen kunnen direct op veel celtypen worden ingebracht of met een verscheidenheid aan vectoren kan genexpressie worden onderdrukt in levende cellen zonder moeizame genetische modificatie. De meest voorkomende RNA knockdown technologie, RNA interferentie (RNAi), maakt gebruik van de endogene RNA-geïnduceerd silencing complex (RISC) te bemiddelen herkenningssequentie en klieving van de doelwit mRNA. Toepassingen van deze techniek, beperkt tot RISC-expressie organismen, vooral eukaryoten. Recentelijk heeft een nieuwe generatie RNA biotechnologen alternatieve mechanismen ontwikkeld voor het reguleren van genexpressie door middel van RNA, enzovoort mogelijk gemaakt RNA-gemedieerde gen knockdowns in bacteriën. Hier beschrijven we een methode voor de silencing-gen expresSion in E. coli die functioneel lijkt RNAi. In dit systeem een synthetisch faagmide is ontworpen om sRNA die kan ontworpen om elk doelwit sequentie tot expressie. Het expressieconstruct wordt geleverd aan een populatie van E. coli-cellen met niet-lytische faag M13, waarna het kan stabiel repliceren als een plasmide. Antisense herkenning en onderdrukking van het doelwit mRNA wordt gemedieerd door de HFQ eiwit endogeen E. coli. Dit protocol omvat werkwijzen voor het ontwerpen van de antisense sRNA, constructie van de faagmide vector, verpakken van de fagemide in M13 bacteriofaag bereiden van een levende celpopulatie geïnfecteerd, en het uitvoeren van de infectie zelf. De fluorescerende eiwit mKate2 en het antibioticum resistentiegen chlooramfenicol acetyltransferase (CAT) zijn gericht om representatieve gegevens te genereren en knockdown effectiviteit kwantificeren.
-RNA-gemedieerde gen knockdowns verlopen in twee fasen. Eerst wordt een RNA-molecuul geïntroduceerd in een cellijn of organisme studie. Ten tweede, endogene RNA-bindende eiwitten te vergemakkelijken RNA-doelwit herkenning en productie van de silencing effect. Alle RNA knockdown technologieën maken van de aanpasbare aard van synthetische sRNAs, die gemakkelijk kan worden geproduceerd om een specifiek doelwit van belang overeenkomen. De moleculaire details van RNA silencing opname en sterk verschillen modelsysteem beperken waar en hoe knockdowns RNA kan worden toegepast.
In nematoden, dubbelstrengs RNA (dsRNA) moleculen kunnen rechtstreeks in de media of het voeden van de wormen met een bevolking van dsRNA tot expressie brengende E. geïntroduceerd coli-cellen 1,2. In Drosophila, kan worden bereikt door RNAi microinjecting embryo's met dsRNA 3, of cellijnen uitgevoerd door eenvoudig toevoegen van dsRNA aan het kweekmedium 4. In zoogdiercellijnen,synthetische kleine interfererende RNA's (siRNA's) kunnen aan levende cellen worden geleverd door elektroporatie 1,2,5, verpakt in liposomen 3,6, of tot expressie van DNA-plasmidevectoren 4,7. Zodra de RNA species het cytosol bereikt, de RNAi pathway voert het RISC complex dsRNA verwerken antisense herkenning van het doel te vergemakkelijken en katalyseren translationele repressie mRNA degradatie of heterochromatinevorming, afhankelijk van de gastheersoort.
Vanwege deze eisen, kunnen de klassieke RNAi alleen uitgevoerd worden in organismen die efficiënt nemen exogene RNA en express RISC of een RISC-achtige activiteit. Met name, dit is exclusief het model bacterie E. coli, waarin de RNAi pathway mist. Echter, de recente ontwikkelingen in de synthetische biologie bieden de tools om zowel de levering probleem en het monddood probleem op te lossen.
In dit protocol wordt sRNA constructen tot expressie gebracht in E. coli door een DNA-vector die aan liVing cellen met behulp van de M13 faagmide / helper systeem. Een fagemide is elk plasmide met een faag f1 afgeleide replicatieplaats. Een helper plasmide, in casu M13KO, draagt de machinerie nodig virale deeltjes produceren, maar is zelf niet bevoegd is voor replicatie en verpakken. Wanneer een faagmide en helper plasmide zijn co-getransformeerd, is het faagmide alleen gerepliceerd naar de f1 oorsprong, verpakt en uitgescheiden. De vectorized faagmide is dan bevoegd om live E. infecteren coli via de F-pilus.
In dit systeem wordt het silencing effect door aangepaste sRNA cassettes combineren van een steiger sequentie met een doelwit bindende sequentie. Het doel bindende sequentie 24 basenparen antisense mRNA een doel, typisch bij de ribosoom bindingsplaats (RBS). Het schavot sequentie, ontwikkeld door Na en collega 8, bevat een HFQ-bindende motief onttrokken MICC, een kleine regulerende RNA endogeen E. coli. De HFQ eiwit stimuleert RNA-RNA binding en mRNA degradatie, waar een rol systeem vergelijkbaar met RISC in RNAi. Figuur 1 toont een volledig schema voor faag-gemedieerde sRNA knockdowns, waaronder de sRNA cassette structuur, faagmide vectorisering en silencing mechanisme.
Als een werkwijze om genexpressie in E. moduleren coli, sRNA silencing is eenvoudig, snel en veelzijdig. De beoogde E. coli wordt niet belast buiten uitdragen van het fagemide en de uiting van de sRNA. Dit kan relevant zijn in het kader van de synthetische biologie of fundamenteel onderzoek waar de uitdrukking van grotere heterologe constructies cellulaire middelen 9 kunnen stam zijn. Faagmiden nieuwe targets kunnen worden met een enkele PCR en geoogst één dag na faagmide transformatie. Tenslotte kan vrijwel elk mRNA gericht. De sRNA regeling cassette (op een standaard plasmide) bleek te werken aan verschillende doelen in het metabolisme typische repressie niveaus> 90% 8.
10. Eerst wordt een verpakt faagmide introduceerde een batch kweek van E. coli-cellen en gebruikt om expressie van het fluorescerende eiwit mKate2 zwijgen. Latere fluorescentieveranderingen bewaakt in real time. Ten tweede, slopen het CAT-gen wordt getoond aan fenotypische chlooramfenicol weerstand op agarplaten te verminderen. In beide gevallen, het faagmide zelf draagt een GFP merker, waardoor infectie te meten, onafhankelijk van de knockdown efficiëntie.
1. Ontwerp en constructie van faagmidevectoren Bearing sRNA Silencing Cassettes
- De Novo ontwerp van sRNA Silencing Cassettes 8
- Identificeer de volledige sequentie van het mRNA te worden uitgezet met een DNA-sequentie database. Om de doelsequentie te genereren, let op de eerste 24 bp van de coderende sequentie van positie 1-24 te beginnen met het startcodon (bijv ATG).
Noot: Silencing minder efficiënt wanneer andere plaatsen of segmenten van het mRNA 8 zijn gericht. - Neem het omgekeerde complement van de doelsequentie om de GUIDE sequentie voor het sRNA cassette produceren. Zie tabel 1 voor voorbeelden van TARGET GUIDE sequenties voor chlooramfenicol-acetyltransferase (CAT).
- Om de 292 bp volledige sRNA expressiecassette ontwerpen, regelen de PR-promotor, GUIDE volgorde, HFQ eiwit bindend domein en T1 / TE transcriptieterminator sequenties in serie (tabel 2).
- Voeg extra kloneringsplaatsen van keuze om klonering van het sRNAs cassette vergemakkelijken in de geselecteerde vector.
- Verkrijgen van een totale sRNA cassette via commerciële gensynthese of een soortgelijke methode en kloneren deze in een faagmide vector met een functionele f1 replicatieoorsprong 11. Zie Ondersteunende informatie voor de volledige sequentie van het uiteindelijke faagmide vector.
- Identificeer de volledige sequentie van het mRNA te worden uitgezet met een DNA-sequentie database. Om de doelsequentie te genereren, let op de eerste 24 bp van de coderende sequentie van positie 1-24 te beginnen met het startcodon (bijv ATG).
- Het veranderen van de Sequence doelwit van een bestaande sRNA expressiecassette met behulp van PCR-gebaseerde plaatsgerichte mutagenese 12
- Identificeer de 24 bp GUIDE sequentie in een bestaande sRNA expressiecassette. Opmerking: De geannoteerde pAB.001 plasmide, gebruikt in dit werk, is beschikbaar als een aanvullende sequentie-bestand.
- Ontwerp voorwaartse en achterwaartse primers met korte gebieden van homologie met de bestaande sRNA cassette flankeren de nieuwe 24 bp GUIDE sequentie. Het verkrijgen van de primers door middel van commerciële oligonucleotidesynthese.
Opmerking: Primer ontwerp voor plaatsgerichte mutagenese depicted in figuur 2. Exact primer matrijs sequenties worden verschaft in Tabel 3. - Bereid een 5 ml cultuur van E. coli die de template sRNA uitdrukking faagmide. Groeien de cellen overnacht bij 37 ° C onder schudden in LB medium met geschikte antibiotica.
- Extraheren en zuiveren de template sRNA uitdrukking faagmide van de 5 ml bacteriecultuur met behulp van een DNA miniprep kit of soortgelijke methode 12.
- Bereid twee PCR reacties onder gebruikmaking van de matrijs sRNA expressie faagmide en high fidelity polymerase, een met de voorwaartse en een met de reverse primer (Tabel 4). Met PCR-omstandigheden zoals aanbevolen door de leverancier polymerase (Tabel 5). Verhoog de template concentratie hoger 10-50x dan een standaard reactie die overeenkomt met het feit dat de enkele primer exponentiële amplificatie reactie niet produceert.
- Combineer de bovengenoemde twee PCR-reacties in een microcentrifugebuis. Anneal de producten door verwarmen tot 98 ° C in een kokend waterbad. Onmiddellijk na plaatsing van de microcentrifugebuis in het waterbad, verwijder de warmtebron en laat het bad langzaam op kamertemperatuur gedurende 1-2 uur.
- Om de gemuteerde sjabloon sRNA uitdrukking faagmide te elimineren, voeg 1 pl. Dpnl restrictie-enzym aan het mengsel en incubeer bij 37 ° C gedurende 1 uur, of de tijd door de fabrikant voor complete digestie.
Opmerking: DpnI verteert alleen gemethyleerd doelplaatsen, die aanwezig zijn op de gastheer gerepliceerd faagmiden maar PCR producten. - Transform gekocht of bereid 13 chemisch competente E. coli met 1-5 pi van het PCR-product gehybridiseerd. Isoleer enkele kolonies van de getransformeerde stam door selectieve plating op LB agarplaten die geschikte antibiotica.
- Om de invoeging van de correcte sequentie GUIDE controleren scherm de resulterende kolonies door kolonie PCR. Met behulp van een 200 ul pipetpunt, collect een kleine hoeveelheid cellen van een enkele getransformeerde kolonie. Mark en het behoud van de oorspronkelijke kolonie voor downstream gebruik na verificatie.
- Voeg de verzamelde cellen 50 ul nuclease-vrij water in een microcentrifugebuis. Meng door en neer te pipetteren.
- Onder toepassing van een tafelmodel thermocycler of een kokend waterbad, lyseren de cellen door verwarmen tot 95 ° C gedurende 2 minuten.
- PCR-amplificeren het faagmide regio middels 1 pl warmte gelyseerde cellen als een DNA-matrijs. PCR-omstandigheden en thermocycler protocollen in de tabellen 6 en 7. Zie de aanvullende pAB.001 sequentie bestand voor verificatie primersequenties.
- Sequentie het PCR product aan invoeging van de correcte sequentie GUIDE verifiëren.
- Inoculeer 5 ml cultuur van de E. coli-kloon die de sequentie geverifieerd sRNA expressie faagmide. Groeien de cellen overnacht bij 37 ° C onder schudden in LB selectieve media.
- Bereid een glycerol voorraadvan de sequentie geverifieerde kloon. Voeg 750 ul van de kweek van een nacht tot 250 ul van 60% glycerol in een cryo tube schroefdop.
- Bewaar de glycerol voorraad bij -80 ° C voor onbepaalde tijd. De rest van de kweek gedurende de nacht kan worden gebruikt als bron voor het sRNA expressie faagmide in stap 2.
2. Productie en Harvest of M13-verpakte Faagmide Stocks
- Bereid een 5 ml cultuur van E. coli die de sRNA uitdrukking faagmide. Groeien de cellen overnacht bij 37 ° C onder schudden in LB medium met geschikte antibiotica. Opmerking: De sRNA expressie faagmide kan worden verkregen via de novo klonen zoals beschreven in stap 1.1.5, of een modificatie van een bestaande faagmide en in stap 1.2.16 geoogst.
- Op dezelfde manier voor te bereiden op 5 ml cultuur van E. coli die het M13KO7 helper plasmide. Groeien de cellen overnacht bij 37 ° C onder schudden in LB selectieve media.
- Extraheren en zuiveren de sRNA expression faagmide en helper plasmide met een DNA extractie kit of soortgelijke werkwijze 12.
- Cotransform gekocht of bereid 13 chemisch competente E. coli met 1 pi elk van sRNA meningsuiting faagmide en helper plasmide. Kies voor cotransformants door het uitplaten op LB-agar met selectieve antibiotica voor beide constructies.
- Maak een cultuur van 10 ml van een enkele kolonie van de gecotransformeerd stam in LB met selectieve antibiotica. Incubeer bij 37 ° C onder schudden gedurende 8-12 uur of overnacht.
- Centrifugeer de cultuur bij 3300 xg gedurende 10 min. Verzamel de bovenstaande vloeistof en filter door een 0,2 pm filter. Let op: In het geval van media morsen, reinig het gebied met verdund bleekwater (0,5%) tot infectieuze faagdeeltjes te vernietigen.
- Bewaar het verpakte faagmide filtraat bij 4 ° C. Opmerking: Monsters kunnen zonder verlies van activiteit weken worden gehandhaafd voor dagen.
3. Voorbereiding van F + Target Cellen voor zwijgen
- Bepalen of de cellen het doelwit zijn voor silencing expressie F pilus 14. Als de F-pilus al aanwezig is, ga dan naar stap 4.
Opmerking: Gemeenschappelijke laboratorium stammen van E. coli geannoteerd als F + en F "de aanwezigheid van het F pilus geven in hun genoom of op een plasmide. - Het verkrijgen van een F + stam van E. coli zoals TOP10F '.
Opmerking: Zorg dat het doel stam draagt een uniek weerstand marker om te worden gescheiden van het F-plasmide donor na conjugatie. - Om F pilus introduceren door conjugatie met een F + stam, voor te bereiden 5 ml culturen van zowel de doelgroep stam en de F-plasmide donor 14. Groeien de cellen overnacht bij 37 ° C onder schudden in LB medium met geschikte antibiotica.
- De volgende dag, verdunnen beide stammen 1: 100 in 5 ml LB selectieve en verder kweken bij 37 ° C onder schudden.
- Bepaal de groeifase van de cellen door het meten van de optsche dichtheid van de cultuur bij 600 nm (OD 600) met behulp van een tafelmodel spectrofotometer. Kweken van de cellen gedurende ongeveer 2 uur totdat een OD 600 van 0,3 wordt bereikt, aangeeft log-fase groei 15.
- Bereid 3 conjugatiereacties in microcentrifugebuizen: 0,5 ml F-plasmide donor + 0,5 ml doel stam, 0,5 ml F-plasmide donor + 0,5 ml LB-medium (negatieve controle) en 0,5 ml doel stam + 0,5 ml LB-medium (negatieve controle). Laat de conjugatie men gedurende 2 uur bij 37 ° C onder schudden.
- Plaat 100 pi van elke conjugatiereactie op selectieve LB-agar met antibiotica specifiek voor het F-plasmide (gewoonlijk tetracycline) en target stam. Plate de negatieve controle reacties te bevestigen dat noch de donor of ontvanger stam uiten beide antibioticaresistenties.
4. Infectie met Verpakt Faagmiden te zwijgen
- Inoculeer een enkele kolonie van F + doelcellen in een 5 ml cultuur van LB medieen met geschikte antibiotica. Incubeer overnacht bij 37 ° C onder schudden.
- De volgende dag verdunnen F + doelcellen 1: 100 in 5 ml selectief medium en LB blijven kweken bij 37 ° C onder schudden.
- Bepaal de groeifase van de cellen door de optische dichtheid van de kweek bij 600 nm (OD 600) met een benchtop spectrofotometer. Kweken van de cellen gedurende ongeveer 2 uur totdat een OD 600 van 0,3 wordt bereikt, aangeeft log-fase groei 15. Opmerking: Expressie van het F pilus en infectie-efficiëntie is het hoogst in de log-fase.
- Voeg de M13-verpakte faagmiden (uit stap 2.6) aan de doelcellen in een volumeverhouding van 1: 100 tot ongeveer 99% infectie van de doelgroep bereiken. Laat de infectie verlopen bij 37 ° C onder schudden voor 30-60 min.
- Testen de sRNA-silencing fenotype volgens de werkwijze van keuze.
Opmerking: Voor een fluorescerend eiwit doel, kan de silencing effect worden gekwantificeerdrechtstreeks door fluorometrie 10. Alternatief kan fenotypische testen worden gebruikt om de fenotypische gevolgen van gen knockdown 8 observeren. - Bereid een glycerol voorraad voor de sRNA expressie faagmide gastheer volgende stappen 1.2.14-1.2.16. Opmerking: het fagemide zal voortplanten in de gastheerstam onbeperkt en kan worden onderhouden met antibiotica vergelijkbaar met een conventionele plasmide.
Silencing van mKate2 Fluorescentie in Liquid Media
Figuur 1 toont het schema voor sRNA-gemedieerde knockdowns in dit werk beschreven, met inbegrip van de sRNA cassette ontwerp, faagmide vectorisering en silencing mechanisme. Volgende protocol 1.2, werd de sRNA zwijgen cassette van plasmide pAB.001 veranderd te richten mKate. De sRNA cassette werd gesynthetiseerd en gekloond in faagmide Litmus28i_J23115-B0032-GFP, een geschenk van Monica Ortiz en Drew Endy 11. Dit faagmide draagt markers voor GFP expressie en kanamycineresistentie, waardoor succesvolle infecties worden bijgehouden. Verpakte faagmide voorraden werden bereid volgens protocol 2.
Een derivaat van E. coli K12 MG1655 het dragen van een constitutief tot expressie gebracht, chromosomaal geïntegreerd mKate2 marker werd voorbereid fagen infectie door vervoeging met een F-plasmide donorstam volgende protocol 3. De cellen werden gekweekt tot mid log fase en de faagmide ingevoerd na protocol 4. Na faagmide infectie werden 200 ul kweken overgebracht naar een fluorescentie plaatlezer en de fluorescentie werd continu gevolgd gedurende 24 uur.
Figuur 3 toont het effect van sRNA-gemedieerde silencing op mKate2 expressie. De stam geïnfecteerd met een anti-mKate2 faagmide vertoonden geen detecteerbare fluorescentie in mKate2 achtergrond. In tegenstelling tot deze stam deed drukken de GFP marker, wat aangeeft succesvolle opname van het faagmide. Niet-geïnfecteerde controle cellen geproduceerd mKate2 fluorescentie maar niet GFP. Een extra controle, waarbij de anti-mKate2 doeldomein werd vervangen door een sequentie gericht CAT, had geen effect op mKate2 fluorescentie.
Silencing van chlooramfenicol Resistance op agarplaten
content "fo: keep-together.within-page =" 1 "> Na protocol 1.1, een sRNA zwijgen cassette werd geproduceerd te richten CAT Een derivaat van E. coli K12 MG1655 het dragen van een constitutief tot expressie gebracht, chromosomaal geïntegreerde CAT marker werd voorbereid. faaginfectie door conjugatie met een F-plasmide donorstam volgende protocol 3. de cellen werden gekweekt tot mid log fase en de faagmide geïntroduceerd volgende protocol 4. Na 1 uur incubatie bij 37 ° C, werden geïnfecteerde cellen serieel verdund en uitgeplaat met een reeks concentraties chlooramfenicol. Platen werden overnacht geïncubeerd en de hoeveelheid van resistente cellen bij elke chloramfenicol werd bepaald door het tellen van kolonievormende eenheden (CFU's) de volgende dag.Figuur 4 toont de invloed van sRNA-gemedieerde silencing op het chloramphenicol resistentie fenotype. Geïnfecteerde cellen of cellen geïnfecteerd met faagmide gericht mKate2, waren resistent tegenchlooramfenicol bij alle geteste concentraties. Daarentegen cellen geïnfecteerd met fagemide gericht CAT vertoonden verminderde overleving bij lage concentraties chlooramfenicol, en bijna 99% doden bij hogere concentraties. Het toevoegen van ampicilline, voor het selecteren van alleen bacteriën die het faagmide, chlooramfenicol verminderde overleving stellen niveaus. Dit is consistent met eerder werk blijkt dat ontsnappen uit faag-infectie is een gebruikelijke route te ontsnappen silencing 10.
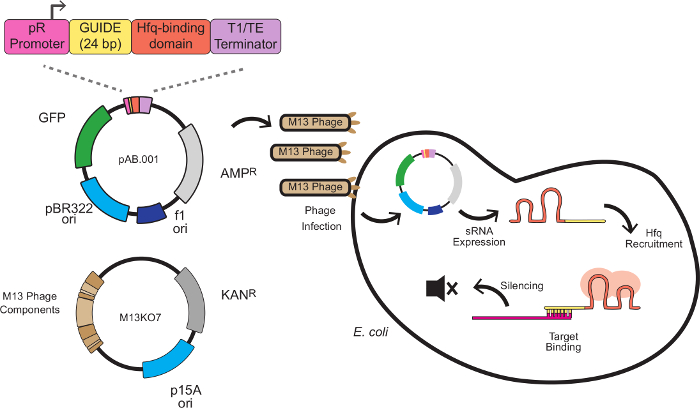
Figuur 1: Gene Silencing in E. coli met sRNA expressiecassettes Geleverd door M13 faag Het sRNA cassette bestaat uit 4 modules. PR promoter (een constitutieve promoter van bacteriofaag lambda), een 24 bp doeldomein, een HFQ bindingsdomein onttrokken MICC en een transcriptieterminator 8 E. coli uiting van de F pilus, waarbij sRNA expressie begint. De sRNA werft dan is de HFQ eiwit (afgebeeld in rood) en bindt een antisense mRNA doel in de buurt van het ribosoom bindingsplaats, wat resulteert in translationele repressie en mRNA degradatie. Klik hier om een grotere versie van deze figuur te bekijken.
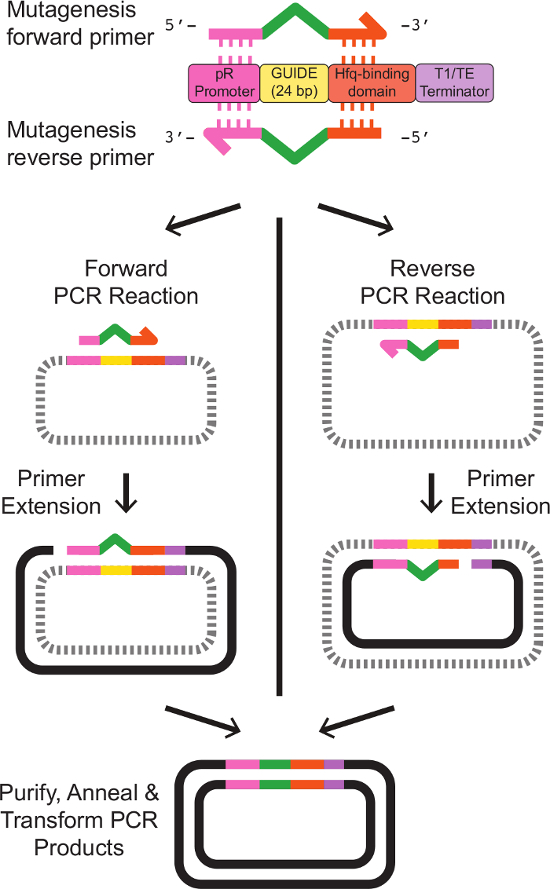
Figuur 2:. Primer ontwerp en plaatsgerichte mutagenese van de sRNAs doelplaats Twee primers worden ontworpen met gedeeltelijke homologie met een bestaande sRNA cassette. De voorwaartse primer omvat 20 bp homoloog aan de pR promoter aan het 5'-uiteinde, gevolgd door24 bp van het nieuwe Gidssequentie dan 18 bp homoloog aan de HFQ-bindingsdomein aan het 3 'uiteinde. De reverse primer is precies omgekeerde complement van de forward primer, met gebieden van homologie met de bestaande sRNA cassette flankeren het omgekeerde complement van de nieuwe GUIDE sequentie. Exacte primer sequenties worden in Tabel 3. Los één primer PCR reacties met de voorwaartse en omgekeerde primers produceren lineair, enkelstrengs DNA met de gewenste gemodificeerde sequentie. Het gloeien van de voorwaartse en achterwaartse reactieproducten, volgende clean-up, zoals beschreven in het protocol, resultaten in dubbelstrengs plasmide-DNA dat de gewenste gewijzigde sRNA cassette. Klik hier om een grotere versie van deze figuur te bekijken.
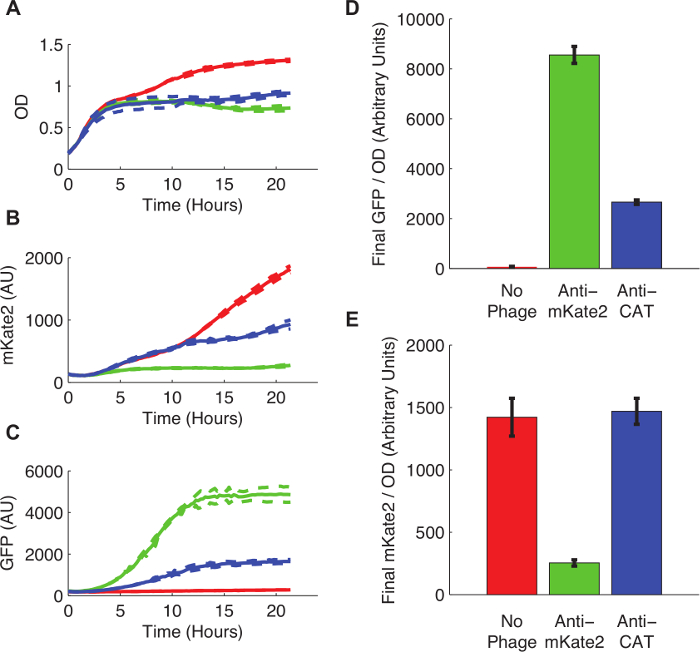
Figuur 3: Knockdown van een chromosomaal geïntegreerde mKate2 Fluorescent Reporter. E. coli K12 MG1655 expressie mKate2 werden onbehandeld gelaten (rode lijnen en staven), geïnfecteerd met een anti-mKate2 faagmide (groene lijnen en staven), of geïnfecteerd met een controle faagmide gericht CAT (blauwe lijnen en staven). (A) Onbehandelde E. coli groeide uit tot een hogere verzadiging dichtheden, wat wijst op een metabole kosten voor faag infectie. Stippellijnen geven standaardafwijkingen van 3 replicaten. (B) De mKate2 signaal werd verlaagd tot bijna achtergrondniveaus in de anti-mKate2 behandelde stam, maar niet in controle stammen. (C) GFP fluorescentie, eveneens gedragen door het faagmide, was alleen detecteerbaar in fagemide-behandelde controles. (D, E) Final fluorescentie metingen na 24 uur van de groei werden genormaliseerd tot OD. GFP signaal, waarbij faagmide infectie, waren afwezig in onbehandelde controles, maar ook aanzienlijk verminderd na anti-CAT phagemid behandeling. Dit kan off-target effecten van het faagmide te geven. De mKate2 signaal werd verminderd anti-mKate2 faagmide behandeling in vergelijking met onbehandelde controles. De CAT-gerichte controle faagmide toonde geen effect op mKate2 fluorescentie. Error bars vertegenwoordigt standaarddeviatie van 3 herhalingen. Klik hier om een grotere versie van deze figuur te bekijken.
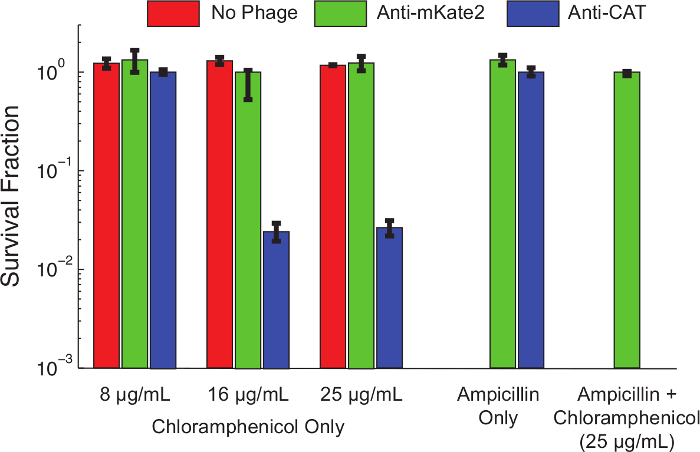
Figuur 4: Knockdown van CAT Herstelt Chloramphenicol Gevoeligheid voor een genetisch resistente E. Bevolking. coli K12 MG1655 expressie van een chromosomaal geïntegreerde CAT-gen werden onbehandeld (rode balken) links, die een controlebehandeling faagmide gericht mKate2 (groene balken), of behandeld met een faagmide tot expressie anti-CAT sRNA (blauwe staven). Na 1 uur van infectie, de levensvatbaarheid op de aangegeven antibiotics werd beoordeeld door seriële verdunningen en plateren. Stammen behandeld met anti-CAT faagmide werden gedood significant (> 90%) van chlooramfenicol bij hogere concentraties, terwijl controlebehandelingen niet beïnvloed. Toevoegen van ampicilline aan het kweekplaten selecteert positief voor faagmide infectie en elimineert ongeïnfecteerde cellen. Onder deze omstandigheden werden geen chlooramfenicol resistente kolonies waargenomen na anti-CAT behandeling. Dit geeft aan dat de meeste overlevenden vormen een falen van infectie in plaats van een falen van silencing. Fout balken geven de standaardafwijking van 3 herhalingen. Klik hier om een grotere versie van deze figuur te bekijken.
| CAT doelsequentie | 5 '- ATGGAGAAAAAAATCACTGGATAT - 3' |
| CAT GUIDE sequentie | 5 '- ATATCCAGTGATTTTTTTCTCCAT - 3' |
Tabel 1:. Een voorbeeld TARGET en GUIDE Sequence voor het CAT-gen Let op de omgekeerde complement relatie.
| pR promotor | TAACACCGTGCGTGTTGACTATTTTACCTCTGGCGGTGATAATGGTTGC | ||||
| GUIDE sequentie | ATATCCAGTGATTTTTTTCTCCAT | ||||
| HFQ bindend domein | TTTCTGTTGGGCCATTGCATTGCCACTGATTTTCCAACATATAAAAAGACAAGCCCGAACAGTCGTCCGGGCTTTTTT TCTCGAG | ||||
| T1 / TE terminator | CTCGAGCCAGGCATCAAATAAAACGAAAGGCTCAGTCGAAAGACTGGGCCTTTCGTTTTATCTGTTTTTGTCGGTGAA CGCTCTCTACTAGAGTCACACTGGCTCACCTTCGGGTGGGCCTTTCTGCGTTTATA | ||||
Tabel 2:. Sequentie Onderdelen van de cassette sRNAs Elke sequentie geschreven 5'-3 '. De volledige cassette is de aaneenschakeling van deze 4 elementen in orde en bestaat uit 292 bp.
| forward Primer | 5 '- CTGGCGGTGATAATGGTTGC [GUIDE] TTTCTGTTGGGCCATTGC - 3' |
| Reverse Primer | 5 '- GCAATGGCCCAACAGAAA [TARGET] GCAACCATTATCACCGCCAG - 3' |
Tabel 3: Primer ontwerp toe aan bestaande geleidingselementen Alter De voorwaartse primer bevat de laatste 20 bp van de promotor pR, de nieuwe GUIDE sequentie en de eerste 18 bp van het HFQ bindingsdomein.. De doelsequentie is precies het omgekeerde complement van het GUIDE reeks. Het omgekeerde primer is precies het omgekeerde complement van de forward primer.
Tabel 4: Aanbevolen Voorwaarden voor de single-Primer mutageen PCR.
| Stap | Temp | Tijd |
| initiële denaturatie | 98 ° C | 30 sec |
| 30 cycli | 98 ° C | 10 sec |
| 55 ° C | 30 sec | |
| 72 ° C | 120 sec | |
| laatste verlenging | 72 ° C | 300 sec |
| opslagruimte | 10 ° C |
Tabel 5: Aanbevolen Thermocycler Protocol voor de single-Primer mutageen PCR.
| bestanddeel | Volume |
| template-DNA | 1 pi |
| 10 uM voorwaartse primer | 0,5 pl |
| 10 uM reverse primer | 0,5 pl |
| Taq 2X Master Mix | 25 gl |
| Nuclease-vrij water | 23 ul |
| Totaal volume | 50 gl |
Tabel 6: Aanbevolen Voorwaarden voor de Sequence Verification PCR.
| Stap | Temp | Tijd |
| initiële denaturatie | 95 ° C | 30 sec |
| 30 cycli | 95 ° C | 30 sec |
| 55 ° C | 30 sec | |
| 68 ° C | 30 sec | |
| laatste verlenging | 68 ° C | 300 sec |
| opslagruimte | 10 ° C |
Tabel 7: Aanbevolen Thermocycler Proprotocol voor de Sequence Verification PCR.
De onderhavige werkwijze bereikt 80% reductie in mKate fluorescentie niveaus in vergelijking met niet-gerichte controles. Dit is in lijn met andere RNA knockdown methoden, waar de volledige silencing niet wordt nageleefd en 50-90% rendement is typisch 16,17. Op de fenotypische niveau-CAT gerichte knockdowns waren in staat om aanzienlijk verzwakken chlooramfenicol resistentie en te elimineren onder bepaalde omstandigheden.
De knock-down fenotype was detecteerbaar op populatieniveau na slechts een paar uur na infectie (Figuur 3B). Hieruit blijkt een belangrijk kenmerk van faag afgiftesysteem: hoge knockdown frequentie kan direct in batch kweek worden verkregen zonder voorafgaande genetische modificatie. In tegenstelling tot conventionele genetische modificaties met behulp van plasmide transformatie of genomische integratie, is faag infectie niet vereist dat een populatie opnieuw uitgegroeid van een enkele geïsoleerde kolonie. Hierdoor kan de effecten van faag infectie zijn explored in populaties met complexe ruimtelijke dynamiek 11, met reeds bestaande ruimtelijke structuren zoals biofilms 18, of bij genetisch gemengde natuurlijke populaties 19.
Een kritische stap in deze werkwijze is de productie van verpakte faagmide met hoge titer. De metabole last in verband met faagdeeltje productie kan leiden tot hoge prijzen van mutatie of plasmide verlies in de faagmide productie stam. Aanbevolen wordt het faagmide productiestam direct vanuit één gecotransformeerd kolonie gekweekt worden en niet gekoeld, bevroren of sub-gekweekt voorafgaand aan oogsten faag. Een lage efficiëntie van co-transformatie kan ook worden waargenomen bij de invoering van de faagmide en helper plasmide E. coli tegelijkertijd. In dit geval kunnen hogere rendementen verkregen door het transformeren van het helper plasmide, daarna bereiding van competente cellen met het helper plasmide voor daaropvolgende transformatie met de faagmide.
Phagemid infectie of sRNA expressie legt ook een detecteerbaar metabole belasting van de doelcellen en soms een aantal fenotypische verstoring. Zo werd een vermindering mKate2 fluorescentie zelfs waargenomen wanneer cellen werden geïnfecteerd met een fagemide gericht CAT (Figuur 3). Infectie met M13 wordt niet gedacht aan systemische stressreacties in E. triggeren coli 20, maar kan transcriptie indirect patronen veranderen. Als alternatief, kan de GFP of ampicillineresistentie merkers opgenomen in de faagmide strijden om cellulaire middelen, reducerende mKate2 expressie en 9 groei. Tenslotte kan de sRNA cassette zich globaal veranderen genexpressieprofielen door titratie van de HFQ eiwit of via off-target mRNA silencing. Naast zit treden vaak op in vivo RNAi gericht 21-23, maar ze moeten nog systematisch onderzocht worden voor dit systeem.
Een beperking van deze werkwijze is dat de infectie efficiëntie minder dan 100%, waardoor een aantal niet-geïnfecteerde bacteriën blijven in de populatie. De resultaten van dit werk en eerder werk 10 suggereren dat niet-geïnfecteerde cellen vertegenwoordigt 1-10% van de uiteindelijke populatie, en zijn verantwoordelijk voor het grootste deel van de nonsilenced fenotypes waargenomen. Een scala van mogelijkheden om M13-weerstand bekend, de meest voorkomende zijn mutatiepatronen verlies van pilus expressie 24. In het licht van deze beperkingen, moeten controles worden gebruikt om hoge tarieven infectie en knockdown efficiëntie te bevestigen.
Een andere potentiële beperking voor sommige toepassingen is de occasionele overdracht van verontreinigende helperfaag. Hoewel M13K07 een gemuteerd verpakkingssignaal bevat, kan worden verpakt in faag capside bij lage frequentie en naar geïnfecteerde populaties, wat resulteert in cellen die competent voor faagproductie en de verdere uitbreiding van faag na de eerste infectie evenement 25. Wijzigingen aan de helperfaag het doeltreffend geblekenvermindering van niet-specifieke verpakking, hoewel soms ten koste van verminderde faagproductie 26.
Engineered bacteriofaag zijn een onmisbaar instrument voor E. geworden coli synthetische biologie, waardoor snelle levering van nieuwe genen voor een groeiende bevolking. Recent werk heeft intercellulaire communicatie circuits 11 geproduceerd of uitgedrukt transcriptiefactoren tot resistentie tegen antibiotica onderdrukken trajecten 27. Het protocol hier gepresenteerde draagt bij aan een groeiende verzameling tools die de controle van bacteriële fysiologie door middel van geprogrammeerde RNA's mogelijk te maken. CRISPR Cas-nucleasen, wanneer gemuteerd nuclease activiteit te elimineren, is aangetoond dat transcriptie onderdrukken bij-RNA geleide gen targets 17,28. In tegenstelling sRNA silencing werkt op het translationele niveau en heeft geen exogeen eiwit expressie vereisen. Next-generation biotechnologie kan transcriptionele en translationele controle te verenigen met faag gemedieerde levering aan complexe fenotype programmerentypes in real time.
The authors have nothing to disclose.
De financiering voor dit werk werd geleverd door de Fondation Bettencourt Schueller ter ondersteuning van de Parijse Bettencourt iGEM team. Wij danken de INSERM U1001 onderzoekseenheid en Chantal Lotton voor technische bijstand en advies. Faagmide Litmus28i_J23115-B0032-GFP werd verstrekt door Monica Ortiz en Drew Endy van Stanford.
| Name | Company | Catalog Number | Comments |
| Plasmid Miniprep Kit | Qiagen | 27104 | |
| DpnI Enzyme | NEB | R0176S | |
| Phusion High Fidelity Polymerase | NEB | M0530S | |
| Taq 2x Master Mix | NEB | M0270L | |
| M13KO7 Helper Phage | NEB | N0315S | |
| DH5α Competent Cells | Life Technologies | 18265-017 | |
| TOP10F' Cells | Life Technologies | C3030-03 | |
| LB Broth | Sigma | L3022-250G | |
| Ampicillin | Sigma | A9393-5G | |
| Kanamycin | Sigma | 60615-5G | |
| Chloramphenicol | Sigma | C0378-5G | |
| Tetracycline | Sigma | 87128-25G |
- Ohkumo, T., Masutani, C., Eki, T., Hanaoka, F. Use of RNAi in C. elegans. RNAi. , 129-137 (2008).
- Fire, A., Xu, S., Montgomery, M. K., Kostas, S. A., Driver, S. E., Mello, C. C. Potent and specific genetic interference by double-stranded RNA in Caenorhabditis elegans. Nature. 391 (6669), 806-811 (1998).
- Iordanou, E., Chandran, R. R., Blackstone, N., Jiang, L. RNAi interference by dsRNA injection into Drosophila embryos. J Vis Exp. (50), e2477 (2011).
- Ramadan, N., Flockhart, I., Booker, M., Perrimon, N., Mathey-Prevot, B. Design and implementation of high-throughput RNAi screens in cultured Drosophila cells. Nat Protoc. 2 (9), 2245-2264 (2007).
- Tsong, T. Y. Electroporation of cell membranes. Biophys J. 60 (2), 297-306 (1991).
- Kim, W. J., Chang, C. -. W., Lee, M., Kim, S. W. Efficient siRNA delivery using water soluble lipopolymer for anti-angiogenic gene therapy. J Control Release. 118 (3), 357-363 (2007).
- Shi, Y. Mammalian RNAi for the masses. Trends Genet. 19 (1), 9-12 (2003).
- Na, D., Yoo, S. M., Chung, H., Park, H., Park, J. H., Lee, S. Y. Metabolic engineering of Escherichia coli using synthetic small regulatory RNAs. Nat Biotechnol. 31 (2), 170-174 (2013).
- Ceroni, F., Algar, R., Stan, G. -. B., Ellis, T. Quantifying cellular capacity identifies gene expression designs with reduced burden. Nat Methods. 12 (5), 415-418 (2015).
- Libis, V. K., Bernheim, A. G., et al. Silencing of Antibiotic Resistance in E. coli with Engineered Phage Bearing Small Regulatory RNAs. ACS Synth Biol. 3 (12), 1003-1006 (2014).
- Ortiz, M. E., Endy, D. Engineered cell-cell communication via DNA messaging. J Biol Eng. 6 (1), 16 (2012).
- Edelheit, O., Hanukoglu, A., Hanukoglu, I. Simple and efficient site-directed mutagenesis using two single-primer reactions in parallel to generate mutants for protein structure-function studies. BMC Biotechnol. 9 (1), 61 (2009).
- Chung, C. T., Miller, R. H. Preparation and storage of competent Escherichia coli cells. Recombinant DNA Part I. , 621-627 (1993).
- Phornphisutthimas, S., Thamchaipenet, A., Panijpan, B. Conjugation in Escherichia coli. Biochem Mol Biol Educ. 35 (6), 440-445 (2007).
- Sezonov, G., Joseleau-Petit, D., D'Ari, R. Escherichia coli Physiology in Luria-Bertani Broth. J Bacteriol. 189 (23), 8746-8749 (2007).
- Mittal, V. Improving the efficiency of RNA interference in mammals. Nat Rev Genet. 5 (5), 355-365 (2004).
- Qi, L. S., Larson, M. H., et al. Repurposing CRISPR as an RNA-guided platform for sequence-specific control of gene expression. Cell. 152 (5), 1173-1183 (2013).
- Lu, T. K., Collins, J. J. Dispersing biofilms with engineered enzymatic bacteriophage. Proc Natl Acad Sci USA. 104 (27), 11197-11202 (2007).
- Yosef, I., Manor, M., Kiro, R., Qimron, U. Temperate and lytic bacteriophages programmed to sensitize and kill antibiotic-resistant bacteria. Proc Natl Acad Sci USA. 112 (23), 7267-7272 (2015).
- Karlsson, F., Malmborg-Hager, A. -. C., Albrekt, A. -. S., Borrebaeck, C. A. K. Genome-wide comparison of phage M13-infected vs. uninfected Escherichia coli. Can J Microbiol. 51 (1), 29-35 (2005).
- Senthil-Kumar, M., Mysore, K. S. Caveat of RNAi in plants: the off-target effect. Methods in molecular biology. 744, 13-25 (2011).
- Jackson, A. L., Linsley, P. S. Recognizing and avoiding siRNA off-target effects for target identification and therapeutic application. Nat Rev Drug Discov. 9 (1), 57-67 (2010).
- Cho, S. W., Kim, S., et al. Analysis of off-target effects of CRISPR/Cas-derived RNA-guided endonucleases and nickases. Genome Res. 24 (1), 132-141 (2014).
- Hagens, S., Blasi, U. Genetically modified filamentous phage as bactericidal agents: a pilot study. Lett Appl Microbiol. 37 (4), 318-323 (2003).
- Kasman, L. M., Kasman, A., Westwater, C., Dolan, J., Schmidt, M. G., Norris, J. S. Overcoming the phage replication threshold: a mathematical model with implications for phage therapy. J Virol. 76 (11), 5557-5564 (2002).
- Chasteen, L., Ayriss, J., Pavlik, P., Bradbury, A. R. M. Eliminating helper phage from phage display. Nucleic Acids Res. 34 (21), e145 (2006).
- Lu, T. K., Collins, J. J. Engineered bacteriophage targeting gene networks as adjuvants for antibiotic therapy. Proc Natl Acad Sci USA. 106 (12), 4629-4634 (2009).
- Bikard, D., Jiang, W., Samai, P., Hochschild, A., Zhang, F., Marraffini, L. A. Programmable repression and activation of bacterial gene expression using an engineered CRISPR-Cas system. Nucleic Acids Res. 41 (15), 7429-7437 (2013).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved