Summary
Abstract
Introduction
Protocol
Representative Results
Discussion
Acknowledgements
Materials
References
Immunology and Infection
Analyse av somatisk hypermutasjon i JH4-intronet til Germinal Center B-celler fra Mouse Peyer's Patches
Presentert her er en analyse for å kvantifisere somatisk hypermutasjon i immunglobulin tungt kjede gen locus ved hjelp av germinal senter B celler fra musen Peyers flekker.
Innenfor de germinale sentrene av lymfoide organer endrer modne B-celler deres uttrykte immunglobulin (Ig) ved å introdusere ikke-templaterte mutasjoner i de variable kodingseksonene til Ig heavy and light chain gene loci. Denne prosessen med somatisk hypermutasjon (SHM) krever enzymet aktiveringsindusert cytidin deaminase (AID), som konverterer deoksycytidiner (C), til deoksyuridiner (U). Behandling av AID-genererte U:G-uoverensstemmelser i mutasjoner av de grunnleggende eksisjons- og mismatchreparasjonsveiene introduserer nye Ig-kodesekvenser som kan gi en høyere affinitet iG. Mutasjoner i AID- eller DNA-reparasjonsgener kan blokkere eller endre mutasjonstypene som observeres i Ig loci betydelig. Vi beskriver en protokoll for å kvantifisere JH4 intronmutasjoner som bruker fluorescensaktivert cellesortering (FACS), PCR og Sanger-sekvensering. Selv om denne analysen ikke direkte måler Ig affinitetsmodning, indikerer den mutasjoner i Ig-variable kodesekvenser. I tillegg bruker disse metodene vanlige molekylærbiologiske teknikker som analyserer mutasjoner i Ig-sekvenser av flere B-cellekloner. Dermed er denne analysen et uvurderlig verktøy i studiet av SHM og Ig diversifisering.
B-celler, medlemmer av det adaptive immunsystemet, gjenkjenner og eliminerer antigener ved å produsere antistoffer, også kjent som immunglobuliner (Ig). Hver Ig består av to tunge (IgH) og to lette (IgL) kjedepolypeptider, som holdes sammen av disulfidbindinger for å danne den karakteristiske "Y" formstrukturen til Ig1. N-termini av IgH og IgL utgjør variabelen (V) regionen av hvert polypeptid og sammen danner de antigenbindingsstedet til Ig, mens den konstante regionen IgH gir effektorfunksjonen til Ig. Utvikling av B-celler i benmargen omorganiserer V-kodeeksonene til IgH og IgL i en prosess kjent som V(D)J rekombinasjon2,3,4. Transkripsjon av de rekombinerte V-eksonene, kombinert med de respektive konstante region exons, danner mRNA som er oversatt til Ig.
Eldre B-celler som uttrykker en membranbundet Ig, også kjent som en B-cellereseptor (BCR), sirkulerer til sekundære lymfoide organer, for eksempel milten, lymfeknuten eller Peyers flekker, hvor de kartlegger miljøet for antigener og samhandler med andre celler i immunsystemet1. Innenfor germinalsentrene (GC) av sekundære lymfoide organer blir B-celler som gjenkjenner antigen gjennom BCR aktivert. Støttet av follikulære dendrittiske celler og follikulære hjelper T-celler, kan aktiverte B-celler deretter spre seg og skille seg ut i plasma- og minneceller, som er viktige effektorer av en robust immunrespons5,6,7,8,9. I tillegg kan disse aktiverte B-cellene gjennomgå sekundære Ig-gendiversifiseringsprosesser - klassebryterrekombinasjon (CSR) og somatisk hypermutasjon (SHM). Under CSR utveksler B-celler standard μ konstant region i IgH-polypeptidet med et annet konstant område (γ, α, ε) gjennom en DNA-slette-rekombinasjonsreaksjon (figur 1). Dette gjør det mulig å uttrykke en annen konstant exon og oversettelse av en ny Ig. B-cellen bytter fra å uttrykke IgM til en annen isotype (IgG, IgA, IgE). CSR endrer effektorfunksjonen til Ig uten å endre dens antigenspektifisitet10,11,12. Under SHM muterer imidlertid B-celler V-kodeområdene IgH og IgL for å muliggjøre produksjon og valg av høyere affinitets-Igs, noe som mer effektivt kan eliminere et antigen13,14,15 ( figur1). Det er viktig at både CSR og SHM er avhengige av funksjonen til ett enzym: aktiveringsindusert cytidindeaminase (AID)16,17,18. Mennesker og mus mangelfull i AID kan ikke fullføre CSR eller SHM og presentere med forhøyede IgM serumtitler eller Hyper-IgM17,19.
I CSR deaminerer AID deoksycytidiner (C) i de repeterende bryterområdene som kommer før hver konstante kodeeksoner, og konverterer dem til deoksyuridiner (U)20,21, som skaper uovertruffen baseparing mellom deoksyuridiner og deoksyguanosiner (U:G). Disse U:G-uoverensstemmelsene konverteres til dobbeltstrengede DNA-pauser, som kreves for DNA-rekombinasjon, enten ved base excision repair (BER) eller mismatch repair (MMR) pathway22,23,24,25,26,27,28,29. I SHM deaminerer AID C i V-kodeeksonene. Replikasjon på tvers av U:G-uoverensstemmelsen genererer C:G til T:A-overgangsmutasjoner, mens fjerning av uracil-basen av BER-proteinet, uracil DNA glykosylase (UNG), før DNA-replikasjon produserer både overgangs- og transversjonsmutasjoner16. Nullmutasjoner i UNG øker C:G til T:A-overgangsmutasjoner21,22. I likhet med CSR krever SHM de komplementære rollene til MMR og BER. Under SHM genererer MMR mutasjoner ved A:T-basispar. Aktivering av mutasjoner i MutS-homologi 2 (MSH2) eller DNA-polymerase η (Polη) reduserer mutasjoner betydelig ved A:T-baser og sammensatte mutasjoner i MSH2 og Polη avskaffer nesten mutasjoner ved A:T-baser21,30,31. I samsvar med den kritiske rollen ber og MMR har i konverteringen av AID-generert U til overgangs- eller transversjonsmutasjoner, viser musene som mangler for både MSH2 og UNG (MSH2-/-UNG-/-) bare C:G til T:A-overgangsmutasjoner som følge av replikering på tvers av U:G-konflikten21.
Analysen av SHM i V-koderegioner forblir komplisert fordi utvikling av B-celler kan rekombinere noen av V (D)J-kodeeksonene i IgH og IgL loci1,2,4. Nøyaktig analyse av disse unikt rekombinerte og somatisk muterte V-områdene krever identifisering og isolering av kloner av B-celler eller Ig mRNA11,13. JH4 intron, som er 3 ' av den siste J-koding exon i IgH locus, havner somatiske mutasjoner på grunn av spredning av mutasjoner 3' av V-promotoren32,33,34 og brukes derfor ofte som surrogatmarkør for SHM i V-regioner31,35 ( Figur1). For å eksperimentelt belyse hvordan spesifikke gener eller genetiske mutasjoner endrer SHM-mønstre eller -rater, kan JH4-intronen sekvenseres fra Peyers patcher (PP) germinalsenter B-celler (GCBCer), som gjennomgår høye hastigheter på SHM36,37,38. GCBCer kan lett identifiseres og isoleres med fluorescerende konjugerte antistoffer mot celleoverflatemarkører (B220+PNAHI)17,39.
En detaljert protokoll presenteres for å karakterisere JH4-intronmutasjoner i PP GCBCer fra mus ved hjelp av en kombinasjon av FACS (fluorescensaktivert cellesortering), PCR- og Sanger-sekvensering (figur 2).
Alle mutante mus ble opprettholdt på en C57BL/6-bakgrunn. Alderstilpassede (2-5 måneder gamle) mannlige og kvinnelige mus ble brukt til alle eksperimenter. Husdyrhold og eksperimenter med mus ble utført i henhold til protokoller godkjent av The City College of New York Institutional Animal Care and Use Committee.
1. Disseksjon av Peyers
- Euthanize musen med 100% CO2 på 3 L / min i 5 min etterfulgt av Cervical dislocation for å bekrefte døden. Steriliser disseksjonsverktøy (saks, tang, fine tang) og hanskede hender med 70% etanol.
- Legg musen på disseksjonsmatten med magen utsatt. Sjenerøst spray musens kropp med 70% etanol før du gjør noen snitt for å sterilisere disseksjonsområdet.
- Lag et snitt i huden over magen og fjern huden fra magen ved å trekke samtidig på begge sider av snittet mot hodet og halen ved hjelp av tang (eller steriliserte, hanskede hender).
- Fest for- og bakre lemmer av musen.
- Klipp bukhulen med saks for å eksponere de indre organene.
- Finn tynntarmen mellom magen og caecum ("J" formet struktur nær tykktarmen). Fjern tynntarmen ved å kutte under magen og over caecum.
- Fjern eventuelt bindevev og fett som forbinder tynntarmens folder sammen.
MERK: Fett vil ha en særegen hvit farge, i motsetning til tynntarmens rosa farge. - Undersøk den ytre overflaten av tynntarmen for Peyers flekker (PPs), som er små (~ 1 mm), ovalformede strukturer som ser hvite ut under et tynt lag med gjennomsiktige epitelceller.
- Utskill forsiktig alle synlige PP med saks.
MERK: En WT-mus (C57BL/6 wild-type) kan gi 4-8 PPer, mens en AID-/- mus har 6-10 PPs. - Samle PPs i et 1,5 ml mikrosenterrør som inneholder 1 ml FACS-buffer på is.
MERK: PP skal synke, mens fett vil flyte til overflaten og kan fjernes.
2. Celleisolasjon for FACS
- Legg et 40 μm filter i en 6-brønns tallerken med 1 ml kald (4 °C) FACS-buffer.
- Hell PPs fra 1,5 ml-røret på filteret.
- Vask PPs med 1 ml kald FACS-buffer, og sørg for at de alltid er i væske og på is.
- Bruk den flate enden av stempelet fra en 1 ml sprøyte som en pestle for å knuse PPs på filteret til bare bindevev forblir på filteret.
- Vask filteret og stempelet med 1 ml kald FACS-buffer for å slippe cellene inn i 6-brønnsfatet.
- Samle ~4 ml celler i kald FACS buffer og filtrer dem gjennom en 40 μm sil cap FACS rør.
- Vask silhetten med 1 ml kald FACS-buffer.
- Pellet cellene ved 600 x g ved 4 °C i 5 minutter i en svingende bøtte sentrifuge.
- Dekanter supernatanten.
- Resuspend cellene i 0,4 ml kald FACS buffer.
- Fjern 10 μL for celletelling for å bekrefte avkastningen (forvent ~5 x 106 celler/mus, se figur 3A)
- Filtrer de resterende cellene gjennom en 40 μm silhette i et FACS-rør og fortsett å fargelegge for FACS.
3. Farging av GCBCer for FACS
- Tilsett 1 μL Fc blokk (umerket antimus CD16/CD32) til 400 μL celle suspensjon og plasser cellene på is i 15 min.
- Tilsett 2 ml kald FACS-buffer for å vaske cellene.
- Pelletsceller ved 600 x g ved 4 °C i 5 minutter og kast supernatanten.
- Resuspend cellene i 80 μL kald FACS buffer.
- Fjern 10 μL celler fra WT PP for hver fargekontroll (totalt 4, inkludert 3 enkelt flekkkontroller og 1 ubegrenset kontroll). La det være 40 μL av WT PP for neste trinn. Alternativt kan du bruke kompensasjonsperler for fargingskontrollene.
- Flekk hver av de eksperimentelle prøvene (f.eks. WT og AID-/-) i 500 μL kald FACS-buffer med 2,5 μL peanøtt agglutinin (PNA)-biotin i 15 min på is.
- Tilsett 2 ml kald FACS-buffer for å vaske cellene.
- Pelletsceller ved 600 x g ved 4 °C i 5 minutter og kast supernatanten.
- Flekk hver eksperimentell prøve med 500 μL av cocktailen i mørket, på is, i 15 min (tabell 1). Forsikre deg om at cellene er helt resuspendert i fargecocktailen.
- Klargjør enkle flekkkontroller for kompensasjonsmatrisen.
- Flekk cellene i 500 μL kald FACS-buffer ved hjelp av fortynningene som er angitt i tabell 2.
- Inkuber fargekontrollene i mørket, på is, i 15 min.
- Tilsett 2 ml kald FACS-buffer til alle rørene i trinn 3.7 og 3.8, pellet cellene, og kast supernatanten for å vaske av ubundne antistoffer eller DAPI.
- Resuspend cellene i 500 μL kald FACS buffer og plasser på is.
- Bruk en cellesortering til å samle B220+PNAHI fra hver fargede eksperimentelle prøve. Figur 3B viser de typiske prosentandelene av B220+ PNAHI hentet fra WT og AID-/- PPs. Figur 3C viser FACS-gatingstrategien.
4. DNA-ekstraksjon fra GCBCer
- Pellet sorterte celler ved 600 x g ved 4 °C i 5 minutter og kaster supernatanten.
- Resuspend cellene i 1 ml kald FACS buffer og overføre cellene til en 1,5 ml mikrocentrifuge rør.
- Pellet cellene ved 600 x g ved 4 °C i 5 minutter og kast supernatanten.
- Resuspend cellene i 500 μL DNA-ekstraksjonsbuffer og 5 μL av 20 mg / ml proteinase K.
- Inkuber ved 56 °C over natten.
- Utfell DNA med 500 μL isopropanol og 1 μL 20 mg/ml glykogen. Bland røret grundig ved å invertere 5-6x.
- Inkuber ved romtemperatur i 10 min.
- Sentrifuge i en mikrocentrifuge i 15 min ved 25 °C ved 21 000 x g.
- Kast supernatanten og behold pelletsen, som inneholder det utfelte DNA-et og glykogenet.
- Vask DNA-pelletsen med 1 ml 70% etanol.
- Pellet DNA i en mikrocentrifuge i 10 min ved 25 °C ved 21 000 x g.
- Fjern 70% etanol og lufttørk DNA-pelletsen i 5-10 min.
MERK: Unngå overtørking, da DNA-et kanskje ikke rehydreres fullstendig.
- Resuspend DNA i 30 μL TE buffer og inkubere over natten ved 56 °C.
5. JH4 intron sekvensforsterkning og analyse
- Kvantifisere DNA ved å måle absorbansen ved en bølgelengde på 260 nm (A260).
MERK: Den typiske konsentrasjonen av DNA gjenvunnet fra sortert B220+PNAHI GCBCs av en C57BL / 6 mus er 20-40 ng / μL. - Utfør nestet PCR for JH4 intron (Tabell 3, Tabell 4). Normaliser den totale mengden genomisk DNA som brukes i den første PCR til den minst konsentrerte prøven. (f.eks. hvis den minst konsentrerte prøven er 5 ng/μL, bruk 58,75 ng DNA for alle prøvene i maksimalt vannvolum (11,75 μL) i PCR-#1).
- Løs PCR-produktet på en 1,5% agarose gel ved 200 V i 20 min. Forventet amplikonstørrelse er 580 bp.
- Slukk amplikonen fra gelen og trekk ut DNA-et ved hjelp av et gelekstraksjonssett i henhold til produsentens instruksjoner (se supplerende figur 1).
- Elute DNA med 30 μL vann og kvantifisere mengden DNA ved å måle A260.
MERK: Den typiske konsentrasjonen av det rensede PCR-produktet er 3-10 ng / μL.
- Elute DNA med 30 μL vann og kvantifisere mengden DNA ved å måle A260.
- Ligat det rensede PCR-produktet i en plasmid med stumpe ender. Standardiser den totale mengden PCR-produkt som brukes i hver ligationreaksjon (Tabell 5).
- Inkuber ligasjonsreaksjonen ved romtemperatur i 5 minutter eller over natten ved 16 °C.
- Transformer elektrokompetente bakterieceller med 2 μL av ligasjonsreaksjonen.
- Elektroporate ved 1,65 kV.
- Redning i 600 μL SOC-medier i 1 time ved 37 °C i en ristende inkubator ved 225 o/min.
- Plate 100 μL av transformerte bakterier på LB supplert med ampicillin (100 μg/ml) agarplater og inkuber over natten ved 37 °C.
- Send inn platen med bakteriekolonier for Sanger-sekvensering ved hjelp av T7 fremoverprimer. Alternativt kan du vokse nattkulturer i hver bakteriekoloni og utføre en plasmid rensing.
- Gjenta om nødvendig PCR, ligation og/eller transformasjon for å optimalisere utbyttet av bakteriekolonier
MERK: Minst 30 kolonier bør plukkes fra hver plate.
- Gjenta om nødvendig PCR, ligation og/eller transformasjon for å optimalisere utbyttet av bakteriekolonier
- Standardisere sekvensdataene i de .txt filene
- Slett plasmidsekvensen.
- Sørg for at hver sekvens er orientert 5 til 3' i henhold til JH4 intron referansesekvens (NG_005838). Generer det omvendte komplementet til en hvilken som helst sekvens etter behov.
- Juster sekvensene som er oppnådd for hver PCR, i forhold til JH4-intronreferansesekvensen (NG_005838) ved hjelp av en ClustalOmega-programvare ( figur 4A).
- Identifisere forskjeller fra referansesekvensen som mutasjoner
- Kontroller at alle mutasjoner er sanne punktmutasjoner ved å undersøke elektroferogrammet til Sanger-sekvenseringen. Gjenta sekvenseringen om nødvendig. (Figur 4B,C).
- Tabulere og kvantifisere unike mutasjoner i JH4-intronet for hver genotype (figur 5).
- Telle sekvenser med identiske mutasjoner bare én gang
MERK: Det er ikke mulig å avgjøre om de identiske sekvensene ble generert under PCR eller identiske SHM-hendelser i forskjellige B-celler. - Tell alle forekomster av WT-germline JH4 intronsekvenser (dvs. de uten mutasjoner) som en unik sekvens.
- Telle sekvenser med identiske mutasjoner bare én gang
Flowcytometri
Eldre B-celler sirkulerer til germinale sentre der de gjennomgår affinitetsmodning, klonisk ekspansjon og differensiering i plasma- eller minneceller40,41,42,43,44. Disse GCBCene kan identifiseres av mange celleoverflatemarkører, inkludert høyt uttrykk for CD45R/B220-reseptoren og binding av peanøtt agglutinin (PNA)45,46. For å isolere aktiverte GCBCer ble PP-celler farget med anti-B220 antistoffer konjugert til phycoerythrin (PE) og biotinylert-PNA, etterfulgt av streptavidin konjugert til APC-eFluor780. Døde celler ble eliminert ved hjelp av fluorescerende 4',6-Diamidino-2-Phenylindole (DAPI) fargestoff, som flekker nukleinsyren av døende eller døde celler47,48. De fargede cellene ble deretter analysert og sortert via strømningscytometri. PPs besto av ~ 80% B220+ celler49,50. WT PPer inneholder i gjennomsnitt 4 x 106 celler per mus (figur 3A). Omtrent 8 % av WT PP-cellene var B220+PNAHI, som er halvparten av antallet som ble observert i AID-/ - ( figur3B). Dermed ble 0,3-0,6 x 106 B220+PNAHI GCBC oppnådd etter sortering, som var tilstrekkelig til å analysere mutasjoner i JH4-intronet.
JH4 Sekvensanalyse
JH4 intron ble forsterket av en nestet PCR ved hjelp av vanlige VHJ558-familieprimere (J558FR3Fw og VHJ558.2) etterfulgt av JH4 intron som spenner over primere VHJ558.3 og VHJ558.435,37. Av de 105 unike sekvensene hentet fra WT GCBCer ble det funnet totalt 226 mutasjoner (figur 5A). Analyse av GCBC-mutasjonsspekteret i WT-musene viste en rekke overganger og transversjoner med en hastighet på 4 x10 -3 mutasjoner / bp, som ble beregnet ved å dele det totale antallet muterte baser med det totale antall baser som ble sekvensert32,36,37,38. I tillegg inneholdt hvert JH4 PCR-produkt fra WT GCBCer 1-25 mutasjoner (figur 5B), der flere mutasjoner ofte ble funnet på en sekvens33,36. Bare to mutasjoner ble identifisert i 113 AID-/- sekvenser (figur 5A). AID-/- B-celler viste 1,66 x 10-5 mutasjoner/bp, som var signifikant lavere enn WT B-celler (p <0,05)36 og sammenligner med feilfrekvensen for polymerase med høy gjengivelse (5,3 x 10-7 sub/base/dobling)51,52. Dermed fungerte AID-/- B-celler som en nyttig negativ kontroll for denne analysen.
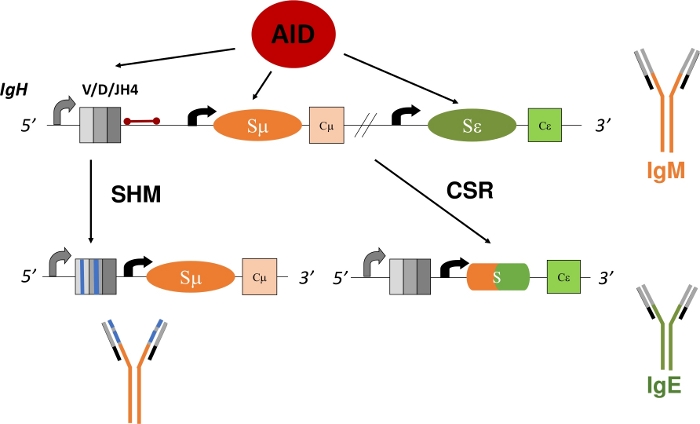
Figur 1: Skjematisk for IgH-genet locus og regionene målrettet av AID under CSR og SHM. Den røde linjen indikerer 580 bp JH4-intronen som er 3' av VDJH4-omorganiseringer og analyseres i denne protokollen. I CSR fremmer AID-avhengig deaminering av introniske bryterregioner (Sμ og Sε) DSB-dannelse som muliggjør sletting av rekombinasjon og uttrykk for en ny antistoffisotype (IgM til IgE). Under SHM akkumulerer V-regioner (grå bokser) mutasjoner (blå linjer) som kan føre til høyere affinitet Ig. Klikk her for å se en større versjon av denne figuren.
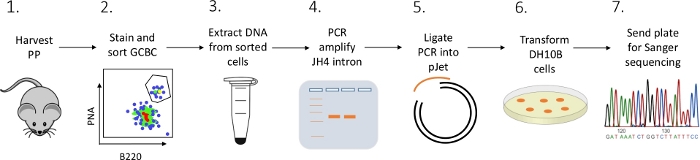
Figur 2: Arbeidsflyt for å analysere SHM for JH4-intronet i GCBCer isolert fra PPs. Klikk her for å se en større versjon av denne figuren.
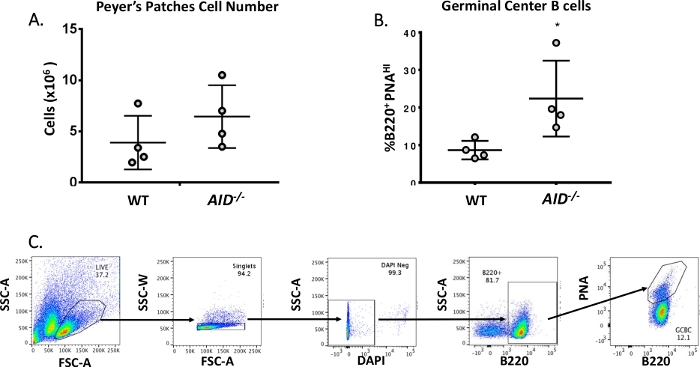
Figur 3: Karakterisering av PP GCBCer. (A) Totalt antall PP-celler fra WT- og AID-/- mus (n = 4 per genotype). Feilfelt representerer standardavvik fra gjennomsnittet. (B) Prosentandel av B220+PNAHI GCBCer hentet fra PPer for WT og AID-/- mus (n = 4 per genotype)36. Feilfelt representerer standardavvik fra gjennomsnittet* p<0,05 ved hjelp av elevens t-test. (C) Representative FACS-plott for å sortere B220+PNAHI GCBCer fra PPs. Klikk her for å se en større versjon av denne figuren.
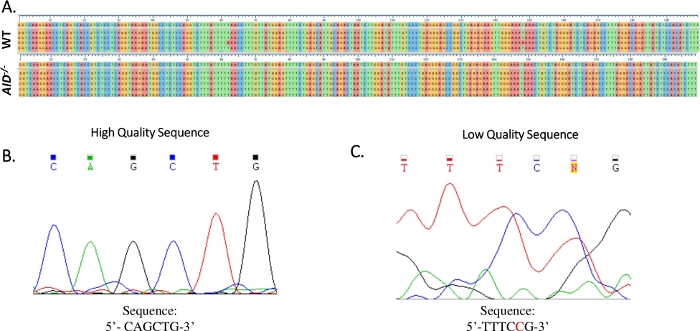
Figur 4: Analyse av JH4 Sanger-sekvensdata. (A) Eksempel på sekvensjusteringer av Sanger-sekvensdata for JH4 PCR-produktet fra WT (øverst) og AID-/- (nederst) GCBCer til referansegenomsekvensen (NG_005838), som er sekvensen rett under de nummererte aksemerkene. Justeringer ble generert ved hjelp av Clustal Omega. (B) Elektropherogram av høykvalitets Sanger sekvensdata, som viste distinkte topper for hver base. (C) Elektropherogram av sekvensdata av lav kvalitet, som viste tvetydige topper og uspesifiserte baser (N). Nukleotidet som vises i rødt, må kommenteres manuelt i sekvenstekstfilen. Klikk her for å se en større versjon av denne figuren.
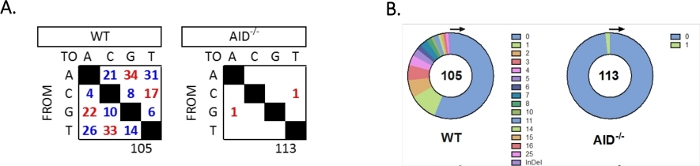
Figur 5: Analyse av mutasjoner i JH4-intronet i WT og AID-/- GCBC. (A) Det totale antallet overgangsmutasjoner (røde) og transversjonsmutasjoner (blå) ved A-, C-, G- og T-baser for hver genotype summeres i tabellene. Det totale antallet sekvenser som analyseres, er angitt under tabellen. (B) Antall mutasjoner per PCR-amplikon for hver genotype er avbildet i sektordiagrammene. Denne figuren er endret fra Choi et al.36 Copyright 2020. The American Association of Immunologists, Inc. Klikk her for å se en større versjon av denne figuren.
| Fargecocktail for GCBC | Volum: 500 μL | ||
| Antistoff eller fargestoff | Fluorofor | Fortynning | μL |
| B220 | Pe | 1000 | 0.5 |
| Streptavidin | APC-eFluor780 | 500 | 1 |
| DAPI | N/a | 500 | 1 |
Tabell 1: Fargecocktailer for GCBC. Cocktail av de angitte antistoffene eller fargestoffet (indikert i kursiv) ved de angitte fortynningene ble brukt til å flekke PP-celler i 500 μL for strømningscytometri.
| Enkeltflekker for kompensasjon | Volum: 500 μL | ||
| Antistoff eller fargestoff | Fluorofor | Fortynning | μL |
| B220 | Pe | 1000 | 0.5 |
| B220 | APC-eFluor780 | 750 | 0.67 |
| DAPI | N/a | 500 | 1 |
Tabell 2: Enkelt flekkkontroller for kompensasjon. B220 antistoffer konjugert til de angitte fluoroforene ble brukt til enkelt flekkkontroller for å kompensere for spektral overlapping.
| PCR-#1 | ||||
| Reagent | Volum | Termosirkuleringsforhold | ||
| 5x buffer | 4 μL | 1 | 95 °C | 3 min |
| 10 mM dNTP | 2 μL | 2 | 94 °C | 30 sek |
| 10 μM J558FR3Fw | 1 μL | 3 | 55 °C | 30 sek |
| 10 μM VHJ558,2 | 1 μL | 4 | 72 °C | 1 minutt og 30 min |
| DNA-polymerase med høy gjengivelse | 0,25 μL | Syklus 2-4 9x | ||
| Dna | x (standardiser til minst konsentrert utvalg) | |||
| H2O | til 20 μL | 5 | 72 °C | 5 min |
| Fortynn PCR-produktet 1:5 i H2O før du går videre til PCR-#2 | ||||
Tabell 3: Nestet PCR for JH4-intronen. PCR-komponenter og termosyklerforhold for den første forsterkningsreaksjonen. Fortynn det første PCR-produktet 1:5 med vann og bruk 1 μL av denne fortynning for den andre PCR.
| PCR-#2 | ||||
| Reagent | Volum | Termosirkuleringsbetingelser #2 | ||
| 5x buffer | 4 μL | 1 | 94 °C | 3 min |
| 10 mM dNTP | 2 μL | 2 | 94 °C | 30 sek |
| 10 μM VHJ558,3 | 1 μL | 3 | 55 °C | 30 sek |
| 10 μM VHJ558,4 | 1 μL | 4 | 72 °C | 30 sek |
| DNA-polymerase med høy gjengivelse | 0,25 μL | Syklus 2-4 21x | ||
| Fortynnet PCR # 1 | 1 μL | |||
| H2O | til 20 μL | 5 | 72 °C | 5 min |
Tabell 4: PCR-komponenter og termosirkuleringsforhold for den andre PCR.
| Reagent | Volum |
| 2x buffer | 10 μL |
| Renset PCR | x (standardiser til minst konsentrert utvalg) |
| Plasmid med stumpe ender | 1 μL |
| T4 DNA-ligase | 1 μL |
| H2O | til 20 μL |
| Inkuber på romtemperatur i 5 min eller over natten ved 16ºC | |
Tabell 5: Ligasjonsreaksjon. Komponenter for ligasjon av renset JH4 intron PCR produkt inn i plasmid.
| FACS-buffer |
| Varm opp FBS ved 56 °C i én time før bruk. Supplement PBS, pH 7,4 (Gibco, #10010049) med 2,5 % (v/v) varmeinaktivert FBS. Oppbevars ved 4 °C. |
| DNA-ekstraksjonsbuffer (100 mM Tris pH 8,0, 0,1 M EDTA, 0,5 % (w/v) SDS) |
| Tilsett 50 ml 1 M Tris pH 8,0, 100 ml 0,5 M EDTA og 12,5 ml 20 % SDS. Tilsett destillert vann til 500 ml. Oppbevars ved romtemperatur. |
| TE-buffer (10 mM tris pH 8,0, 1 mM EDTA) |
| Tilsett 2,5 ml 1 M Tris pH 8,0 og 500 ml 0,5 M EDTA. Tilsett destillert vann til 250 ml. Oppbevars ved romtemperatur. |
Tabell 6: Bufferoppskrifter.
| Oligonukleotider liste | ||
| J558FR3Fw | 5'-GCCTGACATCTGAGGACTCTGC-3' | |
| VHJ558.2 | 5'-CTGGACTTTCGGTTTGGTG-3' | |
| VHJ558.3 | 5'-GGTCAAGGAACCTCAGTCA-3' | |
| VHJ558.4 | 5'-TCTCTAGACAGCAACTAC-3' | |
Tabell 7: Oligonukleotider brukt i analysen.
Supplerende figur 1: Representativt agarosegelbilde etter fullføring av trinn 5.4. JH4 intron nestet PCR-produktet ble løst på en 1,5% agarose gel og 580 bp amplicon ble utskilt. WT PP indikerer at WT PP GCBC genomisk DNA ble brukt som mal for den første PCR og AID PP indikerer at AID-/- PP GCBC genomisk DNA ble brukt som mal for den første PCR. ɸ indikerer pcr-kontrollen uten mal og - indikerer at ingenting ble lastet inn i brønnen på agarosegelen. Det siste kjørefeltet viser en 100 bp DNA-stige. Klikk her for å laste ned denne figuren.
Karakterisering av SHM i IgH- og IgL V-kodesekvensene til en heterogen B-cellepopulasjon utgjør en utfordring, gitt at hver B-celle unikt omorganiserer V-kodingssegmenter under V (D)J rekombinasjon34. I dette dokumentet beskriver vi en metode for å identifisere mutasjoner i JH4-intronet til GCBCer. JH4-intronen, som ligger 3 av det siste J-kodesegmentet i IgH-locus, brukes som surrogat for SHM i V-regioner (figur 1)31,33,34,35. For å katalogisere disse JH4 intronmutasjonene og vurdere hvordan spesifikke gener påvirker produksjonen eller mønsteret av mutasjoner, analyseres PP GCBC-er spesielt. Disse cellene akkumulerer JH4 intronmutasjoner som følge av kronisk stimulering ved tarmmikrobiota53. Videre har B220+PNAHI GCBC fra PPs av uimmuniserte mus et mutasjonsspektra som sammenligner med miltika GCBCer fra immuniserte dyr54,55. Mutasjoner i JH4-intronen kan imidlertid ikke korreleres med Ig-affinitetsmodning fordi disse mutasjonene ikke er koding.
For å avgjøre om SHM endrer Ig affinitet, bør mus immuniseres intraperitonealt med et antigen, for eksempel NP (4-hydroksy-3-nitrophenylacetyl) konjugert til CGG (kylling gamma globulin) eller KLH (nøkkelhull limpet hemocyanin)56. Deretter kan mRNA renses fra milt B220+PNAHI GCBCer for å undersøke SHM innen VH186.2, V-kodeeksonen som oftest gjenkjenner NP og er mutert etter NP-CGG eller NP-KLH-immunisering31,57,58,59,60. Mutasjon av tryptofan-33 til en leucin i VH186.2 har blitt karakterisert for å øke Ig affinitet opp til 10-fold59,60 og er derfor en indikator på at SHM og klonisk utvalg har generert høy affinitet Ig. Måling av NP7- og NP20-spesifikke serum-Ig-titere av ELISA og beregning av det Ig-spesifikke NP7/NP20-forholdet i løpet av immuniseringen dokumenterer også Ig affinitetsmodning som følge av SHM i V-region17,21,36. Begge disse analysene kan brukes til å korrelere SHM innenfor VH186.2-kodesekvensene med endringer i NP-spesifikk Ig affinitetsmodning.
Enten immuniserte eller uimmuniserte dyr brukes til å analysere SHM av VH186.2 eller JH4-intronen, må GCBC-er identifiseres nøyaktig. Vi presenterer en FACS-basert tilnærming for å isolere B220+PNAHI GCBCer. Alternativt kan Fas og ikke-sulfaterte α2-6-sialyl-LacNAc-antigenet, som er anerkjent av GL7-antistoffet61,62,63,64, også brukes til å isolere GCBCer, som er identifisert som B220+Fas+GL7+65 eller CD19+Fas+GL7+37. GL7-uttrykket speiler PNA tett i aktiverte GCBCer i lymfeknuter64,65,66. I tillegg til å bruke antistoffmarkører som er spesifikke for GCBCer, bør farging av cocktailer maksimere eksitasjonen av en fluorofor og deteksjon av en biomarkør samtidig som spektral overlapping av fluorescensutslipp minimeres. Antigener uttrykt ved lave nivåer bør påvises med et antistoff som konjugeres til en fluorofor med en robust utslipp fluorescens67. Den anbefalte fargingsprotokollen ble optimalisert for analyse på en cellesortering utstyrt med fire lasere (405nm, 488nm, 561nm, 633nm) og 12 filtre; Filterkonfigurasjoner og lasertilgjengelighet varierer imidlertid mellom cytometere. For å endre protokollen i henhold til reagens- og utstyrstilgjengelighet henvises leseren til flere ressurser, online spektrumvisere og publisert litteratur67,68,69,70,71,72,73. Den flerfargede fargingsprotokollen som er beskrevet her, krever kompensasjon av spektral overlapping for å sikre at de sorterte cellepopulasjonene er GCBCer i stedet for unøyaktig påvisning av fluorescensutslipp. B220 fungerer som en nyttig fargekontroll for den beskrevne FACS (Tabell 1B) fordi PPer vil ha særegne B220 negative og positive populasjoner (figur 3C), som gir mulighet for passende kompensasjon av spektral overlapping. Gatingstrategien som presenteres i figur 3C, bør brukes som en retningslinje. Strømningscytometriplottene kan variere avhengig av fargingsforholdene og cytometerinnstillingene. Likevel bør 4-10% av levende celler være B220+PNAHI 35, 52.
Alle mutasjoner i JH4-intronet til PP GCBCer må valideres for å sikre at de observerte mutasjonene virkelig reflekterer SHM og ikke en artefakt av PCR eller sekvensering. AID-/- B-celler kan fungere som en nyttig negativ kontroll når du undersøker SHM-fenotypen i andre mutante musemodeller fordi disse cellene ikke kan fullføre SHM17,19. JH4 intronmutasjonsraten i AID-/- GCBCene (1,66 x 10-5 mutasjoner/bp)20,21,36,37,38,50,74 kan sammenlignes med feilfrekvensen til den høye gjengivelsespolymerasen (5,3x10-7 sub/base/dobling)51,52 som brukes til å forsterke DNA-et i nestet PCR. Hvis AID-/- mus ikke er tilgjengelige, sammenligner du det observerte mutasjonsmønsteret og frekvensen med den publiserte litteraturen. Ig V-regioner akkumulerer 10-3-10 -4 mutasjoner per basepardivisjon, som er omtrent 106ganger høyere enn mutasjonsraten til andre genloci73,75. Resultatene kan variere med dyrets alder76. Alternativt kan B220+PNALO-celler, som markerer ikke-GCBCer, brukes som en negativ kontroll i fravær av AID-/- mus52. Hvis mutasjonsfrekvensen i WT GCBC er lavere enn forventet, kan WT-bakterien JH4 intronisk sekvens være uforholdsmessig representert. I dette tilfellet må du sørge for at GCBCene ble farget og sortert på riktig måte, og at PCR-er er fri for WT-bakterie JH4 intronforurensning. I tillegg bør rå sekvenseringsdata i elektroferogrammer analyseres grundig for å sikre at mutasjoner i sekvenstekstdataene ikke er gjenstander av sekvensfeil. Dårlige Resultater av Sanger-sekvensering kan for eksempel redusere påliteligheten til sekvensdataene (Figur 4). Denne kvalitetskontroll av Sanger-sekvensdataene vil øke nøyaktigheten og reproduserbarheten til JH4 intronmutasjonsanalysen.
Forfatterne har ingenting å avsløre.
Vi takker Tasuku Honjo for AID-/- mus. Dette arbeidet ble støttet av National Institute on Minority Health and Health Disparities (5G12MD007603), National Cancer Institute (2U54CA132378) og National Institute of General Medical Sciences (1SC1GM132035-01).
| Name | Company | Catalog Number | Comments |
| 0.2 ml PCR 8-tube FLEX-FREE strip, attached clear flat caps, mixed | USA Scientific | 1402-4708 | |
| Ampicillin sodium salt | Fisher | BP1760-5 | |
| APC-eFluor780 anti-CD45R/B220 | eBioscience | 47-0452-80 | clone RA3-6B2 |
| BD FACSAria II | BD | 643186 | four lasers (405nm, 488nm, 561nm, 633nm) and 12 filters (PacBlue (450/50), AmCyan (502LP; 530/30), SSC (488/10), FITC (502LP; 530/30), PerCP-Cy5.5 (655LP; 695/40), PE (585/15), PE-Texas Red (600LP; 610/20), PE-Cy5 (630LP; 670/14), PE-Cy7 (735LP; 780/60), APC (660/20), Alexa700 (710LP; 730/45), APC-Cy7 (755LP; 780/60)) |
| BD slip tip 1mL syringe | Fisher | 14-823-434 | sterile |
| Biotinylated peanut agglutinin (PNA) | Vector Labs | B-1075-5 | |
| C57BL/6J mice | Jackson Laboratories | 664 | |
| Corning Falcon test tube with cell strainer snap cap | Fisher | 08-771-23 | |
| DAPI (4',6-Diamidino-2-Phenylindole, dihydrochloride) | Fisher | D1306 | 0.5 mg/ml |
| dNTP | NEB | N0447L | 10 mM |
| ElectroMAX DH10B competent cells | Fisher | 18-290-015 | |
| Falcon cell strainer 40mm | Fisher | 08-771-1 | |
| Falcon round-bottom polystyrene tubes (FACS tubes) | Fisher | 14-959-5 | |
| Falcon round-bottom polystyrene tubes (capped) | Fisher | 149591A | |
| Fetal bovine serum | R&D Systems (Atlanta Biologicals) | S11150 | |
| Gibco phosphate buffered saline PBS pH 7.4 | Fisher | 10-010-049 | |
| Glycogen | Sigma | 10901393001 | |
| Lasergene Molecular Biology (MegAlign Pro) | DNA Star | version 15 | |
| PE anti-CD45R/B220 | BD | 553090 | clone RA3-6B2 |
| Proteinase K | Fisher | BP1700-100 | |
| Q5 High-Fidelity DNA Polymerase | NEB | M0491L | |
| QIAquick Gel Extraction Kit | Qiagen | 28706 | |
| Seal-Rite 1.5mL microcentrifuge tubes | USA Scientific | 1615-5500 | |
| Streptavidin APC-eFluor 780 Conjugate | eBioscience | 47-4317-82 | |
| T4 DNA ligase | NEB | M020L | |
| Thermo Scientific CloneJET PCR Cloning Kit | ThermoFisher | FERK1231 | |
| Tissue culture plate 6 well | Fisher | 08-772-1B | sterile |
| Unlabeled anti-mouse CD16/CD32 (Fc block), BD | Fisher | BDB553142 | Clone 2.4G2 |
- Murphy, K., Weaver, C. . Janeyway's Immunobiology. , (2016).
- Alt, F. W., et al. VDJ recombination. Immunology Today. 13 (8), 306-314 (1992).
- Schatz, D. G., Ji, Y. Recombination centres and the orchestration of V (D) J recombination. Nature Reviews Immunology. 11 (4), 251-263 (2011).
- Oettinger, M. A., Schatz, D. G., Gorka, C., Baltimore, D. RAG-1 and RAG-2, adjacent genes that synergistically activate V (D) J recombination. Science. 248 (4962), 1517-1523 (1990).
- Berek, C., Berger, A., Apel, M. Maturation of the immune response in germinal centers. Cell. 67 (6), 1121-1129 (1991).
- Linterman, M. A., et al. Foxp3+ follicular regulatory T cells control the germinal center response. Nature Medicine. 17 (8), 975 (2011).
- Shulman, Z., et al. T follicular helper cell dynamics in germinal centers. Science. 341 (6146), 673-677 (2013).
- Good-Jacobson, K. L., et al. PD-1 regulates germinal center B cell survival and the formation and affinity of long-lived plasma cells. Nature Immunology. 11 (6), 535 (2010).
- Kerfoot, S. M., et al. Germinal center B cell and T follicular helper cell development initiates in the interfollicular zone. Immunity. 34 (6), 947-960 (2011).
- Chaudhuri, J., Alt, F. W. Class-switch recombination: interplay of transcription, DNA deamination and DNA repair. Nature Reviews Immunology. 4 (7), 541-552 (2004).
- Alt, F. W., Zhang, Y., Meng, F. L., Guo, C., Schwer, B. Mechanisms of programmed DNA lesions and genomic instability in the immune system. Cell. 152 (3), 417-429 (2013).
- Xu, Z., Zan, H., Pone, E. J., Mai, T., Casali, P. Immunoglobulin class-switch DNA recombination: induction, targeting and beyond. Nature Reviews Immunology. 12 (7), 517-531 (2012).
- Di Noia, J. M., Neuberger, M. S. Molecular mechanisms of antibody somatic hypermutation. Annual Reviews of Biochemistry. 76, 1-22 (2007).
- Peled, J. U., et al. The biochemistry of somatic hypermutation. Annual Review of Immunology. 26, 481-511 (2008).
- Liu, M., Schatz, D. G. Balancing AID and DNA repair during somatic hypermutation. Trends in Immunology. 30 (4), 173-181 (2009).
- Methot, S., Di Noia, J. Molecular Mechanisms of Somatic Hypermutation and Class Switch Recombination. Advances in Immunology. 133, 37-87 (2017).
- Muramatsu, M., et al. Class switch recombination and hypermutation require activation-induced cytidine deaminase (AID), a potential RNA editing enzyme. Cell. 102 (5), 553-563 (2000).
- Petersen-Mahrt, S. K., Harris, R. S., Neuberger, M. S. AID mutates E. coli suggesting a DNA deamination mechanism for antibody diversification. Nature. 418 (6893), 99 (2002).
- Revy, P., et al. Activation-induced cytidine deaminase (AID) deficiency causes the autosomal recessive form of the Hyper-IgM syndrome (HIGM2). Cell. 102 (5), 565-575 (2000).
- Petersen-Mahrt, S. DNA deamination in immunity. Immunological Reviews. 203 (1), 80-97 (2005).
- Rada, C., Di Noia, J. M., Neuberger, M. S. Mismatch recognition and uracil excision provide complementary paths to both Ig switching and the A/T-focused phase of somatic mutation. Molecular Cell. 16 (2), 163-171 (2004).
- Rada, C., et al. Immunoglobulin isotype switching is inhibited and somatic hypermutation perturbed in UNG-deficient mice. Current Biology. 12 (20), 1748-1755 (2002).
- Schrader, C. E., Vardo, J., Stavnezer, J. Role for mismatch repair proteins Msh2, Mlh1, and Pms2 in immunoglobulin class switching shown by sequence analysis of recombination junctions. The Journal of Experimental Medicine. 195 (3), 367-373 (2002).
- Martin, A., et al. Msh2 ATPase activity is essential for somatic hypermutation at AT basepairs and for efficient class switch recombination. The Journal of Experimental Medicine. 198 (8), 1171-1178 (2003).
- Imai, K., et al. Human uracil-DNA glycosylase deficiency associated with profoundly impaired immunoglobulin class-switch recombination. Nature Immunology. 4 (10), 1023-1028 (2003).
- Masani, S., Han, L., Yu, K. Apurinic/apyrimidinic endonuclease 1 is the essential nuclease during immunoglobulin class switch recombination. Molecular and Cellular Biology. 33 (7), 1468-1473 (2013).
- Guikema, J. E., et al. APE1-and APE2-dependent DNA breaks in immunoglobulin class switch recombination. The Journal of Experimental Medicine. 204 (12), 3017-3026 (2007).
- Schrader, C. E., Guikema, J. E., Wu, X., Stavnezer, J. The roles of APE1, APE2, DNA polymerase β and mismatch repair in creating S region DNA breaks during antibody class switch. Philosophical Transactions of the Royal Society B: Biological Sciences. 364 (1517), 645-652 (2009).
- Roa, S., et al. MSH2/MSH6 complex promotes error-free repair of AID-induced dU: G mispairs as well as error-prone hypermutation of A: T sites. PLoS One. 5 (6), 11182 (2010).
- Delbos, F., Aoufouchi, S., Faili, A., Weill, J. C., Reynaud, C. A. DNA polymerase η is the sole contributor of A/T modifications during immunoglobulin gene hypermutation in the mouse. The Journal of Experimental Medicine. 204 (1), 17-23 (2007).
- Maul, R. W., Gearhart, P. J. AID and somatic hypermutation. Advances in Immunology. 105, 159-191 (2010).
- Shen, H. M., Tanaka, A., Bozek, G., Nicolae, D., Storb, U. Somatic hypermutation and class switch recombination in Msh6-/- Ung-/- double-knockout mice. The Journal of Immunology. 177 (8), 5386-5392 (2006).
- Cheng, H. L., et al. Integrity of the AID serine-38 phosphorylation site is critical for class switch recombination and somatic hypermutation in mice. Proceedings of the National Academy of Sciences. 106 (8), 2717-2722 (2009).
- Lebecque, S. G., Gearhart, P. J. Boundaries of somatic mutation in rearranged immunoglobulin genes: 5'boundary is near the promoter, and 3'boundary is approximately 1 kb from V (D) J gene. The Journal of Experimental Medicine. 172 (6), 1717-1727 (1990).
- Jolly, C. J., Klix, N., Neuberger, M. S. Rapid methods for the analysis of immunoglobulin gene hypermutation: application to transgenic and gene targeted mice. Nucleic Acids Research. 25 (10), 1913-1919 (1997).
- Choi, J. E., Matthews, A. J., Michel, G., Vuong, B. Q. AID Phosphorylation Regulates Mismatch Repair-Dependent Class Switch Recombination and Affinity Maturation. The Journal of Immunology. 204 (1), 13-22 (2020).
- McBride, K. M., et al. Regulation of class switch recombination and somatic mutation by AID phosphorylation. The Journal of Experimental Medicine. 205 (11), 2585-2594 (2008).
- Liu, M., et al. Two levels of protection for the B cell genome during somatic hypermutation. Nature. 451 (7180), 841-845 (2008).
- Ross, M., Birbeck, M., Wills, V., Forrester, J., Davis, A. Peanut lectin binding properties of germinal centers of mouse lymphoid tissues. Nature. 284, 364-366 (1980).
- Zhang, J., MacLennan, I. C., Liu, Y. J., Lane, P. J. Is rapid proliferation in B centroblasts linked to somatic mutation in memory B cell clones. Immunology Letters. 18 (4), 297-299 (1988).
- Nieuwenhuis, P., Opstelten, D. Functional anatomy of germinal centers. American Journal of Anatomy. 170 (3), 421-435 (1984).
- Lau, A. W., Brink, R. Selection in the germinal center. Current Opinion in Immunology. 63, 29-34 (2020).
- Victora, G. D., Nussenzweig, M. C. Germinal centers. Annual Review of Immunology. 30, 429-457 (2012).
- Mesin, L., Ersching, J., Victora, G. D. Germinal center B cell dynamics. Immunity. 45 (3), 471-482 (2016).
- Reichert, R. A., Gallatin, W. M., Weissman, I. L., Butcher, E. C. Germinal center B cells lack homing receptors necessary for normal lymphocyte recirculation. The Journal of Experimental Medicine. 157 (3), 813-827 (1983).
- Rose, M., Birbeck, M., Wills, V., Forrester, J., Davis, A. Peanut lectin binding properties of germinal centers of mouse lymphoid tissues. Nature. 284, 364-366 (1980).
- Hamada, S., Fujita, S. DAPI staining improved for quantitative cytofluorometry. Histochemistry. 79 (2), 219-226 (1983).
- Otto, F. DAPI staining of fixed cells for high-resolution flow cytometry of nuclear DNA. Methods in Cell Biology. 33, 105-110 (1990).
- Butcher, E., et al. Surface phenotype of Peyer's patch germinal center cells: implications for the role of germinal centers in B cell differentiation. The Journal of Immunology. 129 (6), 2698-2707 (1982).
- Rogerson, B. J., Harris, D. P., Swain, S. L., Burgess, D. O. Germinal center B cells in Peyer's patches of aged mice exhibit a normal activation phenotype and highly mutated IgM genes. Mechanisms of Ageing and Development. 124 (2), 155-165 (2003).
- Potapov, V., Ong, J. L. Examining sources of error in PCR by single-molecule sequencing. PloS One. 12 (1), 0169774 (2017).
- Gonzalez-Fernandez, A., Milstein, C. Analysis of somatic hypermutation in mouse Peyer's patches using immunoglobulin kappa light-chain transgenes. Proceedings of the National Academy of Sciences. 90 (21), 9862-9866 (1993).
- Reboldi, A., Cyster, J. G. Peyer's patches: organizing B-cell responses at the intestinal frontier. Immunological Reviews. 271 (1), 230-245 (2016).
- Betz, A. G., Rada, C., Pannell, R., Milstein, C., Neuberger, M. S. Passenger transgenes reveal intrinsic specificity of the antibody hypermutation mechanism: clustering, polarity, and specific hot spots. Proceedings of the National Academy of Sciences. 90 (6), 2385-2388 (1993).
- Rada, C., Gupta, S. K., Gherardi, E., Milstein, C. Mutation and selection during the secondary response to 2-phenyloxazolone. Proceedings of the National Academy of Sciences. 88 (13), 5508-5512 (1991).
- Heise, N., Klein, U. Somatic Hypermutation and Affinity Maturation Analysis Using the 4-Hydroxy-3-Nitrophenyl-Acetyl (NP) System. Methods in Molecular Biology. 1623, 191-208 (2017).
- Smith, F., Cumano, A., Licht, A., Pecht, I., Rajewsky, K. Low affinity of kappa chain bearing (4-hydroxy-3-nitrophenyl) acetyl (NP)-specific antibodies in the primary antibody repertoire of C57BL/6 mice may explain lambda chain dominance in primary anti-NP responses. Molecular Immunology. 22 (10), 1209-1216 (1985).
- Takahashi, Y., Dutta, P. R., Cerasoli, D. M., Kelsoe, G. In situ studies of the primary immune response to (4-hydroxy-3-nitrophenyl) acetyl. V. Affinity maturation develops in two stages of clonal selection. The Journal of Experimental Medicine. 187 (6), 885-895 (1998).
- Allen, D., Simon, T., Sablitzky, F., Rajewsky, K., Cumano, A. Antibody engineering for the analysis of affinity maturation of an anti-hapten response. The EMBO Journal. 7 (7), 1995-2001 (1988).
- Cumano, A., Rajewsky, K. Clonal recruitment and somatic mutation in the generation of immunological memory to the hapten NP. The EMBO Journal. 5 (10), 2459-2468 (1986).
- Smith, K., Nossal, G., Tarlinton, D. M. FAS is highly expressed in the germinal center but is not required for regulation of the B-cell response to antigen. Proceedings of the National Academy of Sciences. 92 (25), 11628-11632 (1995).
- Hao, Z., et al. Fas receptor expression in germinal-center B cells is essential for T and B lymphocyte homeostasis. Immunity. 29 (4), 615-627 (2008).
- Cervenak, L., Magyar, A., Boja, R., László, G. Differential expression of GL7 activation antigen on bone marrow B cell subpopulations and peripheral B cells. Immunology Letters. 78 (2), 89-96 (2001).
- Naito, Y., et al. Germinal center marker GL7 probes activation-dependent repression of N-glycolylneuraminic acid, a sialic acid species involved in the negative modulation of B-cell activation. Molecular and Cellular Biology. 27 (8), 3008-3022 (2007).
- Olson, W. J., et al. Orphan Nuclear Receptor NR2F6 Suppresses T Follicular Helper Cell Accumulation through Regulation of IL-21. Cell Reports. 28 (11), 2878-2891 (2019).
- Dorsett, Y., et al. MicroRNA-155 suppresses activation-induced cytidine deaminase-mediated Myc-Igh translocation. Immunity. 28 (5), 630-638 (2008).
- Goetz, C., Hammerbeck, C., Bonnevier, J. . Flow Cytometry Basics for the Non-Expert. , (2018).
- Hawley, T. S., Herbert, D. J., Eaker, S. S., Hawley, R. G. . Flow Cytometry Protocols. , (2004).
- Costa, E., et al. A new automated flow cytometry data analysis approach for the diagnostic screening of neoplastic B-cell disorders in peripheral blood samples with absolute lymphocytosis. Leukemia. 20 (7), 1221-1230 (2006).
- McKinnon, K. M. Flow cytometry: An overview. Current Protocols in Immunology. 120 (1), 1-11 (2018).
- McKinnon, K. M. Multiparameter Conventional Flow Cytometry. Methods in Molecular Biology. , 139-150 (2018).
- Lucchesi, S., et al. Computational Analysis of Multiparametric Flow Cytometric Data to Dissect B Cell Subsets in Vaccine Studies. Cytometry Part A. 97, 259-267 (2019).
- Longerich, S., Tanaka, A., Bozek, G., Nicolae, D., Storb, U. The very 5' end and the constant region of Ig genes are spared from somatic mutation because AID does not access these regions. The Journal of Experimental Medicine. 202 (10), 1443-1454 (2005).
- Retter, I., et al. Sequence and characterization of the Ig heavy chain constant and partial variable region of the mouse strain 129S1. The Journal of Immunology. 179 (4), 2419-2427 (2007).
- Shen, H. M., Peters, A., Baron, B., Zhu, X., Storb, U. Mutation of BCL-6 gene in normal B cells by the process of somatic hypermutation of Ig genes. Science. 280 (5370), 1750-1752 (1998).
- Richter, K., et al. Altered pattern of immunoglobulin hypermutation in mice deficient in Slip-GC protein. Journal of Biological Chemistry. 287 (38), 31856-31865 (2012).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved