Summary
Abstract
Introduction
Protocol
Representative Results
Discussion
Acknowledgements
Materials
References
Immunology and Infection
Fare Peyer Yamalarından Germinal Center B hücrelerinin JH4 intronunda Somatik Hipermütasyon Analizi
Burada, fare Peyer'in yamalarından germinal merkez B hücrelerini kullanarak immünoglobulin ağır zincir gen lokusu içindeki somatik hipermütasyonu ölçmek için bir test sunulmaktadır.
Lenfoid organların germinal merkezlerinde, olgun B hücreleri, Ig ağır ve hafif zincir gen loci'nin değişken kodlama eksonlarına untemplated mutasyonlar sokarak ifade edilen immünoglobulinlerini (Ig) değiştirir. Bu somatik hipermütasyon (SHM) işlemi, deoksisitidinleri (C) deoksisidinlere (U) dönüştüren enzim aktivasyonuna bağlı stidin deaminazını (AID) gerektirir. AID tarafından oluşturulan U:G uyuşmazlıklarının baz eksizyon ve uyuşmazlık onarım yolları tarafından mutasyonlara işlenmesi, daha yüksek bir benzeşim Ig üretebilecek yeni Ig kodlama dizileri sunar. AID veya DNA onarım genlerindeki mutasyonlar, Ig loci'de gözlenen mutasyon türlerini engelleyebilir veya önemli ölçüde değiştirebilir. Floresan aktif hücre sıralama (FACS), PCR ve Sanger dizilimini kullanan JH4 intron mutasyonlarını ölçmek için bir protokol açıklıyoruz. Bu test ig benzeşimi olgunlaşmasını doğrudan ölçmese de, Ig değişken kodlama dizilerindeki mutasyonların göstergesidir. Ek olarak, bu yöntemler birden fazla B hücre klonunun Ig dizilerindeki mutasyonları analiz eden yaygın moleküler biyoloji tekniklerini kullanır. Bu nedenle, bu tahlil SHM ve Ig çeşitlendirme çalışmasında paha biçilmez bir araçtır.
Adaptif bağışıklık sisteminin üyeleri olan B hücreleri, immünoglobulinler (Ig) olarak da bilinen antikorlar üreterek antijenleri tanır ve ortadan kaldırır. Her Ig, Ig1'inkarakteristik "Y" şekil yapısını oluşturmak için disülfit bağları tarafından bir arada tutulan iki ağır (IgH) ve iki hafif (IgL) zincir polipeptitten oluşur. IgH ve IgL'nin N-termini, her polipeptitin değişken (V) bölgesini oluşturur ve birlikte Ig'nin antijen bağlama bölgesini oluştururken, IgH'nin sabit bölgesi Ig'nin efektör işlevini oluşturur. Kemik iliğinde B hücreleri geliştirmek, IgH ve IgL'nin V kodlama eksonlarını V(D)J rekombinasyon2,3,4olarak bilinen bir işlemde yeniden düzenler. Yeniden birleştirilen V ekzonlarının transkripsiyonu, ilgili sabit bölge eksonları ile birleştiğinde, Ig'ye çevrilen mRNA'yı oluşturur.
B hücre reseptörü (BCR) olarak da bilinen zara bağlı bir Ig'yi ifade eden olgun B hücreleri, dalak, lenf nodu veya Peyer'in yamaları gibi ikincil lenfoid organlara dolaşır, burada antijenler için çevreyi inceler ve bağışıklık sisteminin diğer hücreleriyle etkileşime girer1. sekonder lenfoid organların germinal merkezleri (GC) içinde BCR yoluyla antijeni tanıyan B hücreleri aktive olur. Foliküler dendritik hücreler ve foliküler yardımcı T hücreleri tarafından yardım edilen aktif B hücreleri, daha sonra sağlam bir immün yanıtın önemli etkileri olan plazma ve hafıza hücrelerine çoğalabilir ve farklılaşabilir5, 6,7,8,9. Ek olarak, bu aktif B hücreleri ikincil Ig gen çeşitlendirme süreçlerinden geçebilir - sınıf anahtarı rekombinasyonu (KSS) ve somatik hipermütasyon (SHM). KSS sırasında B hücreleri, IgH polipeptitinin varsayılan μ sabit bölgesini dna silme-rekombinasyon reaksiyonu yoluyla başka bir sabit bölgeyle (γ, α, ε) değiştirir (Şekil 1). Bu, farklı bir sabit aksonun ifade edilmesine ve yeni bir Ig'nin çevirisine izin verir. B hücresi IgM'yi ifade etmekten başka bir izotipe (IgG, IgA, IgE) geçer. KSS, antijen özgüllüğünü değiştirmeden Ig'nin efektör işlevini değiştirir10,11,12. Bununla birlikte, SHM sırasında B hücreleri, bir antijeni daha etkili bir şekilde ortadan kaldırabilen daha yüksek benzeşimli Iglerin üretimini ve seçimini sağlamak için IgH ve IgL'nin V kodlama bölgelerini mutasyona uğratır13,14,15 ( Şekil1). Daha da önemlisi, hem KSS hem de SHM bir enzimin işlevine bağlıdır: aktivasyona bağlı sitidin deaminaz (AID)16,17,18. AID'de eksik olan insanlar ve fareler KSS veya SHM'yi tamamlayamaz ve yükseltilmiş IgM serum titreleri veya Hyper-IgM17,19ile mevcut olamaz.
KSS'de, AID, her sabit kodlama eksonlarından önce gelen tekrarlayan anahtar bölgelerindeki deoksisitidinleri (C) deaminate eder, bunları deoxyuridines (U)20,21'edönüştürür,bu da deoksiyridinler ve deoksyguanosinler (U:G) arasında eşleşmeyen baz eşleştirmesi oluşturur. DNA rekombinasyonu için gerekli olan, taban eksizyon onarımı (BER) veya uyuşmazlık onarımı (MMR) yolu22 , 23,24,25 , 26,27,28,29. SHM'de AID, V kodlama ekzonları içindeki C'yi deaminate eder. U:G uyuşmazlığı boyunca replikasyon C:G'den T:A geçiş mutasyonlarına neden olurken, urasil tabanının BER proteini, urasil DNA glikosilaz (UNG) tarafından çıkarılması, DNA replikasyonundan önce hem geçiş hem de transversiyon mutasyonları üretir16. UNG'deki boş mutasyonlar C:G'yi T:A geçiş mutasyonlarına önemli ölçüde artırır21,22. KSS'ye benzer şekilde, SHM mmr ve BER'in tamamlayıcı rollerini gerektirir. SHM sırasında MMR, A:T baz çiftlerinde mutasyonlar oluşturur. MutS homology 2 (MSH2) veya DNA polimeraz η(Polφ)mutasyonlarını inaktive etmek, A:T bazlarındaki mutasyonları önemli ölçüde azaltır ve MSH2 ve Polφ'daki bileşik mutasyonlar A:T bazlarındaki mutasyonları neredeyse ortadan kaldırır21,30,31. AID tarafından oluşturulan U'yu geçiş veya transversiyon mutasyonlarına dönüştürmede BER ve MMR için kritik rol ile tutarlı olarak, hem MSH2 hem de UNG(MSH2-/-UNG-/-) için eksik olan fareler, U:G uyumsuzluğu21boyunca çoğaltmadan kaynaklanan yalnızca C:G ila T:A geçiş mutasyonlarını görüntüler.
V kodlama bölgelerinde SHM analizi karmaşık kalır, çünkü gelişmekte olan B hücreleri IgH ve IgL loci 1,2,4'tekiV(D)J kodlama eksonlarından herhangi birini yeniden birleyebilir. Bu benzersiz bir şekilde yeniden birleştirilmiş ve somatik olarak mutasyona uğramış V bölgelerinin doğru analizi, B hücrelerinin veya Ig mRNA11 , 13klonlarının tanımlanmasını ve izolasyonunu gerektirir. IgH lokusundaki son J kodlama eksonunun 3' 'ü olan JH4 intron, V promotörü 32 , 33,34'ün 3'mutasyonlarının yayılması nedeniyle somatik mutasyonları barındırır ve bu nedenle V bölgelerinde 31, 35 (Şekil 1)SHM için taşıyıcı işaretleyici olarak sıklıkla kullanılır. Belirli genlerin veya genetik mutasyonların SHM örüntülerini veya oranlarını nasıl değiştirdiğini deneysel olarak anlamak için JH4 intron, Yüksek SHM36 , 37,38oranlarından geçen Peyer'in yamalarından (PP) germinal merkez B hücrelerinden (GCBC' ler) sıralanabilir. GCBC'ler hücre yüzey belirteçlerine karşı floresan konjuge antikorlarla kolayca tanımlanabilir ve izole edilebilir (B220+PNAHI)17,39.
PP GCBC'lerdeki JH4 intron mutasyonlarını farelerden FACS (floresan aktif hücre sıralama), PCR ve Sanger diziliminin bir kombinasyonu kullanılarak karakterize etmek için ayrıntılı bir protokol sunulmuştur (Şekil 2).
Tüm mutant fareler C57BL /6 arka plan üzerinde muhafaza edildi. Tüm deneyler için yaşa uygun (2-5 aylık) erkek ve dişi fareler kullanıldı. New York Şehir Koleji Kurumsal Hayvan Bakım ve Kullanım Komitesi tarafından onaylanan protokollere göre farelerin hayvancılığı ve deneyleri yapıldı.
1. Peyer yamalarının diseksiyonu
- Fareyi 5 dakika boyunca 3 L/ dk'da% 100 CO2 ile ötenazi ve ardından ölümü doğrulamak için servikal çıkık. Diseksiyon aletlerini (makas, tokalar, ince tokalar) ve eldivenli elleri% 70 etanol ile sterilize edin.
- Fareyi karın açıktayken diseksiyon pedi üzerine yatırın. Diseksiyon alanını sterilize etmek için herhangi bir kesi yapmadan önce farenin gövdesini% 70 etanol ile cömertçe püskürtün.
- Karın boyunca cilde bir kesi yapın ve kesiğin her iki tarafına aynı anda baş ve kuyruğa doğru çekmeden deriyi karından çıkarın.
- Farenin ön ve arka uzuvlarını sabitle.
- İç organları açığa çıkarmak için periton boşluğunu makasla kesin.
- Mide ve caecum arasındaki ince bağırsağı bulun ("J" kolonun yakınındaki şekilli yapı). Midenin altında ve kaekumun üstünde keserek ince bağırsağı çıkarın.
- İnce bağırsağın kıvrımlarını birbirine bağlayan bağ dokusunu ve yağı çıkarın.
NOT: Yağ, ince bağırsağın pembe renginin aksine belirgin bir beyaz renge sahip olacaktır. - İnce bağırsağın dış yüzeyini, ince bir yarı saydam epitel hücrelerinin altında beyaz görünen küçük (~1 mm), oval şekilli yapılar olan Peyer'in yamalarını (PP'ler) inceleyin.
- Tüm görünür PP'yi makasla dikkatlice açın.
NOT: Bir C57BL/6 vahşi tip (WT) fare 4-8 PP verebilirken, AID-/- fare 6-10 PP'ye sahip olacaktır. - PP'leri buz üzerinde 1 mL FACS tamponu içeren 1,5 mL mikrosantrifüj tüpünde toplayın.
NOT: PP batmalıdır, oysa yağ yüzeye yüzer ve çıkarılabilir.
2. FACS için hücre yalıtımı
- 1 mL soğuk (4 °C) FACS tamponlu 6 kuyulu bir yemeğe 40 μm filtre yerleştirin.
- 1,5 mL'lik tüpten GP'leri filtreye dökün.
- PP'leri 1 mL soğuk FACS tamponu ile yıkayın, her zaman sıvı ve buz üzerinde olduklarından emin olun.
- Filtredeki PP'leri filtrede sadece bağ dokusu kalana kadar ezmek için pistonun düz ucunun 1 mL şırınnadan haşere olarak kullanın.
- Hücreleri 6 kuyu kabına bırakmak için filtreyi ve pistonu 1 mL soğuk FACS tamponu ile yıkayın.
- Soğuk FACS tamponunda ~4 mL hücre toplayın ve bunları 40 μm süzgeç kapağı FACS tüpünden filtreleyin.
- Süzgeç kapağını 1 mL soğuk FACS tamponu ile yıkayın.
- Sallanan bir kova santrifüjde 5 dakika boyunca 4 °C'de 600 x g'daki hücreleri peletin.
- Süpernatantı yok edin.
- Hücreleri 0,4 mL soğuk FACS arabelleğine yeniden depolar.
- Verimi doğrulamak için hücre sayımı için 10 μL'yi kaldırın (~5 x 106 hücre/fare bekleyin, bkz. Şekil 3A)
- Kalan hücreleri 40 μm süzgeç kapağından bir FACS tüpüne filtreleyin ve FACS için boyamaya devam edin.
3. FACS için GCBC'lerin Boyanması
- 400 μL hücre süspansiyonu için 1 μL Fc bloğu (etiketsiz fare önleyici CD16/CD32) ekleyin ve hücreleri 15 dakika boyunca buza yerleştirin.
- Hücreleri yıkamak için 2 mL soğuk FACS arabelleği ekleyin.
- 5 dakika boyunca 4 °C'de 600 x g'da pelet hücreleri ve süpernatant atın.
- Hücreleri 80 μL soğuk FACS tamponunda yeniden depolar.
- Her boyama kontrolü için WT PP'den 10 μL hücre çıkarın (3 tek leke kontrolü ve 1 lekesiz kontrol dahil olmak üzere toplamda 4). Bir sonraki adım için WT PP'nin 40 μL'sini bırakın. Alternatif olarak, boyama kontrolleri için kompanzasyon boncukları kullanın.
- Deneysel örneklerin her birini (örneğin, WT ve AID-/-) 500 μL soğuk FACS tamponunda 2,5 μL fıstık agglutinin (PNA)-biotin ile buz üzerinde 15 dakika lekelenin.
- Hücreleri yıkamak için 2 mL soğuk FACS arabelleği ekleyin.
- 5 dakika boyunca 4 °C'de 600 x g'da pelet hücreleri ve süpernatant atın.
- Her deneysel örneği karanlıkta, buzda 15 dakika boyunca 500 μL kokteylle lekelenin (Tablo 1). Hücrelerin boyama kokteylinde tamamen yeniden sağlandığından emin olun.
- Kompanzasyon matrisi için tek leke kontrolleri hazırlayın.
- Tablo 2'de belirtilen seyreltmeleri kullanarak hücreleri 500 μL soğuk FACS tamponunda lekelendirin.
- Boyama kontrollerini karanlıkta, buzda 15 dakika kuluçkaya yatırın.
- 3.7 ve 3.8 adımlarındaki tüm tüplere 2 mL soğuk FACS tamponu ekleyin, hücreleri peletleyin ve ilişkisiz antikorları veya DAPI'yı yıkamak için süpernatantı atın.
- Hücreleri 500 μL soğuk FACS tamponunda yeniden depolayın ve buza yerleştirin.
- Bir hücre sıralayıcısı kullanarak, her lekeli deneysel örnekten B220+PNAHI toplayın. Şekil 3B, WT ve AID-/- PP'lerden elde edilen tipik B220+ PNAHI yüzdelerini gösterir.
4. GCBC'lerden DNA ekstraksiyonu
- Pelet, 5 dakika boyunca 4 °C'de 600 x g'da hücreleri sıraladı ve süpernatantı attı.
- Hücreleri 1 mL soğuk FACS tamponunda yeniden depola ve hücreleri 1,5 mL mikrosantrifüj tüpüne aktarın.
- 4 °C'de 600 x g'daki hücreleri 5 dakika boyunca peletin ve süpernatant atın.
- Hücreleri 500 μL DNA ekstraksiyon tamponunda ve 5 μL 20 mg/mL Proteinaz K'de yeniden biriktirin.
- Gece boyunca 56 °C'de kuluçkaya yaslanın.
- DNA'yı 500 μL izopropanol ve 1 μL 20 mg/mL glikojen ile çökeltin. 5-6x ters çevirerek tüpü iyice karıştırın.
- Oda sıcaklığında 10 dakika kuluçkaya yatır.
- 21.000 x g'da25 °C'de 15 dakika boyunca bir mikrosantrifüjde santrifüj.
- Süpernatantı atın ve çökelmiş DNA ve glikojeni içeren peleni koruyun.
- DNA peletini% 70 etanol 1 mL ile yıkayın.
- DNA'yı 21.000 x g'da 25 °C'de 10 dakika boyunca bir mikrosantrifüjde peletle.
- % 70 etanol çıkarın ve DNA peletini 5-10 dakika boyunca havayla kurulayın.
NOT: DNA tamamen yeniden sulandırmayabileceğinden aşırı kurumaktan kaçının.
- DNA'yı 30 μL TE tamponunda yeniden dirin ve 56 °C'de bir gecede kuluçkaya yatırın.
5. JH4 intron dizi amplifikasyonu ve analizi
- Emiciliği 260 nm (A260) dalga boyunda ölçerek DNA'yı ölçün.
NOT: Bir C57BL/6 farenin sıralanmış B220+PNAHI GCBC'lerinden elde edilen tipik DNA konsantrasyonu 20-40 ng/μL'dir. - JH4 intron için iç içe PCR'yi gerçekleştirin (Tablo 3, Tablo 4). İlk PCR'de kullanılan toplam genomik DNA miktarını en az konsantre numuneye normalleştirin. (örneğin, en az konsantre örnek 5 ng/μL ise, PCR #1 maksimum su hacmindeki (11,75 μL) tüm örnekler için 58,75 ng DNA kullanın).
- PCR ürününü 200 V'ta %1,5 agarose jel üzerinde 20 dakika çözün. Beklenen amplicon boyutu 580 bp'dir.
- Amplicon'ı jelden çıkarın ve üreticinin talimatlarına göre jel çıkarma kiti kullanarak DNA'yı çıkarın (bkz. Ek Şekil 1).
- DNA'yı 30 μL su ile katın ve A260'ı ölçerek DNA miktarını ölçün.
NOT: Saflaştırılmış PCR ürününün tipik konsantrasyonu 3-10 ng/μL'dir.
- DNA'yı 30 μL su ile katın ve A260'ı ölçerek DNA miktarını ölçün.
- Saflaştırılmış PCR ürününü künt uçlu bir plazmid haline alın. Her ligasyon reaksiyonunda kullanılan toplam PCR ürün miktarını standartlaştırın (Tablo 5).
- Ligasyon reaksiyonunu oda sıcaklığında 5 dakika veya gece boyunca 16 °C'de kuluçkaya yatırın.
- Elektromanyeter bakteri hücrelerini ligasyon reaksiyonunun 2 μL'si ile dönüştürün.
- Elektroporat 1.65 kV'da.
- 225 rpm'de titreyen bir inkübatörde 37 °C'de 1 saat boyunca 600 μL SOC ortamında kurtarma.
- Plaka 100 μL dönüştürülmüş bakteri, ampisilin (100 μg/mL) agar plakaları ile desteklenmiş LB'ye dönüşür ve gece boyunca 37 °C'de kuluçkaya yatırılır.
- T7 ileri astarı kullanarak Sanger dizilimi için bakteri kolonileri plakasını gönderin. Alternatif olarak, her bakteri kolonisinin gece kültürlerini büyütün ve plazmid saflaştırması gerçekleştirin.
- Gerekirse, bakteri kolonilerinin verimini optimize etmek için PCR, ligasyon ve/veya dönüşümü tekrarlayın
NOT: Her plakadan en az 30 koloni seçilmelidir.
- Gerekirse, bakteri kolonilerinin verimini optimize etmek için PCR, ligasyon ve/veya dönüşümü tekrarlayın
- .txt dosyalarındaki sıra verilerini standartlaştırma
- Plazmid dizisini silin.
- JH4 intron referans dizisine (NG_005838) göre her sıranın 5' ila 3' yönlendirildiğine emin olun. Gerektiğinde herhangi bir sıranın ters tamamlayıcısını oluşturun.
- Clustal Omega yazılımı(Şekil 4A)kullanarak her PCR için elde edilen dizileri JH4 intron referans dizisine (NG_005838) göre hizalayın.
- Referans dizisinden farklılıkları mutasyon olarak tanımlama
- Sanger diziliminin elektroferogramını inceleyerek tüm mutasyonların gerçek nokta mutasyonları olduğunu doğrulayın. Gerekirse sıralamayı yineleyin. (Şekil 4B,C).
- Her genotip için JH4 intronunda benzersiz mutasyonları tablolayıp ölçün (Şekil 5).
- Aynı mutasyonlara sahip dizileri yalnızca bir kez sayma
NOT: Farklı B hücrelerinde PCR veya özdeş SHM olayları sırasında aynı dizilerin oluşturulup oluşturulmadığını belirlemek mümkün değildir. - WT germline JH4 intron dizilerinin (yani mutasyonu olmayanların) her örneğini benzersiz bir dizi olarak sayın.
- Aynı mutasyonlara sahip dizileri yalnızca bir kez sayma
Akış sitometrisi
Olgun B hücreleri, benzeşim olgunlaşması, klonal genişleme ve plazma veya hafıza hücrelerine farklılaşmaya maruz kaldıkları germinal merkezlere dolaşır40 , 41,42,43,44. Bu GCBC'ler, CD45R/ B220 reseptörünün yüksek ekspresyişi ve yer fıstığı aglutinin (PNA)45,46'nınbağlanması da dahil olmak üzere çok sayıda hücre yüzeyi belirteci ile tanımlanabilir. Aktif GCBC'leri izole etmek için PP hücreleri, fitoerythrin (PE) ve biyotiniled-PNA'ya konjuge edilen anti-B220 antikorları ile lekelendi ve ardından APC-eFluor780'e konjuge streptavidin verildi. Ölü hücreler, ölmekte olan veya ölen hücrelerin nükleik asidini lekeleyen floresan 4',6-Diamidino-2-Fenilindole (DAPI) boyası kullanılarak elimine edilmiştir47,48. Lekeli hücreler daha sonra akış sitometrisi ile analiz edildi ve sıralandı. PP'ler ~% 80 B220+ hücre49,50'den oluşuyordu. WT PP'ler fare başına ortalama 4 x 106 hücre içerir (Şekil 3A). WT PP hücrelerinin yaklaşık % 8'i AID-/ - ( Şekil3B)'degözlenen sayının yarısı olan B220+PNAHIidi. Böylece, JH4 intronunda mutasyonları analiz etmek için yeterli olan sıralamadan sonra0.3-0.6 x 10 6 B220+PNAHI GCBC'ler elde edildi.
JH4 Sıra Analizi
JH4 intron, ortak VHJ558 aile primerleri (J558FR3Fw ve VHJ558.2) kullanılarak iç içe geçmiş bir PCR ile güçlendirildi ve ardından VHJ558.3 ve VHJ558.435,37astarlarını kapsayan JH4 intron. WT GCBC'lerden elde edilen 105 benzersiz diziden toplam 226 mutasyon bulundu (Şekil 5A). WT farelerindeki GCBC mutasyon spektrumunun analizi, mutasyona uğramış bazların toplam sayısının32 , 36 , 37 ,38sıralı toplam baz sayısına bölünmesiyle hesaplanan 4 x 10-3mutasyon / bp oranında bir dizi geçiş ve transversiyon gösterdi. Ek olarak, WT GCBC'lerden gelen her JH4 PCR ürünü, bir dizi 33,36'da sık sık birden fazla mutasyon bulunan1-25mutasyon (Şekil 5B) içeriyordu. 113 AID-/- dizisinde sadece iki mutasyon tanımlanmıştır (Şekil 5A). AID-/- B hücreleri 1.66 x 10-5 mutasyon/bp, WT B hücrelerinden (p <0.05)36'dan önemli ölçüde düşüktü ve yüksek doğrulukta polimerazın hata oranıyla karşılaştırıldığında (5.3 x 10-7 alt/baz/iki katına çıkarma)51,52. Bu nedenle, AID-/- B hücreleri bu test için yararlı bir negatif kontrol görevi buldu.
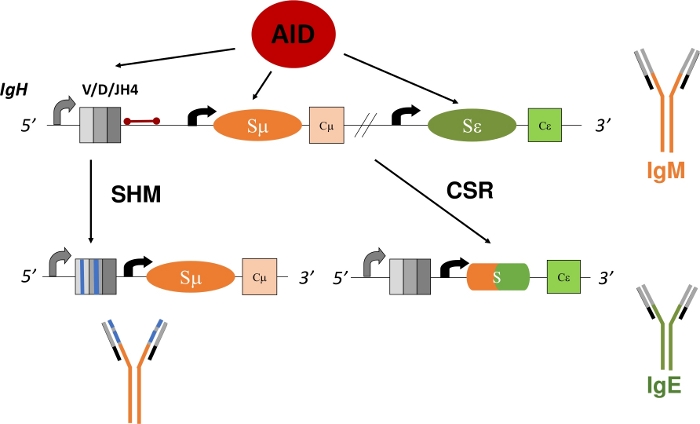
Şekil 1: IGH gen lokusu ve KSS ve SHM sırasında AID tarafından hedeflenen bölgelerin şeması. Kırmızı çubuk, VDJH4 yeniden düzenlemelerinin 3' olan 580 bp JH4 intron'ını gösterir ve bu protokolde analiz edilir. KSS'de, intronik anahtar bölgelerinin (Sμ ve Sφ) AID'ye bağımlı deaminasyonu, silme-rekombinasyona ve yeni bir antikor izotipinin (IgM'den IgE'ye) ifade edilmesine izin veren DSB oluşumunu teşvik eder. SHM sırasında, V bölgeleri (gri kutular) daha yüksek benzeşim Ig'ye yol açabilecek mutasyonlar (mavi çizgiler) biriktirir. Bu rakamın daha büyük bir sürümünü görüntülemek için lütfen buraya tıklayın.
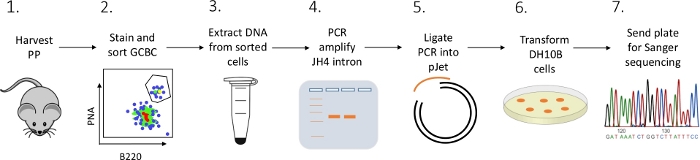
Şekil 2: GP'lerden yalıtılmış GCBC'lerdeki JH4 intronunun SHM'sini analiz etmek için iş akışı. Bu rakamın daha büyük bir sürümünü görüntülemek için lütfen buraya tıklayın.
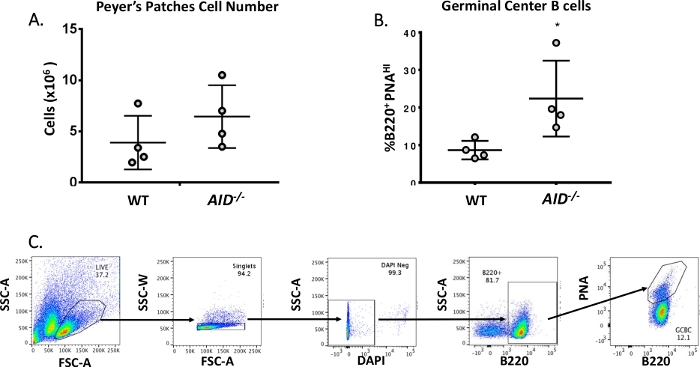
Şekil 3: PP GCBC'lerin karakterizasyonu. (A) WT ve AID-/- farelerden gelen toplam PP hücresi sayısı (genotip başına 4= 4). Hata çubukları ortalamadan standart sapmayı temsil eder. (B) WT ve AID-/- farelerin PC'lerinden elde edilen B220+PNAHI GCBC'lerin yüzdesi (n = genotip başına 4)36. Hata çubukları, öğrencinin t testini kullanarak ortalamadan standart sapmayı temsil eder, *p<0.05. (C) B220+PNAHI GCBC'leri PC'lerden sıralamak için temsili FACS çizimleri.
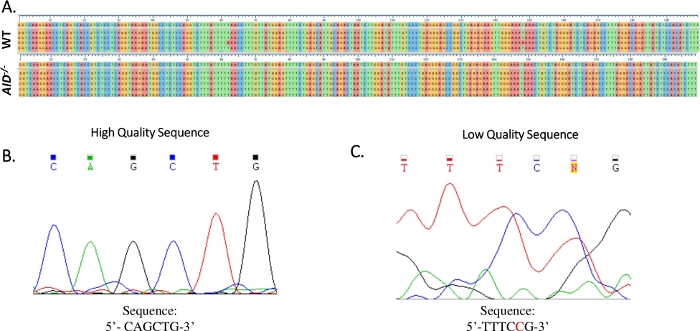
Şekil 4: JH4 Sanger sıra verilerinin analizi. (A) JH4 PCR ürününün Sanger sıra verilerinin WT (üstte) ve AID-/- (altta) GCBC'lerden referans genomik diziye (NG_005838) örnek dizi hizalamaları, numaralı onay işaretlerinin hemen altındaki sıradır. Hizalamalar Clustal Omega kullanılarak oluşturulmuştur. (B) Her taban için farklı zirveler gösteren yüksek kaliteli Sanger sıra verilerinin elektroferogramı. (C) Belirsiz tepeler ve belirtilmemiş bazlar (N) gösteren düşük kaliteli dizi verilerinin elektroferogramı. Kırmızı ile gösterilen nükleotid, sıralı metin dosyasında el ile açıklama eklenmelidir. Bu rakamın daha büyük bir sürümünü görüntülemek için lütfen buraya tıklayın.
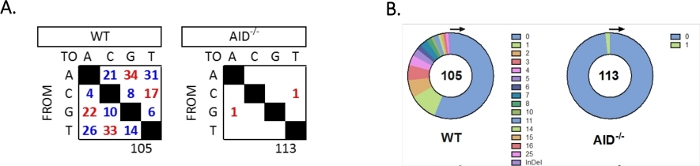
Şekil 5: WT ve AID-/- GCBC'lerde JH4 intronunda mutasyonların analizi. (A) Her genotip için A, C, G ve T tabanlarındaki toplam geçiş (kırmızı) ve transversiyon (mavi) mutasyon sayısı tablolarda özetlenmiştir. Analiz edilen toplam sıra sayısı tablonun altında belirtilir. (B) Her genotip için PCR amplicon başına mutasyon sayısı pasta grafiklerde gösterilmiştir. Bu rakam Choi ve ark.36 Copyright 2020'den değiştirilmiştir. Amerikan İmmünologlar Birliği, Inc. Bu rakamın daha büyük bir versiyonunu görüntülemek için lütfen buraya tıklayın.
| GCBC'ler için Boyama Kokteyli | Hacim: 500 μL | ||
| Antikor veya Boya | Florofor | Seyreltme | μL |
| B220 | Pe | 1000 | 0.5 |
| Streptavidin | APC-eFluor780 | 500 | 1 |
| Demir | Yok | 500 | 1 |
Tablo 1: GCBC'ler için boyama kokteylleri. Belirtilen seyreltmelerde belirtilen antikorların veya boyanın (italik olarak belirtilir) kokteyli, akış sitometrisi için PP hücrelerini 500 μL'de boyamak için kullanıldı.
| Tazminat için Tek Lekeler | Hacim: 500 μL | ||
| Antikor veya Boya | Florofor | Seyreltme | μL |
| B220 | Pe | 1000 | 0.5 |
| B220 | APC-eFluor780 | 750 | 0.67 |
| Demir | Yok | 500 | 1 |
Tablo 2: Tazminat için tek leke kontrolleri. Spektral çakışmayı telafi etmek için tek leke kontrolleri için belirtilen floroforlara konjuge edilen B220 antikorları kullanıldı.
| PCR #1 | ||||
| Reaktif | Birim | Termosikler Koşulları | ||
| 5x Arabellek | 4 μL | 1 | 95 °C | 3 dk |
| 10 mM dNTP | 2 μL | 2 | 94 °C | 30 sn |
| 10 μM J558FR3Fw | 1 μL | 3 | 55 °C | 30 sn |
| 10 μM VHJ558.2 | 1 μL | 4 | 72 °C | 1:30 dk |
| Yüksek DoğrulukTA DNA polimeraz | 0,25 μL | Döngü 2-4 9x | ||
| Dna | x (en az konsantre numuneye standartlaştırın) | |||
| H2O | 20 μL'ye kadar | 5 | 72 °C | 5 dk |
| PCR #2 geçmeden önce PCR ürününü H 2 O'da1:5seyreltin | ||||
Tablo 3: JH4 intronunun iç içe PCR'ı. İlk amplifikasyon reaksiyonu için PCR bileşenleri ve termosikler koşulları. İlk PCR ürününü 1:5 su ile seyreltin ve ikinci PCR için bu seyreltmenin 1 μL'sini kullanın.
| PCR #2 | ||||
| Reaktif | Birim | Termosikler Koşullar #2 | ||
| 5x Arabellek | 4 μL | 1 | 94 °C | 3 dk |
| 10 mM dNTP | 2 μL | 2 | 94 °C | 30 sn |
| 10 μM VHJ558.3 | 1 μL | 3 | 55 °C | 30 sn |
| 10 μM VHJ558.4 | 1 μL | 4 | 72 °C | 30 sn |
| Yüksek DoğrulukTA DNA polimeraz | 0,25 μL | Döngü 2-4 21x | ||
| Seyreltilmiş PCR#1 | 1 μL | |||
| H2O | 20 μL'ye kadar | 5 | 72 °C | 5 dk |
Tablo 4: İkinci PCR için PCR bileşenleri ve termosikler koşulları.
| Reaktif | Birim |
| 2x Arabellek | 10 μL |
| Saflaştırılmış PCR | x (en az konsantre numuneye standartlaştırın) |
| Künt uçlu plazmid | 1 μL |
| T4 DNA Ligase | 1 μL |
| H2O | 20 μL'ye kadar |
| Oda sıcaklığında 5 dakika veya gece boyunca 16ºC'de kuluçkaya yatır | |
Tablo 5: Ligasyon reaksiyon. Saflaştırılmış JH4 intron PCR ürününün plazmid içine ligasyonu için bileşenler.
| FACS Arabelleği |
| Isı, FBS'yi kullanmadan önce bir saat boyunca 56 °C'de devre dışı bırakın. Ek PBS, pH 7.4 (Gibco, #10010049) ve %2.5 (v/v) ısı inaktive FBS. 4°C'de saklayın. |
| DNA Ekstraksiyon Tamponu (100 mM Tris pH 8.0, 0.1 M EDTA, %0.5 (w/v) SDS) |
| 50 mL 1 M Tris pH 8.0, 100mL 0.5 M EDTA ve 12.5 mL% 20 SDS ekleyin. 500 mL'ye damıtılmış su ekleyin. Oda sıcaklığında saklayın. |
| TE Tampon (10 mM Tris pH 8.0, 1 mM EDTA) |
| 2,5 mL 1 M Tris pH 8,0 ve 500 mL 0,5 M EDTA ekleyin. 250 mL'ye damıtılmış su ekleyin. Oda sıcaklığında saklayın. |
Tablo 6: Tampon tarifleri.
| Oligonükleotidler Listesi | ||
| J558FR3Fw | 5'-GCCTGACATCTGAGGACTCTGC-3' | |
| VHJ558.2 | 5'-CTGGACTTTCGGTTTGGTG-3' | |
| VHJ558.3 | 5'-GGTCAAGGAACCTCAGTCA-3' | |
| VHJ558.4 | 5'-TCTAGACAGCAACTAC-3' | |
Tablo 7: Testte kullanılan oligonükleotidler.
Ek Şekil 1: Adım 5.4 tamamlandıktan sonra temsili agarose jel görüntüsü. JH4 intron iç içe PCR ürünü% 1.5 agarose jel üzerinde çözüldü ve 580 bp amplicon eksize edildi. WT PP, WT PP GCBC genomik DNA'sının ilk PCR için şablon olarak kullanıldığını ve AID PP'nin aid-/- PP GCBC genomik DNA'nın ilk PCR için şablon olarak kullanıldığını gösterir. ɸ şablonsuz PCR kontrolünü gösterir ve - agarose jel kuyusuna hiçbir şeyin yüklenmemiş olduğunu gösterir. Son şeritte 100 bp DNA merdiveni var. Bu rakamı indirmek için lütfen tıklayınız.
Heterojen bir B hücre popülasyonunun IgH ve IgL V kodlama dizileri içindeki SHM'yi karakterize etmek, her B hücresinin V(D)J rekombinasyonu34sırasında V kodlama segmentlerini benzersiz bir şekilde yeniden düzenlediği göz önüne alındığında bir zorluk sunar. Bu yazıda, GCBC'lerin JH4 intronunda mutasyonları tanımlamak için bir yöntem açıklanmaktadır. IgH lokusundaki son J kodlama segmentinin 3' 'ü bulunan JH4 intron, V bölgelerinin SHM'si için taşıyıcı olarak kullanılır (Şekil 1)31,33,34,35. Bu JH4 intron mutasyonlarını kataloglamak ve belirli genlerin mutasyonların üretimini veya düzenini nasıl etkilediğini değerlendirmek için PP GCBC'ler özellikle analiz edilir. Bu hücreler, bağırsak mikrobiyotası53tarafından kronik stimülasyonun bir sonucu olarak JH4 intron mutasyonlarını biriktirir. Ayrıca, bağışıklanmamış farelerin PC'lerinden B220+PNAHI GCBC'ler, bağışıklanmış hayvanlardan dalak GCBC'lerine kıyasla bir mutasyon spektrumlarına sahiptir54,55. Bununla birlikte, JH4 intronundaki mutasyonlar Ig benzeşimi olgunlaşması ile ilişkilendirilemez, çünkü bu mutasyonlar kodlama değildir.
SHM'nin Ig benzeşimini değiştirip değiştirmediğini belirlemek için, fareler CGG (tavuk gama globulin) veya KLH (anahtar deliği limpet hemocyanin)56'yakonjuge edilen NP (4-hidroksi-3-nitrophenylacetyl) gibi bir antijen ile intraperitoneally olarak bağışıklanmalıdır. Daha sonra, mRNA, NP'yi en sık tanıyan ve NP-CGG veyaNP-KLH bağışıklama 31 ,57 , 58 , 59,60'dan sonra mutasyona uğrayan V H186.2içindeki SHM'yi incelemek için dalak B220+PNAHI GCBC'lerden arındırılabilir. Triptofan-33'ün VH186.2'de bir lösin mutasyonu, Ig benzeşimini 10 kat59,60'a kadar artırdığı ve bu nedenle SHM ve klonal seçimin yüksek benzeşim Ig ürettiğinin bir göstergesi olduğu karakterize edilmiştir. NP7 ve NP20'ye özgü serum Ig titrelerinin ELISA tarafından ölçülmesi ve bağışıklama sırasında Ig'ye özgü NP7/NP20 oranının hesaplanması, V bölgelerinin SHM'sinden kaynaklanan Ig benzeşim olgunlaşmasını da belgelemektedir17,21,36. Her iki tahlil de VH186.2 kodlama dizilerindeki SHM'yi NP'ye özgü Ig benzeşimi olgunlaşmasındaki değişikliklerle ilişkilendirmek için kullanılabilir.
VH186.2'nin SHM'lerini veya JH4 intron'u analiz etmek için bağışıklanmış veya bağışıklanmamış hayvanlar kullanılsın, GCBC'ler doğru bir şekilde tanımlanmalıdır. B220+PNAHI GCBC'leri izole etmek için FACS tabanlı bir yaklaşım sunuyoruz. Alternatif olarak, GL7 antikoru 61 , 62 , 63,64 tarafından tanınan Fas vesülfatsızα2-6-sialyl-LacNAcantijeni, B220+Fas+GL7+65veya CD19+Fas+GL7+37olarak tanımlanan GCBC'leri izole etmek için de kullanılabilir. GL7 ifadesi, lenf düğümlerinin aktif GCBC'lerindePNA'yı yakındanyansıtır 64,65,66. GCBC'lere özgü antikor belirteçleri kullanmanın yanı sıra, boyama kokteylleri floroforun eksize edilmesini ve bir biyobelirtecinin algılanmasını en üst düzeye çıkarmalı ve floresan emisyonunun spektral çakışmasını en aza indirmelidir. Düşük seviyelerde ifade edilen antijenler, sağlam emisyon floresanlı bir florofora konjuge edilen bir antikor ile tespit edilmelidir67. Önerilen boyama protokolü, dört lazer (405nm, 488nm, 561nm, 633nm) ve 12 filtre ile donatılmış bir hücre sıralayıcısı üzerinde analiz için optimize edilmiştir; ancak filtre konfigürasyonları ve lazer kullanılabilirliği sitometreler arasında değişiklik gösterir. Protokolü reaktif ve ekipman kullanılabilirliğine göre değiştirmek için, okuyucu ek kaynaklara, çevrimiçi spektrum izleyicilerine ve yayınlanan literatür67 , 68,69,70,71,72,73'eatıftabulunulmaktadır. Burada açıklanan çok renkli boyama protokolü, sıralanmış hücre popülasyonlarının floresan emisyonunun yanlış tespiti yerine GCB'ler olduğundan emin olmak için spektral çakışmanın telafisini gerektirir. B220, açıklanan FACS(Tablo 1B)için yararlı bir boyama kontrolü görevi görür, çünkü PP'ler spektral çakışmanın uygun şekilde telafisini sağlayan ayırt edici B220 negatif ve pozitif popülasyonlara (Şekil 3C) sahip olacaktır. Şekil 3C'de sunulan gating stratejisi kılavuz olarak kullanılmalıdır. Akış sitometrisi çizimleri boyama koşullarına ve sitometre ayarlarına bağlı olarak değişebilir. Bununla birlikte, canlı hücrelerin% 4-10'u B220+PNAHI 35, 52olmalıdır.
PP GCBC'lerin JH4 intron içindeki tüm mutasyonlar, gözlemlenen mutasyonların PCR veya dizilemenin bir eseri değil, SHM'yi gerçekten yansıttığından emin olmak için doğrulanmalıdır. AID-/- B hücreleri diğer mutant fare modellerinde SHM fenotipini incelerken yararlı bir negatif kontrol görevi görür, çünkü bu hücreler SHM 17 ,19'utamamlayamaz. AID-/- GCBC'lerde JH4 intron mutasyon oranı (1.66x10-5 mutasyon/bp)20,21,36,37,38,50 ,5074, iç içe geçmiş PCR'deki DNA'yı yükseltmek için kullanılan yüksek kaliteli polimerazın (5,3x10-7 alt/baz/iki katına çıkarma)51,52 hata oranıyla karşılaştırılabilir. AID-/- fareler mevcut değilse, gözlemlenen mutasyon patinatını ve sıklığını yayınlanan literatürle karşılaştırın. Ig V bölgeleri baz çifti bölünmesi başına 10-3-10 -4 mutasyon biriktirir, bu da diğer gen loci73,75'in mutasyon oranından yaklaşık 106kat daha yüksektir. Sonuçlar hayvanın yaşına göre değişebilir76. Alternatif olarak, GCBC olmayanları işaretleyen B220+PNALO hücreleri, AID -/- farelerin yokluğunda negatif kontrol olarak kullanılabilir52. WT GCBC'lerdeki mutasyon sıklığı beklenenden düşükse, WT germline JH4 intronik dizisi orantısız bir şekilde temsil edilebilir. Bu durumda, GCBC'lerin uygun şekilde boyanıp sıralandığını ve PCR'lerin WT germline JH4 intron kontaminasyonundan arındırıldığından emin olun. Ayrıca, sıralı metin verilerindeki mutasyonların sıralama hatalarının eserleri olmadığından emin olmak için elektroferogramlardaki ham sıralama verileri ayrıntılı olarak analiz edilmelidir. Örneğin, kötü Sanger sıralama sonuçları sıra verilerinin güvenilirliğini azaltabilir (Şekil 4). Sanger serisi verilerinin bu kalite kontrolü, JH4 intron mutasyon analizinin doğruluğunu ve tekrarlanabilirliğini artıracaktır.
Yazarların açıklayacak bir şeyi yok.
Tasuku Honjo'ya AID-/- fareler için teşekkür ederiz. Bu çalışma, Ulusal Azınlık Sağlığı ve Sağlık Eşitsizlikleri Enstitüsü (5G12MD007603), Ulusal Kanser Enstitüsü (2U54CA132378) ve Ulusal Genel Tıp Bilimleri Enstitüsü (1SC1GM132035-01) tarafından desteklenmiştir.
| Name | Company | Catalog Number | Comments |
| 0.2 ml PCR 8-tube FLEX-FREE strip, attached clear flat caps, mixed | USA Scientific | 1402-4708 | |
| Ampicillin sodium salt | Fisher | BP1760-5 | |
| APC-eFluor780 anti-CD45R/B220 | eBioscience | 47-0452-80 | clone RA3-6B2 |
| BD FACSAria II | BD | 643186 | four lasers (405nm, 488nm, 561nm, 633nm) and 12 filters (PacBlue (450/50), AmCyan (502LP; 530/30), SSC (488/10), FITC (502LP; 530/30), PerCP-Cy5.5 (655LP; 695/40), PE (585/15), PE-Texas Red (600LP; 610/20), PE-Cy5 (630LP; 670/14), PE-Cy7 (735LP; 780/60), APC (660/20), Alexa700 (710LP; 730/45), APC-Cy7 (755LP; 780/60)) |
| BD slip tip 1mL syringe | Fisher | 14-823-434 | sterile |
| Biotinylated peanut agglutinin (PNA) | Vector Labs | B-1075-5 | |
| C57BL/6J mice | Jackson Laboratories | 664 | |
| Corning Falcon test tube with cell strainer snap cap | Fisher | 08-771-23 | |
| DAPI (4',6-Diamidino-2-Phenylindole, dihydrochloride) | Fisher | D1306 | 0.5 mg/ml |
| dNTP | NEB | N0447L | 10 mM |
| ElectroMAX DH10B competent cells | Fisher | 18-290-015 | |
| Falcon cell strainer 40mm | Fisher | 08-771-1 | |
| Falcon round-bottom polystyrene tubes (FACS tubes) | Fisher | 14-959-5 | |
| Falcon round-bottom polystyrene tubes (capped) | Fisher | 149591A | |
| Fetal bovine serum | R&D Systems (Atlanta Biologicals) | S11150 | |
| Gibco phosphate buffered saline PBS pH 7.4 | Fisher | 10-010-049 | |
| Glycogen | Sigma | 10901393001 | |
| Lasergene Molecular Biology (MegAlign Pro) | DNA Star | version 15 | |
| PE anti-CD45R/B220 | BD | 553090 | clone RA3-6B2 |
| Proteinase K | Fisher | BP1700-100 | |
| Q5 High-Fidelity DNA Polymerase | NEB | M0491L | |
| QIAquick Gel Extraction Kit | Qiagen | 28706 | |
| Seal-Rite 1.5mL microcentrifuge tubes | USA Scientific | 1615-5500 | |
| Streptavidin APC-eFluor 780 Conjugate | eBioscience | 47-4317-82 | |
| T4 DNA ligase | NEB | M020L | |
| Thermo Scientific CloneJET PCR Cloning Kit | ThermoFisher | FERK1231 | |
| Tissue culture plate 6 well | Fisher | 08-772-1B | sterile |
| Unlabeled anti-mouse CD16/CD32 (Fc block), BD | Fisher | BDB553142 | Clone 2.4G2 |
- Murphy, K., Weaver, C. . Janeyway's Immunobiology. , (2016).
- Alt, F. W., et al. VDJ recombination. Immunology Today. 13 (8), 306-314 (1992).
- Schatz, D. G., Ji, Y. Recombination centres and the orchestration of V (D) J recombination. Nature Reviews Immunology. 11 (4), 251-263 (2011).
- Oettinger, M. A., Schatz, D. G., Gorka, C., Baltimore, D. RAG-1 and RAG-2, adjacent genes that synergistically activate V (D) J recombination. Science. 248 (4962), 1517-1523 (1990).
- Berek, C., Berger, A., Apel, M. Maturation of the immune response in germinal centers. Cell. 67 (6), 1121-1129 (1991).
- Linterman, M. A., et al. Foxp3+ follicular regulatory T cells control the germinal center response. Nature Medicine. 17 (8), 975 (2011).
- Shulman, Z., et al. T follicular helper cell dynamics in germinal centers. Science. 341 (6146), 673-677 (2013).
- Good-Jacobson, K. L., et al. PD-1 regulates germinal center B cell survival and the formation and affinity of long-lived plasma cells. Nature Immunology. 11 (6), 535 (2010).
- Kerfoot, S. M., et al. Germinal center B cell and T follicular helper cell development initiates in the interfollicular zone. Immunity. 34 (6), 947-960 (2011).
- Chaudhuri, J., Alt, F. W. Class-switch recombination: interplay of transcription, DNA deamination and DNA repair. Nature Reviews Immunology. 4 (7), 541-552 (2004).
- Alt, F. W., Zhang, Y., Meng, F. L., Guo, C., Schwer, B. Mechanisms of programmed DNA lesions and genomic instability in the immune system. Cell. 152 (3), 417-429 (2013).
- Xu, Z., Zan, H., Pone, E. J., Mai, T., Casali, P. Immunoglobulin class-switch DNA recombination: induction, targeting and beyond. Nature Reviews Immunology. 12 (7), 517-531 (2012).
- Di Noia, J. M., Neuberger, M. S. Molecular mechanisms of antibody somatic hypermutation. Annual Reviews of Biochemistry. 76, 1-22 (2007).
- Peled, J. U., et al. The biochemistry of somatic hypermutation. Annual Review of Immunology. 26, 481-511 (2008).
- Liu, M., Schatz, D. G. Balancing AID and DNA repair during somatic hypermutation. Trends in Immunology. 30 (4), 173-181 (2009).
- Methot, S., Di Noia, J. Molecular Mechanisms of Somatic Hypermutation and Class Switch Recombination. Advances in Immunology. 133, 37-87 (2017).
- Muramatsu, M., et al. Class switch recombination and hypermutation require activation-induced cytidine deaminase (AID), a potential RNA editing enzyme. Cell. 102 (5), 553-563 (2000).
- Petersen-Mahrt, S. K., Harris, R. S., Neuberger, M. S. AID mutates E. coli suggesting a DNA deamination mechanism for antibody diversification. Nature. 418 (6893), 99 (2002).
- Revy, P., et al. Activation-induced cytidine deaminase (AID) deficiency causes the autosomal recessive form of the Hyper-IgM syndrome (HIGM2). Cell. 102 (5), 565-575 (2000).
- Petersen-Mahrt, S. DNA deamination in immunity. Immunological Reviews. 203 (1), 80-97 (2005).
- Rada, C., Di Noia, J. M., Neuberger, M. S. Mismatch recognition and uracil excision provide complementary paths to both Ig switching and the A/T-focused phase of somatic mutation. Molecular Cell. 16 (2), 163-171 (2004).
- Rada, C., et al. Immunoglobulin isotype switching is inhibited and somatic hypermutation perturbed in UNG-deficient mice. Current Biology. 12 (20), 1748-1755 (2002).
- Schrader, C. E., Vardo, J., Stavnezer, J. Role for mismatch repair proteins Msh2, Mlh1, and Pms2 in immunoglobulin class switching shown by sequence analysis of recombination junctions. The Journal of Experimental Medicine. 195 (3), 367-373 (2002).
- Martin, A., et al. Msh2 ATPase activity is essential for somatic hypermutation at AT basepairs and for efficient class switch recombination. The Journal of Experimental Medicine. 198 (8), 1171-1178 (2003).
- Imai, K., et al. Human uracil-DNA glycosylase deficiency associated with profoundly impaired immunoglobulin class-switch recombination. Nature Immunology. 4 (10), 1023-1028 (2003).
- Masani, S., Han, L., Yu, K. Apurinic/apyrimidinic endonuclease 1 is the essential nuclease during immunoglobulin class switch recombination. Molecular and Cellular Biology. 33 (7), 1468-1473 (2013).
- Guikema, J. E., et al. APE1-and APE2-dependent DNA breaks in immunoglobulin class switch recombination. The Journal of Experimental Medicine. 204 (12), 3017-3026 (2007).
- Schrader, C. E., Guikema, J. E., Wu, X., Stavnezer, J. The roles of APE1, APE2, DNA polymerase β and mismatch repair in creating S region DNA breaks during antibody class switch. Philosophical Transactions of the Royal Society B: Biological Sciences. 364 (1517), 645-652 (2009).
- Roa, S., et al. MSH2/MSH6 complex promotes error-free repair of AID-induced dU: G mispairs as well as error-prone hypermutation of A: T sites. PLoS One. 5 (6), 11182 (2010).
- Delbos, F., Aoufouchi, S., Faili, A., Weill, J. C., Reynaud, C. A. DNA polymerase η is the sole contributor of A/T modifications during immunoglobulin gene hypermutation in the mouse. The Journal of Experimental Medicine. 204 (1), 17-23 (2007).
- Maul, R. W., Gearhart, P. J. AID and somatic hypermutation. Advances in Immunology. 105, 159-191 (2010).
- Shen, H. M., Tanaka, A., Bozek, G., Nicolae, D., Storb, U. Somatic hypermutation and class switch recombination in Msh6-/- Ung-/- double-knockout mice. The Journal of Immunology. 177 (8), 5386-5392 (2006).
- Cheng, H. L., et al. Integrity of the AID serine-38 phosphorylation site is critical for class switch recombination and somatic hypermutation in mice. Proceedings of the National Academy of Sciences. 106 (8), 2717-2722 (2009).
- Lebecque, S. G., Gearhart, P. J. Boundaries of somatic mutation in rearranged immunoglobulin genes: 5'boundary is near the promoter, and 3'boundary is approximately 1 kb from V (D) J gene. The Journal of Experimental Medicine. 172 (6), 1717-1727 (1990).
- Jolly, C. J., Klix, N., Neuberger, M. S. Rapid methods for the analysis of immunoglobulin gene hypermutation: application to transgenic and gene targeted mice. Nucleic Acids Research. 25 (10), 1913-1919 (1997).
- Choi, J. E., Matthews, A. J., Michel, G., Vuong, B. Q. AID Phosphorylation Regulates Mismatch Repair-Dependent Class Switch Recombination and Affinity Maturation. The Journal of Immunology. 204 (1), 13-22 (2020).
- McBride, K. M., et al. Regulation of class switch recombination and somatic mutation by AID phosphorylation. The Journal of Experimental Medicine. 205 (11), 2585-2594 (2008).
- Liu, M., et al. Two levels of protection for the B cell genome during somatic hypermutation. Nature. 451 (7180), 841-845 (2008).
- Ross, M., Birbeck, M., Wills, V., Forrester, J., Davis, A. Peanut lectin binding properties of germinal centers of mouse lymphoid tissues. Nature. 284, 364-366 (1980).
- Zhang, J., MacLennan, I. C., Liu, Y. J., Lane, P. J. Is rapid proliferation in B centroblasts linked to somatic mutation in memory B cell clones. Immunology Letters. 18 (4), 297-299 (1988).
- Nieuwenhuis, P., Opstelten, D. Functional anatomy of germinal centers. American Journal of Anatomy. 170 (3), 421-435 (1984).
- Lau, A. W., Brink, R. Selection in the germinal center. Current Opinion in Immunology. 63, 29-34 (2020).
- Victora, G. D., Nussenzweig, M. C. Germinal centers. Annual Review of Immunology. 30, 429-457 (2012).
- Mesin, L., Ersching, J., Victora, G. D. Germinal center B cell dynamics. Immunity. 45 (3), 471-482 (2016).
- Reichert, R. A., Gallatin, W. M., Weissman, I. L., Butcher, E. C. Germinal center B cells lack homing receptors necessary for normal lymphocyte recirculation. The Journal of Experimental Medicine. 157 (3), 813-827 (1983).
- Rose, M., Birbeck, M., Wills, V., Forrester, J., Davis, A. Peanut lectin binding properties of germinal centers of mouse lymphoid tissues. Nature. 284, 364-366 (1980).
- Hamada, S., Fujita, S. DAPI staining improved for quantitative cytofluorometry. Histochemistry. 79 (2), 219-226 (1983).
- Otto, F. DAPI staining of fixed cells for high-resolution flow cytometry of nuclear DNA. Methods in Cell Biology. 33, 105-110 (1990).
- Butcher, E., et al. Surface phenotype of Peyer's patch germinal center cells: implications for the role of germinal centers in B cell differentiation. The Journal of Immunology. 129 (6), 2698-2707 (1982).
- Rogerson, B. J., Harris, D. P., Swain, S. L., Burgess, D. O. Germinal center B cells in Peyer's patches of aged mice exhibit a normal activation phenotype and highly mutated IgM genes. Mechanisms of Ageing and Development. 124 (2), 155-165 (2003).
- Potapov, V., Ong, J. L. Examining sources of error in PCR by single-molecule sequencing. PloS One. 12 (1), 0169774 (2017).
- Gonzalez-Fernandez, A., Milstein, C. Analysis of somatic hypermutation in mouse Peyer's patches using immunoglobulin kappa light-chain transgenes. Proceedings of the National Academy of Sciences. 90 (21), 9862-9866 (1993).
- Reboldi, A., Cyster, J. G. Peyer's patches: organizing B-cell responses at the intestinal frontier. Immunological Reviews. 271 (1), 230-245 (2016).
- Betz, A. G., Rada, C., Pannell, R., Milstein, C., Neuberger, M. S. Passenger transgenes reveal intrinsic specificity of the antibody hypermutation mechanism: clustering, polarity, and specific hot spots. Proceedings of the National Academy of Sciences. 90 (6), 2385-2388 (1993).
- Rada, C., Gupta, S. K., Gherardi, E., Milstein, C. Mutation and selection during the secondary response to 2-phenyloxazolone. Proceedings of the National Academy of Sciences. 88 (13), 5508-5512 (1991).
- Heise, N., Klein, U. Somatic Hypermutation and Affinity Maturation Analysis Using the 4-Hydroxy-3-Nitrophenyl-Acetyl (NP) System. Methods in Molecular Biology. 1623, 191-208 (2017).
- Smith, F., Cumano, A., Licht, A., Pecht, I., Rajewsky, K. Low affinity of kappa chain bearing (4-hydroxy-3-nitrophenyl) acetyl (NP)-specific antibodies in the primary antibody repertoire of C57BL/6 mice may explain lambda chain dominance in primary anti-NP responses. Molecular Immunology. 22 (10), 1209-1216 (1985).
- Takahashi, Y., Dutta, P. R., Cerasoli, D. M., Kelsoe, G. In situ studies of the primary immune response to (4-hydroxy-3-nitrophenyl) acetyl. V. Affinity maturation develops in two stages of clonal selection. The Journal of Experimental Medicine. 187 (6), 885-895 (1998).
- Allen, D., Simon, T., Sablitzky, F., Rajewsky, K., Cumano, A. Antibody engineering for the analysis of affinity maturation of an anti-hapten response. The EMBO Journal. 7 (7), 1995-2001 (1988).
- Cumano, A., Rajewsky, K. Clonal recruitment and somatic mutation in the generation of immunological memory to the hapten NP. The EMBO Journal. 5 (10), 2459-2468 (1986).
- Smith, K., Nossal, G., Tarlinton, D. M. FAS is highly expressed in the germinal center but is not required for regulation of the B-cell response to antigen. Proceedings of the National Academy of Sciences. 92 (25), 11628-11632 (1995).
- Hao, Z., et al. Fas receptor expression in germinal-center B cells is essential for T and B lymphocyte homeostasis. Immunity. 29 (4), 615-627 (2008).
- Cervenak, L., Magyar, A., Boja, R., László, G. Differential expression of GL7 activation antigen on bone marrow B cell subpopulations and peripheral B cells. Immunology Letters. 78 (2), 89-96 (2001).
- Naito, Y., et al. Germinal center marker GL7 probes activation-dependent repression of N-glycolylneuraminic acid, a sialic acid species involved in the negative modulation of B-cell activation. Molecular and Cellular Biology. 27 (8), 3008-3022 (2007).
- Olson, W. J., et al. Orphan Nuclear Receptor NR2F6 Suppresses T Follicular Helper Cell Accumulation through Regulation of IL-21. Cell Reports. 28 (11), 2878-2891 (2019).
- Dorsett, Y., et al. MicroRNA-155 suppresses activation-induced cytidine deaminase-mediated Myc-Igh translocation. Immunity. 28 (5), 630-638 (2008).
- Goetz, C., Hammerbeck, C., Bonnevier, J. . Flow Cytometry Basics for the Non-Expert. , (2018).
- Hawley, T. S., Herbert, D. J., Eaker, S. S., Hawley, R. G. . Flow Cytometry Protocols. , (2004).
- Costa, E., et al. A new automated flow cytometry data analysis approach for the diagnostic screening of neoplastic B-cell disorders in peripheral blood samples with absolute lymphocytosis. Leukemia. 20 (7), 1221-1230 (2006).
- McKinnon, K. M. Flow cytometry: An overview. Current Protocols in Immunology. 120 (1), 1-11 (2018).
- McKinnon, K. M. Multiparameter Conventional Flow Cytometry. Methods in Molecular Biology. , 139-150 (2018).
- Lucchesi, S., et al. Computational Analysis of Multiparametric Flow Cytometric Data to Dissect B Cell Subsets in Vaccine Studies. Cytometry Part A. 97, 259-267 (2019).
- Longerich, S., Tanaka, A., Bozek, G., Nicolae, D., Storb, U. The very 5' end and the constant region of Ig genes are spared from somatic mutation because AID does not access these regions. The Journal of Experimental Medicine. 202 (10), 1443-1454 (2005).
- Retter, I., et al. Sequence and characterization of the Ig heavy chain constant and partial variable region of the mouse strain 129S1. The Journal of Immunology. 179 (4), 2419-2427 (2007).
- Shen, H. M., Peters, A., Baron, B., Zhu, X., Storb, U. Mutation of BCL-6 gene in normal B cells by the process of somatic hypermutation of Ig genes. Science. 280 (5370), 1750-1752 (1998).
- Richter, K., et al. Altered pattern of immunoglobulin hypermutation in mice deficient in Slip-GC protein. Journal of Biological Chemistry. 287 (38), 31856-31865 (2012).
ABOUT JoVE
Copyright © 2024 MyJoVE Corporation. All rights reserved