Для просмотра этого контента требуется подписка на Jove Войдите в систему или начните бесплатную пробную версию.
Фреймворк с открытым исходным кодом для расчета массы терапевтических молекул на основе антител
В этой статье
Резюме
В этой статье описывается использование программного приложения mAbScale для расчета масс для белковой терапии на основе моноклональных антител.
Аннотация
Биотерапевтические массы являются средством проверки идентичности и структурной целостности. Масс-спектрометрия (МС) интактных белков или белковых субъединиц обеспечивает простой аналитический инструмент для различных стадий биофармацевтических разработок. Идентичность белка подтверждается, когда экспериментальная масса из МС находится в пределах заданного диапазона погрешности массы от теоретической массы. Несмотря на то, что существует несколько вычислительных инструментов для вычисления молекулярных масс белков и пептидов, они либо не были разработаны для непосредственного применения в биотерапевтических учреждениях, либо имеют ограничения доступа из-за платных лицензий, либо требуют загрузки белковых последовательностей на хост-серверы.
Мы разработали модульную процедуру расчета массы, которая позволяет легко определять средние или моноизотопные массы и элементный состав терапевтических гликопротеинов, включая моноклональные антитела (mAb), биспецифические антитела (bsAb) и конъюгаты антитело-лекарство (ADC). Модульный характер этой вычислительной платформы на основе Python позволит в будущем распространить эту платформу на другие модальности, такие как вакцины, гибридные белки и олигонуклеотиды, и эта структура также может быть полезна для изучения данных масс-спектрометрии сверху вниз. Создав автономное настольное приложение с открытым исходным кодом и графическим пользовательским интерфейсом (GUI), мы надеемся преодолеть ограничения, связанные с использованием в средах, где конфиденциальная информация не может быть загружена в веб-инструменты. В данной статье описаны алгоритмы и применение этого инструмента, mAbScale, к различным терапевтическим методам на основе антител.
Введение
За последние два десятилетия биотерапевтические препараты превратились в основу современной фармацевтической промышленности. Пандемия SARS-CoV2 и другие опасные для жизни состояния еще больше увеличили потребность в более быстрой и широкой разработке биофармацевтических молекул 1,2,3.
Биотерапевтическая молекулярная масса имеет решающее значение для идентификации молекулы в сочетании с другими аналитическими анализами. Неповрежденные и уменьшенные массы субъединиц используются на протяжении всего жизненного цикла открытия и разработки в рамках стратегий контроля, направленных на поддержание качества, как описано в QTPP (Quality Target Product Profile)4.
Аналитические разработки в биофармацевтической промышленности в значительной степени опираются на измерения массы для анализа интактной массы и глубокой характеристики с использованием пептидного картирования или мониторинга многоатрибутного метода (MAM). В основе этих методов, использующих современные платформы масс-спектрометрии (МС), лежит возможность обеспечения точных измерений массы (ЧСС/АМ) с высоким разрешением. Большинство приборов ЧСС/АМ дают точность измерения массы в диапазоне 0,5-5 ppm, которая зависит от диапазона масс. Возможность точного измерения масс неповрежденных больших молекул позволяет быстро и уверенно идентифицировать крупномолекулярные терапевтические средства. Поскольку изотопное разрешение не может быть достигнуто в типичных экспериментальных условиях для больших молекул (>10 кДа), для сравнения и идентификации необходимо рассчитать средние массы 5,6.
Типичный масс-спектр интактного или субъединичного белка представляет собой общий профиль протеоформы, который содержит сводную информацию о различных молекулярных формах, возникающих в результате посттрансляционных модификаций (ПТМ), и любых первичных структурных различиях, таких как клипсы или варианты последовательностей. Относительная простота и высокая производительность этих измерений делают их привлекательными для определения характеристик и в качестве средств контроля в процессе производства 7,8. Анализ данных для этих экспериментов обычно требует от пользователя определения пространства поиска молекулярных форм (диапазона ПТМ или других молекулярных форм). Для гликозилированных белков это пространство поиска в значительной степени обусловлено гетерогенностью гликоформа. Комбинации нескольких ПТМ, конфигураций дисульфидных связей и других вариаций вдоль первичной структуры делают расчет всех возможных молекулярных форм утомительной задачей. Поэтому ручной расчет возможных молекулярных форм является трудоемким и ресурсоемким процессом с высокой вероятностью человеческой ошибки.
Здесь мы представляем инструмент расчета массы, который был разработан с учетом наиболее важных характеристик биотерапевтических молекул, таких как мАТ, бсАБ, АЦП и т.д. Инструмент позволяет легко вводить переменные пространства поиска для согласованного вычисления масс и элементного состава. Модульный характер этого инструмента позволит в дальнейшем развивать его и применять для вычисления массы и сопоставления масс для других модальностей.
Модуль GUI позволяет пользователю указать входные данные для расчета массы, как показано на рисунке 1; В частности, пользователь вводит однобуквенные аминокислотные последовательности для легких и тяжелых цепочек антител. Общие модификации для циклизации N-конца с тяжелой цепью и клипирования лизина C-концевой включены в качестве флажков. Кроме того, химическая формула/элементный состав могут быть добавлены/вычтены из этих белковых цепей через соответствующее текстовое поле Chem Mod . Это позволяет пользователю гибко добавлять элементный состав, который включает в себя несколько посттрансляционных модификаций или полезную нагрузку из малых молекул в случае АЦП. Поскольку большинство терапевтических мАТ спроектированы таким образом, чтобы удалять сайты гликозилирования в легкой цепи, гликозилирование в легкой цепи остается необязательным и может быть задано с помощью флажка в графическом интерфейсе.
Типичным вариантом анализа интактной массы на антитела является анализ приведенной субъединичной массы, при котором легкая цепь отделяется от тяжелой цепи путем уменьшения межцепочечных дисульфидных связей. В зависимости от силы используемого восстановителя внутрицепочечные дисульфидные связи могут расщепляться или не расщепляться. Пользователи могут вводить общее количество дисульфидных связей в зависимости от подтипа IgG или в случае цистеин-конъюгированного АЦП9.
Приложение рассчитывает массы по принципу «снизу вверх», при этом сначала рассчитываются элементные составы для отдельных тяжелых и легких цепей. Далее N-концевая циклизация тяжелой цепи (HC) Lys-клиппинг учитывается путем корректировки рассчитанного элементного состава. Любые указанные химические модификации затем наносятся на тяжелые и/или легкие цепи. В зависимости от типа анализа и характера дисульфидной связи, заданного пользователем, количество водорода корректируется для двух полипептидных цепей. Массы гликозилированного HC и легкой цепи (LC) (опционально) рассчитываются на основе вводимых пользователем данных. Наконец, несколько масс HC и LC объединяются, и номера дисульфидных связей автоматически обновляются для расчета неповрежденной массы.
С более крупными молекулами, такими как интактные белки, моноизотопные массы не могут быть измерены из-за дефекта аддитивной массы при использовании масс-спектрометров с типичной разрешающей способностью. Вместо этого измеряются номинальные или средние массы 5,10,11,12,13. Средние массы элементов могут варьироваться в зависимости от источника, используемого для курируемых масс14,15. Хотя различия в массах элементов могут быть небольшими, они могут складываться в значительные значения для расчетов молекулярной массы больших молекул. Средние массы элементов, используемые по умолчанию в программном приложении, приведены в Дополнительной таблице 1. Для регулируемых сред, таких как биофармацевтические исследования и разработки (НИОКР), важно поддерживать постоянную молекулярную массу, поскольку изменения масс могут повлечь за собой изменения молекулярной сущности во время подачи заявок в регулирующие органы. Чтобы обеспечить единообразие в использовании элементарных масс, словарь элементарных масс включен в программный инструмент в виде текстового файла с разделителями-запятыми (csv): Element_Mass.csv (Дополнительный файл кодирования 1). Аналогичным образом, включен курируемый список гликановых композиций, обычно встречающихся на мАТ: Glycan.csv (Дополнительный файл кодирования 2). Оба файла сохраняются в той же папке, что и исполняемое приложение, и могут быть изменены пользователем для использования определенного списка элементных масс или библиотеки гликанов.
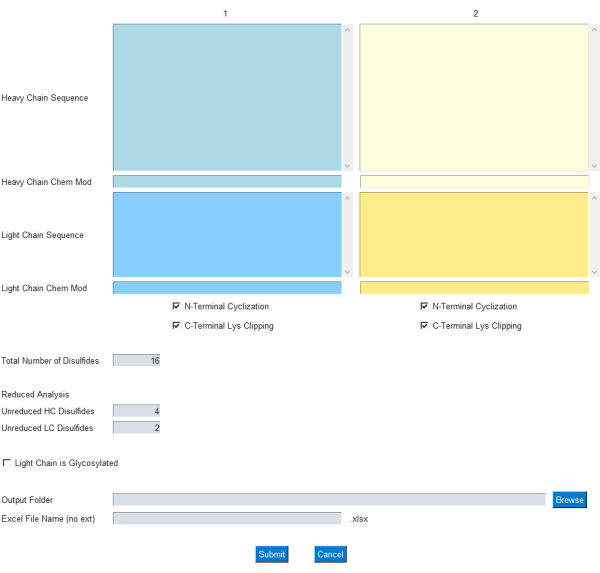
Рисунок 1: Графический интерфейс для приложения mAbScale. Модуль GUI позволяет пользователю указать входные данные для расчета массы. Пользователь вводит однобуквенные аминокислотные последовательности для легких и тяжелых цепочек антител. Общие модификации для циклизации N-конца тяжелой цепи и клипирования лизина C-концевой включены в качестве флажков. Химические формулы/элементные составы могут быть добавлены/вычтены через соответствующее текстовое поле Chem Mod . Пожалуйста, нажмите здесь, чтобы увидеть увеличенную версию этого рисунка.
протокол
Высокоуровневый рабочий процесс для mAbScale показан на рисунке 2. Каждый шаг имеет более сложные внутренние ветви принятия решений, циклы и комбинаторику. Подробный алгоритмический рабочий процесс, описывающий процесс расчета, представлен на дополнительном рисунке 1. Выходные данные приложения сохраняются в формате электронной таблицы в выбранной пользователем папке. Выходной файл состоит из нескольких отдельных листов, которые можно классифицировать как входные данные пользователя, расчеты молекулярной массы и ссылки на производные средней изотопной массы (пример выходных данных представлен в дополнительных таблицах). Рабочие листы, вводимые пользователем, включают в себя последовательности белковых аминокислот и другую информацию, введенную пользователем, усредненные массы элементов и массы гликанов, которые используются для расчета элементного состава и различной молекулярной массы. Таблицы расчета молекулярной массы включают химический состав различных форм, приведенную массу с гликозилированием и химической модификацией и без них, а также интактную массу с гликозилированием и химической модификацией и без них. Листы, содержащие массы полуантител, будут сгенерированы автоматически, если пользователь введет два разных HC и/или два разных LC на странице ввода пользователя, поскольку полуантитела являются первичными примесями, которые необходимо идентифицировать и количественно оценить относительно желаемого гетеродимера. Доступ к исходному коду mAbScale можно получить через следующий репозиторий: https://github.com/kkhatri99/mAbScale.
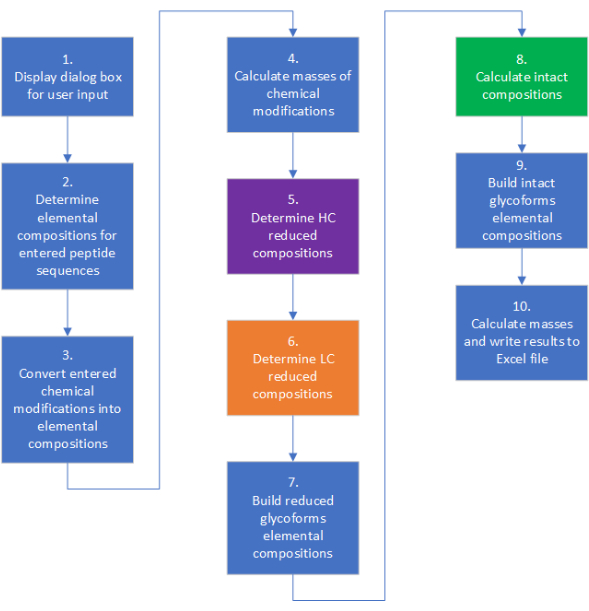
Рисунок 2: Обзор этапов расчета элементного состава и массы с помощью приложения. Цветовая кодировка может быть использована для связи с технологическим процессом, описанным на дополнительном рисунке 1. Пожалуйста, нажмите здесь, чтобы увидеть увеличенную версию этого рисунка.
1. Открытие приложения mAbscale
- Откройте программное приложение, дважды щелкнув по значку исполняемого файла.
2. Ввод последовательности
- Введите последовательности тяжелой и легкой цепей в соответствующие текстовые поля, помеченные цифрой 1 , без пробелов.
- Для bsAb добавьте дополнительные тяжелые или легкие цепочки во второй набор текстовых полей, помеченных цифрой 2. Оставьте 2 пустыми для мАТ с одинаковыми тяжелыми цепями и легкими цепями.
- Установите флажки N-Terminal Cyclization и/ или C-Terminal Clipping , если эти варианты тяжелых цепных клемм применимы.
- Добавьте любые химические модификации, включая линкер и полезную нагрузку для молекул ADC, в текстовые поля Heavy Chain Chem Mod и/или Light Chain Chem Mod .
- Задавайте модификации в виде элементных составов, таких как CaCl2. Модификация будет добавлена к соответствующей белковой субъединице или цепочке.
ПРИМЕЧАНИЕ: Химический состав также может быть вычтен из субъединицы или цепи путем добавления к элементному составу знака -. Например, -H2O вычтет молекулу воды из состава и массы субъединицы.
- Задавайте модификации в виде элементных составов, таких как CaCl2. Модификация будет добавлена к соответствующей белковой субъединице или цепочке.
3. Указание количества дисульфидных связей
- Укажите количество дисульфидных связей в молекулах белка в текстовом поле с пометкой Общее число дисульфидов.
- Введите количество невосстановленных HC-дисульфидов в текстовое поле Невосстановленные HC-дисульфиды и количество невосстановленных LC-дисульфидов в текстовое поле Невосстановленные LC-дисульфиды в зависимости от степени восстановления (полное или частичное).
ПРИМЕЧАНИЕ: Анализ приведенной массы субъединиц мАТ включает в себя восстановление/разделение тяжелых и легких цепей, связанных с дисульфидом. - Если гликозилирование присутствует в легкой цепи мАТ, установите флажок Light Chain is Glycosylated (Легкая цепь гликозилирована ).
4. Настройка выходной папки и запуск приложения
- Нажмите кнопку « Обзор », чтобы выбрать выходную папку для текстового поля «Выходная папка ».
- Введите имя выходного файла без расширения файла (автоматически сохраняется как .xlsx) в текстовое поле Файл Excel (без расширения).
- Нажмите на кнопку «Отправить », чтобы запустить приложение. Выходной файл можно найти в указанной папке.
ПРИМЕЧАНИЕ: Массы элементов и список гликанов могут быть настроены путем редактирования текстовых файлов с разделителями Element_Mass.csv (Дополнительный файл кодирования 1) и Гликан.csv (Дополнительный файл кодирования 2) соответственно. Эти файлы должны быть помещены в ту же папку, что и исполняемый файл mAbScale.exe (Supplementary Coding File 3) для выполнения приложения. Заявка будет закрыта автоматически после одного выполнения. Пользователю придется снова запустить приложение, если потребуется повторный расчет.
Результаты
Были выбраны различные мАТ, представляющие различные типы мАТ. Коммерчески доступный стандарт мАТ был выбран для представления обычного мАТ с идентичными тяжелыми цепями, идентичными легкими цепями и одним сайтом N-связанного гликозилирования в области Fc. Для расширения области приме...
Обсуждение
mAbScale предоставляет интуитивно понятный пользовательский интерфейс с гибкостью для изменения строительных блоков для расчетов массы и элементов. Ожидается, что пользователи будут иметь базовое представление о целевой молекуле, чтобы использовать приложение, получать правильные масс...
Раскрытие информации
Это программное обеспечение выпускается под лицензией Apache 2.0. Авторские права (2022) принадлежат компании GlaxoSmithKline Research & Development Limited. Все права защищены. Лицензируется в соответствии с лицензией Apache версии 2.0 («Лицензия»); Вы не можете использовать этот файл, кроме как в соответствии с Лицензией. Вы можете получить копию Лицензии по адресу http://www.apache.org/licenses/LICENSE-2.0. Если это не требуется применимым законодательством или не согласовано в письменной форме, программное обеспечение, распространяемое по Лицензии, распространяется на условиях «как есть», без каких-либо гарантий или условий, явных или подразумеваемых. Конкретные формулировки, регулирующие разрешения и ограничения в соответствии с Лицензией, см. в Лицензии. Л.С. является сотрудником компании GlaxoSmithKline (GSK). Т.Х. и К.К. разработали это программное обеспечение в качестве сотрудников GSK и в настоящее время являются партнерами Merck и Moderna соответственно.
Благодарности
Авторы благодарят Роберта Шустера за помощь в проверке данных.
Материалы
| Name | Company | Catalog Number | Comments |
| Acquity UPLC system | Waters Corp., Milford, MA | N/A | Modular system |
| Antibody-drug conjugate (ADC) | GlaxoSmithKline | N/A | Proprietory molecule |
| BEH 200 SEC column | Waters Corp., Milford, MA | 176003904 | |
| Bispecific mAb | GlaxoSmithKline | N/A | Proprietory molecule |
| Byos | Protein Metrics, Cupertino, CA | https://proteinmetrics.com/byos/ Version 4.5 | |
| GPMAW | GPMAW | http://www.gpmaw.com/ | |
| LC-MS grade water | Thermo Fisher Scientific, Waltham, MA | W6-1 | |
| mAb standard | Waters Corp., Milford, MA | 186009125 | Waters Humanized mAb Mass Check Standard |
| mAbScale | GlaxoSmithKline | Apache License, Version 2.0 | |
| Xevo G2 Q-TOF mass spectrometer | Waters Corp., Milford, MA | N/A | Modular system |
Ссылки
- Reichert, J. M., Valge-Archer, V. E. Development trends for monoclonal antibody cancer therapeutics. Nature Reviews Drug Discovery. 6 (5), 349-356 (2007).
- Kintzing, J. R., Filsinger Interrante, M. V., Cochran, J. R. Emerging strategies for developing next-generation protein therapeutics for cancer treatment. Trends in Pharmacological Sciences. 37 (12), 993-1008 (2016).
- Wang, M. -. Y., et al. SARS-CoV-2: Structure, biology, and structure-based therapeutics development. Frontiers in Cellular and Infection Microbiology. 10, 587269 (2020).
- ICH Q8 (R2) Pharmaceutical Development - Scientific Guideline. European Medicines Agency Available from: https://www.ema.europa.eu/en/ch-q8-r2-pharmaceutical-development-scientific-guideline (2018)
- Donnelly, D. P., et al. Best practices and benchmarks for intact protein analysis for top-down mass spectrometry. Nature Methods. 16 (7), 587-594 (2019).
- Gadgil, H. S., Pipes, G. D., Dillon, T. M., Treuheit, M. J., Bondarenko, P. V. Improving mass accuracy of high performance liquid chromatography/electrospray ionization time-of-flight mass spectrometry of intact antibodies. Journal of the American Society for Mass Spectrometry. 17 (6), 867-872 (2006).
- Beck, A., Sanglier-Cianférani, S., Van Dorsselaer, A. Biosimilar, biobetter, and next generation antibody characterization by mass spectrometry. Analytical Chemistry. 84 (11), 4637-4646 (2012).
- Camperi, J., Goyon, A., Guillarme, D., Zhang, K., Stella, C. Multi-dimensional LC-MS: the next generation characterization of antibody-based therapeutics by unified online bottom-up, middle-up and intact approaches. Analyst. 146 (3), 747-769 (2021).
- Liu, H., May, K. Disulfide bond structures of IgG molecules. mAbs. 4 (1), 17-23 (2012).
- Jakes, C., Füssl, F., Zaborowska, I., Bones, J. Rapid analysis of biotherapeutics using protein a chromatography coupled to orbitrap mass spectrometry. Analytical Chemistry. 93 (40), 13505-13512 (2021).
- Robotham, A. C., Kelly, J. F., Matte, A. Chapter 1 - LC-MS characterization of antibody-based therapeutics: Recent highlights and future prospects. Approaches to the Purification, Analysis and Characterization of Antibody-Based Therapeutics. , 1-33 (2020).
- Valeja, S. G., et al. Unit mass baseline resolution for an intact 148 kDa therapeutic monoclonal antibody by fourier transform ion cyclotron resonance mass spectrometry. Analytical Chemistry. 83 (22), 8391-8395 (2011).
- Fornelli, L., Ayoub, D., Aizikov, K., Beck, A., Tsybin, Y. O. Middle-down analysis of monoclonal antibodies with electron transfer dissociation orbitrap fourier transform mass spectrometry. Analytical Chemistry. 86 (6), 3005-3012 (2014).
- Berglund, M., Wieser, M. E. Isotopic compositions of the elements 2009 (IUPAC Technical Report). Pure and Applied Chemistry. 83 (2), 397-410 (2011).
- Wang, M., et al. The Ame2012 atomic mass evaluation. Chinese Physics C. 36 (12), 1603-2014 (2012).
- Peri, S., Steen, H., Pandey, A. GPMAW--A software tool for analyzing proteins and peptides. Trends in Biochemical Sciences. 26 (11), 687-689 (2001).
- Tipton, J. D., et al. Analysis of intact protein isoforms by mass spectrometry. The Journal of Biological Chemistry. 286 (29), 25451-25458 (2011).
- De Leoz, M. L. A., et al. interlaboratory study on glycosylation analysis of monoclonal antibodies: Comparison of results from diverse analytical methods. Molecular & Cellular Proteomics. 19 (1), 11-30 (2020).
- Cymer, F., Beck, H., Rohde, A., Reusch, D. Therapeutic monoclonal antibody N-glycosylation - Structure, function and therapeutic potential. Biologicals. 52, 1-11 (2018).
- Baker, P. R., Trinidad, J. C., Chalkley, R. J. Modification site localization scoring integrated into a search engine. Molecular & Cellular Proteomics. 10 (7), (2011).
- Chalkley, R. J., Clauser, K. R. Modification site localization scoring: Strategies and performance. Molecular & Cellular Proteomics. 11 (5), 3-14 (2012).
Перепечатки и разрешения
Запросить разрешение на использование текста или рисунков этого JoVE статьи
Запросить разрешениеThis article has been published
Video Coming Soon
Авторские права © 2025 MyJoVE Corporation. Все права защищены