Method Article
Stratégies d’optimisation de l’acquisition de données de tomographie électronique cryogénique
Dans cet article
Résumé
La demande croissante de collecte de données à grande échelle en tomographie électronique cryogénique nécessite des routines d’acquisition d’images à haut débit. Décrit ici est un protocole qui met en œuvre les développements récents de stratégies d’acquisition avancées visant à maximiser l’efficacité du temps et le débit de la collecte de données tomographiques.
Résumé
La tomographie électronique cryogénique (cryoET) est une méthode puissante pour étudier la structure 3D d’échantillons biologiques dans un état proche du natif. Le cryoET de pointe actuel combiné à l’analyse de la moyenne des sous-tomogrammes permet la détermination structurelle à haute résolution des complexes macromoléculaires présents en plusieurs copies dans les reconstructions tomographiques. Les expériences tomographiques nécessitent généralement l’acquisition d’une grande quantité de séries d’inclinaison au moyen de microscopes électroniques à transmission haut de gamme avec des coûts d’exploitation opérationnels importants. Bien que le débit et la fiabilité des routines d’acquisition de données automatisées se soient constamment améliorés au cours des dernières années, le processus de sélection des régions d’intérêt auxquelles une série d’inclinaison sera acquise ne peut pas être facilement automatisé et repose toujours sur la saisie manuelle de l’utilisateur. Par conséquent, la mise en place d’une session de collecte de données à grande échelle est une procédure fastidieuse qui peut réduire considérablement le temps de microscope restant disponible pour l’acquisition de séries d’inclinaison. Ici, le protocole décrit les implémentations récemment développées basées sur le package SerialEM et le logiciel PyEM qui améliorent considérablement l’efficacité temporelle du criblage de grille et de la collecte de données de série d’inclinaison à grande échelle. Le protocole présenté illustre comment utiliser les fonctionnalités de script SerialEM pour automatiser entièrement le mappage de grille, le mappage de carrés de grille et l’acquisition de séries d’inclinaison. En outre, le protocole décrit comment utiliser PyEM pour sélectionner des cibles d’acquisition supplémentaires en mode hors ligne après le lancement de la collecte automatisée des données. Pour illustrer ce protocole, son application dans le contexte de la collecte de données haut de gamme de la série d’inclinaison Sars-Cov-2 est décrite. Le pipeline présenté est particulièrement adapté pour maximiser l’efficacité temporelle des expériences de tomographie qui nécessitent une sélection minutieuse des cibles d’acquisition et en même temps une grande quantité de séries d’inclinaison à collecter.
Introduction
Les méthodes de microscopie électronique cryogénique (cryoEM) sont basées sur l’imagerie d’échantillons biologiques au moyen d’un microscope électronique à transmission (TEM) après leur vitrification rapide, un processus de préparation d’échantillons qui préserve les structures moléculaires et cellulaires des échantillons dans un état proche du natif et hydraté1,2. En tomographie électronique cryogénique (cryoET), un modèle 3D de l’échantillon vitrifié est obtenu en acquérant un certain nombre d’images de la même région d’intérêt à partir de différentes orientations, la série dite d’inclinaison, suivie de la reconstruction computationnelle du volume tomographique3. Cette technique d’imagerie avancée est devenue une méthode puissante pour l’étude structurelle des processus biologiques dans le contexte de leur environnement cellulaire natif4,5,6.
En plus de l’analyse ultrastructurale de l’échantillon vitrifié, des reconstructions à haute résolution de complexes macromoléculaires présents en plusieurs copies dans le volume tomographique peuvent être obtenues en appliquant un sous-tomgramme de5en moyenne . Cette approche de reconstruction est basée sur l’alignement itératif et la moyenne des sous-volumes contenant la structure d’intérêt et vise à augmenter le rapport signal/bruit et la résolution de la reconstruction finale7,8. La moyenne des sous-totogrammes repose sur la collecte et le traitement d’une grande quantité de données qui nécessitent souvent l’acquisition de centaines de séries d’inclinaison au moyen de TLET haut de gamme avec des coûts d’exploitation opérationnels onéreux.
Actuellement, la configuration de telles sessions cryoET automatisées est un processus fastidieux qui repose généralement sur la saisie manuelle de l’utilisateur9,10,11. En règle générale, les cibles sont identifiées par une inspection visuelle de la grille cartographiée, puis configurées pour la collecte automatisée de données. L’efficacité de l’utilisateur dans l’identification des points d’acquisition est souvent affectée par la nature de l’échantillon, devenant particulièrement difficile lors de l’analyse de macromolécules purifiées avec une concentration sous-optimale ou dans le cas d’événements rares dans des environnements cellulaires surpeuplés, impliquant l’utilisation d’approches corrélatives12. En outre, les flux de travail actuels nécessitent l’acquisition d’images lors de la configuration à différents grossissements qui seront ensuite utilisés pour la localisation précise et le centrage de la cible lors de l’acquisition automatisée11,13,14. Ces étapes de réaignement de haute précision sont cruciales pour les applications haute résolution, qui exigent que l’imagerie soit effectuée à fort grossissement et nécessitent des étapes de centrage précises pour conserver la région d’intérêt dans le petit champ de vision qui en résulte. Au total, plusieurs heures de chaque session de collecte de données sont engagées pour cette procédure fastidieuse au cours de laquelle le TEM n’est pas engagé dans l’acquisition de séries d’inclinaisons. Par conséquent, en fonction de la quantité de séries d’inclinaison requises, l’identification et la configuration des points d’acquisition peuvent avoir un impact considérable sur le temps de microscope disponible pour la collecte de données lors d’une session cryoET.
Vous trouverez ici un protocole optimisé basé sur le progiciel SerialEM15 et la dernière version du logiciel PyEM16 pour mapper les grilles, cartographier les carrés de grille, sélectionner des cibles et configurer l’acquisition automatisée de données pour la collecte de séries d’inclinaison à grande échelle. Le concept clé de cette approche est de fournir à SerialEM des images générées par calcul par PyEM pour chaque élément d’acquisition, appelées cartes virtuelles, pour la localisation et le centrage précis de la cible. Pour gagner du temps d’acquisition réel, la sélection des cibles ainsi que la création des cartes virtuelles sont effectuées hors ligne à l’aide d’une deuxième instance fictive de SerialEM, découpliant le processus de sélection des cibles d’acquisition des opérations TEM. Bien qu’il n’aborde pas la façon d’augmenter la qualité des données13,17 ou la vitesse d’acquisition de la série d’inclinaison18,19,ce protocole est principalement axé sur des stratégies visant à optimiser l’efficacité temporelle de la configuration automatisée de sessions cryoET à grande échelle. Par conséquent, la mise en œuvre du protocole présenté est destinée aux scientifiques qui établissent des flux de travail de collecte de données cryoET et qui souhaitent maximiser le rendement de l’acquisition automatisée de données en augmentant le temps de microscope disponible pour l’acquisition de séries d’inclinaison.
Protocole
Le protocole décrit ici fait partie d’un document plus complet produit par la plate-forme de service EMBL CryoEM qui comprend des instructions détaillées étape par étape et des captures d’écran illustrant l’ensemble de la procédure d’une session cryoET typique, y compris le chargement d’échantillons, la cartographie de la grille, le réglage du microscope, la configuration des points d’acquisition et la collecte automatisée de données. Le protocole complet peut être téléchargé sur le lien suivant : https://oc.embl.de/index.php/s/9OuTl8AazDkCNq0/download
1. Prérequis
- Installez SerialEM version 3.8 et configurez-le pour contrôler le microscope et le détecteur (http://bio3d.colorado.edu/SerialEM/betaHlp/html/setting_up_serialem.htm).
- Installez une instance fictive de SerialEMversion 3.8 (https://sphinx-emdocs.readthedocs.io/en/latest/serialEM-note-setup-dummy.html).
- Installez PyEM (https://git.embl.de/schorb/pyem).
2. Cartographie de la grille
- Chargez une cassette avec des grilles dans le chargeur automatique du microscope.
- Configurez des conditions d’imagerie adaptées à la cartographie de l’ensemble de la grille. Faites-le au grossissement le plus bas possible en tenant compte du champ de vision sur le détecteur utilisé (EFTEM SA 2250x). Enregistrez les conditions d’imagerie en tant qu’état d’imagerie SerialEM pour faciliter une utilisation ultérieure.
- Configurer le montage complet
- Ouvrez le menu SerialEM Navigator.
- Sélectionnez Montaging & Grids.
- Sélectionnez Configurer le montage complet.
- Démarrez le script Grid_Mapping. Laissez le script attendre que le chargeur automatique refroidisse ; faites un inventaire, puis mappez chaque grille trouvée par la procédure d’inventaire. Entrez un e-mail via le menu Tilt Series pour permettre au script d’envoyer facilement un e-mail une fois terminé.
- Enregistrer Navigator.
- Inspectez toutes les cartes de grille à partir de SerialEM Navigator et choisissez la grille à mapper davantage à un grossissement plus élevé.
REMARQUE: De nombreux TLET équipés d’un système de chargement automatique afficheront une rotation de la grille lorsqu’ils seront rechargés. Il est préférable de remapper n’importe quelle grille après l’avoir rechargée. Les systèmes alternatifs ne subissent généralement que quelques décalages, qui peuvent être corrigés dans SerialEM avec une procédure Shift To Marker.
3. Configurer le SerialEM à faible dose
- Définissez le grossissement des modes SerialEM Low Dose View et Preview (cela est nécessaire pour l’étape 6).
- Acquérir une image View et l’enregistrer en tant que carte dans le navigateur.
- Acquérez une image d’aperçu et enregistrez-la en tant que carte dans le navigateur.
- Réglez les deux modes sur le même binning (binning 4 est suggéré). Cela permet d’enregistrer les deux cartes dans une pile d’images.
- Dans la fenêtre SerialEM Navigator, remplacez l’étiquette de la carte View par View et l’étiquette de la carte Preview par Preview.
- Enregistrez et fermez le fichier du navigateur.
REMARQUE: Aucune cible n’est nécessaire pour les images initiales View et Preview, PyEM utilisera simplement leurs paramètres d’imagerie.
4. Cartographie carrée de la grille
- Configurez les conditions d’imagerie pour mapper les carrés de la grille. Il est très important de pouvoir voir l’échantillon d’intérêt et la distribution des billes fiduciaires. Pour garantir un contraste optimal pour les cartes carrées de grille, effectuez les opérations suivantes.
- Insérez une ouverture d’objectif.
- Le cas échéant, insérez la fente du filtre à énergie.
- Utilisez un défocalisez-vous de -100 μm.
- Écran pour de bons carrés de grille adaptés à une cartographie ultérieure. Après une inspection visuelle des carrés à partir de la carte de la grille, prenez des images de test de la place avec les conditions d’imagerie à utiliser pour les cartes carrées de la grille.
- Lorsqu’un bon carré est identifié, marquez son centre dans l’image de la carte de grille à l’aide de la fonction Ajouter des points du navigateur SerialEM.
- Une fois tous les points ajoutés, dans le navigateur SerialEM, appuyez sur Maj + A sur le premier point, puis sur Maj + A sur le dernier point.
REMARQUE: Tous les points ajoutés sont maintenant marqués par un A, ce qui signifie qu’ils sont tous des points d’acquisition. - Appuyez sur Maj + N (créer un nouveau fichier à l’élément) sur le premier point, puis à nouveau sur le dernier point. Dans la boîte de dialogue qui s’affiche, sélectionnez Images montées.
- Lorsque la boîte de dialogue de montage apparaît, configurez une taille de montage qui couvre un carré de grille. Cela dépend du grossissement et de la taille du maillage des grilles utilisées et nécessite généralement 2 x 2 à 4 x 4 montages. Donnez-lui un nom avec un numéro (par exemple, squaremap_01.mrc) pour permettre au SerialEM de numéroter automatiquement tous les fichiers par carré de grille.
- Démarrez le mappage de grille en ouvrant le menu SerialEM Navigator et cliquez sur Acquérir au niveau des éléments.
- Dans le menu contextuel, sélectionnez les options suivantes.
- Sélectionnez Rough Eucentricity.
- Sélectionnez Acquérir une image de carte.
- Sélectionnez Fermer les vannes de colonne à la fin.
- Sélectionnez Envoyer un e-mail à la fin.
5. Sélection des cibles
- Ouvrez une instance SerialEM factice. Cela peut être configuré sur le PC SerialEM qui contrôle le microscope ou sur un autre PC (de support) si les deux ordinateurs partagent une connexion réseau.
- Une fois le premier carré de grille mappé, utilisez l’option de menu Fusion de SerialEM Navigator pour afficher le montage dans l’instance serialEM factice.
- Double-cliquez sur la fenêtre Navigateur pour ouvrir la carte carrée de la grille.
- Recherchez la carte et utilisez l’option fictive SerialEM Navigator Ajouter des points pour ajouter des points d’acquisition d’image sur la cible d’intérêt.
- Lorsque vous avez terminé et après avoir mappé les nouveaux carrés, enregistrez le fichier Navigator et fusionnez à nouveau le Navigator ; continuer jusqu’à ce que tous les carrés de la grille soient mappés.
6. Générer des cartes virtuelles
- Encore une fois, fusionnez le fichier de navigateur avec l’instance fictive de SerialEM.
- Exécutez le script PyEM Virtual maps à partir du menu SerialEM factice, Outils et sélectionnez Virtual Anchor Maps. Cela peut prendre un certain temps en fonction de la taille et de la quantité des cartes carrées de la grille et du binning des cartes Afficher et Prévisualiser.
REMARQUE: PyEM démarre une fenêtre de commande qui se ferme automatiquement lorsque vous avez terminé, puis le nouveau fichier de navigateur peut être ouvert. Par carte montée contenant des points sélectionnés, PyEM écrit une seule carte fusionnée et toutes ses cartes View et Preview. Enfin, il écrit un nouveau fichier Navigator appelé <navigatorfilename>_automaps.nav.
7. Réglage du microscope
- Vérifiez le réglage du microscope. Pour garantir des performances de microscope correctes, utilisez le même grossissement et la même configuration de taille de faisceau pour l’acquisition de données, dans l’ordre suivant.
- Exécutez l’alignement sans Coma de SeriaLEM par CTF (tableau Zemlin).
- Insérez et centrez une ouverture d’objectif.
- Exécutez SerialEM Correct Astigmatism par CTF (auto-stigmate).
- Exécutez GIF Quick Tune (c’est-à-dire uniquement la mise au point à fente).
REMARQUE: Comme les étapes 7.1.1, 7.1.3 et 7.1.4 peuvent nécessiter un débit de dose plus élevé, seule la taille du point doit être modifiée; la taille du faisceau ne doit pas être modifiée car cela provoque une inclinaison du faisceau, ce qui rend les réglages incorrects. Les étapes 7.1.1, 7.1.2 et 7.1.3 sont semi-automatisées dans ce script accessible au public (https://serialemscripts.nexperion.net/script/47).
8. Configurer Navigator
- Dans SerialEM, ouvrez le nouveau fichier de navigation nommé _automaps.nav.
REMARQUE: V_yyyy sont les cartes d’affichage et P_yyyy sont les cartes d’aperçu. Les cartes d’aperçu sont définies comme points d’acquisition. - Dans la fenêtre SerialEM Navigator, désélectionnez tous les points A, sélectionnez le premier V_yyyy carte, sélectionnez Réduire,cliquez deux fois sur A et désélectionnez Réduire.
- Sélectionnez la première position V_yyyy, appuyezsur Maj + T , puis sélectionnez la toute dernière position V_yyyy, puis appuyez à nouveau sur Maj + T.
- Choisissez Images à cadre unique dans les propriétés du fichier à ouvrir dans la boîte de dialogue.
- Dans la boîte de dialogue Propriétés du fichier suivante, sélectionnez les paramètres souhaités en fonction des besoins d’imagerie et de la configuration de l’instrument.
- Lorsque vous y êtes invité, donnez un nom avec un numéro (par exemple, TS_001.mrc) et cliquez sur Enregistrer.
REMARQUE : SerialEM numérot automatiquement les noms de fichiers pour toutes les séries d’inclinaison. - Configurez le contrôleur de la série d’inclinaison pour la première position TS. Lorsque vous avez terminé, cliquez sur OK pour définir ces paramètres pour toutes les séries d’inclinaison après cet élément d’acquisition. Toutes les cartes d’aperçu sont maintenant sélectionnées comme TS (Tilt Series) avec le nom de fichier numéroté TS_xxx.mrc.
REMARQUE: On peut modifier les paramètres manuellement plus tard en utilisant la fonction Navigator TSparams; les modifications seront appliquées pour tous les éléments vers le bas de la liste. L’utilisateur a la possibilité d’exécuter un script personnalisé au lieu de la série d’inclinaison.
9. Définissez les positions de mise au point / piste
- Définissez la distance de mise au point/suivi pour chaque cible si nécessaire (assurez-vous que SerialEM Low Dose est activé).
- Double-cliquez sur la carte d’affichage pour la charger.
- Sélectionnez l’aperçu de la carte dans la liste Navigateur.
- Sélectionnez Modifier le focus dans la fenêtre du navigateur.
- Dans le panneau de commande à faible dose, désélectionnez Rotation de l’axe inter-zones pour positionner Trial et Focus le long de l’axe d’inclinaison de la scène.
- Cliquez sur la région souhaitée dans la carte de vue chargée pour définir la position de mise au point/essai de cette série d’inclinaisons.
- Assurez-vous que l’élément Navigator a TSP défini maintenant ; répétez la procédure pour tous les éléments.
REMARQUE : Les positions de mise au point/piste sont automatiquement copiées vers le bas dans le navigateur. Par conséquent, si la position de mise au point/piste de l’élément précédent est du bon côté et de la bonne distance, il n’est pas nécessaire de la modifier pour l’élément en cours.
10. Configurer des scripts supplémentaires
- Deux scripts gèrent la plage Focus : pretomo et duringtomo. Le script pretomo s’exécute avant chaque série d’inclinaison et le script pendanttomo pendant chaque inclinaison.
- Modifiez la plage de mise au point dans le script pretomo.
- Dans le menu SerialEM Tilt Series, cochez Exécuter le script dans TS et sélectionnez le numéro de script du script duringtomo.
11. Exécuter
- Vérifiez le niveau du réservoir d’azote.
- Vérifiez si l’arrêt turbo du chargeur automatique est sélectionné.
- Vérifiez l’espace libre de stockage des données.
- Dans le menu Fichier SerialEM, désélectionnez l’enregistrement continu pour le fichier journal et fermez tout fichier journal actuellement ouvert. Chaque série d’inclinaison aura son propre fichier journal.
- Dans le menu Navigateur, cliquez sur Acquérir dans Éléments.
- Exécutez le script PreTomo.
- Sélectionnez Tâche principale Acquérir une série d’inclinaisons.
- Sélectionnez Exécuter le script après PostTomo.
- Sélectionnez Fermer les vannes de colonne à la fin.
- Sélectionnez Envoyer un e-mail à la fin.
- Cliquez sur GO.
REMARQUE: SerialEM enverra un e-mail par série d’inclinaison, avec succès ou erreur; cependant, une erreur peut également signifier que la plage d’inclinaison complète n’a pas été atteinte.
Résultats
Cette procédure a été utilisée pour acquérir la série d’inclinaison Sars-Cov-2 décrite dans Turonova et al. 202020; l’ensemble de l’ensemble de données a été produit à l’aide de trois grilles distinctes au cours de trois séances de microscopie à l’EMBL Heidelberg. L’étude actuelle se concentrera sur et décrira la première session de 3 jours (~ 72 h) exécutée avec la première grille.
Après que l’ensemble de la grille a été cartographié à faible grossissement (~10 min, voir étape 2), 71 carrés appropriés ont été sélectionnés sur la carte de la grille, et des cartes à grossissement moyen(cartes carrées)ont été acquises avec des paramètres (grossissement, exposition, défocalisage) qui permettent la visualisation directe et l’identification de l’échantillon d’intérêt, les coronavirus dans ce cas (voir étape 4) (Figure 1A). Le temps d’acquisition était d’environ 3 min par carré, 3 h 45 min au total.
Dès la création de la première carte carrée, une instance SerialEM factice (sans aucun contrôle sur caméra ou microscope) a été ouverte sur un ordinateur séparé pour visualiser la carte carrée et ajouter des points sur des cibles adaptées à l’acquisition de séries d’inclinaison (voir étape 5)(Figure 1B). Les cartes carrées nouvellement acquises ont été récupérées en fusionnant le navigateur SerialEM factice actuel avec le navigateur de l’instance SerialEM acquérante. Après environ 2 h d’acquisition et de sélection de carrés de grille, 50 cibles initiales ont pu être identifiées.
Une fois les acquisitions de cartes carrées terminées, SerialEM à faible dose a été mis en place et des images de référence View et Preview ont été prises et enregistrées sous forme de cartes (voir étape 3). Ces dernières cartes pourraient ensuite être utilisées immédiatement sur l’instance fictive de SerialEM pour générer, à partir des images de carte carrée correspondantes, la vue virtuelle (Figure 1C)et la prévisualisation virtuelle (Figure 1D)des cartes des 50 cibles sélectionnées avec la suite logicielle PyEM, pour un temps de traitement d’environ 30 min (voir étape 6). Ce temps de traitement sur la session fictive SerialEM a été utilisé pour effectuer les derniers préparatifs du microscope pour l’acquisition: réglage du filtre d’énergie, acquisition d’une nouvelle image de référence de gain de caméra, alignement sans astigmatisme et coma de l’objectif.
Une fois le réglage du microscope terminé et les cartes virtuelles des 50 cibles initiales générées, le navigateur SerialEM réel à utiliser pour l’acquisition a été mis en place (voir étape 8), les positions de mise au point et de piste ont été définies (étape 9) et l’acquisition de la série d’inclinaisons a pu être lancée (voir étapes 10 et 11). Les cartes De la vue virtuelle ( Figure1C) ont été utilisées pour un centrage initial de la cible (Figure 1E) suivi d’un centrage final effectué au grossissement d’acquisition de la série d’inclinaison réelle (Figure 1F) à l’aide de la carte Virtual Preview (Figure 1D).
En commençant par la cartographie de la grille à 9h30 du matin, l’acquisition de la série d’inclinaison pour les 50 cibles initiales a commencé vers 15h00. Avec les paramètres utilisés pour l’acquisition tomographique (voir la référence pour plus de détails), une série d’inclinaison a pris environ 20 minutes à acquérir, avec suffisamment de cibles pour passer toute la nuit. Pendant que l’acquisition était en cours, le reste des cartes carrées pouvait être inspecté et d’autres cibles ajoutées, toujours hors ligne via l’instance fictive SerialEM. 121 autres cibles ont été sélectionnées parmi les cartes carrées restantes et ajoutées au navigateur SerialEM d’acquisition après la création de cartes virtuelles pour ces nouvelles cibles, suffisamment pour fonctionner jusqu’à la fin de la session de 72 heures.
Cette procédure (résumée à la figure 2)a permis, en une seule journée ouvrable, la mise en place de 171 cibles pour des acquisitions tomographiques automatisées pour une séance de microscope de 72 h (3 jours).

Figure 1: Exemple de carte carrée avec des cartes virtuelles représentatives et des acquisitions correspondantes après centrage. (A) Carte carrée représentative d’une grille cryoEM Sars-Cov-2 utilisée dans Turonova et al.20. Quatre régions d’intérêt sont marquées d’une croix rouge. Le grossissement du microscope est de 2 250x. (B) Recadrez à partir de la carte carrée en mettant en évidence les zones qui ont été utilisées pour générer les cartes Vue virtuelle (orange) et Aperçu virtuel (jaune) pour la cible sélectionnée (croix rouge) (C) Carte Vue virtuelle. (D) Carte d’aperçu virtuel. (E) Acquisition de la vue réelle après centrage en utilisant la carte de la vue virtuelle comme référence. Le grossissement du microscope est de 11 500x. (F) Acquisition d’inclinaison de 0° à partir de la série d’inclinaison après centrage en utilisant la carte Virtual Preview comme référence. Le grossissement du microscope est de 64 000x. Veuillez cliquer ici pour voir une version agrandie de cette figure.
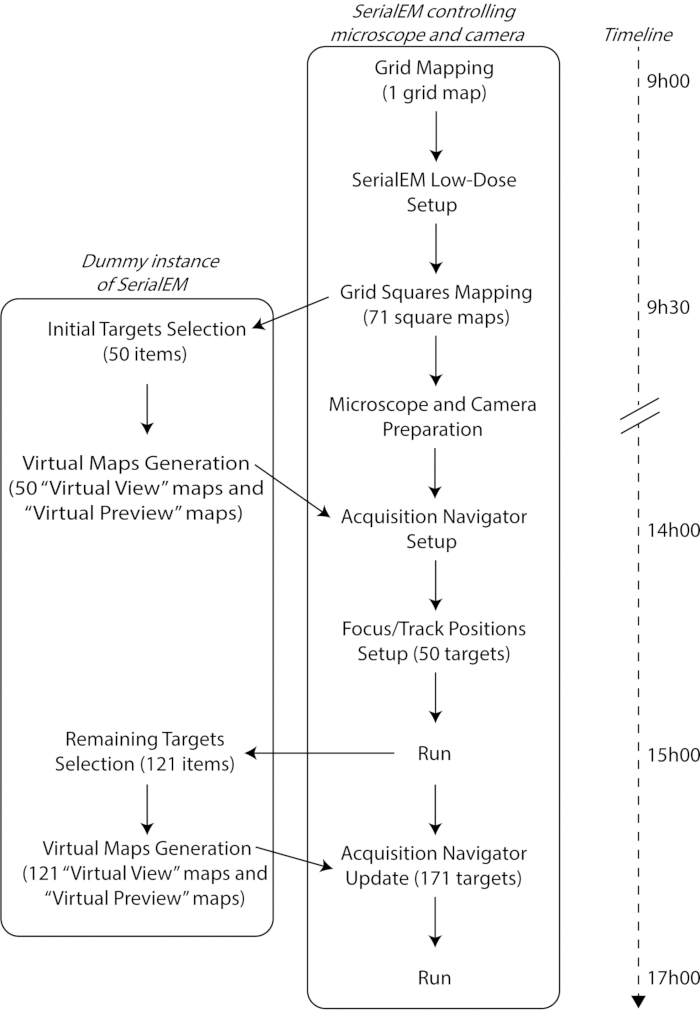
Figure 2: Workflow de session CryoET à l’aide de SerialEM avec les outils PyEM. Veuillez cliquer ici pour afficher une version agrandie de cette figure.
Discussion
D’une technique de niche, cryoET a maintenant mûri en une méthode répandue pour effectuer des études structurelles au niveau cellulaire et moléculaire avec une résolution atteignable sans précédent21,22. La demande toujours croissante d’imagerie cryoEM a mis à rude épreuve les ressources limitées disponibles pour accéder à cette technologie. Malgré l’ouverture d’un certain nombre d’installations cryoEM nationales et les efforts des instituts scientifiques pour augmenter leur capacité de GDT afin de répondre aux besoins de la communauté dans le monde entier, l’accès aux instruments cryoEM est encore limité et le temps disponible pour la collecte de données doit donc être utilisé efficacement par les utilisateurs pour maximiser le rendement de chaque session de microscopie. La nécessité d’acquérir des centaines de séries d’inclinaison, combinée au temps limité disponible pour la collecte de données, a nécessité de nouvelles routines d’acquisition d’images pour obtenir un meilleur débit sans compromettre la qualité des données. Les développements récents dans les flux de travail de matériel et d’imagerie ont considérablement augmenté la vitesse d’acquisition de la série d’inclinaison18,19, entraînant ainsi un changement radical du rapport entre le temps passé à mettre en place un point d’acquisition et le temps nécessaire pour l’acquisition réelle de la série d’inclinaison. Dans l’ensemble, la procédure de mise en place des points d’acquisition devient l’un des principaux goulots d’étranglement pour le débit réalisable des sessions cryoET.
Le protocole optimisé présenté ici nous a permis de mettre en place, en mode hors ligne, 171 positions pour l’acquisition tomographique automatisée au cours du premier jour d’une session cryoET pendant que le microscope était activement engagé dans d’autres opérations (par exemple, la cartographie carrée, le réglage et l’acquisition automatisée de séries d’inclinaison), sans affecter le temps de microscope disponible pour la collecte de données. En plus de maximiser le débit d’une session cryoET, ce pipeline réduit considérablement le temps investi par l’utilisateur dans la phase préparatoire d’une session de collecte de données automatisée. Dans le protocole décrit, l’utilisateur est invité à parcourir les carrés de grille cartographiés pour identifier les régions d’intérêt appropriées et les ajouter au Serial EM Navigator en tant que points d’acquisition. Toutes les cibles seront ensuite automatiquement traitées par lots au sein de SerialEM par l’outil PyEM pour la production des cartes virtuelles16. L’approche computationnelle présentée est donc considérablement plus rapide que l’acquisition de cartes d’ancrage réelles en éliminant les périodes d’attente associées au mouvement de la scène, à l’acquisition d’images, au changement des conditions d’imagerie entre la vue et l’aperçu, et par la réitération éventuelle de ces étapes tout en se centrant à un grossissement élevé. De plus, comme chaque image acquise entraîne une accumulation de dose d’électrons sur l’objet d’intérêt23,l’utilisation de cartes virtuelles pour le réalignement précis des cibles réduit les dommages causés par le rayonnement introduits dans la phase préparatoire d’une session cryoET avant l’acquisition réelle de la série d’inclinaisons. Le protocole décrit ici utilise des cartes virtuelles à grossissement intermédiaire et élevé (Preview et View, respectivement) pour le réalignement de la cible avant l’acquisition de la série d’inclinaison. Cette procédure peut facilement être modifiée pour n’utiliser que le grossissement intermédiaire De l’image lorsque la précision de l’alignement est moins importante, par exemple, dans le cas de grandes structures où la précision cible ultime est moins préoccupante10 ou pour des échantillons d’analyse de particules uniques qui sont mal répartis sur la cryo-grille nécessitant la sélection manuelle par l’utilisateur de chaque point d’acquisition24, 25. Enfin, une approche basée sur l’utilisation hors ligne d’une instance SerialEM factice facilite également la mise en place de points d’acquisition via une connexion à distance en minimisant le besoin de la présence physique de l’utilisateur au microscope, permettant ainsi plus de flexibilité en termes d’organisation opérationnelle de l’installation.
Les progrès récents de la technologie et des méthodes pour cryoET ont considérablement amélioré la vitesse et la fiabilité des sessions de collecte de données automatisées. Toutefois, d’autres développements sont nécessaires pour aborder les étapes restantes de limitation des taux de cette méthode. Plus particulièrement, l’étape initiale de la cartographie en grille et en carré devient maintenant l’un des principaux goulots d’étranglement de la configuration de la session, générant ainsi le besoin d’améliorations matérielles visant à augmenter la vitesse des mouvements des étages du microscope et de l’acquisition d’images par les détecteurs d’électrons directs. En outre, le développement d’approches d’apprentissage automatique pour automatiser entièrement le processus d’identification des cibles sera crucial pour éliminer le besoin d’inspection visuelle des utilisateurs pour sélectionner les régions d’intérêt, une procédure longue qui repose sur l’expertise des utilisateurs.
Déclarations de divulgation
Les auteurs ne déclarent aucun conflit d’intérêts.
Remerciements
Nous reconnaissons le soutien de l’unité de biologie structurale et computationnelle et de l’installation centrale de microscopie électronique du Laboratoire européen de biologie moléculaire à Heidelberg, en Allemagne, ainsi que d’iNEXT-Discovery (numéro de projet 871037). Nous sommes extrêmement reconnaissants de l’excellent soutien de l’auteur du progiciel SerialEM, le professeur David Mastronarde. Nous remercions également Herman Fung pour la lecture critique du manuscrit.
matériels
| Name | Company | Catalog Number | Comments |
| Transmission Electron Microscope | Our protocol is only based on computational workflows. The user will only need acess to a TEM of any kind |
Références
- Adrian, M., Dubochet, J., Lepault, J., McDowall, A. W. Cryo-electron microscopy of viruses. Nature. 308 (5954), 32-36 (1984).
- Cheng, Y. Single-particle cryo-EM-How did it get here and where will it go. Science. 361 (6405), 876-880 (2018).
- Lucic, V., Forster, F., Baumeister, W. Structural studies by electron tomography: From Cells to Molecules. Annual Review of Biochemistry. 74 (1), 833-865 (2005).
- Pfeffer, S., Mahamid, J. Unravelling molecular complexity in structural cell biology. Current Opinion in Structural Biology. 52, 111-118 (2018).
- Schur, F. K. M. Toward high-resolution in situ structural biology with cryo-electron tomography and subtomogram averaging. Current Opinion in Structural Biology. 58, 1-9 (2019).
- Bohning, J., Bharat, T. A. M. Towards high-throughput in situ structural biology using electron cryotomography. Progress in Biophysics and Molecular Biology. , (2020).
- Briggs, J. A. Structural biology in situ--the potential of subtomogram averaging. Current Opinion in Structural Biology. 23 (2), 261-267 (2013).
- Wan, W., Briggs, J. A. G. . Methods in Enzymology. 579, 329-367 (2016).
- Tan, Y. Z., Cheng, A., Potter, C. S., Carragher, B. Automated data collection in single particle electron microscopy. Microscopy. 65 (1), 43-56 (2016).
- Morado, D. R., Hu, B., Liu, J. Using Tomoauto: A protocol for high-throughput automated cryo-electron tomography. Journal of Visualized Experiments: JoVE. (107), e53608 (2016).
- Resch, G. P. . Methods in Cell Biology. 152, 135-178 (2019).
- Bharat, T. A., Kukulski, W. . Correlative Imaging: Focusing on the Future. , 137-153 (2019).
- Hagen, W. J. H., Wan, W., Briggs, J. A. G. Implementation of a cryo-electron tomography tilt-scheme optimized for high resolution subtomogram averaging. Journal of Structural Biology. 197 (2), 191-198 (2017).
- O'Toole, E., vander Heide, P., McIntosh, R. J., Mastronarde, D. . Cellular Imaging: Electron Tomography and Related Techniques. , 95-116 (2018).
- Mastronarde, D. N. Automated electron microscope tomography using robust prediction of specimen movements. Journal of Structural Biology. 152 (1), 36-51 (2005).
- Schorb, M., Haberbosch, I., Hagen, W. J. H., Schwab, Y., Mastronarde, D. N. Software tools for automated transmission electron microscopy. Nature Methods. 16, 471-477 (2019).
- Turonova, B., et al. Benchmarking tomographic acquisition schemes for high-resolution structural biology. Nature Communications. 11 (1), 876 (2020).
- Chreifi, G., Chen, S., Metskas, L. A., Kaplan, M., Jensen, G. J. Rapid tilt-series acquisition for electron cryotomography. Journal of Structural Biology. 205 (2), 163-169 (2019).
- Eisenstein, F., Danev, R., Pilhofer, M. Improved applicability and robustness of fast cryo-electron tomography data acquisition. Journal of Structural Biology. 208 (2), 107-114 (2019).
- Turonova, B., et al. In situ structural analysis of SARS-CoV-2 spike reveals flexibility mediated by three hinges. Science. 370 (6513), 203-208 (2020).
- O'Reilly, F. J., et al. In-cell architecture of an actively transcribing-translating expressome. Science. 369 (6503), 554-557 (2020).
- Tegunov, D., Xue, L., Dienemann, C., Cramer, P., Mahamid, J. Multi-particle cryo-EM refinement with M visualizes ribosome-antibiotic complex at 3.7 Å inside cells. Nature Methods. 18, 186-193 (2020).
- Karuppasamy, M., Karimi Nejadasl, F., Vulovic, M., Koster, A. J., Ravelli, R. B. G. Radiation damage in single-particle cryo-electron microscopy: effects of dose and dose rate. Journal of Synchrotron Radiation. 18 (3), 398-412 (2011).
- Liberta, F., et al. Cryo-EM fibril structures from systemic AA amyloidosis reveal the species complementarity of pathological amyloids. Nature Communications. 10 (1), 1104 (2019).
- Radamaker, L., et al. Cryo-EM structure of a light chain-derived amyloid fibril from a patient with systemic AL amyloidosis. Nature Communications. 10 (1), 1103 (2019).
Réimpressions et Autorisations
Demande d’autorisation pour utiliser le texte ou les figures de cet article JoVE
Demande d’autorisationExplorer plus d’articles
This article has been published
Video Coming Soon