Method Article
Criblage à haut débit pour obtenir des résultats cristallins pour la cristallographie des protéines
Dans cet article
Résumé
Ce protocole détaille le criblage de cristallisation à haut débit, allant de la préparation de 1 536 microplaques de dosage à la fin d’une fenêtre expérimentale de 6 semaines. Des détails sont inclus sur la configuration de l’échantillon, l’imagerie obtenue et la façon dont les utilisateurs peuvent effectuer des analyses à l’aide d’une interface utilisateur graphique activée par l’intelligence artificielle pour identifier rapidement et efficacement les conditions de cristallisation macromoléculaire.
Résumé
La cristallographie aux rayons X est la technique la plus couramment utilisée pour discerner les structures macromoléculaires, mais l’étape cruciale de cristallisation d’une protéine en un réseau ordonné se prêtant à la diffraction reste difficile. La cristallisation des biomolécules est en grande partie définie expérimentalement, et ce processus peut être laborieux et prohibitif pour les chercheurs des institutions aux ressources limitées. Au National High-Throughput Crystallization (HTX) Center, des méthodes hautement reproductibles ont été mises en œuvre pour faciliter la croissance des cristaux, y compris une configuration automatisée de plaque microbatch-under-oil à haut débit de 1 536 puits conçue pour échantillonner un large éventail de paramètres de cristallisation. Les plaques sont surveillées à l’aide de modalités d’imagerie de pointe pendant 6 semaines pour donner un aperçu de la croissance des cristaux, ainsi que pour distinguer avec précision les coups de cristal précieux. En outre, la mise en œuvre d’un algorithme de notation d’intelligence artificielle entraîné pour identifier les résultats cristallins, associé à une interface open source et conviviale pour visualiser des images expérimentales, rationalise le processus d’analyse des images de croissance cristalline. Ici, les procédures et l’instrumentation clés sont décrites pour la préparation des cocktails et des plaques de cristallisation, l’imagerie des plaques et l’identification des coups de manière à assurer la reproductibilité et à augmenter les chances de cristallisation réussie.
Introduction
Même à une époque de progrès considérables dans les méthodes de biologie structurale, la cristallographie aux rayons X continue d’être une méthode fiable et populaire pour générer des modèles structurels de haute qualité de macromolécules. Plus de 85 % de tous les modèles structuraux tridimensionnels déposés dans la Banque de données sur les protéines (PDB) proviennent de méthodes structurales à base de cristaux (en date de janvier 2023). 1 En outre, la cristallographie aux rayons X reste indispensable pour résoudre les structures protéine-ligand, un élément crucial du processus de découverte et de développement de médicaments2. Bien que la cristallisation des protéines soit restée la technique dominante de biologie structurale pendant plus d’un demi-siècle, les méthodes de prédiction de la probabilité de cristallisation basées sur les propriétés physiques3 ou la séquence 4,5 en sont encore à leurs balbutiements.
La prédiction des conditions de cristallisation est encore plus obscure; Des progrès limités ont été réalisés pour prédire les conditions de cristallisation probables, même pour les protéines modèles 6,7. D’autres études ont tenté d’identifier les conditions de cristallisation en se basant sur l’homologie des protéines et les conditions extraites de l’APB 8,9,10. Le pouvoir prédictif que l’on trouve dans le PDB est toutefois limité, car seules les conditions de cristallisation finales et réussies sont déposées, ce qui, par nécessité, manque les expériences d’optimisation souvent étendues nécessaires pour affiner la croissance cristalline. En outre, de nombreuses entrées PDB manquent de métadonnées contenant ces détails, y compris les formules de cocktail, le format de cristallisation, la température et le temps de cristallisation11,12. Par conséquent, pour de nombreuses protéines d’intérêt, le moyen le plus accessible de déterminer les conditions de cristallisation est expérimentalement, en utilisant autant de conditions que possible dans un large éventail de possibilités chimiques.
Plusieurs approches pour rendre le criblage de cristallisation aussi fructueux et approfondi que possible ont été explorées avec beaucoup d’effet, y compris les matrices clairsemées 13, le criblage factoriel incomplet 14, les additifs 15,16, l’ensemencement 17 et les agents de nucléation 18. Le National HTX Center du Hauptman-Woodward Medical Research Institute (HWI) a mis au point un pipeline efficace pour le criblage de cristallisation en utilisant l’approche microbatch-under-oil19, qui utilise des modalités automatisées de manipulation et d’imagerie des liquides pour rationaliser l’identification des conditions de cristallisation initiales en utilisant des volumes d’échantillons et de cocktails relativement minimes (Figure 1). L’ensemble de 1 536 cocktails uniques est basé sur des conditions préalablement déterminées comme propices à la croissance des cristaux de protéines et est conçu pour être chimiquement diversifié afin d’échantillonner une large gamme de conditions de cristallisation possibles20,21,22. Le large échantillonnage des conditions de cristallisation augmente la probabilité d’observer un ou plusieurs fils de cristallisation.
Peu d’analyses formelles du nombre d’affections nécessaires au dépistage ont été publiées dans la littérature. Une étude s’est concentrée sur la disposition d’échantillonnage de différents cribles et a révélé que l’échantillonnage aléatoire des composants (semblable à une factorielle incomplète) représentait la méthode d’échantillonnage la plus complète et la plus efficace23. Une autre étude de dépistage a noté qu’il y a eu de nombreux cas où le criblage très complet 1 536 n’a donné qu’un seul coupde cristal 24, et une étude très récente a souligné que la plupart des cribles commerciaux sous-échantillonnent l’espace de cristallisation connu pour être associé au criblageatteint 25. Toutes les sondes de cristallisation ne donneront pas un cristal de qualité de diffraction adapté à la collecte de données en raison du désordre inhérent au cristal, des limitations de diffraction ou des défauts cristallins; Par conséquent, jeter un filet plus large pour les conditions a l’avantage supplémentaire de fournir des formes cristallines alternatives pour l’optimisation.
Le format des expériences de cristallisation des protéines a également un impact sur le succès du criblage. La diffusion de vapeur est la configuration la plus couramment utilisée pour les applications de cristallisation à haut débit et est utilisée dans les centres de cristallisation de pointe, y compris les centres de criblage à haut débit EMBL Hambourg et Institut Pasteur26,27,28. Le centre HTX utilise la méthode microbatch-under-oil ; Bien que moins couramment utilisée, c’est une méthode robuste qui minimise la consommation d’échantillons et de cocktails de cristallisation20,21,22. L’un des avantages de la méthode microbatch-under-oil, en particulier lors de l’utilisation d’une huile de paraffine à haute viscosité, est que seule une légère évaporation se produit dans la goutte pendant l’expérience, ce qui signifie que la concentration d’équilibre est atteinte lors du mélange des gouttes. Si des résultats de cristallisation positifs sont observés dans la méthode microbatch-under-oil, la reproduction de ces conditions est généralement plus simple que dans les configurations de diffusion de vapeur, dans lesquelles la cristallisation se produit à un point indéfini de l’équilibre entre la goutte de cristallisation et le réservoir. La reproductibilité des résultats est souhaitable pour les approches de cristallisation à haut débit, qui produisent des cristaux de protéines prohibitifs qui doivent généralement être optimisés pour les expériences de rayons X monocristallins.
Le crible de cristallisation à haut débit pour les protéines solubles est composé de cocktails préparés en interne, de cribles commerciaux prêts à l’emploi et de cribles commerciaux modifiés en interne22. Les cocktails ont été initialement développés en utilisant la stratégie factorielle incomplète en utilisant des cocktails de cristallisation précédemment réussis20. Les réactifs disponibles dans le commerce comprennent des réseaux de polymères, des sels de cristallisation, du PEG et des combinaisons d’ions et des cribles qui utilisent une matrice clairsemée et des approches factorielles incomplètes. Il existe également des réactifs qui sont modifiés avant d’être inclus dans le crible : un crible additif, un crible pH et tampon, un crible additif liquide ionique et un crible polymère.
La puissance des conditions et des stratégies de cristallisation connues a été exploitée dans les 1 536 cocktails de cristallisation, ainsi que les avantages du système microbatch-under-oil pour générer un pipeline qui utilise la manipulation automatisée des liquides, l’imagerie automatisée en fond clair et l’imagerie non linéaire de second ordre des cristaux chiraux (SONICC). L’automatisation de la manipulation des liquides et de l’imagerie offre les avantages d’une réduction des heures de laboratoire humide et d’une reproductibilité accrue. La nature à haut débit du criblage automatisé de cristallisation nécessite l’automatisation du processus de surveillance de la croissance des cristaux. Ces progrès sont réalisés grâce à des technologies d’imagerie de pointe pour aider à l’identification des coups cristallins positifs. L’imagerie standard en fond clair des plaques, ainsi que les méthodes multiphotoniques pour une détection améliorée, sont utilisées via un système d’imagerie à cristaux avec SONICC (Figure 2). SONICC combine la microscopie de deuxième génération d’harmoniques (SHG)29 et la microscopie ultraviolette à fluorescence excitée à deux photons (UV-TPEF)30 pour détecter les très petits cristaux, ainsi que ceux obscurcis par le précipité. L’imagerie SONICC indique si les puits contiennent des protéines (via UV-TPEF) et des cristaux (via SHG). Au-delà de l’identification positive des cristaux de protéines, des informations supplémentaires peuvent également être obtenues à l’aide de méthodes d’imagerie de pointe. L’imagerie en cocktail seulement avant l’ajout de l’échantillon sert de contrôle négatif; Ces images peuvent identifier l’apparence du puits avant l’ajout d’échantillons, y compris en termes de cristaux de sel et de débris. De plus, l’imagerie SHG et UV-TPEF aide à différencier les cristaux de protéines des cristaux de sel et peut être utilisée pour visualiser le matériau complexé protéine-acide nucléique31.
Les expériences de cristallisation à haut débit soumises à une surveillance répétée par imagerie donnent lieu à un très grand volume d’images nécessitant un examen. Des méthodes automatisées de notation des cristaux ont été développées pour réduire le fardeau de l’utilisateur et augmenter la probabilité d’identifier les résultats positifs des cristaux. Le Centre HTX a participé au développement de l’algorithme de notation MAchine Recognition of Crystallization Outcomes (MARCO), une architecture de réseau neuronal convolutif profond formée développée par un consortium de partenaires universitaires, à but non lucratif, gouvernementaux et industriels pour classer les images de puits en fond clair32. L’algorithme a été formé sur près d’un demi-million d’images en fond clair provenant d’expériences de cristallisation de plusieurs institutions utilisant différentes méthodes de cristallisation et différents imageurs. L’algorithme produit un score probabiliste indiquant si une image donnée appartient à quatre classes d’images possibles: « cristal », « clair », « précipité » et « autre ». MARCO a une précision de classification rapportée de 94,5%. La détection des cristaux est encore améliorée par un logiciel qui implémente l’algorithme et fournit une interface utilisateur graphique (GUI) pour une visualisation d’image accessible et simple, activée avec les capacités de notation activées par l’IA32,33. L’interface graphique MARCO Polo est conçue pour fonctionner de manière transparente avec la configuration du système d’imagerie et de gestion des données dans le centre HTX pour identifier les résultats dans l’écran de 1 536 puits, avec un engagement humain pour examiner la sortie des listes triées. De plus, en tant que logiciel open source disponible sur GitHub, l’interface graphique est facilement disponible pour modification afin de refléter les besoins spécifiques d’autres groupes de laboratoires.
Ici, le processus de mise en place d’une expérience de microbatch sous huile à haut débit utilisant la manipulation robotique de liquides pour délivrer à la fois le cocktail et la protéine est décrit. Le Centre HTX dispose d’une gamme unique d’instruments et de ressources que l’on ne trouve pas dans d’autres institutions, dans le but de fournir des services de dépistage et des ressources éducatives aux utilisateurs intéressés. La démonstration des méthodes et des capacités des techniques à haut débit basées sur la robotique permettra à la communauté d’avoir une connaissance des technologies disponibles et de prendre des décisions pour ses propres efforts de détermination de la structure.
Protocole
1. Préparation ou achat de cocktails pour seize blocs de puits de 96 puits de profondeur
- Préparez des cocktails chimiques générés en interne en les distribuant dans des blocs de puits profonds (DW) de 96 puits. Utilisez un robot manipulateur de liquides pour distribuer et mélanger des solutions mères de sels, de tampons, de polymères et d’eau.
- Préparez des cocktails chimiques modifiés en interne à l’aide d’un manipulateur de liquide robotisé ou d’une pipette multicanal pour ajouter des composants supplémentaires aux cribles DW à 96 puits achetés dans le commerce.
- Achetez des blocs DW disponibles dans le commerce.
- Conservez les blocs DW à 96 puits étiquetés à -20 °C pendant 12 à 18 mois.
NOTE: Les cocktails préparés à l’étape 1.1. et 1.2. remplir des blocs DW 10/16 96 puits et 5/16 blocs DW 96 puits sont utilisés tels qu’achetés. Un bloc DW de 96 puits dans le crible est installé au moment de la distribution de la plaque de 1 536 puits pour éviter la précipitation du criblage additif (voir la section 3).
2. Distribution des cocktails dans des assiettes de 384 puits
- Décongeler les blocs DW de 96 puits à 4 °C pendant la nuit. Porter à température ambiante (20-23 °C) avant de commencer la préparation des plaques de 384 puits.
NOTE: La température ambiante convient à la préparation des assiettes à cocktail. La principale préoccupation lors de la préparation de ces assiettes est d’éviter les précipités, qui peuvent obstruer les dispositifs de manipulation des liquides et entraîner des changements imprévisibles dans les concentrations des ingrédients du cocktail. - Bien mélanger les blocs par inversion au besoin pour dissoudre tout précipité opaque persistant. Si des puits contiennent du précipité, réchauffer les blocs à 30 °C pour les dissoudre.
- Livrer 50 μL de solution cocktail de quatre blocs DW de 96 puits à une plaque de 384 puits à l’aide d’un robot de manipulation de liquide équipé d’une seringue 96 ou d’une tête de pipettrice. Les quatre blocs DW de 96 puits sont estampés dans la plaque de 384 puits de sorte que les quadrants sont remplis (par exemple, A1 de 96-DW1 à A1 de 384-plate1, A1 de 96-DW2 à B1 de 384-plate1, etc.) (Figure 3).
- Livrer 15 des 16 blocs DW de 96 puits à des plaques de 384 puits pour le stockage.
- Entreposer les plaques de 384 puits à −20 °C jusqu’à 6 mois pour les utiliser dans la préparation des plaques de 1 536 puits.
3. Préparation des plaques de 1 536 puits avec de l’huile et des cocktails de cristallisation
- Livrer 5 μL d’huile de paraffine à chaque puits d’une plaque de 1 536 puits à l’aide d’un système robotisé de manutention des liquides capable de ralentir l’aspiration et la livraison. Conservez les plaques d’huile à 4 °C jusqu’à 6 mois.
- Décongeler les plaques de 384 puits de la section 2 à 4 °C pendant la nuit. Retourner les plaques pour mélanger les solutions et dissoudre le précipité. Incuber les plaques à 30 °C pour dissoudre les précipités persistants.
- Pour préparer les composants de criblage additif, utilisez le bloc DW final de 96 puits contenant 0,1 M HEPES pH 6,8, 30% PEG3350 à mélanger avec le criblage additif commercial à l’aide d’un robot de manipulation de liquide ou d’une pipette multicanal.
- Préparer les solutions de criblage additif en distribuant un mélange 1:1 de la solution tamponnée PEG3350 préparée à l’étape 3.3 et le crible additif jusqu’à un volume final de 50 μL dans la plaque appropriée à 384 puits.
- Utilisez un robot de manipulation de liquide équipé d’une seringue 384 ou d’une tête de pipette pour administrer 200 nL de solution à cocktail dans chaque puits de la plaque de 1 536 puits. Insérer quatre plaques de 384 puits dans la plaque de 1 536 puits de manière à remplir les quadrants (p. ex., A1 de 384 plaques1 à A1 de la plaque de 1 536 puits, A2 de 384 plaques1 à A3 de la plaque de 1 536 puits, etc.) (Figure 3).
- Centrifuger les plaques à 150 × g pendant 5 min avant de les conserver à 4 °C jusqu’à 4 semaines.
4. Soumission d’échantillons
- Pour soumettre un échantillon, envoyez un e-mail de réservation avant la date limite de réservation pour la prochaine série de projection. Inclure le nombre d’expériences de dépistage, le nom, le chercheur principal et l’établissement, ainsi que toute exigence particulière de manipulation de l’échantillon. Les cycles de dépistage sont effectués environ une fois par mois, ce qui donne lieu à 12 essais par année.
- Remplissez un formulaire de soumission d’échantillon avant d’expédier l’échantillon.
- Pour les nouveaux utilisateurs, choisissez un mot de passe qui sera utilisé pour télécharger les images de cristallisation dans la section 7.
- Pour les utilisateurs établis, utilisez un mot de passe existant ou modifiez le mot de passe à cette étape.
- Soumettre l’échantillon dans un tube de 1,5 mL. S’assurer que la macromolécule est homogène et suffisamment concentrée pour favoriser la cristallisation. Utiliser un essai de précristallisation, généralement composé de sulfate d’ammonium ou de PEG 4 000, pour déterminer la concentration appropriée de l’échantillon en observant si les concentrations de l’échantillon testé entraînent des gouttes nettes ou un précipité34.
NOTE: Les tests de qualité appropriés qui peuvent être entrepris avant la soumission de l’échantillon pour vérifier la pureté et l’homogénéité comprennent SDS-PAGE, la filtration sur gel et la diffusion dynamique de la lumière (DLS), entre autres. La cristallisation peut être affectée par la présence d’impuretés, même mineures. Un volume d’échantillon de 500 μL est actuellement nécessaire pour mettre en place une plaque de 1 536 puits. Des tests sont en cours pour réduire le volume requis d’échantillon.- Évitez d’utiliser des concentrations tampons supérieures à 50 mM, ainsi que des phosphates, qui peuvent cristalliser à l’intérieur de l’écran.
- Évitez les agents solubilisants excessifs, y compris les concentrations de glycérol supérieures à 10 % p/v.
- Emballez l’échantillon pour maintenir en toute sécurité une température appropriée en utilisant de la glace sèche, de la glace humide ou des blocs réfrigérants dans un récipient scellé.
- Expédiez la priorité des échantillons pendant la nuit du lundi au mercredi pendant la course.
- Envoyez le numéro de suivi par e-mail une fois l’échantillon expédié.
5. Installation de l’échantillon dans les plaques préparées de 1 536 puits
- Déballez les échantillons et incuber immédiatement à la température demandée par l’utilisateur.
- Une fois décongelé, centrifuger l’échantillon à 10 000 × g pendant 2 min à température ambiante. Observez visuellement l’échantillon pour identifier les précipitations, la couleur et l’état de l’échantillon avant la configuration.
- Réchauffer la plaque de 1 536 puits à 23 °C et centrifuger à 150 × g pendant 5 min. Imaginez l’assiette de cocktail uniquement en utilisant l’imagerie en fond clair comme contrôle négatif.
REMARQUE: Toutes les plaques sont imagées avec l’imagerie en fond clair avant la configuration de l’échantillon, ce qui permet d’identifier les puits qui contiennent déjà des cristaux ou des débris avant l’ajout d’échantillons en tant que contrôle négatif. De plus, il permet d’identifier les puits dans lesquels le cocktail de cristallisation n’a pas été livré. Le réchauffement de la plaque à température ambiante élimine la condensation sur la surface de la plaque, ce qui permet d’obtenir des images claires. - Distribuer 200 nL d’échantillon à chaque puits de la plaque de 1 536 puits à l’aide d’un robot de manipulation des liquides. Plaque de centrifugation à 150 × g et plaques d’incubation à 4 °C, 14 °C ou 23 °C.
REMARQUE: Les expériences de sous-huile par microlots peuvent être mises en place à la main en distribuant la protéine et le cocktail sous l’huile souhaitée. Cependant, il est recommandé d’utiliser pas moins de 1 μL de chaque protéine et cocktail pour obtenir des résultats reproductibles.
6. Surveiller la formation de cristaux dans les plaques de 1 536 puits
- Une fois l’échantillon ajouté aux plaques de 1 536 puits, image avec imagerie en fond clair au jour 1 et à la semaine 1, à la semaine 2, à la semaine 3, à la semaine 4 et à la semaine 6.
- Effectuer l’imagerie SONICC avec SHG et UV-TPEF au point de temps de 4 semaines pour les plaques incubées à 23 °C et au point de 6 semaines pour les plaques incubées à 14 °C ou 4 °C.
REMARQUE: Le calendrier de l’imagerie SONICC est prévu aux points de temps de 4 semaines et 6 semaines pour la plaque de microessai à haut débit 1,536 car, généralement, les cristaux apparaîtront à ces points temporels. Pour la modification d’un microlot de 96 puits dans le cadre d’expériences de diffusion d’huile ou de vapeur, il est conseillé d’effectuer l’imagerie SONICC plus tôt dans la fenêtre temporelle. - Accédez aux images expérimentales qui ont été automatiquement transférées vers le compte utilisateur à l’aide d’un système LIMS interne. Informez les utilisateurs via un démon de messagerie automatisé htslab que l’imagerie a eu lieu.
7. Analyse d’images
- Récupérez les images de filtrage à partir du site FTP HWI pour chaque fichier .rar.
Remarque : La sortie d’image de l’écran 1,536 se traduit par un certain nombre de fichiers contenant des images en fond clair, des images SHG et des images UV-TPEF. Chaque modalité d’imagerie ou point temporel est un fichier .rar distinct. Chaque fichier .rar, lorsqu’il est décompressé, contient une image de chaque puits de la plaque de 1 536 puits à un moment précis en utilisant une modalité d’imagerie spécifique.- Utilisez le client FileZilla ou d’autres options pour accéder aux données ftp.
REMARQUE: Le client FileZilla est la méthode recommandée pour gérer le grand volume de transfert de fichiers afin de minimiser les pannes de calcul.- Si FileZilla Client doit être installé sur l’ordinateur de l’utilisateur, téléchargez le logiciel FileZilla.
- Si FileZilla Client est déjà installé ou lors de l’installation, cliquez sur l’icône FileZilla pour ouvrir le logiciel.
- Connectez-vous au serveur ftp distant à partir de FileZilla en entrant le site Web ftp hôte, le nom d’utilisateur et le mot de passe.
- Téléchargez les fichiers .rar dans le répertoire souhaité.
- Utilisez le client FileZilla ou d’autres options pour accéder aux données ftp.
- Utilisez l’interface graphique open source activée par l’IA pour visualiser, noter et analyser les images de cristallisation.
REMARQUE: L’interface graphique peut être utilisée sur la plupart des systèmes d’exploitation Windows, Mac et Linux, et les instructions de téléchargement spécifiques au système d’exploitation se trouvent sur le site GitHub. MARCO Polo est une interface graphique open-source qui intègre les métadonnées de l’écran de cristallisation à haut débit 1,536 implémenté au HTX Center. Il est disponible pour tout le monde à télécharger à partir de GitHub pour modification afin de refléter les besoins spécifiques d’autres groupes de laboratoires.- Ouvrez le fichier .rar dans l’interface graphique après le téléchargement du fichier (voir la figure supplémentaire S1).
- Cliquez sur Importer, sélectionnez Images dans le menu déroulant, puis sélectionnez À partir de l’archive/répertoire RAR.
- Cliquez sur Rechercher un dossier dans la fenêtre contextuelle, puis accédez au dossier contenant les images.
- Sélectionnez le(s) fichier(s) souhaité(s) et importez-les dans l’interface graphique en cliquant sur Ouvrir. Attendez que le(s) fichier(s) apparaisse(nt) dans la fenêtre Chemins sélectionnés . Sélectionnez un ou plusieurs fichiers à télécharger dans l’interface graphique et cliquez sur Importer des exécutions.
- Affichez l’image du premier puits dans la fenêtre de la visionneuse de diaporama dans l’interface graphique en cliquant sur le symbole > à gauche du nom de l’échantillon, puis en sélectionnant la lecture appropriée en double-cliquant dessus (les lectures sont répertoriées par date et type d’image-brightfield, UV-TPEF ou SHG).
- Agrandissez l’image en redimensionnant toute la fenêtre. La zone Détails de l’image inclut des informations sur l’image, y compris les informations de notation (vide jusqu’à ce que la lecture ait été notée). La zone Détails du cocktail contient des métadonnées sur les composants du cocktail .
- Passez au puits suivant en cliquant sur le bouton Suivant dans le panneau de navigation ou en appuyant sur la touche fléchée droite du clavier. Accédez à un puits spécifique en entrant le numéro de puits dans la fenêtre Par numéro de puits .
- Affichez toutes les lectures (de celles importées dans l’interface graphique) en cochant la case Afficher toutes les dates .
- Affichez tous les spectres (de ceux importés dans l’interface graphique) en cochant la case Afficher tous les spectres . Cliquez sur le bouton Permuter le spectre pour afficher chaque image du spectre individuellement.
- Ouvrez le fichier .rar dans l’interface graphique après le téléchargement du fichier (voir la figure supplémentaire S1).
- Marquez les images cristallines à l’aide de l’algorithme MARCO en mettant d’abord en surbrillance une exécution spécifique de la liste sur le côté gauche de la fenêtre. Ensuite, cliquez sur le bouton Classer l’exécution sélectionnée . Affichez les informations de notation MARCO dans la fenêtre Détails de l’image une fois qu’une lecture d’imagerie a été notée pour les 1 536 puits.
REMARQUE: La classification prend généralement entre 2 et 5 minutes, en fonction de la vitesse de l’ordinateur et de la mémoire disponible. L’algorithme génère des scores qui classent le contenu en classes « cristal », « clair », « précipité » ou « autres ». Les valeurs numériques associées à la classification de chaque puits reflètent la probabilité que le puits contienne des objets de cette classe.- Affichez un sous-ensemble des images notées en cochant la ou les cases souhaitées dans le panneau Filtrage d’images et en cliquant sur le bouton Soumettre les filtres . Par exemple, affichez uniquement les images classées par MARCO comme cristaux en cochant les cases Cristaux et MARCO et en cliquant sur Soumettre les filtres.
- Marquez manuellement les images cristallines pour générer l’ensemble « score humain ». Attribuez une note à un puits en cliquant sur le bouton approprié (les boutons « cristal », « clair », « précipiter » ou « autre » se trouvent dans le panneau Classification au bas de la fenêtre). Vous pouvez également utiliser le pavé numérique du clavier pour attribuer la partition (1 = « cristal », 2 = « clair », 3 = « précipiter », 4 = « autre »). Désigner une image marquée par un humain comme « favorite » en cochant le Favori ? boîte.
REMARQUE: Affichez uniquement les images classées par un humain comme cristaux en cochant les cases Cristaux et Humain et en cliquant sur Soumettre les filtres. Cliquez sur la case Favoris dans le panneau Filtrage pour réduire davantage les images renvoyées, ne renvoyant que les images cristallines marquées par l’homme qui sont également des favoris. - Utilisez l’onglet Plate Viewer pour afficher plusieurs puits à la fois. Dans le deuxième onglet Visualiseur de plaques du panneau Contrôles , sélectionnez 16, 64 ou 96 images dans le menu déroulant de la section Images par plaque . Utilisez l’onglet Filtrage d’image pour griser les images qui ne présentent pas d’intérêt. Cochez la case Appliquer le filtre pour filtrer les images.
REMARQUE: Par exemple, sélectionnez les cases « humain » et « cristal », et seuls les puits qui ont été marqués comme un cristal par un humain seront facilement visibles.- Naviguez dans l’onglet Plate Viewer , en cliquant sur le bouton Suivant pour voir la prochaine série d’images 16/64/96. Par défaut, les images marquées comme des cristaux sont rouges, celles marquées comme claires sont bleues, celles marquées comme précipitées sont vertes et celles marquées comme autres sont orange. Modifiez les couleurs à l’aide des menus déroulants.
- Sélectionnez les informations à afficher sur les puits en cochant différentes cases dans l’onglet Étiquettes .
- Cliquez sur Enregistrer la vue pour enregistrer un fichier image de la vue actuelle.
- Cliquez sur Permuter le spectre pour basculer entre les images en fond clair, SHG et UV-TPEF pour l’image à puits multiples.
- Cliquez sur Exporter et sélectionnez le type de fichier approprié dans le menu déroulant pour exporter les fichiers notés à utiliser dans d’autres programmes.
REMARQUE: Les fichiers CSV (valeurs séparées par des virgules) sont compatibles avec les tableurs tels que Microsoft Excel ou Google Sheets. Les fichiers JSON (JavaScript Object Notation) peuvent être ouverts avec la plupart des éditeurs de texte. PPTX (PowerPoint Presentation) peut être utilisé pour afficher des images de Polo, y compris une comparaison des images en fond clair, UV-TPEF et SHG. Les fichiers sont enregistrés au format .xtal pour être rouverts dans l’interface graphique MARCO Polo.- Enregistrez un fichier au format .xtal en cliquant sur Fichier en haut de la page, puis en sélectionnant Enregistrer l’exécution ou Enregistrer l’exécution sous. Indiquez un nom de fichier et un emplacement de répertoire.
- Ouvrez les fichiers au format .xtal en cliquant sur Importer et en sélectionnant Images , puis à partir de l’exécution enregistrée. Recherchez l’emplacement de fichier approprié, cliquez sur le nom du fichier, puis cliquez sur Ouvrir.
Résultats
Les résultats de l’expérience de criblage de cristaux de 1 536 puits consistent en sept ensembles complets d’images en fond clair recueillies au jour 0 (contrôle négatif), au jour 1, à la semaine 1, à la semaine 2, à la semaine 3, à la semaine 4 et à la semaine 6 (figure 4). Les images SONICC sont collectées au point de temps de 4 semaines pour les plaques incubées à 23 °C et au point de 6 semaines pour les plaques incubées à 4 °C ou 14 °C. Dans l’ensemble, une fois qu’un échantillon a été expédié, les utilisateurs peuvent s’attendre à ce que leurs plaques soient installées dans la 1 journée suivant leur arrivée. Les images seront téléchargées au fur et à mesure de leur collecte. L’expérience de criblage par cristallisation se termine après 6 semaines.
La configuration de la plaque de 1 536 puits permet de mener toutes les expériences de criblage dans la même plaque, limitant ainsi la consommation d’échantillons et facilitant l’imagerie et la comparaison directe entre les modalités d’imagerie. Des résultats représentatifs de l’évolution temporelle de la croissance des cristaux pour une seule condition cocktail sont présentés à la figure 4. L’imagerie automatisée des plaques tout au long de l’expérience permet l’identification des cristaux à croissance rapide et lente par imagerie en fond clair. L’imagerie UV-TPEF et SHG permet une validation croisée des résultats observés par imagerie en fond clair et indique que les cristaux observés sont respectivement protéiques et cristallins (Figure 5A,B). De plus, l’imagerie SONICC permet d’identifier des cristaux qui sont visuellement masqués par le précipité ou les films (Figure 5C) ou les microcristaux qui pourraient autrement être confondus avec le précipité (Figure 5D). Pour certains cristaux, l’absence de signal SHG n’est pas disqualifiante, car certains groupes ponctuels ne produisent pas de signal SHG35,36, comme l’illustre le cristal tétragonal de thaumatine sur la figure 5C. Inversement, il faut s’attendre à un manque de signal UV-TPEF pour les protéines dépourvues de résidus de tryptophane. L’observation des signaux UV-TPEF et SHG facilite également l’identification des cristaux de sel non protéiques, qui apparaîtront en fond clair et présenteront un signal SHG fortement positif, mais qui n’auront pas de signal UV-TPEF (Figure 5E).
L’analyse d’images pour la configuration de la plaque est rationalisée avec l’interface graphique MARCO Polo, qui regroupe également le transfert de données ftp à partir des serveurs HWI (comme alternative au transfert de fichiers avec FileZilla). L’interface graphique MARCO Polo permet une visualisation facile des plaques et des images et effectue une notation d’image informatique à l’aide de l’algorithme MARCO afin que les résultats de l’image puissent être rapidement téléchargés, visualisés et analysés à partir du centre HTX. L’algorithme de notation MARCO, tel qu’implémenté dans l’interface graphique MARCO Polo, est capable de marquer des images de l’ensemble de la plaque de 1 536 puits en moins de 5 minutes. Les images marquées comme cristallines par l’algorithme MARCO peuvent ensuite être triées par l’interface graphique Polo pour affichage. Étant donné que l’algorithme MARCO a été optimisé pour l’identification des cristaux et la minimisation des faux négatifs afin de ne manquer aucun résultat positif, la notation peut entraîner des indicateurs de faux positifs. Néanmoins, la capacité de MARCO à limiter l’ensemble des images à examiner en concentrant l’attention sur les puits à forte probabilité de contenir des cristaux entraîne une réduction substantielle de la charge de traitement des données pour les utilisateurs. La mise en œuvre pratique de l’algorithme dans la plate-forme de visualisation conviviale MARCO Polo, avec sa capacité à trier les images en fonction des scores MARCO, améliore considérablement la capacité de l’utilisateur à analyser rapidement l’ensemble de données et à déterminer avec précision les résultats cristallins.
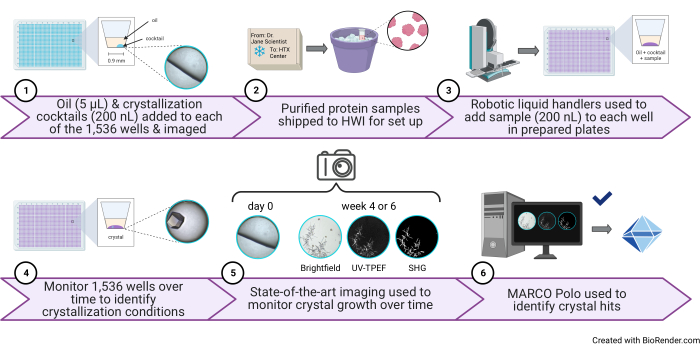
Figure 1 : Schéma d’une expérience de criblage de cristallisation à haut débit de 1 536 puits réalisée au centre HTX. (1) Dans cette étape, 5 μL d’huile de paraffine et 200 nL de cocktail sont ajoutés à chaque puits (étapes 3.1 et 3.5 du protocole). Une illustration de bande dessinée d’un puits ne contenant que du pétrole et un cocktail et une image représentative sont montrées à droite. (2) Les échantillons arrivent au Centre HTX (étape du protocole 5.1). 3) Dans cette étape, 200 nL d’échantillon sont ajoutés à chaque puits (étape du protocole 5.4). (4) Les 1 536 puits sont surveillés au fil du temps à l’aide de l’imagerie en fond clair, 5) ainsi que des modalités UV-TPEF et SHG (étape 6 du protocole). 6) L’interface graphique open source activée par l’IA est utilisée pour visualiser, noter et analyser les images de cristallisation (étape de protocole 7). Abréviations : HTX = cristallisation à haut débit; UV-TPEF = fluorescence excitée par les UV à deux photons; SHG = seconde génération harmonique; IA = intelligence artificielle; GUI = interface utilisateur graphique. Veuillez cliquer ici pour voir une version agrandie de cette figure.

Figure 2 : Plaques uniques de 1 536 puits contenant des expériences de criblage, imagées à l’aide de l’imagerie en fond clair, UV-TPEF et SHG. Les plaques de 1 536 puits sont montrées avec un penny américain pour l’échelle (en haut). Chaque expérience de criblage est imagée une fois avant la configuration et six fois après l’ajout d’échantillon avec l’imagerie en fond clair (sept ensembles d’images en fond clair au total, à gauche). Les plaques subissent une imagerie UV-TPEF (au centre) et SHG (à droite) à 4 semaines ou 6 semaines. Abréviations : UV-TPEF = fluorescence excitée par les UV à deux photons; SHG = seconde génération harmonique. Veuillez cliquer ici pour voir une version agrandie de cette figure.
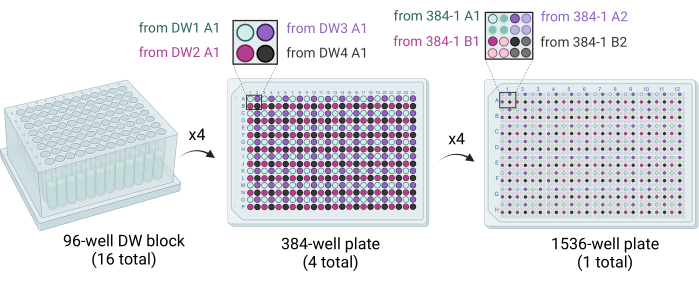
Figure 3 : Schéma montrant comment les plaques de 1 536 puits sont générées. Seize blocs DW de 96 puits sont utilisés pour éliminer quatre plaques de 384 puits, chaque quadrant de chaque plaque de 384 puits étant rempli par des cocktails de cristallisation distribuants. Quatre blocs DW de 96 puits remplissent une plaque de 384 puits (au milieu). Quatre plaques de 384 puits sont utilisées pour étouffer la plaque unique de 1 536 puits (à droite). Abréviation : DW = puits profond. Veuillez cliquer ici pour voir une version agrandie de cette figure.
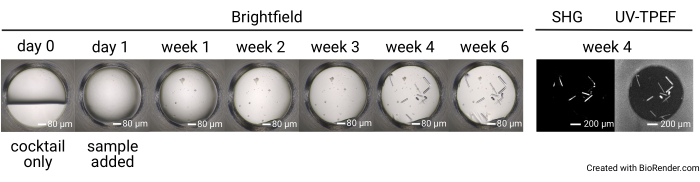
Figure 4 : Évolution temporelle représentative d’un seul puits dans une expérience de criblage de 1 536 puits. Les plaques sont imagées avant la configuration de l’échantillon (jour 0), ainsi qu’avec l’imagerie en fond clair le jour 1, la semaine 1, la semaine 2, la semaine 3, la semaine 4 et la semaine 6. Les plaques incubées à 23 °C sont imagées avec SONICC à la semaine 4. Barres d’échelle = 80 μm (fond clair), 200 μm (SHG, UV-TPEF). Abréviations : SONICC = imagerie non linéaire de second ordre de cristaux chiraux; UV-TPEF = fluorescence excitée par les UV à deux photons; SHG = seconde génération harmonique. Veuillez cliquer ici pour voir une version agrandie de cette figure.
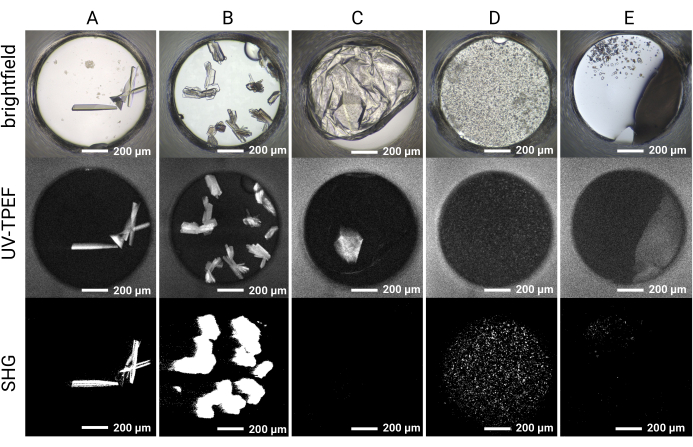
Figure 5 : Résultats d’imagerie représentatifs pour les expériences de criblage cristallin HT 1 536. Les résultats d’imagerie en fond clair, UV-TPEF et SHG sont présentés pour cinq puits d’exemple. (A,B) Les cristaux de protéines observés par imagerie en fond clair, UV-TPEF et SHG sont clairement apparents dans les trois modalités d’imagerie. (C) Un cristal de protéine obscurci par un film en imagerie en fond clair est visible par imagerie UV-TPEF; le cristal n’est pas observé par imagerie SHG en raison d’une incompatibilité de groupe de points. (D) Exemple de microcristaux vérifiés par imagerie UV-TPEF et SHG qui peuvent autrement être considérés comme précipités. (E) Exemple de cristaux de sel qui apparaissent cristallins par imagerie en fond clair et SHG mais qui ne présentent pas de signal UV-TPEF. Barres d’échelle = 200 μm. Diamètre du puits = 0,9 mm. Abréviations : UV-TPEF = fluorescence excitée par les UV à deux photons; SHG = seconde génération harmonique. Veuillez cliquer ici pour voir une version agrandie de cette figure.
Figure supplémentaire S1 : Ouverture de fichiers image dans MARCO Polo. Les fichiers image peuvent être ouverts dans l’interface graphique MARCO Polo en accédant à l’option Importer | Onglet Images en haut (a). Notez que les fichiers peuvent également être transférés via l’outil Depuis FTP directement dans MARCO Polo (a) ou peuvent être transférés via FileZilla comme décrit dans l’étape de protocole 7.2. Pour importer des fichiers qui ont déjà été téléchargés, sélectionnez Images | Depuis Rar Archive/Directory. Dans la fenêtre contextuelle qui apparaît, sélectionnez Rechercher le dossier (b) et accédez au répertoire de fichiers dans lequel les fichiers image de plaque sont enregistrés. Une fois que les fichiers sont dans la fenêtre Chemins sélectionnés (c), mettez un fichier en surbrillance et cliquez sur Importer des exécutions (d). L’interface graphique de MARCO Polo identifiera les métadonnées correctes du fichier cocktail à importer avec les images. Veuillez cliquer ici pour télécharger ce fichier.
Discussion
La méthode décrit un pipeline à haut débit pour le criblage de cristallisation des protéines qui nécessite aussi peu que 500 μL d’échantillon pour 1 536 expériences de cristallisation individuelles dans le format microbatch-under-oil. Le pipeline s’appuie sur la robotique de manipulation des liquides pour faciliter rapidement et de manière reproductible la configuration expérimentale, ainsi que sur la ressource d’analyse d’images informatiques MARCO Polo, qui est personnalisée pour analyser des images de plaques de 1 536 puits à l’aide de l’algorithme MARCO pour identifier et isoler les impacts cristallins.
Le faible volume de gouttes de criblage individuelles (400 nL au total avec un rapport échantillon:cocktail de 1:1) signifie que des volumes d’échantillons extrêmement faibles sont nécessaires pour identifier les conditions de cristallisation positives. Ces petites tailles de gouttes produisent nécessairement de petits cristaux qui ne peuvent pas être pêchés par boucle traditionnelle. Des méthodes ont été mises au point pour récolter à partir des 1 536 planches37; De plus, les plaques avec des cristaux ont été utilisées directement aux sources synchrotron pour la collecte de données in situ 38. Si une méthode robuste de récolte de ces cristaux était mise au point, les progrès de la technologie synchrotron et des faisceaux microfocalisés permettraient d’obtenir des ensembles de données utiles. De plus, les cristaux obtenus pourraient potentiellement être utilisés comme graines pour les efforts d’optimisation.
L’imagerie SONICC est clairement avantageuse pour identifier à la fois les petits cristaux de protéines et les cristaux de protéines cachés sous le précipité. Malgré ces avantages, tous les types d’échantillons ne se prêtent pas à l’imagerie SHG et UV-TPEF. Par exemple, les protéines avec peu ou pas de résidus de tryptophane aromatique montreront un signal UV-TPEF ambigu. De plus, les cristaux dans des groupes spatiaux spécifiques, y compris les groupes centrosymétriques ou le groupe ponctuel 432, ne seront pas détectés par imagerie SHG. Les échantillons contenant des fluorophores interfèrent parfois avec le signal SHG, ce qui entraîne l’annulation du signal ou une augmentation de l’intensité, ce qui signifie qu’une interprétation prudente des signaux SHG est nécessaire pour les protéines contenant des métaux et les protéines contenant des fractions fluorescentes. Cependant, dans de nombreux cas, il est possible de rationaliser l’absence d’un signal SHG ou UV-TPEF, et l’absence de ces signaux ne doit pas nécessairement exclure la présence d’un cristal de protéine.
Le format microbatch-under-oil offre une alternative à la méthode de diffusion de vapeur plus courante utilisée pour la cristallographie à haut débit. Il est important de noter que le format de cristallisation a un impact sur l’identificationdes résultats 39, ce qui justifie l’utilisation de différents formats de cristallisation pour les efforts de criblage à haut débit. L’imagerie automatisée et les modalités SONICC aident à l’identification rapide des cristaux de protéines tout au long du cycle expérimental de 6 semaines. Enfin, l’interface graphique MARCO Polo permet aux utilisateurs d’analyser rapidement les images de 1 536 conditions afin d’identifier les puits prometteurs à optimiser. Les capacités du Centre HTX, y compris la configuration expérimentale à haut débit robotisée, associées aux outils d’imagerie et de calcul de pointe pour les analyses, apportent une contribution majeure à la communauté de la biologie structurale en permettant aux chercheurs de s’attaquer efficacement à un goulot d’étranglement primaire dans le travail structurel à base de cristaux : trouver des conditions de cristallisation.
Déclarations de divulgation
Les auteurs n’ont pas d’intérêts financiers concurrents ou d’autres conflits d’intérêts.
Remerciements
Nous tenons à exprimer notre gratitude à nos utilisateurs pour nous avoir confié leurs précieux échantillons pour le dépistage cristallin, ainsi que pour avoir fourni des commentaires critiques et des demandes qui nous ont aidés à affiner et à développer nos ressources pour mieux servir la communauté de la biologie structurale. Nous tenons également à remercier Ethan Holleman, le Dr Lisa J Keefe et le Dr Erica Duguid, qui ont dirigé le développement de l’interface graphique MARCO Polo. Nous tenons à remercier les collègues de HWI pour leur soutien et leurs suggestions, en particulier la Dre Diana CF Monteiro. Nous reconnaissons le soutien financier des National Institutes of Health, R24GM141256.
matériels
| Name | Company | Catalog Number | Comments |
| 1536 Well Imp@ct LBR LoBase | Greiner Bio-One | 790 801 | |
| Acetic acid | Hampton Research | HR2-853 | |
| AlumaSeal II Sealing Film | Hampton Research | HR8-069 | |
| Ammonium bromide | Molecular Dimensions | MD2-100-247 | |
| Ammonium chloride | Hampton Research | HR2-691 | |
| Ammonium hydroxide | Hampton Research | HR2-855 | |
| Ammonium nitrate | Hampton Research | HR2-665 | |
| Ammonium phosphate dibasic | Hampton Research | HR2-629 | |
| Ammonium phosphate monobasic | Hampton Research | HR2-555 | |
| Ammonium sulfate | Hampton Research | HR2-541 | |
| Ammonium thiocyanate | Molecular Dimensions | MD2-100-301 | |
| Bicine pH 9.0 | Hampton Research | HR2-723 | |
| Bis-tris propane pH 7.0 | Hampton Research | HR2-993-08 | |
| Calcium acetate | Hampton Research | HR2-567 | |
| Calcium chloride dihydrate | Hampton Research | HR2-557 | |
| CAPS pH 10.0 | Rigaku Reagents | none given | |
| ClearSeal Film | Hampton Research | HR4-521 | |
| Cobalt sulfate heptahydrate | Molecular Dimensions | MD2-100-42 | |
| Crystal Screen HT screen | Hampton Research | HR2-130 | |
| Formulator | Formulatrix | ||
| Glycerol | Hampton Research | HR2-623 | |
| Gryphon liquid handling robot | Art Robbins Instruments | ||
| HEPES pH 7.0 | Hampton Research | HR2-902-03 | |
| HEPES pH 7.5 | Hampton Research | HR2-902-08 | |
| HWI HTX Center sample submission form | https://hwi.buffalo.edu/high-throughput-crystallization-screening-center-sample-submission-form/ | ||
| Hydrochloric acid | Hampton Research | HR2-581 | |
| Index HT screen | Hampton Research | HR2-134 | |
| Ionic Liquid screen | Hampton Research | HR2-214 | |
| Lithium bromide | Molecular Dimensions | MD2-100-312 | |
| Lithium chloride | Hampton Research | HR2-631 | |
| Lithium sulfate monohydrate | Hampton Research | HR2-545 | |
| Magnesium acetate tetrahydrate | Hampton Research | HR2-561 | |
| Magnesium chloride hexahydrate | Hampton Research | HR2-559 | |
| Magnesium nitrate hexahydrate | Hampton Research | HR2-657 | |
| Magnesium sulfate heptahydrate | Hampton Research | HR2-821 | |
| Manganese chloride tetrahydrate | Millipore Sigma | 63535-50G | |
| Manganese sulfate monohydrate | Molecular Dimensions | MD2-100-310 | |
| MARCO Polo GUI download | https://hauptman-woodward.github.io/Marco_Polo/ | ||
| Matrix Platemate 2 x 3 liquid handling robot | Thermo Scientific | ||
| MES pH 6.0 | Hampton Research | HR2-943-09 | |
| Mosquito liquid handling robot | SPTLabtech | ||
| Paraffin Oil/White Mineral Oil Saybolt Viscosity 340-365 at 100 °F | Sigma Aldrich | PX0045-3 | |
| PEG 1000 | Hampton Research | HR2-523 | |
| PEG 2000 | Hampton Research | HR2-592 | |
| PEG 20000 | Hampton Research | HR2-609 | |
| PEG 3350 | Hampton Research | HR2-527 | |
| PEG 400 | Hampton Research | HR2-603 | |
| PEG 4000 | Hampton Research | HR2-529 | |
| PEG 6000 | Hampton Research | HR2-533 | |
| PEG 8000 | Hampton Research | HR2-535 | |
| PEG/Ion HT screen | Hampton Research | HR2-139 | |
| PEGRx HT screen | Hampton Research | HR2-086 | |
| Plate reservations | htslab@hwi.buffalo.edu | ||
| Potassium acetate | Hampton Research | HR2-671 | |
| Potassium bromide | Hampton Research | HR2-779 | |
| Potassium carbonate | Molecular Dimensions | MD2-100-311 | |
| Potassium chloride | Hampton Research | HR2-649 | |
| Potassium nitrate | Hampton Research | HR2-663 | |
| Potassium phosphate dibasic | Hampton Research | HR2-635 | |
| Potassium phosphate-monobasic | Hampton Research | HR2-553 | |
| Potassium phosphate-tribasic | Molecular Dimensions | MD2-100-309 | |
| Potassium thiocyanate | Hampton Research | HR2-695 | |
| Rock Imager 1000 with SONICC | Formulatrix | ||
| Rock Imager 54 | Formulatrix | ||
| Rubidium chloride | Millipore Sigma | R2252-10G | |
| SaltRx HT screen | Hampton Research | HR2-136 | |
| Silver Bullets screen | Hampton Research | HR2-096 | |
| Slice pH screen | Hampton Research | HR2-070 | |
| Sodium acetate pH 5.0 | Hampton Research | HR2-933-15 | |
| Sodium bromide | Hampton Research | HR2-699 | |
| Sodium chloride | Hampton Research | HR2-637 | |
| Sodium citrate pH 4.2 | Hampton Research | HR2-935-01 | |
| Sodium citrate pH 5.6 | Hampton Research | HR2-735 | |
| Sodium hydroxide | Hampton Research | HR2-583 | |
| Sodium molybdate dihydrate | Molecular Dimensions | MD2-100-207 | |
| Sodium nitrate | Hampton Research | HR2-661 | |
| Sodium phosphate monobasic | Hampton Research | HR2-551 | |
| Sodium thiosulfate pentahydrate | Molecular Dimensions | MD-100-307 | |
| StockOptions Polymer screen | Hampton Research | HR2-227 | |
| Tacsimate pH 7 | Hampton Research | HR2-755 | |
| TAPS pH 9.0 | bioWORLD | 40121071 | |
| Tris pH 8 | Hampton Research | HR2-900-11 | |
| Tris pH 8.5 | Hampton Research | HR2-725 | |
| ViaFLO 384 | Integra | ||
| ViaFLO 384 384 channel pipettor head (0.5-12.5µL) | Integra | ||
| ViaFLO 384 96 channel pipettor head (300µL) | Integra | ||
| Zinc acetate dihydrate | Hampton Research | HR2-563 |
Références
- PDB data distribution by experimental method and molecular type. RCSB Protein Data Bank Available from: https://www.rcsb.org/stats/summary (2022)
- Maveyraud, L., Mourey, L. Protein X-ray crystallography and drug discovery. Molecules. 25 (5), 1030 (2020).
- Dupeux, F., Röwer, M., Seroul, G., Blot, D., Márquez, J. A. A thermal stability assay can help to estimate the crystallization likelihood of biological samples. Acta Crystallographica Section D: Biological Crystallography. 67 (11), 915-919 (2011).
- Elbasir, A., et al. DeepCrystal: A deep learning framework for sequence-based protein crystallization prediction. Bioinformatics. 35 (13), 2216-2225 (2019).
- Zucker, F. H., et al. Prediction of protein crystallization outcome using a hybrid method. Journal of Structural Biology. 171 (1), 64-73 (2010).
- George, A., Wilson, W. W. Predicting protein crystallization from a dilute solution property. Acta Crystallographica Section D: Biological Crystallography. 50 (4), 361-365 (1994).
- Jia, Y., Liu, X. -. Y. From surface self-assembly to crystallization: prediction of protein crystallization conditions. The Journal of Physical Chemistry B. 110 (13), 6949-6955 (2006).
- Slabinski, L., et al. XtalPred: A web server for prediction of protein crystallizability. Bioinformatics. 23 (24), 3403-3405 (2007).
- Abrahams, G. J., Newman, J. BLASTing away preconceptions in crystallization trials. Acta Crystallographica Section F: Structural Biology Communications. 75 (3), 184-192 (2019).
- Rosa, N., et al. Tools to ease the choice and design of protein crystallisation experiments. Crystals. 10 (2), 95 (2020).
- Newman, J., et al. On the need for an international effort to capture, share and use crystallization screening data. Acta Crystallographica Section F: Structural Biology and Crystallization Communications. 68 (3), 253-258 (2012).
- Lynch, M. L., Dudek, M. F., Bowman, S. E. A searchable database of crystallization cocktails in the PDB: analyzing the chemical condition space. Patterns. 1 (4), 100024 (2020).
- Jancarik, J., Kim, S. -. H. Sparse matrix sampling: a screening method for crystallization of proteins. Journal of Applied Crystallography. 24 (4), 409-411 (1991).
- Carter, C. W. Efficient factorial designs and the analysis of macromolecular crystal growth conditions. Methods. 1 (1), 12-24 (1990).
- McPherson, A., Cudney, B. Searching for silver bullets: An alternative strategy for crystallizing macromolecules. Journal of Structural Biology. 156 (3), 387-406 (2006).
- McPherson, A., Nguyen, C., Cudney, R., Larson, S. The role of small molecule additives and chemical modification in protein crystallization. Crystal Growth & Design. 11 (5), 1469-1474 (2011).
- Luft, J. R., DeTitta, G. T. A method to produce microseed stock for use in the crystallization of biological macromolecules. Acta Crystallographica Section D: Biological Crystallography. 55 (5), 988-993 (1999).
- Thakur, A. S., et al. Improved success of sparse matrix protein crystallization screening with heterogeneous nucleating agents. PLoS One. 2 (10), 1091 (2007).
- Chayen, N. E., Stewart, P. D. S., Blow, D. M. Microbatch crystallization under oil-a new technique allowing many small-volume crystallization trials. Journal of Crystal Growth. 122 (1-4), 176-180 (1992).
- Luft, J. R., et al. A deliberate approach to screening for initial crystallization conditions of biological macromolecules. Journal of Structural Biology. 142 (1), 170-179 (2003).
- Luft, J. R., Snell, E. H., DeTitta, G. T. Lessons from high-throughput protein crystallization screening: 10 years of practical experience. Expert Opinion on Drug Discovery. 6 (5), 465-480 (2011).
- Lynch, M. L., Snell, M. E., Potter, S. A., Snell, E. H., Bowman, S. E. 20 years of crystal hits: Progress and promise in ultrahigh-throughput crystallization screening. Acta Crystallographica Section D: Biological Crystallography. , (2023).
- Segelke, B. W. Efficiency analysis of sampling protocols used in protein crystallization screening. Journal of Crystal Growth. 232 (1-4), 553-562 (2001).
- Luft, J. R., Newman, J., Snell, E. H. Crystallization screening: the influence of history on current practice. Acta Crystallographica Section F. 70 (7), 835-853 (2014).
- Mlynek, G., Kostan, J., Leeb, S., Djinovic-Carugo, K. Tailored suits fit better: Customized protein crystallization screens. Crystal Growth & Design. 20 (2), 984-994 (2019).
- Mueller-Dieckmann, J. The open-access high-throughput crystallization facility at EMBL Hamburg. Acta Crystallographica Section D: Biological Crystallography. 62 (12), 1446-1452 (2006).
- Weber, P., et al. High-throughput crystallization pipeline at the crystallography core facility of the Institut Pasteur. Molecules. 24 (24), 4451 (2019).
- Lin, Y. What's happened over the last five years with high-throughput protein crystallization screening. Expert Opinion on Drug Discovery. 13 (8), 691-695 (2018).
- Haupert, L. M., Simpson, G. J. Screening of protein crystallization trials by second order nonlinear optical imaging of chiral crystals (SONICC). Methods. 55 (4), 379-386 (2011).
- Madden, J. T., DeWalt, E. L., Simpson, G. J. Two-photon excited UV fluorescence for protein crystal detection. Acta Crystallographica Section D: Biological Crystallography. 67 (10), 839-846 (2011).
- Fleming, A. M., et al. Second harmonic generation interrogation of the endonuclease APE1 binding interaction with G-quadruplex DNA. Analytical Chemistry. 94 (43), 15027-15032 (2022).
- Bruno, A. E., et al. Classification of crystallization outcomes using deep convolutional neural networks. PLoS One. 13 (6), 0198883 (2018).
- Holleman, E. T., Duguid, E., Keefe, L. J., Bowman, S. E. Polo: An open-source graphical user interface for crystallization screening. Journal of Applied Crystallography. 54 (2), 673-679 (2021).
- Niesen, F. H., et al. An approach to quality management in structural biology: Biophysical selection of proteins for successful crystallization. Journal of Structural Biology. 162 (3), 451-459 (2008).
- Padayatti, P., Palczewska, G., Sun, W., Palczewski, K., Salom, D. Imaging of protein crystals with two-photon microscopy. Biochemistry. 51 (8), 1625-1637 (2012).
- Haupert, L. M., DeWalt, E. L., Simpson, G. J. Modeling the SHG activities of diverse protein crystals. Acta Crystallographica Section D: Biological Crystallography. 68 (11), 1513-1521 (2012).
- Luft, J. R., Grant, T. D., Wolfley, J. R., Snell, E. H. A new view on crystal harvesting. Journal of Applied Crystallography. 47 (3), 1158-1161 (2014).
- Bruno, A. E., Soares, A. S., Owen, R. L., Snell, E. H. The use of haptic interfaces and web services in crystallography: An application for a 'screen to beam' interface. Journal of Applied Crystallography. 49 (6), 2082-2090 (2016).
- Baldock, P., Mills, V., Stewart, P. S. A comparison of microbatch and vapour diffusion for initial screening of crystallization conditions. Journal of Crystal Growth. 168 (1-4), 170-174 (1996).
Réimpressions et Autorisations
Demande d’autorisation pour utiliser le texte ou les figures de cet article JoVE
Demande d’autorisationThis article has been published
Video Coming Soon