Method Article
Microscopie à super-résolution du complexe synaptonémique dans la lignée germinale de Caenorhabditis elegans
Dans cet article
Résumé
La microscopie à super-résolution peut fournir un aperçu détaillé de l’organisation des composants au sein du complexe synaptonémique dans la méiose. Ici, nous démontrons un protocole pour résoudre les protéines individuelles du complexe synaptonemal Caenorhabditis elegans .
Résumé
Pendant la méiose, les chromosomes homologues doivent se reconnaître et adhérer les uns aux autres pour permettre leur ségrégation correcte. L’un des événements clés qui sécurise l’interaction des chromosomes homologues est l’assemblage du complexe synaptonémique (SC) dans la prophase méiotique I. Même s’il y a peu d’homologie de séquence entre les composants protéiques au sein du SC entre les différentes espèces, la structure générale du SC a été hautement conservée au cours de l’évolution. En micrographie électronique, le SC apparaît comme une structure tripartite, semblable à une échelle, composée d’éléments latéraux ou d’axes, de filaments transversaux et d’un élément central.
Cependant, l’identification précise de la localisation des composants individuels dans le complexe par microscopie électronique pour déterminer la structure moléculaire du SC reste difficile. En revanche, la microscopie à fluorescence permet d’identifier les composants protéiques individuels du complexe. Cependant, comme le SC n’a qu’une largeur de ~100 nm, sa sous-structure ne peut pas être résolue par la microscopie à fluorescence conventionnelle limitée par diffraction. Ainsi, la détermination de l’architecture moléculaire du SC nécessite des techniques de microscopie optique à super-résolution telles que la microscopie à illumination structurée (SIM), la microscopie à déplétion par émission stimulée (STED) ou la microscopie de localisation à molécule unique (SMLM).
Pour maintenir la structure et les interactions des composants individuels au sein du SC, il est important d’observer le complexe dans un environnement proche de son environnement natif dans les cellules germinales. Par conséquent, nous démontrons un protocole d’immunohistochimie et d’imagerie qui permet l’étude de la sous-structure du SC dans le tissu germinale intact et extrudé de Caenorhabditis elegans avec SMLM et microscopie STED. La fixation directe du tissu sur la lamelle de couverture réduit le mouvement des échantillons pendant l’imagerie et minimise les aberrations dans l’échantillon pour atteindre la haute résolution nécessaire pour visualiser la sous-structure du SC dans son contexte biologique.
Introduction
Réduire de moitié le nombre de chromosomes pendant la méiose est essentiel pour générer une progéniture saine chez les organismes à reproduction sexuée. Pour obtenir cette réduction du nombre de chromosomes, les chromosomes homologues doivent apparier et se séparer pendant la méiose I. Pour assurer la ségrégation précise des chromosomes homologues, les cellules germinales subissent une prophase I étendue, au cours de laquelle les chromosomes homologues s’apparient, se synapsent et se recombinent pour générer des liens physiques entre les homologues1. Le SC est devenu la structure centrale clé pour réguler la progression correcte à travers la prophaseméiotique 2.
Le SC est un complexe dont la structure générale est conservée au cours de l’évolution, même s’il y a peu d’homologie entre ses composants protéiques. Le SC a d’abord été identifié en micrographie électronique comme une structure tripartite, semblable à une échelle, composée de deux éléments latéraux ou axes, d’une région centrale formée de filaments transversaux et d’un élément central 3,4. La détermination de l’organisation des composants individuels au sein du complexe est essentielle pour faire progresser notre compréhension du rôle du CS pendant la prophase méiotique.
L’organisme modèle C. elegans est idéal pour étudier la structure et la fonction du SC puisque ses lignées germinales contiennent un grand nombre de noyaux méiotiques avec des SC5 entièrement assemblés. Des études génétiques et biochimiques ont révélé que les axes chromosomiques sont formés par trois complexes de cohésinedistincts 6,7 et quatre protéines du domaine HORMA appelées HTP-1/2/3 et HIM-3 7,8,9,10,11 chez C. elegans. Dans la région centrale du SC, six protéines contenant des domaines enroulés ont été identifiées à ce jour 12,13,14,15,16,17. Pour combler la distance entre les deux axes, SYP-1, -5 et -6 se dimérisent de manière directe (Figure 1), tandis que trois protéines supplémentaires stabilisent leur interaction dans l’élément central16,17,18,19.
L’obtention d’un aperçu détaillé de l’organisation de ces protéines est essentielle pour comprendre les nombreuses fonctions du SC pendant la méiose. Comme la largeur de la région centrale du SC n’est que de ~100 nm, sa sous-structure ne peut pas être résolue par la microscopie à fluorescence limitée par diffraction. Cependant, la visualisation des composants dans une structure de cette taille est facilement réalisable par microscopie à super-résolution. En effet, la microscopie à illumination structurée (SIM), la microscopieà expansion 20, la microscopie à déplétion par émission stimulée (STED) 21 et la microscopie de localisation à molécule unique (SMLM)22,23 sont apparues comme des outils essentiels pour étudier l’architecture moléculaire du SC chez les espèces 16,24,25,26,27,28,29, 30.
Pour surmonter la limite de résolution, la microscopie STED repose sur la superposition du point limité par diffraction de la lumière d’émission avec un faisceau en forme de beignet du laser STED, ce qui restreint théoriquement la fonction d’étalement du point jusqu’aux dimensions moléculaires31,32. Cependant, la résolution pratiquement réalisable par STED dans les échantillons biologiques reste de l’ordre de quelques dizaines de nanomètres en xy33.
Une résolution encore plus élevée dans les échantillons biologiques peut être obtenue avec les techniques SMLM. SMLM exploite les propriétés de clignotement de fluorophores spécifiques pour résoudre des objets au niveau de sous-diffraction en séparant les fluorophores qui se chevauchent spatialement dans le temps. L’échantillon est ensuite imagé à plusieurs reprises pour capturer différents sous-ensembles de fluorophores. La position des fluorophores dans l’échantillon est ensuite déterminée en ajustant la fonction d’étalement ponctuel (PSF) aux signaux obtenus sur toutes les images, ce qui peut résoudre des structures jusqu’à 15 nm23,34.
Prises ensemble, les images localisées codent les positions de tous les fluorophores. La résolution du SMLM est déterminée par la densité de marquage et les caractéristiques de clignotement du fluorophore. Selon le critère de Nyquist-Shannon, il est impossible de résoudre de manière fiable des objets dont la distance moyenne est inférieure à deux fois la distance moyenne d’étiquette à étiquette. Ainsi, une densité d’étiquetage élevée est nécessaire pour l’imagerie haute résolution. Pour le SC chez C. elegans, une densité de marquage élevée peut être obtenue en utilisant des marqueurs épitopiques attachés à des sites spécifiques de protéines endogènes en utilisant l’édition du génome. Les marqueurs d’épitopes peuvent ensuite être colorés à haute densité à l’aide d’anticorps monoclonaux spécifiques à forte affinité19,30. Dans le même temps, le cycle en cours des fluorophores individuels doit être suffisamment court pour garantir que les fluorophores qui se chevauchent dans l’espace ne sont pas capturés en même temps35.
En raison de ces deux exigences, la résolution de la structure de grands complexes macromoléculaires tels que le SC nécessite l’imagerie d’un nombre suffisamment important d’images, et peut donc prendre plusieurs heures. Le piège des longs temps d’imagerie est que les échantillons ont tendance à dériver en raison du mouvement de l’étage ou de petits courants dans le tampon de l’échantillon; Même de petits mouvements de l’ordre de 10 nm sont préjudiciables à la résolution nm et doivent être corrigés. Cependant, les méthodes de correction de la dérive couramment utilisées ne sont pas assez robustes pour superposer avec précision les images de deux canaux imagées séquentiellement36. Ceci est problématique car les questions biologiques demandent souvent une détection et une localisation précises de plusieurs cibles au sein d’un même échantillon. Pour contourner ces problèmes, des méthodes telles que l’imagerie ratiométrique ont été développées. L’imagerie ratiométrique permet l’imagerie simultanée de plusieurs fluorophores avec des spectres d’excitation et d’émission qui se chevauchent, avec une assignation ultérieure de chaque signal détecté à son fluorophore respectif en fonction du rapport des intensités dans des canaux spectralement distincts37,38.
De plus, l’étude de l’organisation de complexes macromoléculaires tels que le SC nécessite des informations tridimensionnelles (3D). Pour obtenir une super-résolution en trois dimensions (3D-SMLM), une lentille cylindrique est incorporée dans le trajet optique de la lumière émise qui déforme la forme du PSF d’un fluorophore en fonction de sa distance au plan focal. Par conséquent, la position précise d’un fluorophore dans le plan z peut être extrapolée en analysant la forme de son signal d’émission35,39. La combinaison de ces avancées en SMLM permet d’imager l’organisation 3D des complexes macromoléculaires, y compris le SC.
Protocole
1. Préparation des solutions et des feuillets de recouvrement
REMARQUE : Voir le tableau des matériaux pour plus de détails sur tous les matériaux et réactifs et le tableau 1 pour la composition des solutions utilisées dans ce protocole.
- Feuillets enduits de poly-L-lysine
- Préparer de la poly-L-lysine à 0,01 % (p/v) (voir tableau 1).
- Lavez une lamelle de couverture de précision (24 mm de diamètre; 0,17 ± 0,005 mm, n ° 1,5) dans de l’éthanol pendant 10-30 min. Rincer le couvercle avec duddH2Opour éliminer l’éthanol et laisser sécher le couvercle à température ambiante.
- Nettoyez au plasma le couvercle à l’aide d’un nettoyant plasma.
REMARQUE: Le nettoyage au plasma augmente l’hydrophilie de la lamelle de couverture et facilite les étapes suivantes. Si un nettoyant plasma n’est pas disponible, cette étape peut être ignorée, bien que cela puisse nécessiter un ajustement du volume et / ou de la concentration de la solution de poly-L-lysine. Cette modification n’a pas été testée. - Déposer une goutte (120 μL) de poly-L-lysine à 0,01 % (p/v) sur la lame. Incuber pendant 10 min à température ambiante.
- Après incubation, rincer la lamelle de couverture dans ddH2Oet sécher à température ambiante. Conserver à 4 °C jusqu’à 1 mois.
- Fragments F(ab')2 conjugués à des colorants organiques fluorescents
- Ajouter dans l’ordre suivant dans un tube de PCR : 10 μL de fragment F(ab')2 de 0,6-0,7 mg/mL dans du PBS, 1 μL de 0,1 M deNaHCO3 (pH 8,3) et 1 μL de 1 mM de fluorophore réactif ester de succinimidyl (NHS) dans le DMSO (rapport molaire de F(ab')2:colorant est ~1:17). Bien mélanger en pipetant de haut en bas.
- Incuber pendant 1 h à température ambiante.
- Séparer le fragment F(ab')2 du colorant réactif libre restant à l’aide d’une colonne de dessalage (7K MWCO) conformément aux spécifications du fabricant. Utilisez 1x PBS pour l’équilibration de la colonne et l’élution du fragment F(ab')2 étiqueté.
- Conservez le fragment F(ab')2 étiqueté à 4 °C jusqu’à 3 mois.
REMARQUE: Les durées de stockage de plus de 3 mois n’ont pas été testées.
2. Dissection et fixation
NOTE: Les procédures de dissection et de fixation sont modifiées par rapport aux procédures précédemment recommandées16,40 afin d’obtenir des échantillons optimaux pour la microscopie à super-résolution.
- Dissection
- Prélever des vers C. elegans appariés selon l’âge (cultivés à 20 °C pour cette étude) dans une goutte de 30 μL d’EBTT (1x tampon d’œufs41 avec 0,2 % de détergent non ionique, tableau 1) sur une lamelle de couverture (22 mm x 22 mm, no 1). Placez le couvercle sur une lame de verre pour faciliter la manipulation. Laver avec 30 μL d’EBTT en tuytant de haut en bas plusieurs fois. Retirer 30 μL de la solution pour laisser une goutte de 30 μL sur la lame.
REMARQUE: De petites quantités de détergent non ionique doivent être ajoutées à toutes les solutions dans lesquelles les vers sont pipetés pour empêcher les vers de coller aux embouts en plastique. - Utilisez une lame de scalpel pour couper la tête et/ou la queue des vers afin d’extruder la gonade (figure 2A).
- Prélever des vers C. elegans appariés selon l’âge (cultivés à 20 °C pour cette étude) dans une goutte de 30 μL d’EBTT (1x tampon d’œufs41 avec 0,2 % de détergent non ionique, tableau 1) sur une lamelle de couverture (22 mm x 22 mm, no 1). Placez le couvercle sur une lame de verre pour faciliter la manipulation. Laver avec 30 μL d’EBTT en tuytant de haut en bas plusieurs fois. Retirer 30 μL de la solution pour laisser une goutte de 30 μL sur la lame.
- Fixation
- Pipeter 30 μL de solution fixatrice (tableau 1) dans la goutte des vers disséqués et pipeter de haut en bas pour mélanger.
REMARQUE: Pipeter de haut en bas plusieurs fois peut aider à libérer plus de gonades. - Corriger pendant exactement 1 min après avoir ajouté la solution fixatrice.
- Arrêtez la fixation en transférant les vers dans un tube de PCR rempli de TBST (tableau 1). Transférer les vers dans le moins de volume possible (~15 μL).
- Faites tourner le tube PCR sur une mini centrifugeuse de paillasse (2 000 × g, 10 s). Retirer le surnageant et laver 2x avec 200 μL de TBST chacun.
- Laver avec 200 μL de PBST (tableau 1) pendant 5-10 min. Répétez les étapes 2.1.1 à 2.2.5 pour un maximum de quatre échantillons tout en conservant les échantillons disséqués sur la glace.
REMARQUE : Si vous traitez plus de quatre échantillons, passez aux étapes 2.2.6 à 2.2.7 tous les quatre échantillons pour vous assurer que la fixation de l’échantillon demeure uniforme dans tous les échantillons. - Faites tourner les échantillons disséqués sur une mini-centrifugeuse de paillasse (2 000 × g, 10 s), retirez le PBST et ajoutez 50 à 100 μL de méthanol froid (-20 °C).
ATTENTION : Le méthanol est toxique. Portez un équipement de protection et évitez l’inhalation. - Mélanger en pipetant de haut en bas et laisser les échantillons dans du méthanol pendant 30-60 s. Laver les échantillons 2x dans 200 μL de PBST.
REMARQUE : Si vous traitez plus de quatre échantillons, procéder à la dissection des échantillons restants (étapes 2.1.1 à 2.2.7). - Lavez les échantillons une troisième fois avec 200 μL de PBST.
- Pipeter 30 μL de solution fixatrice (tableau 1) dans la goutte des vers disséqués et pipeter de haut en bas pour mélanger.
3. Incubations d’anticorps
- Bloquant
- Bloquer les échantillons dans 1x Solution de blocage (Tableau 1) pendant 45 à 60 minutes à température ambiante.
NOTE: Le temps d’incubation peut varier de 30 min à température ambiante à plusieurs jours à 4 °C (les tests ont été effectués jusqu’à 3 jours).
- Bloquer les échantillons dans 1x Solution de blocage (Tableau 1) pendant 45 à 60 minutes à température ambiante.
- Solution d’anticorps primaires
- Diluer les anticorps anti-HTP-3 (poulet42) et anti-HA (souris) (ou les anticorps de votre choix) contre les solutions de travail (1:250 pour SMLM et 1:1 000 pour les échantillons de microscopie STED) dans 1x solution bloquante.
REMARQUE : Les anticorps utilisés pour marquer les échantillons SMLM sont plus concentrés que pour les échantillons STED puisqu’une densité de marquage plus élevée est recommandée pour la microscopie SMLM. - Faites tourner les échantillons sur une mini-centrifugeuse de paillasse (2 000 × g, 10 s), retirez le tampon de blocage et ajoutez 30 à 50 μL de la solution d’anticorps primaire. Incuber pendant une nuit à 4 °C (de préférence) ou pendant 1-2 h à température ambiante.
- Après l’incubation, laver 3 x 5-15 min avec PBST.
- Diluer les anticorps anti-HTP-3 (poulet42) et anti-HA (souris) (ou les anticorps de votre choix) contre les solutions de travail (1:250 pour SMLM et 1:1 000 pour les échantillons de microscopie STED) dans 1x solution bloquante.
- Solution de travail de fragments F(ab')2 conjugués à un colorant fluorescent
- Diluer les fragments F(ab')2 marqués (étape 1.2.4) dans les solutions de travail (1:100 pour SMLM et 1:1 000 pour les échantillons de microscopie STED) dans 1x solution de blocage.
REMARQUE: Pour les deux techniques de super-résolution, des paires de fluorophores précédemment signalées ont été utilisées, à savoir AlexaFluor647 / CF680 pour SMLM et AlexaFluor594 / Abberior STAR635P pour STED. AlexaFluor647 et STAR645P ont été utilisés pour marquer des fragments anti-souris (Fab')2 pour cibler l’extrémité C de SYP-5, et des fragments anti-poulet marqués CF680 / AlexaFluor594 (Fab')2 pour cibler HTP-3. - Faites tourner les échantillons sur une mini-centrifugeuse de paillasse (2 000 × g, 10 s), retirez le PBST et ajoutez 30 à 50 μL de solution d’anticorps secondaires. Incuber pendant 30 min à 2 h à température ambiante (de préférence) ou toute la nuit à 4 °C. Lavez 3 x 5-15 min avec PBST.
- Diluer les fragments F(ab')2 marqués (étape 1.2.4) dans les solutions de travail (1:100 pour SMLM et 1:1 000 pour les échantillons de microscopie STED) dans 1x solution de blocage.
4. Montage d’échantillons sur un bordereau de couverture
- Post-fixation
REMARQUE : Traitez les échantillons individuellement à travers les étapes 4.1.1-4.2.1.- Faites tourner les échantillons colorés et retirez le surnageant. Ajouter 50 μL de PBST0,2 et transférer les vers colorés sur une lamelle de couverture no 1 de 22 mm x 22 mm.
REMARQUE : Utilisez du PBST 0,2 frais avec un détergent non ionique à0,2 % (Tableau 1) pour cette étape afin d’empêcher les vers d’adhérer à la lamelle de couverture. - Pipet 5,7-6,3 μL de solution postfixatrice sur une lamelle de couverture de poly-L-lysine.
NOTE: Les lamelles de couverture en poly-L-lysine conservées à 4 °C doivent d’abord être portées à température ambiante. - Enlever les vers disséqués dans le même volume (5,7-6,3 μL) et transférer dans la goutte de fixateur sur la lamelle de couverture de poly-L-lysine (figure 2B).
REMARQUE: Dans cette étape et la suivante, il est très important de retenir le tissu disséqué au centre de la lame de couverture recouverte de poly-L-lysine. Ceci est particulièrement important si vous montez les échantillons dans un support personnalisé pour s’adapter au microscope SMLM personnalisé utilisé ici (voir étape 5.1, Figure 2B). - Couvrir l’échantillon d’une petite lamelle de couverture (12 mm de diamètre, figure 2B). Retirez l’excès de liquide à l’aide d’un petit morceau de papier filtre (figure 2B). Fixer pendant 3-5 min dans une chambre sombre.
- Faites tourner les échantillons colorés et retirez le surnageant. Ajouter 50 μL de PBST0,2 et transférer les vers colorés sur une lamelle de couverture no 1 de 22 mm x 22 mm.
- « Fissuration par congélation »
- Congeler les échantillons en les plaçant sur un bloc d’aluminium dans de la glace sèche (figure 2B).
REMARQUE: Le bloc d’aluminium doit être bien refroidi dans la glace sèche avant de placer les échantillons dessus. Procéder à la postfixation des échantillons restants (étapes 4.1.1 à 4.2.1). L’échantillon doit être sur glace sèche pendant au moins 20 minutes ou jusqu’à 1 heure avant l’étape suivante (4.2.2). - Retirez le plus petit couvercle à l’aide d’un rasoir (Figure 2B).
NOTE: Pour STED, passez à l’étape 5.2.1. Pour SMLM, passez à l’étape 4.2.3. - Trempez la lamelle de couverture dans un tube conique de 50 ml contenant du PBS glacé (de préférence) ou du méthanol à -20 °C pendant environ 10 s.
REMARQUE: La température est un facteur très important pour cette étape. Par conséquent, utilisez du PBS fraîchement décongelé ou conservé dans un bain de glace / éthanol. - Placez la lamelle de couverture dans un puits d’une plaque à six puits remplie de tampon PBST. Retirez le PBST des puits et ajoutez du PBS frais. Laissez les échantillons dans PBS pendant 5 min.
REMARQUE : Placez le PBS sur le côté du puits pour éviter d’endommager et de détacher les échantillons. - Laver avec du PBS frais et laisser les échantillons à 4 °C jusqu’à l’imagerie.
REMARQUE: Les échantillons sont stables jusqu’à 2 semaines, mais les meilleurs résultats sont obtenus si les échantillons sont imagés dans les 2 jours. - Avant l’imagerie, évaluez la qualité du montage de l’échantillon au stéréomicroscope.
REMARQUE: Les lignées germinales montées avec succès sont fixées de manière stable sans mouvement discernable par rapport à la lamelle de couverture. Les lignées germinales mal attachées battent dans la solution tampon.
- Congeler les échantillons en les plaçant sur un bloc d’aluminium dans de la glace sèche (figure 2B).
5. Imagerie
- Microscopie de localisation d’une seule molécule
REMARQUE : Les images ont été acquises au Centre d’imagerie de l’EMBL à l’aide d’un microscope de localisation à molécule unique construit sur mesure autour d’un corps personnalisé, tel que mentionné précédemment.38,43, avec les caractéristiques uniques spécifiées dans le Tableau des matériaux; Reportez-vous à https://www.embl.org/about/info/imaging-centre- Acquisition de l’étalonnage 3D des billes
- Préparer une lamelle de couverture de précision (24 mm de diamètre; 0,17 ± 0,005 mm, n° 1,5) avec des billes fluorescentes adhérentes de 100 nm comme décrit précédemment38,44.
- Placer l’échantillon d’étalonnage de l’étape 5.1.1.1 sur un porte-échantillon.
- Ajouter une goutte d’huile d’immersion sur l’objectif d’huile propre 100x/1.5 et monter l’échantillon d’étalonnage sur le microscope.
- Dans MicroManager 2 45,46, spécifiez15 à 20 positions dans l’échantillon d’étalonnage.
- Dans la fenêtre47 du plugin EMU, configurez l’acquisition d’une image z-stack pour chacune des positions de l’étape 5.1.1.5.
REMARQUE: Ici, une lentille cylindrique composée fournit l’astigmatisme requis pour l’imagerie 3D, et 201 coupes z ont été acquises pour chaque position couvrant la plage comprise entre -1 μm et 1 μm, avec un incrément de 10 nm. Un éclairage laser de 2 kW/cm2 640 nm a été utilisé pendant 25 ms pour chaque tranche z. - Acquérir les images z-stack des billes fluorescentes de 100 nm par un chemin optique identique qui sera utilisé pour acquérir des images d’échantillon à l’étape 5.1.11.
- À l’aide de la plateforme d’analyse microscopique à super-résolution (SMAP48), générer un modèle cspline de la fonction expérimentale d’étalement de point (PSF) qui sera utilisé pour ajuster les données 3D-SMLM à l’étape 5.1.13.
- Préparez le porte-échantillon. Pour le support sur mesure utilisé ici qui utilise un anneau magnétique pour créer la chambre d’imagerie (Figure 2B), enveloppez l’anneau magnétique avec un parafilm.
REMARQUE: Alternativement, une lame de microscope avec une cavité de dépression concave peut être utilisée pour monter des échantillons pour les microscopes avec des porte-lames. - Préparer 1 mL de tampon d’imagerie44 (tableau 1).
- Prenez un bordereau de couverture de l’étape 4.2.6 et placez-le dans le support sur mesure. Fixez la glissière dans le support à l’aide de l’anneau magnétique enveloppé d’un parafilm (étape 5.1.2).
- Pipeter doucement le tampon d’imagerie (étape 5.1.3) dans la chambre créée par l’anneau magnétique au-dessus de l’échantillon (Figure 2B). Scellez la chambre avec un morceau de parafilm.
- Pour monter l’échantillon, ajoutez une goutte d’huile d’immersion sur l’objectif d’huile propre 100x/1.5. Sans introduire d’air dans l’huile d’immersion, placez délicatement le porte-échantillon avec l’échantillon monté (étape 5.1.5) sur la platine du microscope.
REMARQUE: Avant de placer l’échantillon sur le microscope, nettoyez le fond de la lamelle de couverture avec du mouchoir et de l’éthanol à 70%. - À l’aide de la fenêtre du plug-inEMU 47 dans MicroManager 245,46, déplacez l’étage piézoélectrique jusqu’à ce que le signal du laser de verrouillage de mise au point soit détecté au niveau de la photodiode du quadrant (QPD).
REMARQUE: Pour maintenir une mise au point fixe pendant toute la durée de l’imagerie, le verrouillage de la mise au point est obtenu par réflexion interne totale d’un laser couplé à fibre proche infrarouge à partir de la lamelle de couverture et détection ultérieure sensible à la hauteur sur une photodiode quadrant (QPD). Le signal QPD fournissait un contrôle en boucle fermée de la monture piézoélectrique de l’objectif. - Acquérir une image du plan focal arrière avec un laser d’excitation de 640 nm à faible puissance (c.-à-d. 1-5%) pour confirmer l’absence de bulles d’air dans l’huile d’immersion.
REMARQUE : Retirez l’échantillon de la scène si une bulle d’air est détectée. Nettoyez le bas de la fiche de couverture et l’objectif et répétez les étapes 5.1.6-5.1.8. Sinon, procédez au verrouillage du focus dans le logiciel UEM47. - Localisez le tissu gonade à l’aide de l’éclairage en fond clair. À l’aide d’un éclairage de faible intensité de 640 nm, concentrez-vous sur la section du tissu qui contient de nombreux étirements SC.
REMARQUE : Ne vous concentrez pas sur les structures situées à plus de 2 μm de la lamelle de couverture. N’utilisez pas une puissance laser plus élevée pour localiser l’échantillon, car cela pourrait transformer prématurément certains fluorophores en un état clignotant. Ici, 1 kW/cm2 a été utilisé en mode ascendant avec une impulsion réglée sur 1 000. - Procéder à l’exposition de l’échantillon avec un éclairage de 640 nm à un éclairement énergétique élevé (27 kW/cm2) pendant ~30 s jusqu’à ce qu’un taux de clignotement approprié soit atteint (vidéo supplémentaire 1).
- Acquérir 200 000 images avec un temps d’exposition de 20 ms à l’aide de l’outil d’acquisition multidimensionnelle de MicroManager 245,46.
- Pendant ce temps, configurez l’activation UV en utilisant l’option d’activation du plugin EMU38,47 pour maintenir le taux de clignotement souhaité.
REMARQUE: Utilisez le laser UV à une irradiance de 3 kW / cm2 en mode ascendant avec une longueur d’impulsion maximale réglée sur 10 000. - Effectuez la reconstruction et le post-traitement d’images SMLM.
REMARQUE : Pour reconstruire des images à partir de données SMLM brutes, reportez-vous aux méthodes publiées. Les données présentées ici ont été traitées à l’aide du logiciel SMAP48,49. La reconstruction d’image super résolue, l’attribution de canaux, la correction de la dérive et le filtrage des localisations avec une précision de localisation médiocre et un filtre de vraisemblance maximale ont été effectués dans le logiciel SMAP48.
- Acquisition de l’étalonnage 3D des billes
- Microscopie à déplétion par émission stimulée
REMARQUE : Les images ont été acquises sur le système microscopique STED intégré équipé d’un laser à lumière blanche, d’un laser STED pulsé de 775 nm et du module de vieillissement IMFALCON FLuorescence Lifetime (Table of Materials) au Centre d’imagerie EMBL (https://www.embl.org/about/info/imaging-centre).- Placez une goutte de 20 μL de support de montage (table des matériaux) sur une lame de microscope. Prenez un couvercle de l’étape 4.2.2 et placez doucement l’échantillon sur la lame faisant face au support de montage (Figure 2B).
REMARQUE: Évitez d’introduire des poches d’air dans le support de montage. - Laissez le milieu de montage durcir pendant la nuit.
REMARQUE : Imagez les échantillons le lendemain ou conservez-les à 4 °C jusqu’à l’imagerie. - Pour monter l’échantillon, ajouter une goutte d’huile d’immersion sur la feuille de couverture de l’échantillon de l’étape 5.2.2. Placez délicatement l’échantillon sur la platine du microscope à l’aide d’un objectif d’huile 100x/1,40.
- Concentrez-vous sur l’échantillon et localisez le tissu germinal à l’aide de l’éclairage en champ clair.
- À l’aide du logiciel de microscope, spécifiez la région d’intérêt pour laquelle l’image TauSTED sera acquise.
- Sélectionnez les lasers d’excitation et leur puissance appropriée utilisés pour exciter les fluorophores utilisés dans l’échantillon.
REMARQUE: Ici, le laser 580 nm à 4% de puissance a été utilisé pour imager les fragments d’anticorps secondaires F(ab')2 conjugués AlexaFluor 594, et 635 nm à 3% de puissance pour imager les fragments F(ab')2 conjugués STAR 635P. - À l’aide du logiciel de microscope, sélectionnez une puissance laser d’épuisement STED appropriée et configurez la détection d’image.
REMARQUE: Ici, la puissance du laser d’épuisement STED 775 nm a été réglée sur 40%. Le détecteur a été utilisé en mode comptage avec une valeur de gain de 10 pour la détection de photons, avec une fréquence de balayage de 100 Hz et à une taille de pixel de 17 nm. L’accumulation de quatre lignes a été utilisée pour l’acquisition de TauSTED.
- Placez une goutte de 20 μL de support de montage (table des matériaux) sur une lame de microscope. Prenez un couvercle de l’étape 4.2.2 et placez doucement l’échantillon sur la lame faisant face au support de montage (Figure 2B).
Résultats
Pour imager le SC dans le tissu germinal de C. elegans par SMLM, nous avons utilisé le ratio 3D-SMLM à 2 couleurs pour localiser HTP-3, un composant des axes chromosomiques, et l’extrémité C du filament transversal SYP-5 marqué de manière endogène avec une étiquette d’hémagglutinine (HA). L’emplacement des deux protéines dans le SC de C. elegans a déjà été déterminé par d’autres études16,30.
Pour minimiser la diffusion de la lumière et les aberrations optiques inhérentes aux échantillons biologiques épais, nous avons imagé la section z la plus basse des noyaux méiotiques qui contiennent les SC (Figure 3, lignes jaunes). Pour chaque image acquise, la position de l’étage piézoélectrique du plan d’imagerie a été marquée par rapport à la position de l’étage piézoélectrique lorsque l’objectif était focalisé sur la lamelle de couverture. Cela a permis de calculer la distance piézoélectrique par rapport à la lamelle de couverture. Les échantillons montés avec succès sont fixés de manière stable près de la lamelle de couverture et conservent la forme de la gonade (c.-à-d. que le tissu n’est pas écrasé entre les deux lamelles de couverture pendant l’étape de postfixation). La qualité du montage de l’échantillon peut facilement être évaluée au stéréomicroscope puisque les gonades bien attachées ne montrent aucun mouvement en solution (étape 4.2.6). Néanmoins, en raison de la stochasticité du processus de montage, le tissu gonade ne sera pas nécessairement disposé complètement à plat sur la lamelle de couverture. Par conséquent, le plan inférieur des noyaux contenant des SC peut être trouvé à des distances variables par rapport à la lamelle de couverture dans la même gonade.
Pour illustrer comment la résolution change en fonction de la fixation du tissu au couvercle, nous avons acquis des images à différentes distances piézoélectriques par rapport au couvercle. Pour évaluer la qualité d’une image individuelle, les courbes de corrélation en anneaux de Fourier (FRC)50,51 ont été calculées et la résolution a été déterminée à l’aide du plugin FRCResolution dans le logiciel SMAP48. Deux noyaux représentatifs extraits de deux images 3D-SMLM distinctes prises à différentes distances de la lamelle de couverture sont représentés à la figure 4. Dans les SC situés près de la lamelle de couverture, les axes chromosomiques et l’extrémité C de SYP-5::HA sont bien résolus dans les trois dimensions (Figure 4A, 0,8 μm de la lamelle de couverture). Pour résoudre deux structures séparées par une distance donnée, la résolution FRC obtenue doit généralement être inférieure à la moitié de cette distance dans la résolution axiale.
Pour séparer latéralement les mêmes structures, des valeurs de résolution FRC encore plus petites doivent être atteintes. En effet, dans les échantillons situés à proximité immédiate de la lamelle de couverture, la résolution FRC est de 38 nm pour le canal AlexaFluor 647 et de 34 nm pour le canal CF680, et donc bien en dessous de la distance attendue de 84 nm entre les terminus C de SYP-516. Cette résolution résout donc facilement l’organisation du CS non seulement en vue frontale mais aussi en vue latérale (Figure 4B i,ii). En revanche, la résolution se détériore dans les SC situés à une distance de 5 μm de la lamelle de couverture en raison de la diffusion de la lumière et des aberrations sphériques (Figure 4B). Les résolutions FRC à cette distance tombent à 47 nm (AlexaFluor 647) et 41 nm (CF680), ce qui ne peut pas résoudre complètement les terminus C de SYP-5. Étant donné que les aberrations optiques altèrent la résolution latérale plus sévèrement que la résolution axiale, les bandes HTP-3 et SYP-5 ne sont plus clairement résolues dans la section transversale de la vue latérale dans les échantillons situés à une distance de 5 μm de la lamelle de couverture (figure 4B ii). La comparaison de la résolution FRC des images acquises à différentes distances piézoélectriques du bordereau de couverture a révélé que le tissu imagé ne devrait pas se trouver à plus de 2 μm du glissement de couverture (Figure 5). Ce résultat souligne l’importance d’une exécution correcte de l’étape postfixation, au cours de laquelle le tissu doit être réticulé avec succès au revêtement poly-L-lysine de la lamelle de couverture.
Pour démontrer la résolution réalisable avec une autre technique de super-résolution, nous avons également imagé des SC dans un tissu germinal intact fixe avec la microscopie TauSTED. La figure 6A montre les images TauSTED avec la résolution la plus élevée et la plus faible obtenue dans cette étude, estimées à partir des profils linéaires du SC en vue frontale (figure 6B). Dans les deux noyaux, nous avons pu résoudre les deux bandes de localisation de HTP-3 dans les axes chromosomiques et les terminus C de SYP-5 dans la région centrale, démontrant que la résolution réalisable dans TauSTED en utilisant ce protocole optimisé est inférieure à 84 nm. Dans des conditions optimales (Figure 6A, en haut), nous avons pu résoudre les C-termini dans des vues légèrement inclinées du SC qui n’étaient séparées que par 50 nm (Figure 6A, rectangle jaune et 6C).

Figure 1 : Schéma de l’organisation du complexe synaptonémique chez Caenorhabditis elegans. La caricature montre une structure simplifiée du SC chez C. elegans reliant deux chromosomes homologues (gris). La structure est représentée en vue frontale, latérale et en coupe transversale. Les axes chromosomiques sont affichés sous forme de barres rouges tandis que les filaments transversaux sont représentés en cyan. Les protéines de filament transversal (SYP-1, 5, 6 chez C. elegans) sont orientées de manière directe (graphiques cyan ball-stick) dans la région centrale pour combler la distance entre les deux axes. Les distances attendues entre les axes et les terminus C des filaments transversaux sont indiquées. Abréviation : SC = complexe synaptonémique. Veuillez cliquer ici pour voir une version agrandie de cette figure.
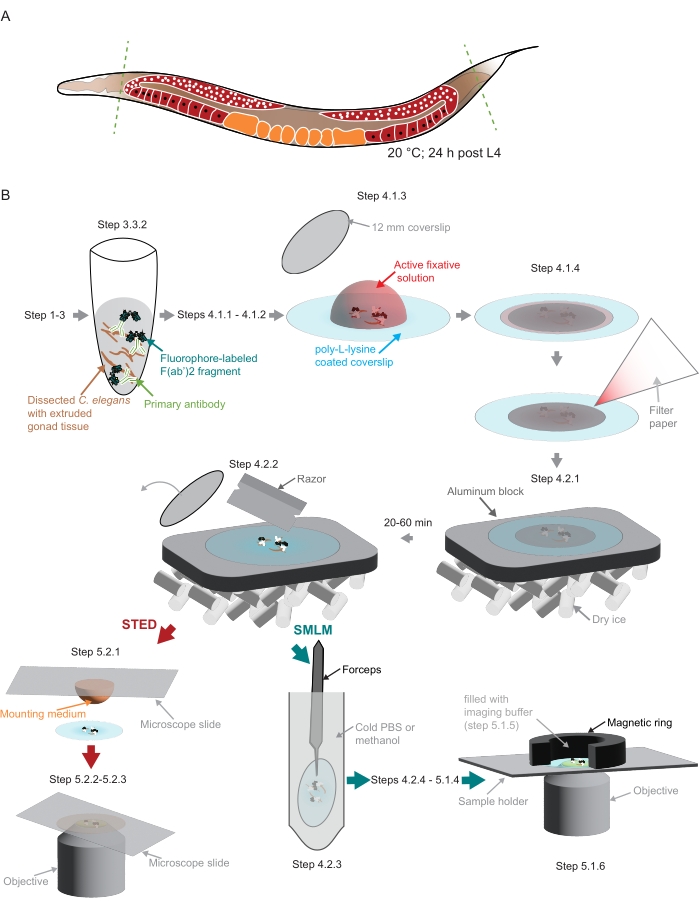
Figure 2 : Illustration de la préparation de l’échantillon utilisée dans l’étude. (A) Les jeunes adultes de C. elegans sont disséqués à la tête ou à la queue (verts, lignes pointillées) et traités comme décrit dans le protocole. (B) Les étapes individuelles de la méthode sont indiquées par des graphiques reliés par des flèches grises. Abréviations : STED = appauvrissement des émissions stimulées; SMLM = microscopie de localisation à molécule unique; PBS = solution saline tamponnée au phosphate. Veuillez cliquer ici pour voir une version agrandie de cette figure.
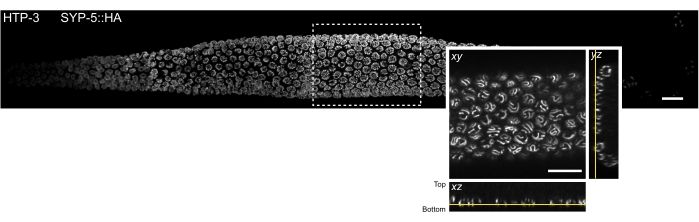
Figure 3 : Localisation de la coupe tissulaire qui peut être observée par microscopie de localisation d’une seule molécule. MIP d’une image confocale à disque rotatif d’une gonade entière du mont C. elegans. Le tissu a été coloré pour HTP-3 et l’extrémité C de SYP-5 (SYP-5::HA), et le signal combiné est indiqué en gris. Des images confocales individuelles ont été assemblées à l’aide du plugin Fiji52 de Grid/Collection Stitching pour créer une image de la gonade entière. L’encart montre une vue xy du plan z le plus bas contenant les SC. La localisation de ce plan est montrée dans les vues orthogonales de la section tissulaire indiquée par un rectangle dans l’image MIP de la gonade (lignes jaunes). Barres d’échelle = 10 μm. Abréviations : PIM = projection de l’intensité maximale; SC = complexes synaptonémiques. Veuillez cliquer ici pour voir une version agrandie de cette figure.
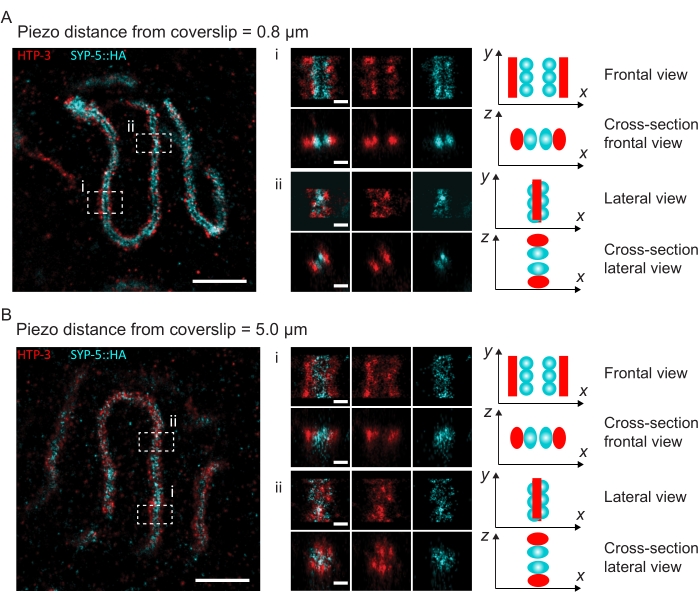
Figure 4 : Microscopie de localisation d’une seule molécule de HTP-3 et des terminus C du SYP-5. (A,B) À gauche : images SMLM montrant des noyaux de pachytène colorés pour HTP-3 (rouge) et l’extrémité C de SYP-5 (SYP-5::HA, cyan) (barre d’échelle = 1 μm). Centre: Images agrandies des régions d’intérêt indiquées dans A et B avec les vues en coupe correspondante affichées sous chaque image (i, ii; barre d’échelle = 100 nm). Les tronçons du SC dans les images zoomées sont tournés pour orienter les axes chromosomiques parallèlement à l’axe y. Droite: Représentation graphique de la localisation des protéines d’intérêt dans le SC représentant l’orientation du SC dans les régions zoomées affichées au centre de la figure. Abréviations : SMLM = microscopie de localisation à molécule unique; SC = complexe synaptonémique. Les données brutes pour reconstruire les images SMLM sont disponibles dans la base de données BioStudies60 (ID d’acquisition : S-BIAD504). Veuillez cliquer ici pour voir une version agrandie de cette figure.
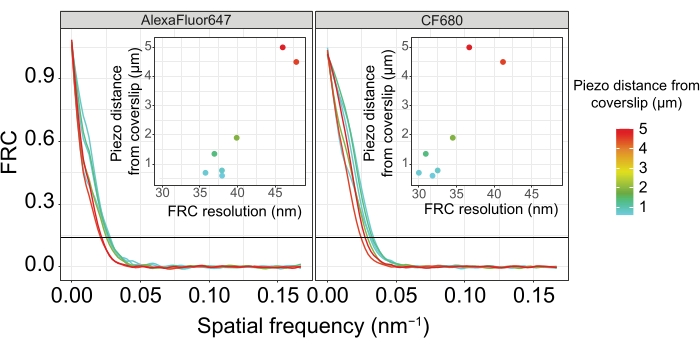
Figure 5 : La résolution de corrélation en anneau de Fourier des images de microscopie de localisation monomoléculaire dépend de la distance entre le plan z imagé et le plan de la lame. Les lignes colorées montrent les courbes FRC des images acquises à différentes distances (comme illustré par la barre de couleur) à partir de la lame. Le seuil 1/7 utilisé pour déterminer la résolution FRC est indiqué par une ligne horizontale noire. Les encarts montrent la dépendance de la résolution FRC sur la distance piézoélectrique de la lamelle de couverture. Le traçage a été effectué par un script R personnalisé (version 4.1.2, Fichier supplémentaire 1) dans lequel les courbes originales ont été lissées avec des fonctions du paquet « ggplot2 ». Abréviations : FRC = corrélation de l’anneau de Fourier; SMLM = microscopie de localisation à molécule unique; SC = complexe synaptonémique. Les données pour les courbes FRC et les données SMLM sont disponibles dans la base de données BioStudies60 (ID d’acquisition : S-BIAD504). Veuillez cliquer ici pour voir une version agrandie de cette figure.

Figure 6 : La microscopie à déplétion des émissions stimulées améliorée par les informations basées sur la durée de vie de fluorescence (TauSTED) résout deux bandes de localisation pour HTP-3 et l’extrémité C de SYP-5. (A) Deux images représentatives de TauSTED montrent des noyaux de pachytène colorés pour HTP-3 (rouge) et l’extrémité C de SYP-5 (SYP-5::HA, cyan) avec une définition structurelle supérieure (en haut) et inférieure (en bas) (barre d’échelle = 1 μm). Les rectangles marquent les régions avec les terminus C résolus de SYP-5 en frontal (blanc) et une vue légèrement inclinée (jaune) du SC. (B,C) Distribution du HTP-3 (rouge) et de l’extrémité C du signal SYP-5 (cyan) résolus par TauSTED. Les profils linéaires des régions d’intérêt qui contiennent le SC en vue frontale (B) ou légèrement inclinée (C) sont représentés sous forme de lignes pleines avec une intensité normalisée à la valeur maximale. Les profils de ligne ont été générés à l’aide de Fiji ImageJ. Les lignes pointillées dans B montrent les données moyennes pour chaque protéine. La ligne cyan épaisse en C correspond au profil de ligne avec la distance résolue la plus courte entre les terminus C de SYP-5. Pour déterminer les distances entre les anticorps ciblant des protéines spécifiques, les profils de lignée (n = 9 (B), n = 7 (C)) ont été ajustés avec des gaussiens doubles à l’aide d’un script R écrit sur mesure (version 4.1.2, fichier supplémentaire 1). La distance moyenne ±écart type (B) et la plage dont la valeur minimale est indiquée en gras (C) sont indiquées en haut de chaque graphique, respectivement. Abréviations : STED = microscopie à déplétion par émission stimulée; SC = complexe synaptonémique. Les images affichées et les points de données des profils linéaires tracés sont disponibles dans la base de données BioStudies60 (ID d’acquisition : S-BIAD504). Veuillez cliquer ici pour voir une version agrandie de cette figure.
Tableau 1 : Composition des tampons et des solutions utilisés dans ce protocole. Veuillez cliquer ici pour télécharger ce tableau.
Vidéo supplémentaire 1 : Acquisition par microscopie à localisation d’une seule molécule. Vidéo montrant des fluorophores clignotant à une vitesse appropriée (50 images sont montrées, barre d’échelle = 5 μm, 20 ms / image). Veuillez cliquer ici pour télécharger cette vidéo.
Fichier supplémentaire 1 : Script d’analyse des données. Veuillez cliquer ici pour télécharger ce fichier.
Discussion
L’organisation en échelle du SC, essentielle à la recombinaison et à la ségrégation correctes des chromosomes homologues, a été observée pour la première fois il y a près de 70 ans en microscopie électronique 3,4. Alors que l’organisation globale du SC est facilement résolue en microscopie électronique, la localisation des composants individuels au sein de ce complexe nécessite une approche plus ciblée. Avec sa largeur de seulement ~100 nm, la sous-structure du SC ne peut pas être résolue par la microscopie à fluorescence conventionnelle. Cependant, la microscopie à super-résolution est devenue un moteur majeur de nouvelles découvertes sur la structure et la fonction du complexe synaptonémique 16,19,24,25,26,27,28,29,30. Pour faciliter cette recherche, nous avons démontré une procédure de montage qui permet d’étudier l’architecture du SC dans le tissu gonade de C. elegans avec SMLM et microscopie STED.
Une étape critique pour optimiser la résolution dans l’imagerie SMLM consiste à réticuler directement le tissu germinal à une lame de couverture recouverte de poly-L-lysine (étape 4). La fixation covalente du tissu à la lamelle de couverture est essentielle pour réduire les mouvements à l’intérieur de l’échantillon qui entraîneraient de grandes dérives et rendraient impossible l’imagerie sur de longues périodes pour SMLM. De plus, même une fixation sous-optimale qui laisse les noyaux contenant des SC à distance de la lamelle de couverture entraîne une baisse significative de la résolution réalisable résultant d’aberrations sphériques (Figure 4). Alternativement à l’accessoire covalent utilisé ici, le tissu germinal coloré peut également être immobilisé entre deux lamelles de couverture scellées dans une petite goutte de tampon d’imagerie19,30. Cependant, cette méthode d’immobilisation réduit considérablement le volume de tampon d’imagerie dans l’échantillon de 1 mL utilisé dans le protocole optimisé ici à seulement quelques μL, ce qui entraînera une acidification du tampon d’imagerie et réduira considérablement le temps pendant lequel l’échantillon peut être imagé 38,53,54.
Les longs temps d’acquisition pour la microscopie SMLM et STED limitent l’utilisation de ces méthodes à l’imagerie d’échantillons fixés chimiquement. Ici, la fixation du paraformaldéhyde garantit que la structure du SC est préservée pendant la préparation et l’imagerie des échantillons. Cependant, malgré les précautions prises ici pour imager le SC dans un tissu intact, la structure résultante du SC après fixation n’est pas nécessairement identique à la structure à l’état natif dans un organisme vivant. De plus, puisqu’une seule image du SC fixe représente un seul « instantané » de la structure biologique, cette approche reste aveugle à la dynamique de la structure native in vivo.
Cependant, des informations sur la dynamique et la variabilité des structures macromoléculaires peuvent également être obtenues en acquérant non pas un seul, mais de nombreux « instantanés ». Bien que cette approche puisse résoudre les changements dans la structure du SC au cours du pachytène19, plusieurs facteurs limitent le nombre d’images pouvant être acquises à partir d’un seul échantillon préparé à l’aide de ce protocole. Premièrement, les puissances laser élevées utilisées lors de l’acquisition d’images entraînent un blanchiment permanent des fluorophores et empêchent l’imagerie de régions d’intérêt adjacentes ou de plusieurs plans Z, réduisant ainsi considérablement le nombre d’images pouvant être acquises à partir d’un seul échantillon. Deuxièmement, la densité de l’échantillon ou du tissu sur la lamelle de couverture préparée par cette méthode est faible, ce qui limite considérablement le nombre d’images pouvant être acquises à partir d’une seule lamelle de couverture. La faible densité d’échantillons interdit également l’utilisation de pipelines automatisés d’acquisition d’images qui ont permis de faire la lumière sur d’autres questions biologiques 34,55,56,57,58,59. Cependant, la densité de l’échantillon peut être légèrement augmentée par un utilisateur expérimenté.
Le protocole présenté ici est optimisé pour obtenir une densité d’étiquetage élevée nécessaire pour obtenir une résolution optimale dans SMLM35. Alors que les protocoles précédents fixaient de manière covalente le tissu à la lamelle de couverture avant l’immunomarquage16, ce nouveau protocole ne relie le tissu au couvercle qu’après que les échantillons aient été colorés en solution. Cette modification permet aux anticorps utilisés pour l’immunomarquage d’accéder librement au tissu de tous les côtés, tandis que la fixation covalente du tissu à la lamelle de couverture peut empêcher les anticorps d’atteindre les noyaux les plus proches de la lame, réduisant ainsi le degré de marquage. Ensemble, les modifications décrites ici améliorent la résolution de 40-50 nm (résolution FRC)16 à 30-40 nm (ce protocole).
Il est important de noter que, bien qu’une densité de marquage élevée et une concentration élevée d’anticorps soient essentielles pour SMLM, nous avons constaté que de meilleures images de microscopie STED sont obtenues en utilisant des concentrations d’anticorps plus faibles (étape 3). À une résolution de plusieurs dizaines de nanomètres, la taille des molécules utilisées pour marquer la protéine d’intérêt devient de plus en plus importante. Nous avons donc utilisé des fragments F(ab')2 qui font la moitié de la taille des anticorps pleine longueur. L’amélioration du contraste local due à une source de signal plus petite, et donc à la résolution obtenue par cette modification par rapport à l’utilisation d’anticorps secondaires pleine longueur, a permis la résolution des deux terminus C de SYP-5 dans la région centrale par TauSTED, qui ne sont pas résolus par STED conventionnel utilisant des anticorps pleine longueur (16 et données non présentées). Nous prévoyons que ce protocole optimisé pour l’imagerie des SC dans les lignées germinales intactes de C. eleganfacilitera l’étude de la relation structure-fonction du SC pendant la méiose.
Déclarations de divulgation
Les auteurs ne déclarent aucun conflit d’intérêts.
Remerciements
Nous tenons à remercier Jonas Ries et le laboratoire Ries d’avoir partagé des tampons d’imagerie pour l’imagerie SMLM. Nous remercions également Yumi Kim pour la souche C. elegans utilisée dans ce protocole et Abby F. Dernburg pour l’anticorps poulet-anti-HTP-3. Nous remercions Marko Lampe et Stefan Terjung de l’Advanced Light Microscopy Facility de l’EMBL Heidelberg pour leur soutien dans l’utilisation du microscope confocal Olympus iXplore SPIN SR. Ce travail a été soutenu par le Laboratoire européen de biologie moléculaire et la Deutsche Forschungsgemeinschaft (DFG, Fondation allemande pour la recherche - 452616889, SK). Nous reconnaissons l’accès et les services fournis par le Centre d’imagerie du Laboratoire européen de biologie moléculaire (EMBL IC), généreusement soutenu par la Fondation Boehringer Ingelheim.
matériels
| Name | Company | Catalog Number | Comments |
| 100x/1.5 oil objective | Olympus | UPLAPO100XOHR | UPLAPO100XOHR |
| 2-mercaptoethylamine (MEA) | Sigma-Aldrich | 30070-10G | Dissolved in MilliQ water to 5 M solution, pH 8.7 adjusted with HCl. Aliquoted to a single-use volume, frozen, and kept at -80 °C. |
| Additional 640 nm booster laser | Toptica | IBEAM-SMART-640-S-HP | |
| AlexaFluor 594, NHS ester | ThermoFischer Scientific | A37572 | Dissolved in DMSO to 1 mM solution, aliquoted to single use volume, frozen and kept at -80 °C |
| AlexaFluor 647, NHS ester | ThermoFischer Scientific | A37573 | Dissolved in DMSO to 1 mM solution, aliquoted to single use volume, frozen and kept at -80 °C |
| anti-HA | Thermo Fisher Scientific | 2-2.2.14 | Mouse monoclonal, 1:250 (SMLM), 1:1,000 (STED Microscopy) |
| anti-HTP-3 | a gift from Abby F. Dernburg | MacQueen et al., 2005 | Chicken polyclonal, 1:250 (SMLM), 1:1,000 (STED Microscopy) |
| Caenorhabditis elegans strain YKM349 | a gift from Yumi Kim | Hurlock et al., 2020 | syp-5(kim9[syp-5::HA]) I; meIs8[pie-1p::GFP::cosa-1, unc-119(+)] II |
| CF6680, NHS ester | Biotium | 92139 | Dissolved in DMSO to 1mM solution, aliquoted to single use volume, frozen and kept at -80 °C |
| Circular cover glass 12 mm No. 1 | Menzel-Gläser; VWR | 631-0713 | |
| Circular cover glass 24 mm No. 1.5 | Carl Roth | PK26.1 | |
| Cylindrical lenses | Thorlabs | LJ1516RM-A, LK1002RM-A | |
| Egg Buffer (10x) | Edgar 1995 | 250 mM HEPES, 1.18 M NaCl, 480 mM KCl, 20 mM EDTA, 5 mM EGTA, pH 7.4 | |
| Ethanol (absolute for analysis) | Merck | 64-17-5 | |
| F(ab’)2 fragment anti-chicken IgY | Jackson Immunoresearch | AB_2340347 | Donkey polyclonal, 1:100 (SMLM), 1:1,000 (STED Microscopy) |
| F(ab’)2 fragment anti-mouse IgG | Jackson Immunoresearch | AB_2340761 | Donkey polyclonal, 1:100 (SMLM), 1:1,000 (STED Microscopy) |
| Fisherbrand Microscope slides T/F Ground 0.8-1.0 mm thick | Fisher scientific | 7107 | |
| Gauge Worm Pick 30 diameter 0.254 mm - Iridium 10% | Kisker | 789265 | |
| Glucose oxidase/Catalase enzyme mix (GlOX/Cat ) | a gift from Jonas Ries | Hoess, Mund, Reitberger, & Ries, 2018 | 20x, 1916 U/mL glucose oxidase (Sigma G7141), 42350 U/mL catalase (Sigma C3155), 50 mM Tris-HCl pH 8.0, 51% glycerol, MilliQ water. Stored at -20 °C. |
| Imaging buffer base | a gift from Jonas Ries | Hoess, Mund, Reitberger, & Ries, 2018 | 50 mM Tris-HCl, pH 8.0, 10 mM NaCl, 10% D-Glucose. Aliquoted to a single-use volume (950 μL), frozen, and kept at -80 °C. |
| Invitrogen ProLong Glass Antifade Mountant | ThermoFischer Scientific | P36982 | |
| Leica Stellaris 8 STED FALCON | Leica | N/A | The microscope is equiped with the latest generation white light laser, a 775nm pulsed STED laser, the FALCON Fluorescence Lifetime IMaging module, HC PL APO CS2 100x/1.40 oil objective, and Leica HyD X detector. The system is capable of FLIM module enhanced Tau-STED which measures the specific fluorescence lifetime of a dye and is therefore capable of removing background signal based on differences in fluorescence lifetimes of the dyes, and dye conditions in the sample. Additionally, the resolution is increased by accounting for the variation of fluorescence lifetimes in different areas of the depletion donut. |
| Longwave channel emission filter | AHF Analysentechnik | F47-702 | 700/100 nm bandpass |
| Methanol (absolute for analysis) | Merck | 67-56-1 | |
| NaHCO3 | Sigma-Aldrich/Merck | S5761-500G | 100 mM NaHCO3, pH 8.3 |
| Near-infrared fiber-coupled laser | Toptica | IBEAM-SMART-PT-CD | Custom Design, 808 nm - 75mW |
| Objective lens piezo mount (PIFOC ) | Physik Instrumente | P-726.1.CD | 100 µm travel range |
| Orca Fusion BT sCMOS camera | Hamamatsu | C15440-20UP | |
| PCR tubes | Greiner Bio-One | 673283 | 0.2 mL |
| Phosphate Saline Buffer (PBS 10x) | N/A | 137 mM NaCl, 2.7 mM KCl, 10 mM Na2HPO4, 1.8 mM KH2PO4, pH 7.4 | |
| Pierce 16% formaldehyde (w/v), methanol free | ThermoFischer Scientific | 28906 | 16% formaldehyde is transferred from the original glass ampule into 1.5 mL tube and kept at room temperature. |
| PlasmaPrep2 plasma cleaner | GaLa Instrumente GmbH | N/A | |
| Poly-L-lysine hydrobromide | Sigma-Aldrich/Merck | P2636-25MG | 0.1% w/v solution was prepared in Milli-Q water, and stored in aliquots at -20 °C. |
| Primary dichroic (illumination reflecting) | AHF Analysentechnik | F73-866S | quad bandpass @ 405, 488, 561, 640 |
| Quadnotch filter | AHF Analysentechnik | F40-072 | 405/488/561/640 nm |
| Quadrant photodiode (QPD) | Laser Components | SD197-23-21-041, LC301DQD-PV | |
| Razor blades | Apollo Herkenrath Solinger | N/A | |
| Refractive beam shaper | AdlOptica | PiShaper 6_6_VIS | |
| Roche Blocking Reagent | Roche | 11096176001 | 10x solution was prepared according to recommendation. Frozen aliquots were stored at -20 °C. |
| Scalpel blade (Feather brand #11, No. 3) | Heinz Herenz Medizinalbedarf GmbH | 1110911 | |
| Scalpel removal box | Fisher scientific | 10002-50 | |
| Secondary dichroic (emission reflecting) | AHF Analysentechnik | F38-785S | 750 nm longpass |
| Shortpass filter | Semrock | BSP01-785R-25 | 750 nm |
| Shortwave channel emission filter | AHF Analysentechnik | F37-677 | 676/37 nm bandpass |
| Single molecule localization microscope | EMBL Imaging Centre | Diekmann et al., 2020 with modifications | The microscope provides widefield epi-illumination via a single-mode fiber-coupled laser engine, additional booster laser, and refractive beam shaper to provide a uniform illumination field (Stehr et al, 2019). Widefield images are captured on a sCMOS camera and appropriate relay optics for a system magnification of 61x and a pixel size of 106 nm. For ratiometric imaging of spectrally overlapping far-red dyes, an image splitter produces two spectrally distinct images on the camera (splitting dichroic: 665 nm long pass, shortwave channel emission filter: 676/37 nm bandpass, longwave emission filter: 700/100 nm bandpass. An additional 405/488/561/640 nm quadnotch filter and 750 nm shortpass filter are common to the two paths and provide additional laser blocking). A compound cylindrical lens provides the astigmatism required for 3D imaging. To maintain a fixed focus across acquisitions exceeding 2 hours in time (comprising 200 000 - 250 000 images), focus locking is achieved by total internal reflection of a near-infrared fiber-coupled laser from the coverslip and subsequent height sensitive detection on a quadrant photodiode (QPD). The QPD signal provided closed-loop control of the objective lens piezo mount. For access to this microscope, refer to https://www.embl.org/about/info/imaging-centre or contact ic-contact@embl.de |
| Single-mode fiber-coupled multi-laser engine | Toptica | iCHROME MLE-LFA-HP | Provides widefield epi-illumination of 100 mW at 405, 488, 561, 640 nm |
| Splitting dichroic | AHF Analysentechnik | F48-665SG | 665 nm long pass |
| Square cover glass 22 x 22 mm No.1 | Menzel-Gläser; VWR | 630-2882 | |
| STAR 635P, NHS ester | Abberior | ST635P-0002-1MG | Dissolved in DMSO to 1 mM solution, aliquoted to single use volume, frozen and kept at -80 °C |
| Stereo microscope Stemi 305 Stand K LAB | Zeiss | N/A | |
| Tetramisole hydrochloride | Sigma-Aldrich/Merck | T1512-2G | 1% (w/v) solution was prepared in Milli-Q water. Frozen aliquots were stored at -20 °C. Thawed aliquot was kept at 4 °C and used for several months. |
| TetraSpeck Microspheres | ThermoFischer Scientific | T7279 | 0.1 µm, fluorescent blue/green/orange/dark red |
| Tris Saline Buffer (TBS 10x) | N/A | 200 mM Tris-HCl, 1.5 M NaCl, pH 7.5 | |
| TWEEN 20 | Sigma-Aldrich/Merck | P9416-50ML | Kept at room temperature in original packaging. |
| WormStuff worm pick | Kisker | 789277 | |
| XY microscope stage | Smaract | N/A | Custom Design |
| Zeba Micro Spin Desalting Column | ThermoFischer Scientific | 89877 | 7K MWCO, 75 µL |
Références
- Zickler, D., Kleckner, N. Meiotic chromosomes: integrating structure and function. Annual Review of Genetics. 33, 603(1999).
- Ur, S. N., Corbett, K. D. Architecture and dynamics of meiotic chromosomes. Annual Review of Genetics. 55, 497-526 (2021).
- Fawcett, D. W. The fine structure ot chromosomes in the meiotic prophase of vertebrate spermatocytes. The Journal of Biophysical and Biochemical Cytology. 2 (4), 403-406 (1956).
- Moses, M. J. Chromosomal structures in crayfish spermatocytes. The Journal of Biophysical and Biochemical Cytology. 2 (2), 215-218 (1956).
- Hillers, K. J., Jantsch, V., Martinez-Perez, E., Yanowitz, J. L. Meiosis. WormBook. , 433-434 (2017).
- Pasierbek, P., et al. A Caenorhabditis elegans cohesion protein with functions in meiotic chromosome pairing and disjunction. Genes & Development. 15 (11), 1349-1360 (2001).
- Severson, A. F., Ling, L., Van Zuylen, V., Meyer, B. J. The axial element protein HTP-3 promotes cohesin loading and meiotic axis assembly in C. elegans to implement the meiotic program of chromosome segregation. Genes & Development. 23 (15), 1763-1778 (2009).
- Zetka, M. C., Kawasaki, I., Strome, S., Müller, F. Synapsis and chiasma formation in Caenorhabditis elegans require HIM-3, a meiotic chromosome core component that functions in chromosome segregation. Genes & Development. 13 (17), 2258-2270 (1999).
- Martinez-Perez, E. HTP-1-dependent constraints coordinate homolog pairing and synapsis and promote chiasma formation during C. elegans meiosis. Genes & Development. 19 (22), 2727-2743 (2005).
- Couteau, F., Zetka, M. HTP-1 coordinates synaptonemal complex assembly with homolog alignment during meiosis in C. elegans. Genes & Development. 19 (22), 2744-2756 (2005).
- Goodyer, W., et al. HTP-3 Links DSB Formation with Homolog Pairing and Crossing Over during C. elegans Meiosis. Developmental Cell. 14 (2), 263-274 (2008).
- Colaiácovo, M. P., et al. Synaptonemal complex assembly in C. elegans is dispensable for loading strand-exchange proteins but critical for proper completion of recombination. Developmental Cell. 5 (3), 463-474 (2003).
- MacQueen, A. J., Colaiácovo, M. P., McDonald, K., Villeneuve, A. M. Synapsis-dependent and -independent mechanisms stabilize homolog pairing during meiotic prophase in C. elegans. Genes & Development. 16 (18), 2428-2442 (2002).
- Smolikov, S., et al. Synapsis-defective mutants reveal a correlation between chromosome conformation and the mode of double-strand break repair during Caenorhabditis elegans meiosis. Genetics. 176 (4), 2027-2033 (2007).
- Smolikov, S., Schild-Prüfert, K., Colaiácovo, M. P. A yeast two-hybrid screen for SYP-3 interactors identifies SYP-4, a component required for synaptonemal complex assembly and chiasma formation in Caenorhabditis elegans meiosis. PLoS Genetics. 5 (10), 1000669(2009).
- Hurlock, M. E., et al. Identification of novel synaptonemal complex components in C. Elegants. The Journal of Cell Biology. 219 (5), (2020).
- Zhang, Z., et al. Multivalent weak interactions between assembly units drive synaptonemal complex formation. The Journal of Cell Biology. 219 (5), (2020).
- Schild-Prüfert, K., et al. Organization of the synaptonemal complex during meiosis in Caenorhabditis elegans. Genetics. 189 (2), 411-421 (2011).
- Köhler, S., Wojcik, M., Xu, K., Dernburg, A. F. The interaction of crossover formation and the dynamic architecture of the synaptonemal complex during meiosis. bioRxiv. , (2020).
- Chen, F., Tillberg, P. W., Boyden, E. S. Expansion microscopy. Science. 347 (6621), 543-548 (2015).
- Klar, T. A., Jakobs, S., Dyba, M., Egner, A., Hell, S. W. Fluorescence microscopy with diffraction resolution barrier broken by stimulated emission. Proceedings of the National Academy of Sciences. 97 (15), 8206-8210 (2000).
- Rust, M. J., Bates, M., Zhuang, X. Sub-diffraction-limit imaging by stochastic optical reconstruction microscopy (STORM). Nature Methods. 3 (10), 793-796 (2006).
- Betzig, E., et al. Imaging intracellular fluorescent proteins at nanometer resolution. Science. 313 (5793), 1642-1645 (2006).
- Schücker, K., Holm, T., Franke, C., Sauer, M., Benavente, R. Elucidation of synaptonemal complex organization by super-resolution imaging with isotropic resolution. Proceedings of the National Academy of Sciences. 112 (7), 2029-2033 (2015).
- Cahoon, C. K., et al. Superresolution expansion microscopy reveals the three-dimensional organization of the Drosophila synaptonemal complex. Proceedings of the National Academy of Sciences. 114 (33), 6857-6866 (2017).
- Zwettler, F. U., et al. Tracking down the molecular architecture of the synaptonemal complex by expansion microscopy. Nature Communications. 11 (1), 1-11 (2020).
- Yoon, S., Choi, E. H., Kim, J. W., Kim, K. P. Structured illumination microscopy imaging reveals localization of replication protein A between chromosome lateral elements during mammalian meiosis. Experimental & Molecular Medicine. 50 (8), 1-12 (2018).
- Prakash, K., et al. Superresolution imaging reveals structurally distinct periodic patterns of chromatin along pachytene chromosomes. Proceedings of the National Academy of Sciences. 112 (47), 14635-14640 (2015).
- Xu, H., et al. Molecular organization of mammalian meiotic chromosome axis revealed by expansion STORM microscopy. Proceedings of the National Academy of Sciences. 116 (37), 18423-18428 (2019).
- Köhler, S., Wojcik, M., Xu, K., Dernburg, A. F. Superresolution microscopy reveals the three-dimensional organization of meiotic chromosome axes in intact Caenorhabditis elegans tissue. Proceedings of the National Academy of Sciences. 114 (24), 4734-4743 (2017).
- Hell, S. W. Far-field optical nanoscopy. Science. 316 (5828), 1153-1158 (2007).
- Hein, B., Willig, K. I., Hell, S. W. Stimulated emission depletion (STED) nanoscopy of a fluorescent protein-labeled organelle inside a living cell. Proceedings of the National Academy of Sciences. 105 (38), 14271-14276 (2008).
- Jahr, W., Velicky, P., Danzl, J. G. Strategies to maximize performance in STimulated Emission Depletion (STED) nanoscopy of biological specimens. Methods. 174, 27-41 (2019).
- Thevathasan, J. V., et al. Nuclear pores as versatile reference standards for quantitative superresolution microscopy. Nature Methods. 16 (10), 1045-1053 (2019).
- Xu, K., Shim, S. -H., Zhuang, X. Super-resolution imaging through stochastic switching and localization of single molecules: an overview. Far-Field Optical Nanoscopy. , 27-64 (2013).
- Wang, Y., et al. Localization events-based sample drift correction for localization microscopy with redundant cross-correlation algorithm. Optics Express. 22 (13), 15982(2014).
- Winterflood, C. M., Platonova, E., Albrecht, D., Ewers, H. Dual-color 3D superresolution microscopy by combined spectral-demixing and biplane imaging. Biophysical Journal. 109 (1), 3-6 (2015).
- Diekmann, R., et al. Optimizing imaging speed and excitation intensity for single molecule localization microscopy. Nature Methods. 17 (9), 909(2020).
- Huang, B., Wang, W., Bates, M., Zhuang, X. Three-dimensional super-resolution imaging by stochastic optical reconstruction microscopy. Science. 319 (5864), 810-813 (2008).
- Phillips, C. M., McDonald, K. L., Dernburg, A. F. Cytological analysis of meiosis in Caenorhabditis elegans. Methods in Molecular Biology. 558, 171-195 (2009).
- Edgar, L. G. Blastomere culture and analysis. Methods in Cell Biology. 48, 303-321 (1995).
- MacQueen, A. J., et al. Chromosome sites play dual roles to establish homologous synapsis during meiosis in C. elegans. Cell. 123 (6), 1037-1050 (2005).
- Stehr, F., Stein, J., Schueder, F., Schwille, P., Jungmann, R. Flat-top TIRF illumination boosts DNA-PAINT imaging and quantification. Nature Communications. 10 (1), 1-8 (2019).
- Hoess, P., Mund, M., Reitberger, M., Ries, J. Dual-color and 3D super-resolution microscopy of multi-protein assemblies. Methods in Molecular Biology. 1764, 237-251 (2018).
- Edelstein, A., Amodaj, N., Hoover, K., Vale, R., Stuurman, N. Computer Control of microscopes using µManager. Current Protocols in Molecular Biology. 92 (1), 14-20 (2010).
- Edelstein, A. D., et al. Advanced methods of microscope control using µManager software. Journal of Biological Methods. 1 (2), 10(2014).
- Deschamps, J., Ries, J. EMU: reconfigurable graphical user interfaces for Micro-Manager. BMC Bioinformatics. 21 (1), 1-13 (2020).
- Ries, J. SMAP: a modular super-resolution microscopy analysis platform for SMLM data. Nature Methods. 17 (9), 870-872 (2020).
- Li, Y., et al. Global fitting for high-accuracy multi-channel single-molecule localization. Nature Communications. 13 (1), 1-11 (2022).
- Nieuwenhuizen, R. P. J., et al. Measuring image resolution in optical nanoscopy. Nature Methods. 10 (6), 557-562 (2013).
- Banterle, N., Bui, K. H., Lemke, E. A., Beck, M. Fourier ring correlation as a resolution criterion for super-resolution microscopy. Journal of Structural Biology. 183 (3), 363-367 (2013).
- Preibisch, S., Saalfeld, S., Tomancak, P. Globally optimal stitching of tiled 3D microscopic image acquisitions. Bioinformatics. 25 (11), 1463-1465 (2009).
- Shi, X., Lim, J., Ha, T. Acidification of the oxygen scavenging system in single-molecule fluorescence studies: in situ sensing with a ratiometric dual-emission probe. Analytical Chemistry. 82 (14), 6132-6138 (2010).
- Olivier, N., Keller, D., Rajan, V. S., Gönczy, P., Manley, S. Simple buffers for 3D STORM microscopy. Biomedical Optics Express. 4 (6), 885-899 (2013).
- Mund, M., et al. Superresolution microscopy reveals partial preassembly and subsequent bending of the clathrin coat during endocytosis. bioRxiv. , (2022).
- Mund, M., et al. Systematic nanoscale analysis of endocytosis links efficient vesicle formation to patterned actin nucleation. Cell. 174 (4), 884-896 (2018).
- Sabinina, V. J., et al. Three-dimensional superresolution fluorescence microscopy maps the variable molecular architecture of the nuclear pore complex. Molecular Biology of the Cell. 32 (17), 1523-1533 (2021).
- Cieslinski, K., et al. Nanoscale structural organization and stoichiometry of the budding yeast kinetochore. bioRxiv. , (2021).
- Sieben, C., Banterle, N., Douglass, K. M., Gönczy, P., Manley, S. Multicolor single-particle reconstruction of protein complexes. Nature Methods. 15 (10), 777-780 (2018).
- Sarkans, U., et al. The BioStudies database—one stop shop for all data supporting a life sciences study. Nucleic Acids Research. 46, (2018).
Réimpressions et Autorisations
Demande d’autorisation pour utiliser le texte ou les figures de cet article JoVE
Demande d’autorisationThis article has been published
Video Coming Soon