このコンテンツを視聴するには、JoVE 購読が必要です。 サインイン又は無料トライアルを申し込む。
Method Article
ケーススタディとして、タバコにおける一過性タンパク質発現:実験アプローチのデザインを使用した複雑系のキャラクタリゼーション
要約
我々は、植物におけるモノクローナル抗体およびレポータータンパク質の一過性発現に対する導入遺伝子の調節エレメント、植物の成長および発達パラメータ、およびインキュベーション条件の影響を決定し、モデル化するのに使用することができる実験アプローチの設計を記載している。
要約
植物は、低コスト、拡張性、安全性などのバイオ医薬品の生産のための複数の利点を提供します。一過性の発現は、短期開発と生産時間の付加的な利点を提供していますが、発現レベルは、このように適正製造基準の文脈における規制の懸念を生じさせるバッチ間で大きく異なります。我々は、バッチ間の発現の変動性に発現中に調節発現構築物の要素、植物の成長および発達パラメータ、およびインキュベーション条件、などの主要な要因の影響を決定するための実験計画法(DoE)アプローチの設計を用いる。私たちは、モデル抗HIVモノクローナル抗体(2G12)、蛍光マーカータンパク質(DsRedの)を発現する植物をテストしました。我々は、モデルの特定のプロパティを選択するための理論的根拠を議論し、その潜在的な制限を識別します。一般的なアプローチは、容易に他の問題に転送することができるため、モデルaの原理広く適用日時:知識ベースのパラメータの選択、より小さなモジュールに最初の問題を分割することにより、複雑さの低減、最適な実験の組み合わせのソフトウェア誘導セットアップと段階的なデザイン増強。そのため、方法論だけでなく、植物におけるタンパク質発現を特徴付けるためだけでなく、機械論的な説明を欠いている他の複雑なシステムの調査のために有用である。パラメータ間の相互接続性を記述した予測式は、他の複雑なシステムのための機械論的なモデルを確立するために使用することができます。
概要
植物が成長する安価であるため、植物における生物薬剤学的タンパク質の産生が有利で あり、プラットフォームは、単により多くの植物を成長させることによってスケールアップすることができ、ヒト病原体1,2を複製することができない。 アグロバクテリウムツメファシエンスと葉の浸潤に例えば基づく一過性発現戦略DNA送達および精製された製品の納入の時点までの時間が2ヶ月未満〜3年に短縮されるため、追加の利点を提供します。一過性発現は、機能喪失型変異体を補完するか、タンパク質相互作用4-6を調査する能力についての遺伝子を試験するために、例えば 、機能分析のために使用される。しかしながら、一過性発現レベルは、トランスジェニック植物7-9における発現レベルよりも大きいバッチ間の変動を示す傾向がある。これは、バイオ医薬品製造プロセスは、一過性発現のWiに基づいて、可能性を減少させる再現性が重要な品質属性であるとリスク評価10される場合がありますので、適正製造基準(GMP)のコンテキストで承認されちゃう。このような変化も、研究者が調査する予定の相互作用をマスクすることができます。したがって、我々は、植物において一過性発現レベルに影響を与える主な要因を特定するために、高品質の定量的な予測モデルを構築するために設定してください。
1ファクターを1つずつ割り当てる(OFAT)アプローチは、多くの場合、実験11の結果( レスポンス )上の特定のパラメータ( 要因 )の影響( 効果 ) を特徴づけるために使用されている。調査( 実験 )中の個々のテスト( 実行 ) を試験している要因によって張ら潜在的な面積( 設計空間 )を介して文字列に真珠のように整列されますので、しかし、これは次善である。設計空間のカバレッジ、したがって実験から得られる情報の程度である図1A 12に示すように、低い。 図1B 13に示すように、さらに、異なる因子( 因子相互作用 )間の相互依存性が悪くモデルおよび/ または偽最適の予測をもたらす隠されたままにすることができる。
上述の欠点は、複数の因子が二つの実験14の間に変化することを意味し、実験の実行は、設計空間の全体にわたってより均一に散乱された実験計画法(DoE)アプローチの設計を使用することによって回避することができる。そこの混合物は、スクリーニングの要因( 要因計画 )に特化したデザインがあるとレスポンス( 応答曲面法、RSM S)15上の要因の影響の定量。さらに、中央のRSMは、複合デザインとして実現できるだけでなく、実行の選択のための異なる基準を適用することができ、特殊なソフトウエアを使用することによって効果的に達成することができる。例えば、いわゆるD-optimalitY基準はIV -最適性基準が設計空間15,16を通して最も低い予測分散を実現するランを選択し、一方、そのように得られたモデルの係数での誤差を最小化するために実行を選択します。我々はここで説明するRSMは、植物における一過性タンパク質発現の正確な定量を可能にするが、それは簡単にいくつかの(〜5-8)、数値の要因( 例えば 、温度、時間、濃度)、および2〜(数に関係する任意のシステムに転送することができます- 4)機械論的な説明がモデルに使用できないか、複雑すぎる合式因子( 例えばプロモーター 、色)が。
実験計画アプローチは農業科学の起源が、それは、それが信頼性のあるデータを得るために必要な実行回数を低減し、複雑なプロセスの記述的モデルを生成するのに有用である任意の状況に転送可能であるため、他の領域に広がっている。これは、順番には、「指導における実験計画の包含につながっている業界は、ヒト用医薬品(ICH)17を登録するための技術要件の調和に関する国際会議で発表さQ8(R2)の医薬品開発は「。エネルギー省は、現在の科学的研究と産業18で広く使用されているが、介護は時に注意が必要複数線形回帰モデル( ベースモデル )のための不適当な多項式の次数を選択しているため、計画、実験の実行が正しく、すべての因子の影響をモデル化するために追加の実行の必要性が生じる可能性があります。また、破損または欠落したデータが正しくないモデルと欠陥のあるを生成予測、さらには、プロトコルと議論のセクション18で説明したようにいずれのモデル構築の試みを防ぐことができます。プロトコル]セクションで、我々は最初に、RSMベースの実験のための最も重要な計画手順を設定し、エネルギー省に基づいて設計を説明しますソフトウェアのDesignExpert V8.1は。しかし、同じようなデザインは、他のソフトウェアincludiを使用して構築することができますNG JMP、Modde、およびSTATISTICA。実験手順は、データ分析·評価するための指示が続きます。
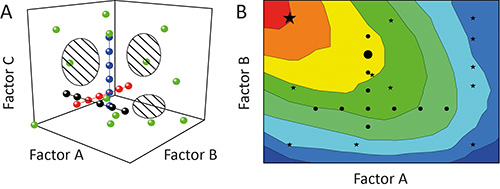
図1。 OFATとDOEの比較。A。実験(黒、赤と青の円)での時間(OFAT)にして1つの要素の逐次変化は設計空間(斜線領域)の低カバレッジを実現しています。これとは対照的に、実験(DOE)戦略(緑の円)のデザインを使用して、一度に複数の因子の変動が取材し、得られたモデル。Bをこのように精度が向上します。偏った設計空間カバレッジはOFAT実験(黒丸)も、最適な動作領域(赤)を特定し、次善の策(大きな黒丸)を予測するために失敗する可能性があることを意味し、一方、エネルギー省のstrategiES(黒い星)が好ましい条件(大きな黒い星)を識別する可能性が高くなります。
プロトコル
1。エネルギー省戦略の計画
- デザインに含めるための関連要因と応答を識別します。
- 測定のための1または複数の応答を定義します。ここで、2G12およびDsRedの発現レベルを使用した(μg/ ml)を、関連するとみなさ検出可能な最小の差を含む(10および20μg/ml/ mlのそれぞれ)とシステムの推定標準偏差の近似値(4,8μgの/ mLであった)先の実験に基づく。
- 入手可能な文献を使用し、これまでの実験や特殊なスクリーニングの設計からデータがインパクト応答に定量化されます( 表1)7,8,19,20有意な因子を選択する( 例:要因計画は、導入を参照してください)。
- (数値または合式)のファクタ·タイプを割り当てて、数値の要因はエネルギー省の調査( 表1)の間に変化される範囲内の範囲を選択します。
- numeriを識別C因子れる連続的な変化が実現するのは困難である。
- 一定のレベルに正確に調整することができない要因のための連続的な変化の使用は避けてください。 例えば 、培養温度は、通常、±2℃以内に制御することができ、このような27.2℃、25.9℃、29.3℃のマストなどの値を使用して、したがって連続的に変化避けること。
- その代わりに、これらの要素( 表1)のために別々のレベルの数を選択します。レベルの数は、予想されるベースモデル(ステップ1.2)と一致する必要があります。 中央の複合設計は常に離散的因子レベルを有するので、これは、最適な設計のためにのみ重要である。
- 、合式要因は、公称であるかどうかを割り当てる暗黙の順序( 例えば 、異なる製造業者)、または序ため、個別の数値パラメータ(植物上などさまざまな葉を)のIE ん 。
- 合式要因の両方のタイプのレベルを選択します。
- 便利なベースモデルを選択します。
- 予備実験や文献に基づいて、各因子と応答だけでなく、要因の相互作用と応答との関係を期待しています。例えば、直鎖(より良い)、二次(シングル最適な非線形増加/減少)や立方(最適スキュー)。
- 離散数値の要因のためのレベルの数は、nが要因と応答の関係を多項式の次数であることで、N + 1であることを確認してください。例えば、もし温度がn = 2の二次応答に影響を与えることが予想されるので、少なくとも3つの温度レベルは、二次効果に適合を達成するために調査されるべきである。
- 予測の分散が特定のしきい値(アルファレベル)以下でなければならないそのためのデザインスペースの割合(FDS)を定義します。 FDSは、全体で堅牢な予測をもたらすモデルを実現するために(設計空間の95%以上をカバー)> 0.95である必要があり全体設計空間の21〜23。
注:0.05の閾値は5%の有意水準(タイプIエラー)に対応し、典型的な値である。この値を大きくすると、エネルギー省の戦略に必要な実験の数が減少しますが、同時に重大な影響は逃したし、応答に与える影響の推定値が不正確になることがされる可能性を増加します。

表1。変動を含め、タバコの一過性タンパク質発現に影響を与える要因は、エネルギー省の間にわたる。太字の要因のみが斜体の要因に対し、「異なるプロモーター/の5'UTRを使用して一過性発現の間のDsRedの蓄積の記述モデル」の下に記載された実験のための設計に含まれていた唯一の "incubatio最適化するための設計に含まれていたn個の条件および「一過性発現を用いて、植物におけるモノクローナル抗体の産生のための収穫スキーム。
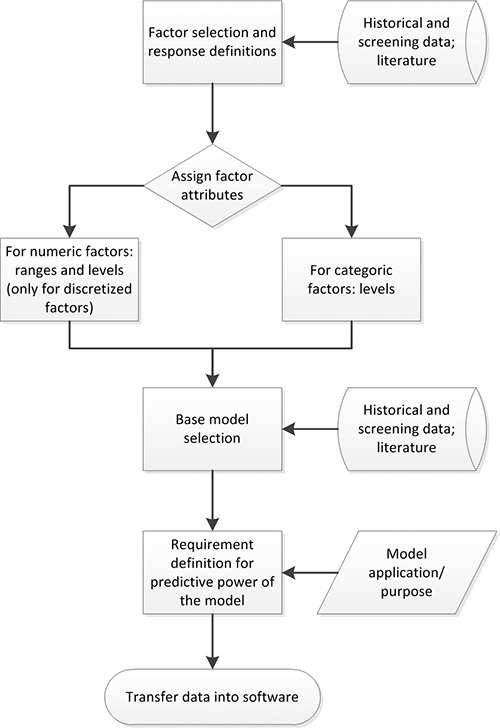
図2。エネルギー省の計画プロセス。調査中の応答に重要な影響を持つ要因は、利用可能なデータに基づいて選択される。その後、因子の属性( 例えば 、数値)、範囲とレベルが割り当てられます。以前の知識および実験は、適切なベースモデルを定義するために使用される。予測力要件は、最終的なモデルの適用/目的に基づいて定義されています。コンパイルされたデータは、その後、適切な実験計画ソフトウェアに転送することができる。
2。 DesignExpertでRSMを設定する
- DesignExpertを起動し、「新しいデザイン」を選択します。 「レスポンス面」ウィンドウで、選択した"最適」とセクション1.1で選択した数値と合式の要素)の数を入力してください。
- 対応するフィールド内のすべての要因要因名、単位、型、サブタイプ、レベル/レベルの境界とレベルの値の数を入力します。
- 次のページにして下に続けて「検索」オプションは、「最良の」だけでなく、所望の「最適性」の基準は、ここ「D-最適」を選択します。
- )「編集モデル... "メニューでは、セクション1.2で予想要因との相互作用を含むモデルを選択します。不確かな場合は、ここでは、特定の多項式の次数ためのすべての要素との相互作用、「二次」をカバーしてフルモデルを選択します。 (すべての相互作用を含む)の完全なモデルを選択すると、エネルギー省に必要な実験の数を増加させることができることに注意してください。
- 「ブロック」の数を選択します。すべての植物が同じバッチからのものであったので、ここでは、単一のブロックが使用された、すべての細菌を同時に培養したとすべての注射は、同じオペレータにより同日に行った。植物の複数のバッチが使用したり、複数の作業者が注射を扱うされている場合、複数のブロックを使用しています。
- デザインのバランスをとる
- 、合式因子レベル間で均等に実験の実行を分配するために、テストされ例えば 、異なるプロモーターを「合式のバランスを強制的に」可能にする。
注:これはDesignExpertが最適アルゴリズムによって選択された点に応じて、%値として報告されます程度に設計の最適性を減らすことができます。 - 最適性の低下を最小限に抑えるために実装ランダムシードアルゴリズムを用いて設計を複数回再計算する。
最適性の損失は、同じ入力データを用い〜百分の3から40の範囲であることができるが、反復の数が合式のバランスを維持するために使用することができる変える注:。
- 、合式因子レベル間で均等に実験の実行を分配するために、テストされ例えば 、異なるプロモーターを「合式のバランスを強制的に」可能にする。
- ソフトウェアは、ベースモデルに基づいて、「モデル点」の数の値を提案します、ここ70実行されます。 「レプリケート」のランの数を調整し、それがここにそれぞれのための「モデル点」、10回、各数の> 5%であることを保証するために、「フィットの欠如を推定するために」。
- 応答の数を選択して、自分の名前と単位を入力し、次のページに進んでください。追加の応答も、設計上の任意の負の影響を与えることなく、データ評価中の任意の時点で添加することができる。
- エネルギー省のランの因子レベルを計算するアルゴリズムを起動し続けています。選択した基本モデルは、特定の要因のためにレベルの数と一致しない場合、通知が表示され、計算が開始されません。この場合、次のいずれか
- この要因のためのレベルの数を増やす、または、
- レベルの現在の数に基づいて計算することができないベースモデルの用語の選択を解除します。
- 例えば、Tの要因「インキュベーション時間」T(すなわち 2 Dと5 D)には2つのレベルが存在する場合、彼の現在のデザインと2を選択した単語tを含む二次ベースモデルは、Tのための第3レベル( つまり 8 D)を追加したり、モデルから率T 2を削除いずれか。
- 計算が完了すると表示され、最適な係数の組み合わせを含むスプレッドシートを保存します。
- 「デザイン」ノードに「評価」のサブノードを選択し、「グラフ」タブに移動します。
- 「グラフツール」の「FDS」を選択し、「FDSグラフ」ボックスに、エラーの種類として「PRED "を選択します。そして、それぞれ「D」と「S」の値のDsRedのため(ここ20および8μg/ ml)をなどのセクション1.1.1で定義されたシステムの推定標準偏差の最小検出可能な差異だけでなく、近似値)を入力します。また、アプリケーションに適したアルファレベル(許容%は大きな影響がありません)、一般的に0.05(5%)を入力します。
- )を計算し、FDSはセクション1.3で定義された割合と一致していることを確認してください(予測モデルのため、一般に> 0.95)。 FDSプロットにおける曲線は平坦な設計空間全体にわたって均一な予測精度を示すことが好ましい。
- このような場合(ここで見られるように、図3(a)に示すように、FDSは1%であった)でない場合は、「戻る」デザイン」ノードに移動し、タスクバーの「設計ツール」は、選択し「増補デザインを...」を選択「増補。
- 以前と同じ「検索」と「最適性」の基準を選択します。また、同じ「編集モデル」と「合式のバランスを強制的に」設定を選択しました。デザイン増強が(ここで行ったように)任意の実験の前に実行された場合、変更するには、「ブロック1」に設定する」ブロックに実行を張って下さい "。
- 「実行し」セクションに不足を推定するには」「レプリケート」を少なくとも5%を維持し、追加の「モデル点」の数を入力します。適合の「トータルデザインで、ここでは、100の追加の実行を加えず、「レプリケート」と「フィット性の欠如を見積もる」は含まれていなかった。
- 計算が終了すると、上述したように、FDSグラフを見直す。 FDSはまだ十分ではない場合、上記のように設計増強を繰り返す。ここFDSは、拡張後の100%であったので、これ以上の増強は、( 図3B)は必要なかった。

図3 FDSプロットの比較。 90の実行からなる。A DOEは検出可能な最小差(20μg/ ml)をし、推定の値と組み合わせて、二次ベースモデルを使用して、予測の標準誤差のためにわずか1%の不十分FDSを生成システム(8μg/ ml)を。Bの標準偏差を交配。 210ランの合計エネルギー省の増強は、設計空間全体モデルの均一な精度を示す100%FDSとフラットカーブを達成しました。
3。クローニングと発現解析カセット
- 5ミリリットルのLB培地中で大腸菌を育成(11 g / Lのトリプトン、5g / L酵母抽出物、170 mMのNaClを、50mg / Lのアンピシリン、LB-寒天プレートを15グラム/ Lの寒天を含むための)6 37℃で160 rpmでオービタルシェーカー-8時間または一晩。注意:アンピシリンが有害物質である。ピペットチップを用いてプレート上で生育したコロニーからの液体培養物または細胞の転写50μlのいずれかでLB培地に接種する。
- PSOプラスミドDNAの精製、およびE.からPPAM(GenBankアクセッションAY027531)の他の誘導体については、 大腸菌 K12株DH5αを、DNA精製キットマニュアル24の指示に従ってください。注意:浄化Kそれは(詳細については取扱説明書上記を参照)有害な化学物質が含まれています。プラスミド配列を図4に買主ら 20によって記載されている。
- 光度計デバイスにおける260nmで2μLのサンプルの吸光度を測定することにより、精製溶出液中のDNA濃度を決定します。
- 制限エンドヌクレアーゼ(RES)で消化することによって精製されたプラスミドDNAの同一性を確認する。
- ユニークな識別可能なフラグメントパターンが生成されるように、プラスミド配列に従ってのREを選択する。このような安定化ウシ血清アルブミンの反応体積、時間、温度、濃度などの消化条件のため、メーカーの推奨に従ってください。感度に応じて分析装置は、消化当たりのプラスミドDNAの50〜500 ngのを使用しています。
- トリス - ホウ酸-EDTA(TBE)バッファー(; pH8.0の90 mMトリス、90 mMのホウ酸、2mMのEDTA)中でアガロース沸騰させることにより、DNA断片の分離のための0.8から2.0パーセントゲルを準備します。 T彼より大きな期待断片、あまりアガロースゲルで使用されるべきである。
- の50μlに5倍のサンプル緩衝液5μl(5×SABU、0.1%(w / v)のブロモフェノールブルー、0.1%(w / v)のキシレンシアノール、10%(TBEに溶解w / v)のグリセロール)を追加DNAサンプル再処理し、約40分、またはその断片の明確な分離が達成されるまで、100Vで、アガロースゲル電気泳動により断片を分離。各ゲル上で、比較のためにDNAラダーサイズマーカーを含むレーン、 例えば 2〜3μlの1 KBのはしごがあります。
- 他の3の5'UTRの1でPSOオメガ5'UTRを交換してください。
- 〜60分間のEco RI-HFおよび37℃でのNE緩衝液4中のNcoI-HF REの20単位で処理することにより、約4μgの精製されたPSO DNAからオメガ5'UTRシーケンスを解放します。のセクション3.4.2と3.4.3で説明したように、その後断片を分離。
- 余分なゲルを用いるアガロースゲルから大きなフラグメント(psで、「骨格」)を単離するctionキット)を製造者の取扱説明書25によるとセクション3.3で説明したように精製したDNAの濃度を測定する。注意:ゲル抽出キットは、有害な化学物質が含まれ、詳細はマニュアル参照。
- 〜60分間37℃でNE緩衝液4中のEco RI-HFとのNcoI-HF RESの20単位の各ベクトルの〜10μgを処理することにより、適切なドナーベクターからCHS、CHS-LPHとTLの5'UTRを分離します。その後のセクション3.4.2と3.4.3で説明したように断片を分離し、セクション3.5.2で説明したように小さい5'UTR含有断片を精製。
- メーカーの推奨26による5分間25℃で単離された精製線形のPSベクトルに別々のアリコート中の単離された精製の5'UTRを連結。ベクターDNAと全量20μl中の5'UTRのDNAの3倍モル過剰の〜50 ngのを使用してください。
- THと変換大腸菌細胞E組換えプラスミド26,27。
- 追加〜10 ngの連結混合物(約4〜5μL)(3.5.4項を参照)50μLRbClをコンピテント大腸菌 、穏やかに混合した後、氷上で30〜60分間インキュベートする。 5〜30分間、氷上で42℃、寒さで1.5分間の熱ショック。
- 抗生物質を含まないLB培地950μLを加え、37℃で1時間、および160 rpmでインキュベートする。形質転換体の選択のために、アンピシリンを含むLB寒天プレート上に培養物の50および100μLを広げ、37℃で〜16〜20時間インキュベートする
- アンピシリンを含むLB培地5 mlのアリコートに3.1節で説明した各プロモーター5'UTRライゲーションを表す5-10別個のコロニーを接種する。その後、プラスミドDNAを精製し、各項3.2から3.4で説明したように、その同一性を確認する。
- NEBuff における ASC および EcoRIたREを使用して、4つの5'UTRのプラスミドのそれぞれにおけるNOSプロモーターと35SSプロモーターを交換してください1時間37℃でER 4のセクション3.5と3.6で説明したように。
- Aに8得られたプラスミドのそれぞれを紹介エレクトロポレーション28でpMP90RK:ひずみGV3101 ツメファシエンス 。
- 50μL有能Aに精製されたプラスミドDNAの〜500 ngのを追加氷上で細胞ツメファシエンス 。穏やかに混合し、予冷0.2cmのエレクトロポレーションキュベットに移す。混合物はキュベットの底にあり、気泡が含まれていないことを確認してください。
- 5ミリ秒のために2.5 kVの時のパルス細胞とパルスの強度と期間を確認してください。
- DNA試料またはコンピテントA.の不適切な調製において塩濃度の上昇を回避これらは大幅に形質転換効率を低下させる、細胞懸濁液の瞬間蒸発を引き起こす高いイオン電流をもたらすことができるので、細胞ツメファシエンス 。
- 抗生物質を含まないYEB培地950μlの(5g / Lの牛肉抽出物、1g / Lの酵母エキス、5g / Lのペプトンを追加電子物、5g / Lのスクロース、2mMのMgSO 4を、pH7.0)を、穏やかに混合し、滅菌した1.5mlの反応管に直ちに移す。 26〜28℃、160 rpmで2〜4時間インキュベートする。
- 抗生た(50mg / Lを含有するYEB寒天プレート上に1〜2μLを広げ 形質転換体の選択のためのカルベニシリン、25 mg / Lのカナマイシン、25 mg / Lのリファンピシン)。注意:リファンピシンは有毒物質である。
- 各プロモーター-5'UTR連結を表す別々のコロニーからの細胞を用いて抗生物質を含むYEB培地の3の5mlずつ接種し、26〜28℃、160 rpmで48〜72時間インキュベートする。
- Aの成功を確認する変態ツメファシエンス 。
- PCRマスター48μlのアリコート(各10μMのプライマー株式(各プライマー400 nMの最終濃度)の2液を分離するためのセクション3.8.6から各アリコートの移転2μL1μlの10 mMのdNTPミックス(各デオキシヌクレオシド三リン酸200μMの最終濃度)、5μlの10倍0.75μL)、高忠実度の酵素ミックスを展開し、39.25μlの滅菌蒸留水、15のMgCl 2を、高忠実度のバッファを展開します。
- 適切なプライマーを用いて、各プラスミドの発現カセット(FWDを増幅:5'-CCT GAA CAG GAG CAA TAC-3 '、プロモーターの上流に1026個のヌクレオチドを結合させる工程REV:5'-CCA AAG CGA GTA CAC AAC-3'結合適切なPCR条件下で)35Sポリアデニル化部位内である。ここで、94°Cで15秒間、94℃での変性を30サイクル、続いて初期変性のために使用した、30秒及び120秒間72℃での伸長のための51℃のアニーリング、および8 72℃での最終伸長工程分。
- セクション3.4.3で説明したように、アガロースゲル電気泳動によりPCR産物のサイズを決定します。
- Aを調製でグリセロールストックツメファシエンス500μlの50%を混合Aの500μlの(V / V)の滅菌グリセロール変換が確認されているセクション3.8.6からツメファシエンス培養 (セクション3.9.3)。さらに使用するまで-80℃でグリセロールストックを保管してください。
- RNAfoldウェブサーバ29を使用して異なるmRNAのフォールディングエネルギーを計算し、コード領域の最初の50塩基対に至る転写開始部位からヌクレオチド配列を含む。
- 「アルゴリズムと基本的なオプションを折る」の「最小自由エネルギー(MFE)とパーティション機能」を選択し、オプションの「単離された塩基対を避ける」。
- の「高度な折りたたみオプション」は、「どのような場合に螺旋の両側にエネルギーをダングリング "を選択し、「RNAパラメータ(ターナーモデル、2004年)」および25℃に」与えられた温度(℃)にエネルギーパラメータを再スケール」に変更
- 「出力オプション」セクションのすべてのオプションを選択します。 出力ファイルのセクション「熱力学的アンサンブル予測の結果」、比較のために、「熱力学的アンサンブルの自由エネルギー "と値"アンサンブルでのMFE構造の周波数を "抽出物から。
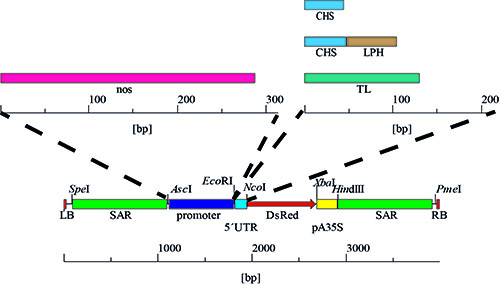
図4プロモーター及び5 'UTRは、発現カセットは配列のnosは、4つの付加的な変異を生じると、このプロモーターの置換、続い35SSのCaMVプロモーターを有する4つの組み合わせ、その結果、5'UTRの段階的な交換によって作製した。変異 8異なるプロモーター/ 5'UTRの組み合わせの合計。
4。植物栽培
- 肥料の0.1%溶液を調製FertypHは5.9で、脱イオン水に2メガ。
- 残留化学物質を除去し、最終的には肥料と平衡を脱イオン水で十分に洗い流しにより10×10×8センチロックウールブロックを準備します。
- 肥料は、種子を洗い流しないように注意しながらで短いフラッシュに続いて、各ロックウールブロックに1〜2タバコの種子を配置することにより、種子タバコ植物を。
- 発芽し、22分の25℃の昼/夜温、相対湿度70%、16時間の光周期の温室で42日間タバコ植物を栽培(180ミリモル秒-1メートル-2を 、λ= 400〜700 nm)の。この光周期の間に、15分間の肥料を水耕栽培での毎時間を灌漑。
5。一過性のタンパク質発現
- Aを調製葉に注入するためツメファシエンス 。
- 1%のAと抗生物質を含むYEB培地5〜50ミリリットルに接種クライオ保存培養ツメファシエンスおよびOD <まで27℃でインキュベートサブ> 600nmでは5.0(〜48〜72時間のボリュームと容器の種類に応じて)に達した。
- A.を希釈水および注射に必要なOD 600nmが一致するように2倍の浸潤培地(4.3 g / Lのムラシゲおよびスクーグ塩液(pH 5.6)、5 g / Lのスクロース、1.8グラム/ Lのグルコース、100mMのアセトシリンゴン)を有するツメファシエンス培養物。ただ、注入前のOD 600nmのを確認してください。注意:1.0対応ミリリットル当たりの単位を形成することに〜1.43±0.12×10 9コロニーのOD 600nmのを 。
- A.を注入葉にサスペンションツメファシエンス 。
- 選択して( 例:エネルギー省の戦略に従って)で処理されるように、その上noncotyledon葉や位置にラベルを付ける。
- 異なるAを注入しないでください同じ肋間フィールドにソリューションツメファシエンス 。その代わりに、半ば静脈軸の両側にある反対側の部分を使用しています。二つ以上の異なる溶液を同じ位置で注入する必要がある場合additionaを使用L工場。
- 徹底的にAを振る1ミリリットルのシリンジに希釈し、吸引の準備以来、定住した可能性のある細胞を再懸濁するツメファシエンスソリューション 。
- そっとAの流入を促進するためにピペットチップまたは類似の注射を対象とした位置に表皮を傷つけツメファシエンス·ソリューション 。そうしながら、葉身を破裂しないようにします。
- 処理され、ゆっくりと葉の下側に(接続しない針で)コンセントをプッシュする肋間フィールドに対してバレルに触れ葉身に垂直に注射器を持ちます。シフトや破裂から葉身を防ぐために、ゆっくりと同時に、葉の上側を押してください。
- 優しく注射器のピストンを押し下げる。 A.暗い緑としっとり現れる処理領域で示されるようにツメファシエンスのソリューションは、葉身の中に細胞間隙に入ります。全体肋間までいくつかの位置で、この手順を繰り返しますLフィールドはAに浸透さツメファシエンス 。その後、次の肋間のフィールドに進みます。
- 注射器は、リーフに垂直のままにしてください。注射器を傾けることは、高圧力下で飛ばし細菌懸濁液の原因となります。
- 場合は、別のA.ツメファシエンスのソリューションは、( 例えば 、異なるプロモーターをテストするために)使用されている、次の解決方法を適用する前に、同じような紙タオルやを使用して、最初の注射からの葉の下側に残った余分な溶液を除去する。
- 植物やサンプリング後の浸潤のインキュベーション。
- Doeのに必要なレベルでの温度と湿度の平衡を可能にするために、注射の前に〜24時間処理した植物のためのファイトトロンを準備します。
- 注入後、ファイトトロンに工場を移すとDOEによって決定インキュベーション期間の終わりになるまで水で灌漑のための十分な大きさのトレイに入れます。
- 16時間のPHOTを確立0.7メートル2(;λ= 400〜700nmの75ミリモル秒-1メートル-2)当たり6オスラムクールホワイト36 Wの蛍光管を使用してoperiod。 0.7メートル2当たり6に植物の数を制限することにより、相互にシェーディングから植物を防ぐ。
- サンプリングの前に、正しい肋間フィールドはセクション5.2.1とDOE計画に追加されたラベルを比較することにより、選択されたことを確認してください。
- DOEが示す位置と時間で処理肋間フィールドから4-5葉ディスクを削除するためにコルクボーラーを使用してください。サンプリング中に植物から全葉を削除しないでください。破裂を防ぐために、ディスクを除去しながら、手持ちの紙タオルで葉を安定させる。
- 各試料の質量を決定し、サンプル名と質量で標識した1.5ミリリットルのプラスチック反応チューブに入れてください。タンパク質定量の前に、-20℃または-80℃でサンプルを保管してください。プロセスは、サンプルの安定性に応じて、数ヶ月間、この段階で一時停止することがありますおよび保存温度。
6。タンパク質定量
- リーフディスクサンプルからタンパク質を抽出する。
- 抽出緩衝液3mlの(50 mMリン酸ナトリウム、500mM塩化ナトリウム、pH8.0)に入れるサンプル質量mg当たりにし、大きな断片がなくなるまで電気乳棒を用いて反応チューブ内で葉ディスクを挽く。サンプルの過熱を防ぐ。
- 4℃で20分間16,000 xgで2回遠心分離することによって試料を分散させて固形物を除去ペレットを乱すことなく、各工程の後に新しい1.5 ml反応チューブに上清を移す。
- 遠心分離後、プロセスは、植物サンプルの安定性および保存温度に依存して数ヶ月間、-20℃または-80℃で凍結することによって抽出する一時停止されてもよい。凍結融解サイクルは、標的タンパク質の濃度に影響を与えないことを確認。
- DsRedの蛍光を測定します。
- 黒色96ウェルハーフエリアプレート(ウェルあたり50μlの抽出液)に各サンプルの3技術的反復を準備します。ピペッティング時の気泡の形成を回避する。
- ライナー基準曲線を生成するために、96ウェルプレートあたりのDsRed標準六希釈(0、25、75、125、175および225μg/ mlの)のセットを使用する。 PBSに希釈液を調製し、3カ月以内に使用するために4℃で保管してください。
- 25分の530 nmの励起および35分の590 nmの発光フィルターを取り付けた96ウェルプレートリーダーで、順次、二回蛍光を測定する。
- 各サンプルについて、2以上の蛍光読み取り、3技術的反復を平均し、0μg/ mlののDsRedを含むブランクコントロールに記録された値を引きます。また、標準希釈液の読み込みからこの値を減算して(縦原点を)基準曲線が得られ、線形回帰のためにこれらのブランク補正値を使用します。
- fは変換するために、基準曲線の傾きを使用するのDsRed濃度へのサンプルについて測定luorescence。必要であれば、読み出しが基準の濃度区間内に収まるように試料を希釈し、その後の計算で、この希釈係数を考慮する。
- 2G12の濃度を測定する。
- つのフロー細胞の活性化表面にプロテインAを結合することによって抗体濃度の測定のために、表面プラズモン共鳴(SPR)装置を準備する。タンパク質30,31のカップリングせずに表面を不活性化することによって基準となる別のフロー· セルを使用してください。
- 植物はSPRランニング緩衝液(10mMのHEPES pH7.4中、3mMのEDTA、150mM塩化ナトリウム、0.05%v / vのTween-20)で1:20を抽出し、希三に、プロテインAに結合する抗体の応答単位(RU)を測定90μL注入(30μL/分で180秒)の終了時に各サンプルの技術的反復。実験フロリダで測定RUから参照フローセル(無プロテインA)で測定されたRUを差し引くわー細胞(プロテイン面)。
- 各試料10〜15の後に585 ng / mlの2G12標準を測定し、上記のように基準流量細胞において測定した値を減算します。縦原点を線形参照曲線を計算するために、これらの基準の平均RUを使用してください。
- 1:20希釈して基準曲線の傾きに基づいて、サンプル中の2G12濃度を計算します。
- これが破損する可能性があり、測定、基準セルへの強い非特異的結合を確認してください。また、より大きな変化がタンパク質表面の老化を反映したよう2G12基準は、分析を通じてほぼ一定の値(<5%の変動)を維持するかどうかを確認します。
7。データ分析と評価
- 手動による測定誤差を示す(i)の極値(高または低)のための発現実験で観察された応答を分析し、(ii)異常 な結果は、その遺伝子などの要因の組み合わせデータ交換を示す予想外の応答を評価、および(iii)の値が欠落している。
注:障害のあるデータに基づいてモデル構築を防ぐために、これらのアクションを使用しています。 - DesignExpertの「デザイン」ノードに分析されたレスポンスデータ(ここではタンパク質濃度)を転送します。レスポンスデータが正しく対応する係数の設定に割り当てられていることを確認してください。側面は下記宛てカバーDesignExpertソフトウェアで利用できる豊富なヘルプセクションがあります。
- 「分析」ノードでは、分析しようとする応答を選択し、最初の変換タブで「なし」を選択してください。
注意:変換は、10を超えるレスポンスの最小値/最大値の比率を推奨します。最も有用な変換は、以下に示す「診断ツール」(セクション7.8)の「診断」セクションにある「診断」タブにあるボックス - コックス - プロットから求めることができる。ログ10の変換は、多くの場合に適しています。 調査対象のシステム( 例えば二要素の相互作用、二次効果)のために重要な要因に関する一般的な情報を提供する「フィットサマリー」タブに進みます。ソフトウェアは、その重要性に基づいて、初期のモデルを提案します。 - 「モデル」タブでは、初期モデルは、「フィット要約」の結果に基づいてあらかじめ選択されています。このモデルを編集するために自動化されたモードを使用します。
- 提案したモデルが「2FI」(2因子の相互作用)であれば、「二次」を選択して一桁提案したモデルの上にある「処理順序」 などを選択します。
- 反復して、最初は0.100であるべき「アルファアウト」値に基づいて、「分散分析」タブに進んで後のモデルから有意でない用語を削除している、「選択」フィールドに「後方」を選択します。
- ソフトウェアによって要求された場合、これはnecessarであるため、常に自動的にモデル階層を修正信頼性の高いモデル32,33を生成するY。
- 「分散分析」タブでは、提案したモデルと含ま要因を調査する。必要な場合は、手動で「選択」を変更し、バック「モデル」タブに切り替えて(5%有意水準に対応し、ここでは0.05)事前に定義されたしきい値を上回ったp値を持つ要素を削除するか、可能性は低い機械論的考察に基づいているもの「手動」にし、モデルから適切な要因を排除する。
- 戻る「分散分析」タブで、「モデル」(これは重要性を示しているため、低い値が望ましい)と「不足·オブ·フィット」(高い値のp値でリフレッシュモデルを評価することが望ましいこれは重要性の欠如)だけでなく、「R二乗」の値を示しているので(> 0.80の値は、すべての3の値に望ましい)、「R二乗調整」と「R二乗予測」。
- のfoこれらの値を比較いくつかの有意水準での要因を除く/含む異なるモデルをr。
注:それは「デザイン」ノード内の回答欄を複製し、個別に分析を実行するか、スプレッドシートなど別のプログラムに全体の "分散分析"テーブルをエクスポートするのに役立つかもしれない。
- のfoこれらの値を比較いくつかの有意水準での要因を除く/含む異なるモデルをr。
- モデルの品質を確認し、「診断ツール」のすべてのタブ(「診断」と「影響」を参照して)調べることによって、モデルに大きな影響を持っているデータセット内の潜在的な異常値を検出するために、「診断」タブに進みます。
- 「診断ツール」の「診断」の項に、次の操作を実行します。
- 確実にポイントをランダムでの限度内で散乱されたグラフを「残差対は、予測された」。ここで、山形の分布は、データ変換の必要性を示している。
- ポイントがランダムでの制限内で散在していることを確認チャートを「残差対は、予測された」。ここで、山形の分布は、データ変換の必要性を示している。
- 調査「残差のラン対「チャート散布のポイントがランダムに制限内かどうか。パターン( 例えば 「階段」)は、モデルへの影響を相殺するために使用することができ、データブロックの建物の傾向を示している。
- プロット「実際対予測」の理想的なモデルを示す直線の対角線を探します。対角、精度の低いモデルの周りのデータのばらつきも大きい。
- データ変換を示す青(最良)と緑色のボックス - コックス - プロットの(実際の)縦のラインの重なりをチェックします。緑の線が一致しない場合は青1は(区間外に赤い縦線で示されている)、バックセクション7.3に戻り、ボックス·コックスプロットによって提案されたデータ変換を選択することにより、モデル構築のラウンドを向上させる。もう一度再の重複応答列は、異なるモデルを比較するのに役立ちます。
- 「ファクター対残差」のチャートでのポイントは(各モデルの要因のために、1つの図があります)の制限内でランダムに散乱していることを確認してください。データ配信の曲は、モデルに欠けている要因がある可能性があります。
- なしの「診断ツール」の「影響」の項の「外部スチューデント化残差」の制限内でのデータのランダムな散乱があることを確認し、「活用」、「DFFITS」および「DFBETAS」プロットと均等に低い分布「クックの距離 "プロットの極値。
- 「診断ツール」の「診断」の項に、次の操作を実行します。
- 「モデルのグラフ」タブでは、評価されたモデルを視覚化する。数値の要因限られた数の( 例えば 3)応答曲面(「3D表面」)の表現は、手動で最適解/特徴を評価することは有用である。
注:応答曲面は2つのFACの影響を示す調査中の応答に役。応答に追加の因子の影響は、「要因ツール」ウィンドウにその値(数値の要因)またはレベル(合式の要因)を変えることによって明らかにされている。代わりに、要因は「要因ツール」画面でそれらを右クリックして目的の独立変数の軸を選択して、プロット軸に割り当てることができます。- 因子レベルを操作し、「要因ツール」を使ってグラフの縦軸に割り当てます。
- 「ファイル」タブ内のコマンドを "...ファイルにエクスポートするグラフ」を使用して、エクスポートグラフ。
- を介して( 例えば、制限および重み)が順番に一定の制約を適用することができるように、モデルの因子に依存して(範囲で、最大化、最小化)を数値的応答を最適化する「最適化」ノードの「数値」サブノードを使用「基準」タブをクリックします。
- 「ソリューション」で計算し、数値解を調べるタブには、「基準」タブに設けられた入力に基づく。
- 高いまたは低い応答値に関連する要因の設定を明らかにし( 例えばヒストグラム)さらなる分析のために他のソフトウェア( 例えばスプレッドシート)にこれらのソリューションをエクスポートします。
注:以上の3つの数値の要因を調査している場合、これは便利ですし、3D表現が困難である。
- 具体的な要因の設定のための応答を予測する「点予測「サブノードを使用します。
- すべての設定が(ここでは、すべてのプロモーターと5'UTRの組み合わせだけでなく、すべての葉やインキュベーション時間や葉の位置やインキュベーションの温度)を評価されるため、この予測を使用してください。
- 全てのリーフ位置またはアクロにわたって平均予測値をエクスポートして、タバコ植物における一過性発現を記載するために使用することができるデータアレイにコンパイルし、特定の時間に特定のプロモーター、5'UTR組み合わせの式を計算することによって、例えば植物のSSはすべての葉。
- 具体的な発現量(μgのG -1)、または特定の発現率(100μgのG -1時間-1)を得異なる葉の質量に基づいて、発現データを正規化する。
- 代わりに、スプレッドシートに「分散分析」タブの一番下から「最終式」の係数をエクスポートして、同じデータ配列を生成する要因の設定の配列でそれらを掛けます。
注:あてはめたモデル式を外挿には適していないので、この配列は、最初の設計空間内からファクタ値を含んでもよい。
- 主要な関心のあるモデル点の確認実験を行う。
- 「ポイント予測」(セクション7.11)のために選択された条件下で一過性タンパク質発現を行う。Egが同じ温度や葉などを使用
- この一過式eのためのタンパク質濃度を決定として(セクション6)上記の記述とモデルによって予測された値と比較しxperiment。
- 確認実験の平均タンパク質濃度は点予測の間に得られた応答曲面モデルの予測区間内にあるかどうか確認してください。試合は、モデルの予測力を肯定。ミスマッチが低いモデル品質と付加ランが必要になることができることを示します。
- 注意:工場バッチ間のばらつきが予測区間を拡大し、植物の異なるバッチで行っ確認実験を切り下げることがあります。しかしながら、モデルを生成するために使用されるが、サンプルは、モデルに含まれるようにそれが同じ植物のバッチに由来しなかった試料は、効果的な管理を果たすことができる。
結果
異なるプロモーターとの5'UTRを使用して一過性発現の際のDsRedの蓄積のための記述的モデル
葉の抽出物中のDsRed蛍光は、組換えタンパク質の発現レベルを示すために使用されたので、実験計画戦略の応答として使用した。我々は、関連すると考え検出可能な最小の違いは、20μg/ mlのであり、システムの推定標準偏差は、最初の実験に基づいて8μg/ mlのだっ?...
ディスカッション
リソースは、多くの場合、希少かつ高価であるため、すべての実験は慎重な計画が必要です。計画段階( 例えば、すべての重要な要因の相互作用をカバーしていないベースモデルを選択する)中にエラーが発生し、実質的に生じたモデルの予測力を減少させるため、実験全体を切り下げることができるので、これはエネルギー省の戦略のために特に当てはまります。しかしながら、こ...
開示事項
公開手数料は、部分的に原稿やその内容については責任を負いの作成に携わっに関与していなかった企業Statease社(米国)とStatcon(ドイツ)が主催した。
謝辞
著者らは、この研究で使用したタバコ植物を栽培するためにPPAMの植物発現ベクターとイブラヒムアルAmediを提供するための博士トーマスラーデマッヘルに感謝しています。私たちは、原稿を編集すると、彼の援助のためリチャード·M·ワイマンに感謝したいと思います。この作業は、部分的には、欧州研究評議会上級助成「未来ファーマ」、提案番号269110とフラウンホーファーZukunftsstiftung(フラウンホーファー未来財団)によって資金を供給された。
資料
| Name | Company | Catalog Number | Comments |
| Design-Expert(R) 8 | Stat-Ease, Inc. | n.a. | DoE software |
| Tryptone | Carl Roth GmbH | 8952.2 | Media component |
| Yeast extract | Carl Roth GmbH | 2363.2 | Media component |
| Sodium chloride | Carl Roth GmbH | P029.2 | Media component |
| Ampicillin | Carl Roth GmbH | K029.2 | Antibiotic |
| Agar-Agar | Carl Roth GmbH | 5210.2 | Media component |
| Escherichia coli K12 DH5a | Life Technologies | 18263-012 | Microorganism |
| pPAM | GenBank | AY027531 | Cloning/expression vector; |
| NucleoSpin Plasmid | MACHEREY-NAGEL GmbH | 740588.250 | Plasmid DNA isolation kit |
| NucleoSpin Gel and PCR Clean-up | MACHEREY-NAGEL GmbH | 740609.250 | Plasmid DNA purification kit |
| NanoDrop 2000 | Thermo Scientific | n.a. | Spectrophotometer |
| NcoI | New England Biolabs Inc. | R3193L | Restrictionendonuclease |
| EcoRI | New England Biolabs Inc. | R3101L | Restrictionendonuclease |
| AscI | New England Biolabs Inc. | R0558L | Restrictionendonuclease |
| NEB 4 | New England Biolabs Inc. | B7004S | Restrictionendonuclease buffer |
| TRIS | Carl Roth GmbH | 4855.3 | Media component |
| Disodium tetraborate | Carl Roth GmbH | 4403.3 | Media component |
| EDTA | Carl Roth GmbH | 8040.2 | Media component |
| Agarose | Carl Roth GmbH | 6352.4 | Media component |
| Bromophenol blue | Carl Roth GmbH | A512.1 | Color indicator |
| Xylene cyanol | Carl Roth GmbH | A513.1 | Color indicator |
| Glycerol | Carl Roth GmbH | 7530.2 | Media component |
| Mini-Sub Cell GT Cell | BioRad | 170-4406 | Gel electrophoresis chamber |
| Agrobacterium tumefaciens strain GV3101:pMP90RK | DSMZ | 12365 | Microorganism |
| Electroporator 2510 | Eppendorf | 4307000.658 | Electroporator |
| Beef extract | Carl Roth GmbH | X975.2 | Media component |
| Peptone | Carl Roth GmbH | 2365.2 | Media component |
| Sucrose | Carl Roth GmbH | 4621.2 | Media component |
| Magnesium sulfate | Carl Roth GmbH | 0261.3 | Media component |
| Carbenicillin | Carl Roth GmbH | 6344.2 | Antibiotic |
| Kanamycin | Carl Roth GmbH | T832.3 | Antibiotic |
| Rifampicin | Carl Roth GmbH | 4163.2 | Antibiotic |
| FWD primer | Eurofins MWG Operon | n.a. | CCT CAG GAA GAG CAA TAC |
| REV primer | Eurofins MWG Operon | n.a. | CCA AAG CGA GTA CAC AAC |
| 2720 Thermal cycler | Applied Biosystems | 4359659 | Thermocycler |
| RNAfold webserver | University of Vienna | n.a. | Software |
| Ferty 2 Mega | Kammlott | 5.220072 | Fertilizer |
| Grodan Rockwool Cubes 10 x10 cm | Grodan | n.a. | Rockwool block |
| Greenhouse | n.a. | n.a. | For plant cultivation |
| Phytotron | Ilka Zell | n.a. | For plant cultivation |
| Omnifix-F Solo | B. Braun | 6064204 | Syringe |
| Murashige and Skoog salts | Duchefa | M 0222.0010 | Media component |
| Glucose | Carl Roth GmbH | 6780.2 | Media component |
| Acetosyringone | Sigma-Aldrich | D134406-5G | Phytohormon analogon |
| BioPhotometer plus | Eppendorf | 6132 000.008 | Photometer |
| Osram cool white 36 W | Osram | 4930440 | Light source |
| Disodium phosphate | Carl Roth GmbH | 4984.3 | Media component |
| Centrifuge 5415D | Eppendorf | 5424 000.410 | Centrifuge |
| Forma -86C ULT freezer | ThermoFisher | 88400 | Freezer |
| Synergy HT | BioTek | SIAFRT | Fluorescence plate reader |
| Biacore T200 | GE Healthcare | n.a. | SPR device |
| Protein A | Life Technologies | 10-1006 | Antibody binding protein |
| HEPES | Carl Roth GmbH | 9105.3 | Media component |
| Tween-20 | Carl Roth GmbH | 9127.3 | Media component |
| 2G12 antibody | Polymun | AB002 | Reference antibody |
参考文献
- Fischer, R., Emans, N. Molecular farming of pharmaceutical proteins. Transgenic research. 9, 277-299 (2000).
- Commandeur, U., Twyman, R. M., Fischer, R. The biosafety of molecular farming in plants. AgBiotechNet. 5, 9 (2003).
- Shoji, Y., et al. A plant-based system for rapid production of influenza vaccine antigens. Influenza Other Resp. 6, 204-210 (2012).
- Goodin, M. M., Zaitlin, D., Naidu, R. A., Lommel, S. A. Nicotiana benthamiana: Its history and future as a model for plant-pathogen interactions. Mol Plant Microbe In. 21, 1015-1026 (2008).
- Berg, R. H., Beachy, R. N. Fluorescent protein applications in plants. Method Cell Biol. 85, 153 (2008).
- Chung, S. M., Vaidya, M., Tzfira, T. Agrobacterium is not alone: gene transfer to plants by viruses and other bacteria. Trends in plant science. 11, 1-4 (2006).
- Sheludko, Y. V., Sindarovska, Y. R., Gerasymenko, I. M., Bannikova, M. A., Kuchuk, N. V. Comparison of several Nicotiana species as hosts for high-scale Agrobacterium-mediated transient expression. Biotechnology and Bioengineering. 96, 608-614 (2007).
- Wydro, M., Kozubek, E., Lehmann, P. Optimization of transient Agrobacterium-mediated gene expression system in leaves of Nicotiana benthamiana. Acta Biochimica Polonica. 53, 289-298 (2006).
- Buyel, J. F., Fischer, R. Processing heterogeneous biomass: Overcoming the hurdles in model building. Bioengineered. 4, (2013).
- Fischer, R., Schillberg, S., Hellwig, S., Twyman, R. M., Drossard, J. GMP issues for recombinant plant-derived pharmaceutical proteins. Biotechnol Adv. 30, 434-439 (2012).
- Daniel, C. One-at-a-time plans. Journal of the American Statistical Association. 68, 353-360 (1973).
- Czitrom, V. One-Factor-at-a-Time versus Designed Experiments The American Statistician. 53, 6 (1999).
- Anderson, M. J., Kraber, S. L. Keys to successful designed experiments. ASQ - The global voice of quality. 6, 6 (1999).
- Montgomery, D. C. . Design and Analysis of Experiments. , (2007).
- Myers, R. H., Montgomery, D. C., Anderson-Cook, C. M. . Response Surface Methodology: Process and Product Optimization Using Designed Experiments. , (2009).
- Piepel, G. F. Programs for generating extreme vertices and centroids of linearly constrained experimental regions. J Qual Technol. 20, 15 (1988).
- . . FDA. , (2009).
- Shivhare, M., McCreath, G. Practical Considerations for DoE Implementation in Quality By Design. BioProcess International. 8, 9 (2010).
- Buyel, J. F., Fischer, R. Predictive models for transient protein expression in tobacco (Nicotiana tabacum L.) can optimize process time, yield, and downstream costs. Biotechnology and bioengineering. 109, 2575-2588 (2012).
- Buyel, J. F., Kaever, T., Buyel, J. J., Fischer, R. Predictive models for the accumulation of a fluorescent marker protein in tobacco leaves according to the promoter/5'UTR combination. Biotechnology and bioengineering. 110, 471-482 (2013).
- Anderson, M. J., Whitcomb, P. J. . DOE Simplified: Practical Tools for Effective Experimentation. , (2000).
- Anderson, M. J., Whitcomb, P. J. . Response Surface Methods Simplified. , (2005).
- De Gryze, S., Langhans, I., Vandebroek, M. Using the correct intervals for prediction: A tutorial on tolerance intervals for ordinary least-squares regression. Chemometr Intell Lab. 87, 147-154 (2007).
- . . Plasmid DNA purification User manual. , (2012).
- . . PCR clean-up Gel extraction User manual. , (2012).
- . . Quick Ligation Protocol. 4, (2009).
- Inoue, H., Nojima, H., Okayama, H. High-Efficiency Transformation of Escherichia-Coli with Plasmids. Gene. 96, 23-28 (1990).
- Main, G. D., Reynolds, S., Gartland, J. S. Electroporation protocols for Agrobacterium. Methods in Molecular Biology. 44, 405-412 (1995).
- Gruber, A. R., Lorenz, R., Bernhart, S. H., Neubock, R., Hofacker, I. L. The Vienna RNA websuite. Nucleic acids research. 36, 70-74 (2008).
- Howell, S., Kenmore, M., Kirkland, M., Badley, R. A. High-density immobilization of an antibody fragment to a carboxymethylated dextran-linked biosensor surface. J Mol Recognit. 11, 200-203 (1998).
- Newcombe, A. R., et al. Evaluation of a biosensor assay to quantify polyclonal IgG in ovine serum used for the production of biotherapeutic antibody fragments. Process Biochem. 41, 842-847 (2006).
- Peixoto, J. L. Hierarchical Variable Selection in Polynomial Regression-Models. Am Stat. 41, 311-313 (1987).
- Peixoto, J. L. A Property of Well-Formulated Polynomial Regression-Models. Am Stat. 44, 26-30 (1990).
- Sanders, P. R., Winter, J. A., Barnason, A. R., Rogers, S. G., Fraley, R. T. Comparison of cauliflower mosaic virus 35S and nopaline synthase promoters in transgenic plants. Nucleic acids research. 15, 1543-1558 (1987).
- Ma, J. K. C., et al. Generation and Assembly of Secretory Antibodies in Plants. Science. 268, 716-719 (1995).
- Wycoff, K. L. Secretory IgA antibodies from plants. Curr Pharm Design. 11, 2429-2437 (2005).
- Pace, C. N., Vajdos, F., Fee, L., Grimsley, G., Gray, T. How to measure and predict the molar absorption coefficient of a protein. Protein Sci. 4, 2411-2423 (1995).
転載および許可
このJoVE論文のテキスト又は図を再利用するための許可を申請します
許可を申請さらに記事を探す
This article has been published
Video Coming Soon
Copyright © 2023 MyJoVE Corporation. All rights reserved