Method Article
Preparación de muestras para criotomografía in situ de células de mamíferos
En este artículo
Resumen
Este método proporciona un protocolo accesible y flexible para la preparación de rejillas de microscopía electrónica (EM) para criotomografía celular in situ y microscopía óptica y electrónica correlativa (CLEM).
Resumen
La criotomografía celular in situ es una técnica poderosa para estudiar objetos complejos en su contexto celular nativo congelado-hidratado, lo que la hace muy relevante para la biología celular y la virología. El potencial de combinar la criotomografía con otras modalidades de microscopía la convierte en una técnica perfecta para la obtención de imágenes integrativas y correlativas. Sin embargo, la preparación de la muestra para la tomografía celular in situ no es sencilla, ya que las células no se adhieren ni se estiran fácilmente sobre la rejilla de microscopía electrónica. Además, las propias rejillas son frágiles y pueden romperse si se manipulan con demasiada fuerza, lo que provoca la pérdida de áreas visibles. La geometría de las placas de cultivo de tejidos también puede suponer un reto a la hora de manipular las rejillas con pinzas. Aquí, describimos los consejos y trucos para superar estos (y otros) desafíos y preparar muestras de buena calidad para criotomografía celular in situ e imágenes correlativas de células de mamíferos adherentes. Con los continuos avances en la tecnología de criomicroscopía, esta técnica es muy prometedora para avanzar en nuestra comprensión de los sistemas biológicos complejos.
Introducción
La criotomografía celular in situ es una técnica potente que permite el estudio de estructuras biológicamente relevantes en células sin fijación química. Al unir las células a las rejillas EM y congelar las rejillas en un criógeno, los objetos de interés se congelan en sus contextos celulares naturales sin la formación de hielo cristalino a partir del agua intracelular 1,2. Tanto la fijación química como la formación de hielo cristalino pueden alterar las estructuras de moléculas relevantes, como proteínas y lípidos, reduciendo la precisión biológica de las imágenes obtenidas con estas técnicas 3,4. En tomografía, las imágenes de cuadrículas se obtienen en ángulos incrementales mediante microscopía electrónica, y estas imágenes se utilizan para construir representaciones tridimensionales de la región objetivo de la que se obtiene la imagen5. La criotomografía in situ se puede utilizar junto con otras técnicas de microscopía para la obtención de imágenes integrativas y correlativas, como la obtención de imágenes de criofluorescencia, la tomografía de rayos X blandos y la crioFIB/SEM (microscopía electrónica criogénica de barrido por haz de iones focalizado)6,7,8,9,10,11 . La integración de múltiples técnicas permite obtener más información sobre una estructura o proceso de la que podría lograr una sola técnica de microscopía.
A pesar de todos los beneficios de la criotomografía celular in situ , la preparación de muestras puede resultar difícil por una variedad de razones. Debido a su fragilidad, la manipulación forzada de las rejillas de microscopía electrónica puede provocar daños, siendo la fina capa de carbono en particular delicada y propensa a romperse, lo que reduce el área de imagen de las rejillas. Las rejillas de microscopía electrónica también son difíciles de manipular debido a su pequeño tamaño y son propensas a desprenderse de la superficie de los pocillos o microportaobjetos utilizados para cultivar células. La manipulación de las rejillas dentro de los pozos o microportaobjetos puede resultar difícil debido a la geometría de estos. La preparación inadecuada de las rejillas (p. ej., dejarlas flotar) puede conducir a una baja densidad celular y reducir el número de áreas potenciales de imágenes, especialmente cuando las celdas no son propensas a adherirse a las rejillas mismas. Para la criotomografía celular directa, las células deben extenderse muy delgadamente, lo que puede interrumpirse por muchas razones, incluidas las temperaturas inadecuadas o el manejo brusco de las rejillas.
A través de una variedad de optimizaciones, las técnicas presentadas en este artículo están destinadas a manejar estos escollos más comunes que surgen durante la preparación de rejillas de microscopía electrónica para criotomografía. El uso de pinzas angulares de 5/15 permite la manipulación de rejillas dentro de placas de pocillos o microportaobjetos. Una solución de fibronectina aplicada a ambos lados de las rejillas antes del recubrimiento hace que las rejillas flotantes sean menos probables, lo que es beneficioso para garantizar que las rejillas tengan una densidad celular adecuada y que sea menos probable que las rejillas se dañen debido a la manipulación. Al mantener las rejillas incubadas a 37 °C hasta justo antes de la congelación por inmersión, también nos aseguramos de que las células se mantengan en un entorno cómodo para evitar que las células retraigan sus bordes delgados. Secar las rejillas de la parte posterior también evita que las células se dañen por la fuerza mecánica. En conjunto, estas medidas aumentan la tasa de éxito de la preparación de muestras para estudios de criotomografía celular in situ , lo que aumenta la accesibilidad de este enfoque de imagen.
Protocolo
1. Preparación de la cuadrícula
NOTA: En el diseño experimental, planifique un máximo de 8 a 12 rejillas en total por sesión de inmersión y congelación y de 4 a 5 rejillas por pozo. Más que eso conducirá a una sesión de congelación por inmersión muy larga, lo que puede causar un aumento del estrés celular, contaminación por hielo y errores del usuario.
- Descarga de incandescencia
- Cargue un número adecuado de rejillas con una película de soporte de carbono perforada para que se descargue a 15 mA durante 45 s a una atmósfera de 0,39 mBar en un dispositivo de descarga incandescente.
- Asegúrese de que el lado de carbono de la rejilla esté hacia arriba. Cuando termine, transfiera las rejillas a un recipiente limpio forrado con papel de filtro (Figura 1A 1).
NOTA: Se pueden usar otras rejillas siempre que el material no sea tóxico para las celdas (lo que excluye cualquier rejilla de cobre). Las cuadrículas de búsqueda son útiles para estudios correlativos. También son posibles las rejillas hechas de otros materiales. Muchos laboratorios han obtenido buenos resultados en el cultivo de células sobre rejillas de soporte deSiO2 8,9.
- Tratamiento adherente
- Transfiera las rejillas, la fibronectina, el PBS, las placas y las pinzas a un gabinete de bioseguridad. Tratar ambos lados de las rejillas con 20 μg/ml de fibronectina bovina mediante el micropipeteo de dos puntos de solución adherente de tamaño generoso sobre una superficie estéril, como la tapa de una placa de 6 pocillos. Asegúrese de que los puntos sean lo suficientemente grandes como para envolver toda la cuadrícula (se recomiendan alrededor de 100 μL).
NOTA: Antes del tratamiento con la solución adherente seleccionada, existe la opción de foto-micropatrón de la cuadrícula aquí para optimizar la fijación de las celdas en el centro de los cuadrados de la cuadrícula. La reducción de la capacidad de las celdas para adherirse a las barras aumentará el número de celdas de las que se puede obtener una imagen. Esto es ideal para experimentos que involucran molienda crioFIB. - Usa pinzas de 5/15 para manipular las cuadrículas. Asegúrese de tratar ambos lados de la rejilla en solución.
NOTA: Se pueden utilizar otras soluciones adhesivas (fibrinógeno, colágeno, otros componentes de la matriz extracelular, etc.). Aquí se utiliza la fibronectina, ya que da buenos resultados con una amplia variedad de líneas celulares. (U2OS, HeLa, Vero, Calu-3, Tzm-bl). La pinza 5/15 es útil ya que su geometría permite una mejor maniobrabilidad alrededor de las placas de 6 pocillos, las placas de 35 mm y las microcorrederas. Esto da como resultado menos estrés mecánico en las rejillas y una película de carbono más intacta. Asegúrese de que todos los materiales necesarios estén colocados en el gabinete de bioseguridad antes de comenzar, ya que esto reduce la posibilidad de contaminación de la red.
- Transfiera las rejillas, la fibronectina, el PBS, las placas y las pinzas a un gabinete de bioseguridad. Tratar ambos lados de las rejillas con 20 μg/ml de fibronectina bovina mediante el micropipeteo de dos puntos de solución adherente de tamaño generoso sobre una superficie estéril, como la tapa de una placa de 6 pocillos. Asegúrese de que los puntos sean lo suficientemente grandes como para envolver toda la cuadrícula (se recomiendan alrededor de 100 μL).
- Adjuntar rejillas
- Una vez tratada con fibronectina bovina, la rejilla se volverá pegajosa. Con unas pinzas de 5/15, toque suavemente la superficie sin carbono de la rejilla con el fondo de un plato/plato vacío y abra las pinzas. La rejilla debe adherirse fácilmente a la nueva superficie (Figura 1A2).
NOTA: Trate de evitar colocar rejillas en el centro directo o en los bordes del plato/plato. Al agregar células, existe una tendencia a que la densidad celular se acumule en el centro de la placa. Esto puede dar lugar a redes con una densidad celular excesiva. Alternativamente, se pueden usar soportes de rejilla impresos en 3D en lugar de unir celdas directamente a la superficie del plato/placa12.
- Una vez tratada con fibronectina bovina, la rejilla se volverá pegajosa. Con unas pinzas de 5/15, toque suavemente la superficie sin carbono de la rejilla con el fondo de un plato/plato vacío y abra las pinzas. La rejilla debe adherirse fácilmente a la nueva superficie (Figura 1A2).
- Incubación
- Incubar las rejillas durante 30 min en la solución adherente de fibronectina (20 μg/mL). Para asegurarse de que las rejillas no se sequen durante este proceso, micropipetee 1-2 gotas de solución más adherente directamente sobre las rejillas cada 15 minutos (Figura 1A3).
NOTA: El período de incubación variará según la solución adherente utilizada. Para la fibronectina bovina, el tiempo recomendado es de 30 min.
- Incubar las rejillas durante 30 min en la solución adherente de fibronectina (20 μg/mL). Para asegurarse de que las rejillas no se sequen durante este proceso, micropipetee 1-2 gotas de solución más adherente directamente sobre las rejillas cada 15 minutos (Figura 1A3).
- Lavado
- Después del período de incubación, elimine el exceso de solución adherente mediante micropipeteo. Lave las rejillas mediante el micropipeteo de gotas de PBS directamente sobre las rejillas. Repita esto 2-3 veces. (Figura 1A4).
- Esterilización
- Utilice luz ultravioleta para esterilizar las rejillas de la cabina de bioseguridad durante 1 h. Coloque las rejillas lo más cerca posible de la fuente UV para maximizar la esterilización (Figura 1A5). Para asegurarse de que las rejillas no se sequen durante este proceso, micropipetee 1-2 gotas de PBS directamente sobre las rejillas cada 10 minutos.
NOTA: Los pasos 1.4-1.6 se pueden realizar simultáneamente.
- Utilice luz ultravioleta para esterilizar las rejillas de la cabina de bioseguridad durante 1 h. Coloque las rejillas lo más cerca posible de la fuente UV para maximizar la esterilización (Figura 1A5). Para asegurarse de que las rejillas no se sequen durante este proceso, micropipetee 1-2 gotas de PBS directamente sobre las rejillas cada 10 minutos.
2. Rejillas de siembra
- Contar celdas:
- Separe y cuente las células utilizando métodos mecánicos o enzimáticos. Determine el número óptimo de celdas que se utilizarán para la siembra antes de contar. Para U2OS sembrado en una placa de 6 pocillos, use entre 6 x 104 y 1.6 x 105 celdas por pocillo (Figura 1B1).
NOTA: El número de células sembradas variará según el tipo de célula, el área de superficie del pocillo, plato o microportaobjetos utilizado, el tiempo entre la siembra y la congelación por inmersión, y el diseño experimental. Pruebe un rango de números de celdas para identificar las condiciones que darán como resultado 0.25-1 celdas por cuadrado de cuadrícula en el momento de la congelación por inmersión. Es importante tener en cuenta que la alta densidad celular reduce la velocidad de transferencia de calor y puede afectar el proceso de vitrificación. Para combatir esto, algunos laboratorios han tenido éxito utilizando filtros celulares, que actúan para evitar quese formen grupos celulares. Finalmente, este protocolo da como resultado la unión aleatoria de las células a la capa de carbono. Si es necesario un accesorio específico, se puede utilizar el fotomicropatrón (véase el paso 1.3)14.
- Separe y cuente las células utilizando métodos mecánicos o enzimáticos. Determine el número óptimo de celdas que se utilizarán para la siembra antes de contar. Para U2OS sembrado en una placa de 6 pocillos, use entre 6 x 104 y 1.6 x 105 celdas por pocillo (Figura 1B1).
- Adición de células y medio de crecimiento: Añadir células a través de micropipeta a los pocillos, evitando burbujas (Figura 1B2). En una placa de 6 pocillos, se recomienda un volumen total de pocillos de 1,5 a 2,0 ml.
NOTA: Se recomienda humedecer cuidadosamente alrededor de las rejillas antes de agregar todo el volumen. Esto ayudará a evitar que las rejillas se desprendan y floten en la solución. Mueva suavemente la placa de lado a lado para facilitar la distribución homogénea de las células en el pocillo. No gire la placa con movimientos circulares, ya que esto dará como resultado una asignación excesiva de densidad celular en el centro del pocillo. - Incubación: Incubar los portaobjetos a 37 °C durante un tiempo adecuado según el diseño experimental, que dependerá de las aplicaciones posteriores. Para este ejemplo (transfección de clones moleculares del VIH), incubar entre 16-24 h (Figura 1B3).
NOTA: Los tiempos de incubación más largos darán como resultado más ciclos de división celular. Por lo tanto, ajuste el número inicial de celdas para la siembra en consecuencia.
3. Transfección
- Preparación de la mezcla de transfección:
- Preparar un reactivo catiónico liposomado apropiado para la transfección de plásmidos en la línea celular seleccionada.
- En este ejemplo de transfección, utilice 1 μg de ADN plasmídico total por pocillo (en una placa de 6 pocillos) para transfectarlo en una proporción de 1:3 de plásmido VIHiΔEnv a plásmido psPAX2. Para cada pocillo, diluir 1 μg de ADN en 50 μL de DMEM sin suero. Homogeneizar la mezcla mediante micropipeteo repetido o un suave remolino de la placa.
- Para cada pocillo, diluir 3 μL de reactivo de transfección en DMEM sin suero y, a continuación, homogeneizar la mezcla de nuevo mediante micropipeteo o remolino suave. Añadir toda la mezcla diluida de reactivos de transfección a la mezcla de ADN diluida (paso 3.1.2) e incubar a temperatura ambiente (RT) durante 15 min (Figura 1C1).
NOTA: Mientras se incuba esta mezcla, reemplace el medio en los pocillos con 1.5 ml de DMEM fresco. Tenga cuidado de no desalojar las rejillas del fondo del pozo.
- Para aplicar la mezcla de transfección, pipetear 100 μL de la mezcla del paso 3.1.3 gota a gota en cada pocillo, concentrando las gotas sobre las rejillas para asegurar el contacto (Figura 1C2). Cambie el medio de cultivo 16-24 h después de la transfección (Figura 1C3).
4. Congelación por inmersión
NOTA: Mantenga las células a 37 °C hasta que las necesite para el secado. Además, asegúrese de tomar nota del lado de carbono de las rejillas durante todo el proceso.
- Densidad celular
- Verifique las rejillas en un microscopio óptico invertido y anote las densidades celulares en cada rejilla.
NOTA: Las cuadrículas con menos de 0,25 celdas por cuadrado de cuadrícula (o una celda cada 4 cuadrados de cuadrícula) se consideran "vacías". Las cuadrículas con 0,25-1 celdas por cuadrado de cuadrícula se consideran "normales". Las cuadrículas con más de 1 celda por cuadrado de cuadrícula se consideran "completas". - Tome nota de la densidad celular en cada cuadrícula para permitir la marcación de los tiempos de transferencia más tarde durante la congelación por inmersión. Añadir 2-3 ml de PBS a un plato/plato vacío y calentar a 37 °C.
- Verifique las rejillas en un microscopio óptico invertido y anote las densidades celulares en cada rejilla.
- Preparación de fiduciales
- Para preparar fiduciales de oro para aplicaciones de criotomografía posteriores, pipetee 50 μL de solución de perlas de oro coloidal de 10 nm en un tubo limpio de 1,5 mL. Añadir 2 μL de 1 mg/mL de BSA al tubo y homogeneizar mediante micropipeteo repetidamente.
- Centrifugar el tubo a 15.000-20.000 x g durante 15 min. Micropipeta para eliminar la mayor cantidad posible de sobrenadante sin alterar el gránulo.
NOTA: El pellet quedará muy suelto. - Añadir 50 μL de PBS al gránulo y volver a suspender. Centrifugar el tubo de nuevo a 15.000-20.000 x g durante 15 min.
- Con una punta de 10 μL, aspire directamente 4 μL del gránulo y transfiéralo a un tubo limpio de 1,5 ml (Figura 1D 1). Utilice 1 μL del oro lavado y concentrado por rejilla.
NOTA: El tipo de fiduciales utilizados depende de las aplicaciones posteriores. Para la tomografía TEM, utilice perlas de oro de 10 nm. Para la tomografía de rayos X suaves, utilice perlas de oro de 200 nm. Para la microscopía de correlación, utilice perlas de látex fluorescentes. Normalmente, los fiduciales no son necesarios para los experimentos que involucran molienda crioFIB, ya que el proceso de molienda los destruirá.
- Blot
- Configure la cámara ambiental al 95 % de humedad y a 30 °C (Figura 1D 1). Seleccione una cuadrícula con las pinzas de 5/15.
- Lave las rejillas con PBS y transfiéralas a unas pinzas de inmersión (Figura 1D2). Una vez asegurado, retire las pinzas de 5/15 y deslice la abrazadera en las pinzas de inmersión.
- Inserte la rejilla en el congelador de inmersión, manteniendo la abrazadera segura (Figura 1D3). Agregue 1 μL de fiduciales de oro a la parte posterior de la cuadrícula (Figura 1D4). Agregue 2-3 μL de PBS al lado de carbono de la rejilla. Utilice un secado automático para secar la parte posterior de la rejilla y sumergir la congelación en etano líquido (Figura 1D5).
NOTA: Se recomienda tener entre 3-4 μL de volumen por rejilla para una transferencia óptima. Las rejillas pueden retener una cantidad variable de PBS después del lavado. Ajuste el volumen agregado de PBS para tener en cuenta la retención de líquidos preexistente en la red. Se recomienda que los fiduciales dorados se agreguen a la parte posterior de la cuadrícula. La adición en la parte delantera puede dar lugar a charcos de fiduciales de oro cerca del punto de inserción, mientras que la adición desde la parte posterior da como resultado una solución más homogeneizada. La duración del secado depende de la odontología celular de la red. 2 s para las cuadrículas vacías, 3 s para las normales y 4 s para las completas, respectivamente. El tipo de congelador de inmersión disponible puede determinar cómo se aborda la transferencia: El congelador de inmersión Leica GP2 es el que se utiliza en este protocolo y es capaz de transferir automáticamente una sola cara de forma predeterminada. Thermo Fisher Vitrobot realiza transferencias automáticas de doble cara, aunque esto a menudo daña las células unidas al lado de carbono. También es posible el bómbolo manual en el Vitrobot, así como los émbolos de gravedad manuales.
Resultados
Después de la cotransfección de HIViGFPΔEnv y psPAX2, todas las rejillas tuvieron un desgarro mínimo en la capa de carbono. Las imágenes de las rejillas se obtuvieron mediante microscopía de luz de fase y microscopía de luz fluorescente 24 h después de la incubación con el reactivo de transfección (Figura 2). Las celdas tanto de las cuadrículas simuladas como de las cuadrículas cotransfectadas contenían celdas viables en varios cuadrados de cuadrícula.
psPAX2 codifica todas las proteínas estructurales y enzimáticas del VIH-1 sin ningún marcado de fluorescencia. HIViGFPΔEnv es similar a psPAX2 pero con códigos para una proteína Gag del VIH marcada con GFP. Ambos plásmidos son ΔEnvelope. La cotransfección da como resultado el ensamblaje nativo y la gemación de partículas fluorescentes del VIH-1, lo que lo convierte en un excelente sistema para los estudios CLEM del VIH en condiciones de nivel 1 de bioseguridad. Las rejillas co-transfectadas mostraron un subconjunto de células que exhibían fluorescencia verde, lo que indica una cotransfección exitosa. Ninguna célula de la rejilla simulada mostró fluorescencia, lo que validó aún más la cotransfección utilizando HIViGFPΔEnv y psPAX2. Después de ver las rejillas utilizando microscopía basada en la luz, las rejillas se congelaron por inmersión y se trasladaron a un almacenamiento a largo plazo en nitrógeno líquido.
La Figura 3 muestra los resultados de las cuadrículas producidas utilizando el mismo método experimental pero utilizando construcciones de plásmidos ligeramente diferentes. Las rejillas que contenían U2OS se transfectaron conjuntamente utilizando diferentes clones del VIH (HIVmCherryΔEnv y NL4-3ΔEnvGFP en una proporción de 1:6). Dado que se utilizó una mayor masa de plásmidos marcados con fluorescencia, estas rejillas permitieron la observación de un mayor número de células transfectadas, lo que proporcionó una ventaja al capturar imágenes utilizando cryoCLEM y cryoET. Utilizando cryoCLEM, se generaron atlas de cuadrícula completa para cada cuadrícula utilizando criofluorescencia para registrar las ubicaciones de todas las células cotransfectadas. Una vez conocida la ubicación de las células, se realizó la crioET. Se recolectó un atlas completo de cuadrícula de bajo aumento y se superpuso con el atlas fluorescente recolectado en criofluorescencia (Figura 3A). Se recolectaron criotomografías en sitios celulares que capturaron detalles intrincados del ciclo de vida viral, incluido el ensamblaje y la gemación del VIH a partir de las células (Figura 3B).
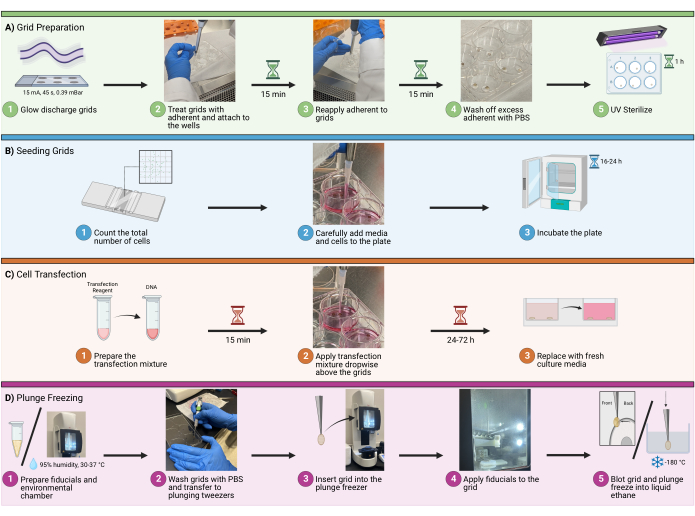
Figura 1: Flujo de trabajo de propagación de celdas en cuadrículas. Un esquema que representa el procedimiento general para sembrar células en rejillas crioEM. El proceso se divide en cuatro pasos principales, que incluyen (A) la preparación de rejillas en los pocillos para la siembra, (B) la adición de la cantidad adecuada de celdas a cada pocillo, (C) la transfección opcional de celdas para la obtención de imágenes fluorescentes y (D) la congelación por inmersión de las rejillas para permitir la vitrificación de la muestra. Haga clic aquí para ver una versión más grande de esta figura.

Figura 2: Cotransfección de U2OS usando HIViGFPΔEnv y psPAX2. Las células U2OS se transfectaron conjuntamente con HIViGFPΔEnv y psPAX2 que contenían GFP en una proporción de 1:3. Las imágenes de las rejillas se obtuvieron mediante contraste de fase y microscopía de fluorescencia. Las células que muestran tener expresión de GFP indican una cotransfección exitosa. Barra de escala: 500 μm. Barra de escala (recuadros): 100 μm. Haga clic aquí para ver una versión más grande de esta figura.
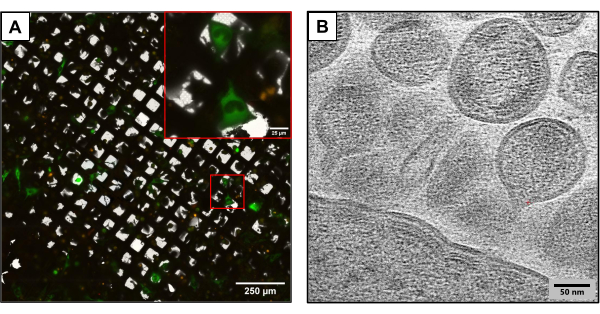
Figura 3: Posibles métodos basados en crioterapia aguas abajo . (A) Una imagen de crioCLEM con células U2OS co-transfectadas. Las células en verde representan las células productoras del VIH y se utilizan para medir el éxito de la cotransfección. Los puncta rojos representan mCherry etiquetado como mordaza HIV-1. Barra de escala: 250 μm. Barra de escala (recuadro): 25 μm (B) Una imagen crioET de múltiples partículas de VIH que brotan de la membrana plasmática de las células U2OS. Barra de escala: 50 nm Haga clic aquí para ver una versión más grande de esta figura.
Discusión
Aquí, hemos proporcionado un protocolo accesible, flexible y reproducible para células semilla en rejillas de microscopía electrónica para aplicaciones de tomografía crioelectrónica in situ . Este método se puede adaptar fácilmente para adaptarse a las necesidades de las aplicaciones posteriores y/o a los requisitos experimentales. Además de una gran flexibilidad, hemos descrito un flujo de trabajo que optimiza y reduce los errores comunes en la siembra de la cuadrícula, en particular el daño extenso a la capa de carbono, la baja densidad celular y la mala integridad estructural de las proyecciones de celdas delgadas.
Aunque el protocolo descrito aquí ofrece varias alternativas, hay algunos pasos críticos que deben seguirse para optimizar los resultados generales. Uno de los mayores problemas con la siembra de celdas de cuadrícula es el desprendimiento y la flotación de las rejillas del pozo o microportaobjetos. Por lo tanto, es importante humedecer completamente la rejilla con una solución adherente en ambos lados y evitar que se seque durante el período de incubación. Si utiliza soportes de rejilla impresos en 3D, tenga en cuenta que los múltiples cambios de medios en estos soportes tienen el potencial de producir rejillas flotantes, ya que el aire atrapado debajo de la rejilla puede forzarlo a salir del soporte.
Nuestra elección de pinzas también mejora la calidad de la rejilla en el sentido de proporcionar una forma geométricamente favorable de manipular las rejillas sin una flexión extensa de la rejilla que dañaría la capa de carbono. Mantener las células a 37 °C durante el mayor tiempo posible antes de sumergirlas reduce el sufrimiento celular y mejora el número de células delgadas que se pueden fotografiar en la cuadrícula. Finalmente, el secado del lado dorado protegerá las células de las fuerzas mecánicas agresivas que podrían provocar daños en las frágiles estructuras celulares.
Si bien no está incluido en este protocolo, se ha demostrado que el fotomicropatrón de cuadrícula aumenta el número de celdas de las que se pueden obtener imágenes al optimizar su unión al centro de los cuadrados de la cuadrícula14. Por último, los soportes de rejilla impresos en 3D se han utilizado recientemente para reducir el daño a la rejilla limitando la manipulación directa de la rejilla12.
Puede ser importante tener en cuenta que este protocolo está optimizado para obtener imágenes de bordes delgados y protuberancias de células para la aplicación de criotomografía. Sugerimos solucionar una variedad de condiciones de nuestras recomendaciones en el protocolo para encontrar el mejor resultado para las aplicaciones posteriores de elección. En general, este protocolo proporciona un método confiable pero versátil para sembrar celdas en cuadrículas que se pueden ajustar para necesidades específicas.
Divulgaciones
Los autores declaran no tener intereses contrapuestos.
Agradecimientos
Nos gustaría agradecer al laboratorio Mansky por el acceso a los equipos de congelación por inmersión. Parte de este trabajo se llevó a cabo en las instalaciones de caracterización de la Universidad de Minnesota, que recibe apoyo parcial de la National Science Foundation (NSF) a través del Centro de Investigación de Ciencia e Ingeniería de Materiales (MRSEC; Número de adjudicación DMR-2011401) y la Iniciativa Nacional de Currículo de Neurociencia (NNCI; Número de adjudicación ECCS-2025124). Nos gustaría agradecer el financiamiento del Centro de Comportamiento del VIH en Entornos Virales (B-HIVE; 1U54AI170855-01) y el Centro de Biología Estructural del VIH de Duke (DCHSB; U54AI170752) centro.
Materiales
| Name | Company | Catalog Number | Comments |
| 10 nm colloidal gold bead solution | Sigma-Aldrich | 741957 | |
| 6 well multidish, 100/CS | Fisher Scientific | FB012927 | |
| Allegra V-15R Benchtop Centrifuge, IVD 120 V 60 Hz | Beckman-Coulter | C63125 | |
| Au G300F1 with R2/2 Quantifoil carbon | Quantifoil | TEM-G300F1-AU | |
| Bovine serum albumin | MilliporeSigma | A9647 | |
| BRAND counting chamber BLAUBRAND Neubauer improved | Sigma-Aldrich | BR717805-1EA | |
| DMi1 Inverted Microscope | Leica | 22A00G119 | |
| Dulbecco's modified eagle's medium - high glucose, no glutamine | Gibco | 11-960-044 | |
| Dumont 5/15 tweezer | Electron Microscopy Sciences | 0103-5/15-PO | |
| EM GP2 | Leica | 587085 | Automated plunge freezer |
| Fetal Bovine Serum | Gibco | A5209 | |
| Fibronectin from bovine plasma, cell culture grade | MilliporeSigma | F1141 | |
| GenJet version II in vitro DNA transfection reagent | SignaGen Laboratories | SL100489 | |
| GlutaMAX I 100x | Fisher Scientific | 35050061 | Media supplement |
| Neslab EX-211 Heating Circulator | Neslab | Out of production | Water bath for media warming |
| Original Portable Pipet-Aid Pipette Controller | Drummond Scientific | 4-000-100 | |
| PBS, pH 7.4 | Gibco | 10010023 | |
| Pelco easyGlow device | Pelco | 91000S | Glow discharge device |
| Penicillin-Streptomycin | Sigma-Aldrich | P0781 | Media supplement |
| Pipetman P1000, 100–1000 µL, Metal Ejector | Gilson | F144059M | |
| Pipetman P2, 0.2–2 µL, Metal Ejector | Gilson | F144054M | |
| Pipetman P20, 2–20 µL, Metal Ejector | Gilson | F144056M | |
| Whatman number 2 filter paper, 55 mm | Whatman | 28455-041 | Blotting paper |
Referencias
- Zhang, P., Mendonça, L. Analysis of Viruses in the Cellular Context by Electron Tomography. Encyclopedia of Virology. 1, 242-247 (2021).
- Fäßler, F., Dimchev, G., Hodirnau, V. -. V., Wan, W., Schur, F. K. M. Cryo-electron tomography structure of Arp2/3 complex in cells reveals new insights into the branch junction. Nature Communications. 11, 6437 (2020).
- McDowall, A. W., et al. Electron microscopy of frozen hydrated sections of vitreous ice and vitrified biological samples. Journal of Microscopy. 131 (Pt 1), 1-9 (1983).
- Stewart, M., Vigers, G. Electron microscopy of frozen-hydrated biological material. Nature. 319 (6055), 631-636 (1986).
- Gan, L., Jensen, G. J. Electron tomography of cells. Quarterly Reviews of Biophysics. 45 (1), 27-56 (2012).
- Yang, J. E., Larson, M. R., Sibert, B. S., Shrum, S., Wright, E. R. CorRelator: Interactive software for real-time high precision cryo-correlative light and electron microscopy. Journal of Structural Biology. 213 (2), 107709 (2021).
- Mendonça, L., et al. Correlative multi-scale cryo-imaging unveils SARS-CoV-2 assembly and egress. Nature Communications. 12 (1), 4629 (2021).
- Klumpe, S., et al. A modular platform for automated cryo-FIB workflows. eLife. 10, e70506 (2021).
- Wagner, F. R., et al. Preparing samples from whole cells using focused-ion-beam milling for cryo-electron tomography. Nature Protocols. 15 (6), 2041-2070 (2020).
- Klein, S., et al. IFITM3 blocks influenza virus entry by sorting lipids and stabilizing hemifusion. Cell Host & Microbe. 31 (4), 616.e20-633.e20 (2023).
- Shah, P. N. M., et al. Characterization of the rotavirus assembly pathway in situ using cryoelectron tomography. Cell Host & Microbe. 31 (4), 604.e4-615.e4 (2023).
- Fäßler, F., Zens, B., Hauschild, R., Schur, F. K. M. 3D printed cell culture grid holders for improved cellular specimen preparation in cryo-electron microscopy. Journal of Structural Biology. 212 (3), 107633 (2020).
- Hoffmann, P. C., et al. Electron cryo-tomography reveals the subcellular architecture of growing axons in human brain organoids. eLife. 10, e70269 (2021).
- Toro-Nahuelpan, M., et al. Tailoring cryo-electron microscopy grids by photo-micropatterning for in-cell structural studies. Nature Methods. 17 (1), 50-54 (2020).
Reimpresiones y Permisos
Solicitar permiso para reutilizar el texto o las figuras de este JoVE artículos
Solicitar permisoExplorar más artículos
This article has been published
Video Coming Soon
ACERCA DE JoVE
Copyright © 2025 MyJoVE Corporation. Todos los derechos reservados