JoVE 비디오를 활용하시려면 도서관을 통한 기관 구독이 필요합니다. 전체 비디오를 보시려면 로그인하거나 무료 트라이얼을 시작하세요.
Method Article
탠덤 이온 이동성 실험을 위한 순환 이온 이동성 분광계 사용
요약
이온 이동성 분광법 (IMS)은 생체 분자의 특성화를위한 질량 분광법에 대한 흥미로운 보완물이며, 특히 이성체에 민감하기 때문입니다. 이 프로토콜은 분자의 분리 및 그 단편의 이동성 프로파일의 생성을 허용하는 탠덤 IMS (IMS/IMS) 실험을 설명합니다.
초록
화학 구조의 정확한 특성화는 근본적인 생물학적 메커니즘과 기능적 특성을 이해하는 데 중요합니다. 질량 분광법 (MS)은 인기있는 도구이지만 모든 구조적 특징을 완전히 드러내기에 항상 충분하지는 않습니다. 예를 들어, 탄수화물은 생물학적으로 관련이 있지만, 그 특성화는 수많은 수준의 이성체에 의해 복잡합니다. 이온 이동성 분광법 (IMS)은 이온 입체 형태에 민감하고 따라서 이성체에 민감하기 때문에 흥미로운 보완물입니다.
또한, 최근 발전으로 기술이 크게 향상되었습니다: 마지막 세대의 순환 IMS 계측기는 향상된 분해능 또는 탠덤 이온 이동성(IMS/IMS) 실험을 수행할 수 있는 가능성과 같은 선형 IMS 계측기에 비해 추가 기능을 제공합니다. IMS/IMS 동안, 이온은 이온 이동성에 기초하여 선택되고, 단편화되고, 그 단편에 대한 이온 이동성 정보를 얻기 위해 재분석된다. 최근의 연구에 따르면 이러한 IMS / IMS 데이터에 포함 된 단편의 이동성 프로파일은 특정 글리 칸의 지문으로 작용할 수 있으며 구조적으로 관련된 방식으로 글리코믹 데이터 세트를 구성하기위한 분자 네트워킹 전략에 사용될 수 있습니다.
따라서 이 프로토콜의 목표는 샘플 준비부터 재현 가능한 스펙트럼을 산출하는 이온 이동성 차원의 최종 CCS(충돌 횡단면) 교정에 이르기까지 IMS/IMS 데이터를 생성하는 방법을 설명하는 것입니다. 하나의 대표적인 글리칸의 예를 들자면, 이 프로토콜은 순환 IMS 장비에 IMS/IMS 제어 시퀀스를 구축하는 방법, IMS 도달 시간을 드리프트 시간(즉, 이온에 적용된 효과적인 분리 시간)으로 변환하기 위해 이 제어 시퀀스를 설명하는 방법, 그리고 원시 데이터로부터 관련 이동성 정보를 추출하는 방법을 보여줄 것이다. 이 프로토콜은 IMS/IMS 실험의 중요 사항을 명확하게 설명하도록 설계되었으므로 새로운 순환 IMS 사용자가 간단하고 재현 가능한 인수를 수행할 수 있도록 도와줍니다.
서문
생체 분자의 완전한 화학적 특성화는 근본적인 생물학적 및 기능적 특성을 이해하는 열쇠입니다. 이를 위해 "omics"과학은 최근 몇 년 동안 생물학적 농도에서 화학 구조의 대규모 특성화를 목표로 발전했습니다. 프로테오믹스 및 대사체학에서 MS는 생물학적 매질에서 발견되는 구조적 이질성을 푸는 핵심 도구가되었으며, 특히 탠덤 MS (MS / MS)를 통해 구조 정보를 제공 할 수있는 감도와 능력 덕분입니다. MS / MS 전략에서 이온은 질량에 따라 선택된 다음 단편화되고 마지막으로 분자의 지문을 확립하기 위해 단편의 질량을 획득합니다. MS/MS 스펙트럼은, 특히, 스펙트럼 데이터베이스1,2와 일치시키거나, 부모 구조들3,4를 잠정적으로 재구성하는데 사용될 수 있다. 유사한 스펙트럼이 유사한 화합물에 속한다는 가정 하에서, MS/MS 데이터는 유사성 점수5,6을 통해 관련 종을 연결하는 분자 네트워크(MN)를 구축하는데 사용될 수도 있다.
그러나, 이온의 질량 대 전하 비율 (m/z)을 검출하는 MS의 고유 한 특성 때문에, 기술은 (스테레오) 이성질체의 범위 내에 속하는 다수의 구조적 특징에 눈이 멀다. 예를 들어, 탄수화물은 몇몇 단당류 서브유닛으로 만들어지며, 이들 중 다수는 입체이성질체 또는 심지어 에피머(예를 들어, Glc vs. Gal 또는 Glc vs. Man)이다. 이들 서브유닛은 글리코시드 결합에 의해 연결되며, 이는 아노머 탄소의 결합(regioisomerism) 및 입체 구성(anomerism)의 위치에 의해 상이할 수 있다. 이러한 특성은 독립형 MS가 탄수화물 이성질체7를 구별하는 것을 어렵게 만들고, 고에너지 활성화 방법8,9,10을 사용하여 위치 이성체주의만을 해결할 수 있다. 유도체화는 입체이성체기11의 동등성을 방해하는 옵션이지만, 광범위한 샘플 준비가 필요하다. 또 다른 더 간단한 옵션은 MS를 IMS와 같은 이성체에 민감한 분석 차원과 결합하는 것입니다.
이 프로토콜은 IMS의 기본 개념에 이미 익숙한 사용자를 위해 설계되었으며 자세한 검토는 다른 곳에서12,13 사용할 수 있기 때문에 IMS의 원칙에 대한 간략한 개요 만 여기에 나와 있습니다. IMS는 버퍼 가스 및 전기장과의 이온의 상호 작용에 의존하여 궁극적으로 기상 형태에 따라 이온을 분리하는 기상 분리 방법입니다. MS에 결합된 IMS의 다른 원리는 상용 기기에서 찾을 수 있습니다: 일부는 높은 전기장과 낮은 전기장(필드 비대칭 IMS, FAIMS)을 번갈아 가며 작동하는 반면, 대부분은 낮은 필드 한계 내에서 작동하며, 특히 드리프트 튜브 IMS(DTIMS, 선형적으로 감소하는 전기장), 이동파 IMS(TWIMS, 대칭 전위파), 갇힌 IMS(TIMS, 전기장에 대한 버퍼 가스 포획 이온의 높은 흐름)13 . 낮은 필드 방법은 분리 중에 버퍼 가스와 상호 작용하는 이온의 표면 (Å2 또는 nm2)을 나타내는 이온 - 가스 쌍의 특성 인 소위 CCS에 대한 액세스를 허용합니다. CCS는 이론적으로 계측기와 무관하므로 서로 다른 실험실 간에 재생할 수 있는 데이터를 생성하는 데 유용합니다14. 이온 이동성 분리는 다양한 파라미터, 특히 이동성 셀의 가스 압력 및 가스 온도의 변동에 의해 영향을 받을 수 있습니다. CCS 교정은 교정제와 관심 종 모두 유사하게 영향을 받기 때문에이를 해결할 수있는 방법입니다13. 그러나 온도 조절실에 계측기를 설치하고 신뢰할 수있는 가스 압력 제어 시스템을 갖추어야합니다.
IMS의 흥미로운 진화는 IMS / IMS로, 2006 년 Clemmer의 그룹에 의해 MS / MS15,16의 아날로그로 처음 소개되었습니다. IMS/IMS에서, 관심 이온은 이온 이동성에 기초하여 선택적으로 분리된다; 이어서, 활성화되고(가능한 단편화까지), 활성화된 이온 또는 단편의 새로운 IMS 분석이 수행된다. 첫 번째 도구 설계에서는 두 개의 IMS 셀을 직렬로 배치하여 활성화가 서있는 이온 깔때기로 분리했습니다. 그 이후로 여러 IMS / IMS 설정이 제안되었지만 (검토를 위해 Eldrid 및 Thalassinos17 참조), IMS / IMS 기능을 갖춘 최초의 상업용 질량 분광계는 201918 년에만 사용할 수있게되었습니다. 이 장비는 IMS 셀의 순환 설계라는 또 다른 기술적 혁신과 결합하여 초기 개념을 크게 개선했습니다.
순환 IMS 셀은 이론적으로 드리프트 경로 길이를 거의 무한히 증가시킬 수 있게 하며, 따라서 계측기의 분해능19을 증가시킨다. 이것은 순환 TWIMS 셀이 주 이온 광학 축에 직교하여 배치되는 특정 계측기 형상에 의해 달성되었다. IMS 셀의 입구에 있는 다기능 어레이 영역은 이온 경로의 방향을 제어할 수 있게 한다: (i) IMS 분리를 위해 이온을 옆으로 보내는 것, (ii) MS 검출을 위해 앞으로 보내는 것, 또는 (iii) IMS 셀로부터 후진하여 프리어레이 셀에 저장될 수 있다. 이러한 프리어레이 저장 세포로부터, 이온이 활성화될 수 있고 단편이 이온 이동성 측정을 위해 IMS 셀에 재주입될 수 있으며, 이는 입체이성질체20을 특성화하는데 성공적으로 사용된 접근법이다. 궁극적으로, 수집된 데이터에는 전구체 및 그 단편에 대한 이온 이동성 및 m/z 정보가 포함됩니다.
글리칸 분석을 위해이 순환 설계를 사용한 최근 간행물 (Ollivier et al.21)에서 우리는 그러한 IMS / IMS 데이터에 포함 된 단편의 이동성 프로파일이 분자 네트워킹 전략에 사용될 수있는 생체 분자의 지문으로 작용한다는 것을 보여주었습니다. IM-MN이라고 불리는 결과 네트워크는 구조적으로 관련된 방식으로 글리코믹스 데이터 세트를 구성하게 된 반면, MS/MS 데이터(MS-MN)로만 구축된 네트워크는 거의 정보를 공개하지 않았습니다. 이 간행물을 보완하고 Cyclic IMS 사용자가 이 워크플로를 구현하는 데 도움이 되도록 이 프로토콜은 데이터 수집에 사용되는 프로토콜에 대한 전체 설명을 제공합니다. 이 프로토콜은 사용자가 IM-MN 네트워크(see21)를 구축하는 데 사용할 수 있는 IMS/IMS 데이터 생성에만 초점을 맞춥니다. IM-MN의 구축은 분자 네트워킹을 위한 프로토콜이 이미 이용가능하기 때문에22 본 명세서에서 고려되지 않을 것이다. 가치 있고 재현 가능한 IMS/IMS 인수를 생성하기 위해 따라야 할 중요한 사항이 강조됩니다. Ollivier et al.에 의해 연구 된 올리고당 중 하나의 예를 들면. 도 21에 도시된 바와 같이, 다음의 단계들이 상세하다: (i) 샘플 준비, (ii) 사이클릭 IMS 계측기의 튜닝, (iii) 데이터의 자동화된 피크 피킹, 및 (iv) CCS 캘리브레이션.
프로토콜
참고: 프로토콜에 대한 개요는 그림 1에 나와 있습니다. 본 프로토콜에 기재된 실험에 사용된 파라미터는 보충 표 S1 및 보충 표 S2에서 찾을 수 있다.
1. 시료용액의 제조
참고: 프로토콜은 아라비녹실란 펜타사카라이드(23-α-L-아라비노푸라노실-크실로테트라오스 또는 XA2XX; 표 참조)를 예로 들어 설명한다.
- 용매의 제조: 50:50 H2O:MeOH 중의 500 μM LiCl (vol./vol.).
- 212 mg의 LiCl을 칭량하여 H2O 중의 100 mM 염화리튬(LiCl) 원액을 제조하고, 50 mL의 폴리프로필렌 코니컬 튜브에 50 mL의 고순도 탈이온수(H2O)를 첨가한다. 완전히 녹을 때까지 흔들어 주십시오.
참고: 용매는 분광계의 이온 소스에서 [M+Li]+ 부가물의 형성을 촉진하기 위해 리튬 염으로 도핑되며, 이는 일반적으로 다른 알칼리 부가물에 비해 더 나은 품질의 단편화 스펙트럼을 산출하기 때문입니다. LiCl의 사용은 유기산 (따라서 그들의 염)이 이전에 IMS 프로파일에 영향을 미치는 것으로 밝혀 졌기 때문에 권장됩니다.23. - 유리 병에 LiCl 원액을 200x로 희석하십시오 : 원액 250 μL에 H2O 24.75 mL를 첨가하십시오. 메탄올 (MeOH) 25 mL를 첨가하여 50:50 H2O : MeOH (v / v)에서 500 μM의 LiCl의 최종 농도에 도달하십시오. 용매를 탈기시키기 위해 2 분 동안 초음파 처리하십시오.
참고: MeOH는 건강상의 위험(H225, H301, H311, H331, H370)을 나타냅니다. 실험실 코트, 장갑 및 눈 보호 장치를 착용 추출기 후드 아래에서 조작하십시오. 50:50 MeOH/H2O (v/v)의 비율은 올리고당의 이온화에 가장 적합한 용매인 것으로 보인다; 그러나, MeOH는 필요한 경우 아세토니트릴(ACN)에 의해 치환될 수 있다.
- 212 mg의 LiCl을 칭량하여 H2O 중의 100 mM 염화리튬(LiCl) 원액을 제조하고, 50 mL의 폴리프로필렌 코니컬 튜브에 50 mL의 고순도 탈이온수(H2O)를 첨가한다. 완전히 녹을 때까지 흔들어 주십시오.
- 1.5 mL 폴리프로필렌 튜브에서, 탄수화물 1 mg의 무게를 측정한다. 500 μM LiCl의 적절한 부피로 용해시켜 1 mg/mL의 농도에 도달한다. 50:50 MeOH/H2O + 500 μM LiCl에서 10 μg/mL의 최종 농도로 희석한다. 4°C에서 보관한다.
참고: 10 μg/mL의 농도는 IMS/IMS-MS 동안 모든 단편 이온에 대한 신호를 최적화하기 위해 선택되었습니다(이것은 순수한 화합물에 대한 것이며, 혼합물에서 작업할 때 농도를 증가시킵니다). 기준 IMS/IMS 스펙트럼의 획득을 위해, 샘플을 더 희석하지 마십시오: 계측기가 이를 교정할 수 있는 옵션을 제공하지만, 단편화 전에 MS 검출기의 포화가 예상된다(단계 3.2 참조).
2. 순환 IMS 질량 분광계의 튜닝
참고: 소프트웨어 관련 지침(창, 메뉴 및 명령)은 굵게 강조 표시됩니다.
- 계측기 제어 소프트웨어(MS 튜닝 페이지, 재료 표의 소프트웨어 세부 정보 참조)에서 계측기 콘솔을 열고 계측기를 작동 모드로 전환합니다. IMS 셀에서 고전압이 안정화될 때까지 최소 3시간 동안 기다립니다.
참고: 최상의 재현성을 위해서는 IMS 셀의 전압을 완전히 안정화해야 합니다. 고전압을 켜고 순환 IMS 분석 전에 하룻밤 사이에 장비를 안정화시키십시오. 또한, 이온 이동성 셀의 압력과 온도는 가능한 한 일정하게 유지되어야 한다. 압력에 대한 리드백은 진공 탭에서 사용할 수 있지만 온도에 대한 읽기백은 사용할 수 없습니다. 장비를 열경화 실험실에 보관하십시오. 이 작업에 사용되는 기기는 20°C에서 열경화된 실험실에서 1.75mbar에서 작동합니다. - 순환 IMS 기기 설정
주: 표준 솔루션은 장비 설정을 위해 내장된 유체 시스템을 사용하여 주입해야 합니다.- 유체 시스템에 적절한 제조업체가 제공 한 표준으로 채워진 유체 용기를 놓으십시오 : 저수지 B ( 'Lockmass') : 50:50 ACN / H2O + 0.1 % 포름산에 10 pg / μL 류신 엔케팔린 (LEU ENK); 저수지 C ( '칼리브란트') : 메이저 믹스.
참고: 이 프로토콜에서는 MajorMix 교정 솔루션을 사용하여 m/z 및 CCS 치수를 모두 교정합니다. 실용적인 이유로, 외부 CCS 캘리브레이션이 수행될 것이다(프로토콜의 단계 5 참조); 따라서, CCS를 위한 사내 교정제 혼합물 및 m/z 에 대한 다른 교정제(예를 들어, 나트륨 포르메이트 또는 소듐 요오드화물)를 사용하는 것도 가능하다. - Quartz 콘솔의 튠 페이지에서 Fluidics 탭으로 이동합니다. 샘플 유체학을 저장소 C로 설정하고 기준 유체학을 저장소 B로 설정합니다. 두 용액을 이온 소스에 연속적으로 주입하여 MS 신호를 확인합니다.
- 제조업체의 지침에 따라 계측기 설정 페이지에서 ADC 설정, 검출기 설정(LEU ENK 사용) 및 질량 교정(교정 솔루션에 대한 재료 표 참조)을 수행합니다.
- 유체 시스템에 적절한 제조업체가 제공 한 표준으로 채워진 유체 용기를 놓으십시오 : 저수지 B ( 'Lockmass') : 50:50 ACN / H2O + 0.1 % 포름산에 10 pg / μL 류신 엔케팔린 (LEU ENK); 저수지 C ( '칼리브란트') : 메이저 믹스.
- 단일 패스 분리로 교정 솔루션의 IMS 획득을 기록합니다(외부 IMS 교정에 사용).
참고: 이온 소스와 이동파(TW) 파라미터(정파 높이 및 파속도)는 모든 획득(교정 및 획득) 동안 일정하게 유지되어야 합니다. 사용자가 샘플에 대한 최적 파라미터에 대한 사전 지식이 없는 경우, 이 단계는 프로토콜의 단계 3 이후에 수행될 수 있다(중성 올리고당의 [M+Li]+ 부가물의 경우, 대표적인 결과는 16V의 TW 높이 및 350m/s의 TW 속도를 사용하여 최상의 결과를 제공한다).- Fluidics 탭에서 배플 위치 샘플을 선택하고 10μL/min의 유속으로 '샘플' 프로브를 통해 이온 소스(내장 유체 시스템 사용)에 교정제(재료 표 참조)를 주입합니다.
- 단일 패스 IMS 시퀀스를 설정합니다. 튜닝 페이지에서 계측기를 이동성 모드로 설정하고 순환 시퀀스 제어 창을 엽니다. 고급 모드를 선택합니다. 이 새 창의 순환 함수 탭에서 번들 추가를 선택한 다음 단일/멀티패스를 선택합니다. 일련의 이동성 이벤트가 동일한 창의 시퀀스 탭에 나타날 때까지 기다립니다.
참고: 실시간 디스플레이를 활성화하려면 계측기 매개변수를 적용해야 합니다: TOF 모드에서 튜닝 또는 이동성 모드에서 실행을 클릭하십시오. TOF 모드와 이동성 모드 간에 계측기를 전환하기 전에 실행 중인 수집(튜닝 페이지 디스플레이 포함)을 중단해야 합니다. 이온의 상대적 풍부도는 이온 전송 파라미터의 변화로 인해 TOF 모드와 이동성 모드 사이에서 달라질 수 있다. - 모든 교정 이온이 순환 IMS 경마장 주위를 단일 통과하도록 시퀀스를 조정합니다. 주입 시간 또는 꺼내기 및 획득 시간을 변경하지 마십시오. 그러나 분리 시간을 시퀀스 탭에서 1ms로 낮춥니다. 보정 혼합물의 일부 이온이 표시된 도달 시간 창에 맞지 않으면 ADC 설정 탭에서 빈당 푸시 수를 늘려 IMS와 직교 가속도 TOF 분석기의 푸셔의 동기화를 변경하십시오.
참고: 제어 시퀀스의 시간은 이온 게이팅을 위한 다기능 배열만 제어합니다. 이온이 레이스 트랙 주위의 첫 번째 (또는 n번째) 패스에 관여하는 한, 그 동안 배열에서 TW의 방향이 변경되더라도 해당 패스를 완료합니다. 분리 시간을 1ms로 낮추면 어레이가 1ms 후에 배출 모드로 전환됩니다. 이렇게 하면 더 빠른 이온이 어레이를 통과하고 느린 이온이 첫 번째 패스를 완료하기 전에 두 번째 패스에 참여할 시간이 충분하지 않습니다. 따라서, 모든 이온은 IMS 캘리브레이션을 수행하는 데 필요한 동일한 수의 패스(즉, 하나의 패스)를 받게 될 것이다. - 2 분 인수를 기록하십시오. 순환 시퀀스 제어 창에서 획득 을 클릭하여 획득 설정 팝업 창을 엽니다. 파일 이름, 설명 및 획득 길이(최소)를 입력하고 저장을 클릭합니다.
- 2.3단계와 동일한 조건에서 교정 솔루션을 2분 더 획득한 것을 기록하십시오(CCS 교정의 품질을 확인하기 위해 이것을 사용하십시오). 순환 시퀀스 제어 창에서 획득 을 클릭하여 획득 설정 팝업 창을 엽니다. 파일 이름, 설명 및 획득 길이(최소)를 입력하고 저장을 클릭합니다.
- 엿보기 튜브에서 교정제가 결정화되지 않도록 50:50 H2O/ACN으로 유체 시스템을 철저히 세척하십시오.
3. IMS/IMS-MS 인수
- 시린지 펌프를 사용하여 10μg/mL의 (리튬 도핑된) 샘플을 10μL/min의 유속으로 샘플 프로브를 통해 주입합니다.
- 계측기를 TOF 모드( MS 튜닝 페이지에서)로 전환하여 신호의 안정성을 확인합니다. 샘플의 전체 MS 획득 (1 분)을 기록하고, 이는 동위원소 패턴 및 잠재적 오염 물질의 존재를 확인하는데 유용 할 것이다.
참고: 단편에 대한 양호한 이온 신호를 얻기 위해 샘플 농도가 선택되기 때문에, 이 단계에서 TOF 포화가 관찰될 수 있다. TOF 포화는 다음의 아티팩트를 사용하여 확인될 수 있다: (i) 인위적으로 증가된 MS 분해능, (ii) 동위원소 비율의 변화, 및 (iii) 동위원소 사이의 다수의 저풍부 피크. DRE 렌즈(동적 범위 향상, 기본 튜닝 페이지의 쿼드/MS 프로파일/DRE 탭)를 사용하여 이온 전송을 감쇠하고 TOF 모드에서 채도를 버립니다(그림 2A,B). - 계측기를 MSMS 모드(기본 튜닝 페이지의 쿼드/MS 프로파일 탭)에 놓고 MSMS 질량 필드에서 사중극자에서 분리할 대상 이온의 질량을 선택합니다(예: 아라비녹실란 오각류의 [M+Li]+ 이온 종에 해당하는 685.2의 m/z). 데이터를 처리할 때 전구체 분리를 확인하기 위해 1분 수집을 기록합니다.
참고: 리튬 부가물은 단동위원소 피크의 -1 Da에서 동위원소를 가지며, 이는 처리 단계를 방해하지 않도록 MS/MS 선택 창에서 제거해야 합니다. 쿼드/MS 프로파일 탭의 LM 분해능 및 HM 분해능 매개변수를 사용하여 선택 범위를 좁혀서 제거할 수 있습니다(그림 2C). - "슬라이싱" IMS 서열을 설정하여 관심 있는 이성질체의 이동성 기반 선택을 수행한다.
- 계 측기를 이동성 모드로 전환합니다(2.3.2단계 참조). 순환 시퀀스 제어 창의 순환 함수 탭에서 번들 추가를 선택한 다음 슬라이싱을 선택합니다. 복잡한 이동성 이벤트 시퀀스가 시퀀스 탭에 나타날 때까지 기다립니다(그림 3).
참고: IMS/IMS 프로세스의 각 단계를 시각화할 수 있습니다: 시퀀스 탭에서 꺼내기 및 가져오기 이벤트를 클릭합니다. 빨간색으로 강조 표시되면 위쪽 및 아래쪽 단추를 사용하여 시퀀스 내에서 적절한 위치로 이동합니다. - 꺼내기 및 획득 이벤트를 첫 번째 분리 이벤트 바로 뒤에 배치한 다음(즉, 그림 3에 표시된 순서대로 시퀀스에서 8행이 아닌 행 3으로 이동) 실행을 클릭합니다. 실시간으로 표시되는 초기 분리 결과를 찾습니다. IMS 피크의 분해능이 만족스러울 때까지 시퀀스에서 이 이벤트에 대한 시간 값을 변경하여 멀티패스 분리에 대한 첫 번째 분리 이벤트의 지속 시간을 늘립니다. 참고를 위해 1분 획득을 기록하십시오.
참고: ADC 설정 탭의 ADC 시작 지연 값을 기록해 둡니다. 분리의 품질을 확인하는 것이 유용합니다. - 일시 중지를 클릭합니다. 초기 분리 결과가 표시되지만 사용자가 실행을 다시 클릭할 때까지 제어 시퀀스의 수정 내용이 적용되지 않습니다. 꺼내기 및 획득 이벤트를 꺼내기 아래에 배치하고, 꺼내기를 사전 저장하고, 이벤트를 보류 및 꺼내기로 합니다. 대상 피크가 미리 저장으로 꺼내기 영역에 있고 다른 이온이 꺼내기 또는 보류 및 꺼내기 영역에 있도록 이벤트 지속 시간을 조정합니다.
참고: 도착 시간 분포(ATD)와 비교한 이 세 이벤트의 지속 시간은 Mobilogram 탭의 이동성 스펙트럼 아래에 있는 색상 코드 막대를 사용하여 시각화할 수 있습니다(그림 3). - 꺼내기 및 획득 이벤트를 시퀀스의 끝, 사전 저장소의 재주입 및 두 번째 개별 이벤트 아래에 배치합니다. 실행을 클릭하여 선택한 모집단을 표시합니다.
참고: 선택한 모집단이 IMS 셀을 떠났기 때문에 이전의 모든 분리가 손실되었으며 다시 단일 통과 분리(원하는 경우)로 돌아갑니다. - 절연의 품질을 확인합니다. 관심 피크만이 선택되었는지 확인하기 위해, 도 4에 도시된 바와 같이 재주입 전과 동일한 분리(즉, 동일한 분리 시간)를 재주입 후에 수행한다. 참고를 위해 1분 획득을 기록하십시오.
참고: 사용자는 배출된 인구를 확인하는 것이 좋습니다. 사전 저장소로 꺼내기 시간 창은 기준 수준이어야 합니다(그림 4B). 이를 확인하려면 ADC 설정 탭의 ADC 시작 지연을 수동 모드로 설정하고 3.4.2단계에서 설명한 지연 시간을 입력합니다. 참고를 위해 1분 획득을 기록하십시오. - 시퀀스 탭의 사용자 정의 이벤트 시간(빨간색으로 강조 표시된 Time Abs 열) 옆의 열에서 모든 이벤트의 합계 시간을 찾습니다. CCS 보정을 수행하기 위해 Pre-Store 이벤트의 Reinject 라인에서 발견 된 Time Abs를 기록하십시오.
- 계 측기를 이동성 모드로 전환합니다(2.3.2단계 참조). 순환 시퀀스 제어 창의 순환 함수 탭에서 번들 추가를 선택한 다음 슬라이싱을 선택합니다. 복잡한 이동성 이벤트 시퀀스가 시퀀스 탭에 나타날 때까지 기다립니다(그림 3).
- IMS의 두 라운드 사이에 있는 타겟 피크를 조각화합니다. 재주입 단계의 전압을 변경하여 이온의 운동 에너지를 증가시키고, 이온 이동성 가스와의 충돌시 이들을 파편화한다.
- 꺼내기 및 획득 직전의 개별 이벤트 기간을 1ms로 설정합니다(2.3.3단계의 설명 참조).
- 사전 저장소에서 재주입 줄에서 활성화 사용 상자를 선택하고 기본 제공 컨트롤을 사용하여 조각화를 최적화합니다. 스펙트럼이 만족스러우면(예를 들어, 베이스 피크가 단편이라면), 직접 단계 3.5.4로 진행한다.
참고: 활성화를 활성화하면 라인의 세 가지 전압이 회색으로 바뀝니다. 이 전압은 전압의 수동 최적화가 필요한 경우 사용자가 변경해야 하는 전압입니다(다음 단계 참조). 이 세 전압(Pre-Array Gradient, Pre-Array Bias 및 Array Offset)은 이온을 활성화하는 데 사용되는 그라디언트를 형성합니다. 이온의 운동 에너지는 사전 어레이 바이어스와 어레이 오프셋 사이의 기울기에 따라 증가합니다(그림 5 참조). 그라디언트 → 바이어스 → 오프셋 값의 기본값은 다음과 같습니다: 활성화 없이 85 → 70 → 45V; 내장 기능의 최대 활성화 185 → 170 → -5 V (+150 V). 단편화 후 DRE 렌즈를 사용하여 이온 전송을 재조정하는 것을 잊지 마십시오 (신호의 감쇠 감소) (3.2 단계 참조). - 조각화가 내장 컨트롤로 만족스럽지 않으면 활성화 활성화 상자의 선택을 취소하고 재주입 전압을 수동으로 최적화하십시오. 사전 어레이 그라디언트 전압을 높이고(프리 어레이 바이어스 전압은 항상 프리 어레이 그라디언트보다 15V 낮게 유지되어야 함), 결과가 만족스러울 때까지 어레이 오프셋 전압(음수로 설정할 수 있음)을 낮춥니다.
참고: 다기능 어레이의 전압을 수동으로 튜닝할 때 사용자는 'Mobilogram' 뷰에서 다기능 어레이(PE 다이어그램)에 적용된 전압의 대화식 회로도로 전환하여 전압 설정을 더 잘 시각화할 수 있습니다(그림 5A). - 2 분 인수를 기록하십시오. 획득 팝업 창에서 드리프트 시간 유지 옵션을 선택하여 도착 시간 대 m/z (크로마토그래피 분석에 사용되는 수집 시간(보존 시간)가 파일에서 제거됨)만 포함하는 파일을 생성합니다. 이 파일의 레이블은 *_dt입니다. 라우.
참고: 사용자가 드리프트 시간 유지 옵션을 확인하는 것을 잊어버린 경우에도 Driftscope 2.9 소프트웨어(파일 |를 사용하여 IMS 치수를 추출할 수 있습니다. 매스 린스에 수출 | 드리프트 시간 유지).
- 기본 튜닝 페이지에서 계측기를 TOF 모드로 되돌리고 다음 샘플을 진행하기 전에 50:50 MeOH/H2O로 시스템을 완전히 헹구십시오.
4. MZmine 224를 사용한 IMS/IMS-MS 처리
참고: MZmine 2는 자료표에 제공된 URL에서 사용할 수 있습니다. MZmine 2.51을 사용하는 것이 좋습니다. 이 원고를 준비 할 때 이후 버전은 가져 오기 기능이 변경되어 순환 IMS 장비에서 RAW 파일을 열 수 없습니다.
- IMS 및 m/z 치수(*_dt만 포함하는 원시 파일을 가져옵니다. RAW) 원시 데이터 메소드를 사용하여 | 원시 데이터 가져오기.
참고: 원시 파일은 기본 MZmine 창의 왼쪽에 나타납니다. 원본 *을 가져오지 마십시오 . 보존 시간 차원이 여전히 포함된 RAW 파일입니다. MZmine은 보존 시간과 IMS 도착 시간을 구분하지 않으며 두 차원의 데이터 요소가 겹칩니다. - 대표 파일에서 워크플로우 매개변수를 선택하여 최적화합니다. 원시 데이터 파일 목록.
- 데이터의 노이즈 수준을 평가합니다. 원시 데이터 파일 목록에서 파일을 마우스 오른쪽 버튼으로 클릭하고 TIC 표시 를 선택한 다음 기본 피크 "크로마토그램"(BPC)을 표시합니다. 눈으로 관찰할 수 있는 가장 작은 피크를 두 번 클릭하여 질량 스펙트럼을 표시합니다. 데이터의 잡음 레벨이 이 스펙트럼에서 염기 피크의 두 번째 동위원소의 잡음 레벨 주위에 있다고 생각하고, 다음 처리 단계에서 모든 강도 임계값에 대해 동일한 값을 사용한다.
참고: 데이터는 사중극자 격리를 사용하여 수집되었으므로 MZmine은 MS/MS로 간주합니다. 전체 MZmine 처리 전반에 걸쳐 MS 레벨 = 2에서 작업해야 합니다. - Raw 데이터 방법을 사용하여 대량 감지를 수행 하| 기능 감지 | 질량 감지. 프로파일 모드에서 수집한 데이터의 경우 웨이블릿 변환 알고리즘을 사용합니다. MZmine에서 알고리즘의 매개 변수를 설정하려면 알고리즘 옆에있는 [...] 버튼을 클릭하고 미리보기 표시 옵션을 사용하여 매개 변수를 최적화하면서 데이터를 시각화하십시오.
참고: 이 단계에서 알고리즘에 의해 선택된 피크는 미리 보기 창에 빨간색으로 표시됩니다. 독점 RAW 파일에서 웨이블릿 변환 알고리즘을 사용할 때 MZmine은 프로파일 데이터 포인트를 중심 피크로 착각하는 경우가 있습니다. 소프트웨어는 사용자가 중심 스펙트럼에서 프로파일 알고리즘을 실행하고 있다는 메시지를 표시합니다.이 메시지를 무시하고 확인을 클릭하십시오. - Raw 데이터 방법을 사용하여 각 단편 질량에 대해 추출된 이온 이동성 스펙트럼(EIM)을 재구성 하| 기능 감지 | ADAP 크로마토그램 빌더 는 이전 단계에서 생성된 '질량' 질량 목록에 있습니다. 이 단계에서 m/z 공차 입력은 스캔-스캔 공차이므로 전체 예상 정확도보다 최소 3-4배 이상 높게 유지해야 합니다.
- 이전 단계에는 미리 보기 옵션이 없으므로 기본 MZmine 창의 오른쪽 패널에 나타난 기능 목록을 사용하여 피크 피킹의 품질을 직접 확인하십시오. 기능 목록을 열고 모든 행을 선택하고 마우스 오른쪽 버튼을 클릭한 다음 표시/XIC(대화 상자)를 선택합니다. 모두를 클릭하여 이동성 스펙트럼의 모든 이온을 표시합니다. 색상으로 나타나는 선택된 봉우리를 검사하여 명백한 누락 된 봉우리가 없는지 확인하십시오.
- EIM을 디컨볼브하여 여러 피쳐에서 서로 다른 피크를 포함하는 m/z 를 분할합니다. 기능 목록 메서드 사용 | 기능 감지 | 크로마토그램 디컨볼루션을 선택하고 웨이블릿(ADAP) 알고리즘을 선택합니다. 미리 보기 표시 옵션과 S/N 임계값, 계수/영역 임계값 및 RT 웨이블릿 범위의 주요 매개 변수를 사용하여 데이터에 대한 알고리즘을 최적화합니다.
참고: 디컨볼루브 스펙트럼의 측면을 확인하는 것이 좋습니다. 4.2.4단계에서 설명한 대로 크로마토그램 시각화 도구를 사용합니다. 비컨볼루브된 피크는 컬러로 나타나고, 도 6A에 제시된 바와 같이 동일한 질량의 피크는 분할되어야 한다. - 피처 리스트 메소드를 사용하여 디컨볼브된 EIM을 디동위원소 화하| 동위원소 | 동위원소 피크 그루퍼. m/z 공차 값에 대해 계측기의 예상 정확도를 사용하고, IMS 분리 중에 동위원소가 분해되지 않으므로 도달 시간 허용 오차를 0.1ms(MZmine에서 보존 시간 허용 오차 0.1분으로 표시)로 설정합니다. 피쳐 목록 확인: 동위원소가 남아 있으면 공차 값을 늘립니다.
참고: 디이소토핑은 이론적으로 피처 리스트 처리의 어느 순간에나 수행될 수 있지만, 충전 값을 내보낼 수 있도록 마지막으로 수행하는 것이 중요합니다(다른 단계에 사용되는 알고리즘은 때때로 충전 상태 정보를 제거합니다).
- 데이터의 노이즈 수준을 평가합니다. 원시 데이터 파일 목록에서 파일을 마우스 오른쪽 버튼으로 클릭하고 TIC 표시 를 선택한 다음 기본 피크 "크로마토그램"(BPC)을 표시합니다. 눈으로 관찰할 수 있는 가장 작은 피크를 두 번 클릭하여 질량 스펙트럼을 표시합니다. 데이터의 잡음 레벨이 이 스펙트럼에서 염기 피크의 두 번째 동위원소의 잡음 레벨 주위에 있다고 생각하고, 다음 처리 단계에서 모든 강도 임계값에 대해 동일한 값을 사용한다.
- 여러 IMS/IMS-MS 스펙트럼을 처리하는 경우 이러한 최적화된 매개 변수를 사용하여 처리를 반복합니다. 모든 스펙트럼에 대해 동일한 매개 변수를 유지하십시오.
- 여러 스펙트럼의 경우 단일 테이블에 그룹화하여 내보냅니다. 그렇지 않은 경우 4.5단계로 바로 건너뜁니다. 스펙트럼을 그룹화하려면 피쳐 목록 메서드를 사용하여 다음을 수행| 정렬 | 얼라이너에 가입합니다. 목표는 피크를 실제로 정렬하는 것이 아니므로 m/z 와 도착 시간 모두에 대해 제한적인 공차 값을 사용합니다. 두 차원 모두에 동일한 가중치를 부여하십시오.
- 최종 피쳐 목록을 *.csv 파일로 내보냅니다. 기능 목록 메서드 사용 | 내보내기/가져오기 | CSV 파일로 내보내고 행 m/z , 내보내기 행 보존 시간(실제 IMS 도착 시간), 피크 m/z 및 피크 높이와 같은 값을 내보냅니다. 쉼표를 필드 구분 기호로 사용합니다.
5. 중심 IMS/IMS 스펙트럼의 TWCCSN2
참고: 이 프로토콜에서는 로그 적합도 보정25,26이 사용되며, 이는 선형 보정보다 더 나은 결과를 제공하는 경향이 있으며 스프레드시트 또는 사내 처리 스크립트에서 구현하기 쉽습니다. 사내 스크립트 (R로 작성)는 자료 표에 제공된 URL에서 사용할 수 있습니다.
- 교정자 수집에서 기준 도달 시간 값을 선택합니다(2.3단계 참조). 생성자 소프트웨어( 재료 표 참조)를 사용하여 수동으로 이 작업을 수행하여 모든 IMS 교정 피크의 양상을 확인합니다.
- 크로마토그램 창에서 *_dt를 엽니다. 캘리브란트에 해당하는 RAW 파일.
- 각 교정 지점에 대해 Display |를 사용하여 EIM을 생성합니다 . 질량 옵션.
- EIM의 프로파일을 확인하십시오. 일부가 잘못 정의 된 경우 Process |를 사용하여 부드럽게하십시오 . 부드러운 옵션 (일반적으로 Savitzky-Golay 알고리즘으로 최상의 결과를 얻을 수 있으므로 3 개의 빈에서 2 번 부드럽게). 스프레드시트에서 정점 값을 보고합니다.
참고: 참조 지점은 일반적으로 저해상도 DTIMS 장치를 사용하여 획득되므로 교정자에 따라 순환 IMS에 일부 다중 모드 분포가 나타날 수 있습니다. 교정 목록에서 이러한 분포를 나타내는 피크를 제거합니다.
- 교정자에서 로그 적합 매개변수를 계산합니다.
- 모든 교정점에 대해 다음을 계산합니다.
- Eq (1)을 사용하여 드리프트 시간을 계산하십시오.
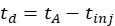 (1)
(1)
td를 드리프트 시간으로, tA는 IMS 세포에 주입하는 시간(모두 ms)을 측정하고, tinj는 도달된 시간을 측정한다.
참고: 올리고당 단편과 같은 소분자의 경우, 서로 다른 질량 사이의 데드 타임(IMS 세포로부터의 출구와 검출기 사이의 비행 시간) 변동은 CCS 교정의 오차 범위 내에 있으며 무시할 수 있습니다. - Eq (2)를 사용하여 이온의 중성 질량을 계산하십시오.
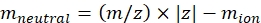 (2)
(2)
z는 이온의 전하 상태이고, mion은 반대 이온의 질량(Da에서)이다. 불확실성을 피하기 위해 정확한 질량을 사용하십시오. 반대 이온 대신 원자 손실이 있는 경우 음의 밈 값을 사용합니다(예: [M-H]-mneutral = (m/z) * |z| - (- 1.007276) = (m/z) * |z| + 1.007276). - Eq (3)을 사용하여 CCS의 매개 변수를 계산하십시오.
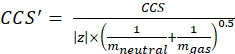 (3)
(3)
CCS를 사용하여 기준 드리프트 튜브 DTCCSN2 값 (nm2 단위) 및 드리프트 가스의 질량을 mgas (Da; 질소의 경우 ex. : mgas = 28.01 Da). - Eq (4)를 사용하여 td '매개 변수를 계산하십시오.
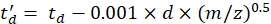 (4)
(4)
d를 사용하면 검출기 시작 지연이 실험적으로 사용 된 데드 타임 (일반적으로 ~ 1.5ms)을 수정합니다. - 위의 매개 변수의 로그를 계산합니다.
ln (CCS') 및 ln (t'd)
- Eq (1)을 사용하여 드리프트 시간을 계산하십시오.
- 선형 회귀를 수행하여 Eq (5)를 사용하여 R2 계수와 로그 적합의 x 및 y 매개 변수 (기울기 x 및 절편 ln (y) 포함)를 결정합니다.
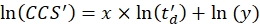 (5)
(5)
참고: 사용자는 ln(CCS') 대 ln(td') 값을 플롯하여 교정 결과를 시각적으로 확인할 수 있지만 이는 선택 사항입니다.
- 모든 교정점에 대해 다음을 계산합니다.
- 실험 데이터에 캘리브레이션을 적용하여 *.csv 파일로 내보낸 모든 IMS/IMS 스펙트럼에 대해 MZmine이 선택한 피크를 보정합니다. 각 점에 대해 다음을 계산합니다.
- Eq (6)을 사용하여 드리프트 시간을 계산하십시오.
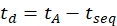 (6)
(6)
tseq 를 사용하여 최종 IMS 분리 이전의 시간 (단계 3.4.6에서 언급 된 'Time Abs'값).
참고: 서로 다른 시퀀스로 획득한 여러 IMS/IMS 스펙트럼을 교정하는 경우 tseq 값을 주의 깊게 확인하십시오. - Eq (7)를 사용하여 이온의 중성 질량을 계산하십시오.
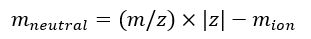 (7)
(7) - Eq (8) 및 Eq (9)를 사용하여 td ' 및 td''매개 변수를 계산하십시오.
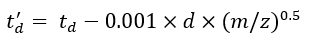 (8)
(8)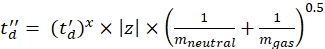 (9)
(9) - Eq(10)를 사용하여 최종 보정된 CCS 값(nm2의 TWCCSN2)을 계산합니다.
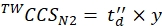 (10)
(10)
참고 : 5.2.2 단계이지만. ln(y) 를 절편으로 제공하고, y는 최종 CCS 값을 얻기 위해 사용되어야 합니다. 지수 함수를 적용하는 것을 잊지 마십시오.
- Eq (6)을 사용하여 드리프트 시간을 계산하십시오.
- 단계 2.4에서 획득한 교정 용액의 두 번째 획득에 교정을 적용하여 교정의 정확성을 확인하십시오.
참고: 보정은 ~1-2%의 오차가 있는 결과를 산출해야 합니다.
결과
아라비녹실란 오타당류인 XA2XX가 이 프로토콜을 설명하기 위한 예로 선택되었다. 이 화합물은 상업적으로 입수가능하지만, 단지 다른 아라비녹실란 펜타사카라이드 XA3XX(순수한 XA3XX도 상업적으로 입수가능함)와의 혼합물로서만 입수가능하다. XA2XX 및 XA3XX의 구조는 보충 그림 S1에 나와 있습니다. 상용 혼합물 중의 XA2XX와 XA3XX의 비율이...
토론
SELECT SERIES 순환 IMS는 업스트림 크로마토그래피 분리 없이 정의된 이온 집단(주어진 m/z 및 이온 이동성)을 선택할 수 있는 강력한 도구입니다. 이 계측기는 MS/MS 및 IMS/IMS 스펙트럼을 모두 추출할 수 있는 이 이온 집단의 이차원 단편화 맵을 생성할 수 있는 가능성을 제공합니다. 그러나 사용자는 실험 프로세스 중에주의가 필요한 몇 가지 중요한 점에 유의해야합니다.
먼...
공개
저자는 공개 할 이해 상충이 없습니다.
감사의 말
S.O.는 그의 박사 학위 (보조금 ANR-18-CE29-0006)에 자금을 지원 한 프랑스 국립 연구소에 감사드립니다.
자료
| Name | Company | Catalog Number | Comments |
| 33-α-L- plus 23-α-L-Arabinofuranosyl-xylotetraose (XA3XX/XA2XX) mixture | Megazyme Ltd., Wicklow, Ireland | O-XAXXMIX | XA2XX + XA3XX mixture |
| 33-α-L-Arabinofuranosyl-xylotetraose (XA3XX) | Megazyme Ltd., Wicklow, Ireland | O-XA3XX | Pure XA3XX standard |
| Eppendorf Safe-Lock Tubes, 1.5 mL, Eppendorf Quality, colorless, 1,000 tubes | Eppendorf, Hamburg, Germany | 0030120086 | Used to prepare the carbohydrate stock solution and dilution |
| FALCON 50 mL Polypropylene Conical Tube 30 x 115 mm | Corning Science México S.A. de C.V., Reynosa, Tamaulipas, Mexico | 352070 | Used to prepare the aqueous stock solution of 100 mM LiCl |
| Lithium Chloride (ACS reagent, ≥99 %) | Sigma-Aldrich Inc., Saint Quentin Fallavier, France | 310468 | Used to dope the sample with lithium |
| Major Mix IMS/Tof Calibration Kit | Waters Corp., Wilmslow, UK | 186008113 | Calibration solution for MS and IMS |
| MassLynx 4.2 SCN1016 Release 6 (Waters Embedded Analyser Platform for Cyclic IMS 2.9.1 Release 9) | Waters Corp., Wilmslow, UK | 721022377 | Cyclic IMS vendor software for instrument control and data processing |
| Methanol for HPLC PLUS Gradient grade | Carlo-Erba Reagents, Val de Reuil, France | 412383 | High-purity solvent |
| MS Leucine Enkephaline Kit | Waters Corp., Wilmslow, UK | 700002456 | Reference compound used for tuning of the mass spectrometer |
| SCHOTT DURAN 100 mL borosilicate glass bottle | VWR INTERNATIONAL, Radnor, Pennsylvania, US | 218012458 | Used to prepare the solution of 500 µM LiCl in 50:50 MeOH/Water |
| SELECT SERIES Cyclic IMS | Waters Corp., Wilmslow, UK | 186009432 | Ion mobility-mass spectrometer equipped with a cylic IMS cell |
| Website: http://mzmine.github.io/ | MZmine Development Team | - | Link to download the MZmine software |
| Website: https://github.com/siollivier/IM-MN | INRAE, UR BIA, BIBS Facility, Nantes, France | - | Link to an in-house R script containing a CCS calibration function |
참고문헌
- Allard, P. -. M., et al. Integration of molecular networking and in-silico MS/MS fragmentation for natural products dereplication. Analytical Chemistry. 88 (6), 3317-3323 (2016).
- Wang, M., et al. Mass spectrometry searches using MASST. Nature Biotechnology. 38 (1), 23-26 (2020).
- David, M., Fertin, G., Rogniaux, H., Tessier, D. SpecOMS: a full open modification search method performing all-to-all spectra comparisons within minutes. Journal of Proteome Research. 16 (8), 3030-3038 (2017).
- Dührkop, K., et al. SIRIUS 4: a rapid tool for turning tandem mass spectra into metabolite structure information. Nature Methods. 16 (4), 299-302 (2019).
- Wang, M., et al. Sharing and community curation of mass spectrometry data with Global Natural Products Social Molecular Networking. Nature Biotechnology. 34 (8), 828-837 (2016).
- Nothias, L. -. F., et al. Feature-based molecular networking in the GNPS analysis environment. Nature Methods. 17 (9), 905-908 (2020).
- Gray, C. J., et al. Advancing solutions to the Carbohydrate Sequencing Challenge. Journal of the American Chemical Society. 141 (37), 14463-14479 (2019).
- Ropartz, D., et al. Online coupling of high-resolution chromatography with extreme UV photon activation tandem mass spectrometry: Application to the structural investigation of complex glycans by dissociative photoionization. Analytica Chimica Acta. 933, 1-9 (2016).
- Wolff, J. J., et al. Negative electron transfer dissociation of glycosaminoglycans. Analytical Chemistry. 82 (9), 3460-3466 (2010).
- Ropartz, D., et al. Charge transfer dissociation of complex oligosaccharides: comparison with collision-induced dissociation and extreme ultraviolet dissociative photoionization. Journal of the American Society for Mass Spectrometry. 27 (10), 1614-1619 (2016).
- Morelle, W., et al. Fragmentation characteristics of permethylated oligosaccharides using a matrix-assisted laser desorption/ionization two-stage time-of-flight (TOF/TOF) tandem mass spectrometer. Rapid Communications in Mass Spectrometry. 18 (22), 2637-2649 (2004).
- Gabelica, V., Marklund, E. Fundamentals of ion mobility spectrometry. Current Opinion in Chemical Biology. 42, 51-59 (2018).
- Gabelica, V., et al. Recommendations for reporting ion mobility mass spectrometry measurements. Mass Spectrometry Reviews. 38 (3), 291-320 (2019).
- Hernandez-Mesa, M., et al. Interlaboratory and interplatform study of steroids collision cross section by traveling wave ion mobility spectrometry. Analytical Chemistry. 92 (7), 5013-5022 (2020).
- Koeniger, S. L., et al. An IMS-IMS analogue of MS-MS. Analytical Chemistry. 78 (12), 4161-4174 (2006).
- Merenbloom, S. I., Koeniger, S. L., Valentine, S. J., Plasencia, M. D., Clemmer, D. E. IMS−IMS and IMS−IMS−IMS/MS for separating peptide and protein fragment ions. Analytical Chemistry. 78 (8), 2802-2809 (2006).
- Eldrid, C., Thalassinos, K. Developments in tandem ion mobility mass spectrometry. Biochemical Society Transactions. 48 (6), 2457-2466 (2020).
- Giles, K., et al. A cyclic ion mobility-mass spectrometry system. Analytical Chemistry. 91 (13), 8564-8573 (2019).
- Merenbloom, S. I., Glaskin, R. S., Henson, Z. B., Clemmer, D. E. High-resolution ion cyclotron mobility spectrometry. Analytical Chemistry. 81 (4), 1482-1487 (2009).
- Ollivier, S., et al. Anomeric retention of carbohydrates in multistage cyclic ion mobility (IMSn): de novo structural elucidation of enzymatically produced mannosides. Analytical Chemistry. 93 (15), 6254-6261 (2021).
- Ollivier, S., Fanuel, M., Rogniaux, H., Ropartz, D. Molecular networking of high-resolution tandem ion mobility spectra: a structurally relevant way of organizing data in glycomics. Analytical Chemistry. 93 (31), 10871-10878 (2021).
- Aron, A. T., et al. Reproducible molecular networking of untargeted mass spectrometry data using GNPS. Nature Protocols. 15 (6), 1954-1991 (2020).
- McKenna, K. R., Li, L., Krishnamurthy, R., Liotta, C. L., Fernández, F. M. Organic acid shift reagents for the discrimination of carbohydrate isobars by ion mobility-mass spectrometry. The Analyst. 145 (24), 8008-8015 (2021).
- Pluskal, T., Castillo, S., Villar-Briones, A., Orešič, M. MZmine 2: Modular framework for processing, visualizing, and analyzing mass spectrometry-based molecular profile data. BMC Bioinformatics. 11, 395 (2010).
- Ruotolo, B. T., Benesch, J. L. P., Sandercock, A. M., Hyung, S. -. J., Robinson, C. V. Ion mobility-mass spectrometry analysis of large protein complexes. Nature Protocols. 3 (7), 1139-1152 (2008).
- Bush, M. F., Hall, Z., Giles, K., Hoyes, J., Robinson, C. V., Ruotolo, B. T. Collision cross sections of proteins and their complexes: a calibration framework and database for gas-phase structural biology. Analytical Chemistry. 82 (22), 9557-9565 (2010).
- Ropartz, D., et al. Structure determination of large isomeric oligosaccharides of natural origin through multipass and multistage cyclic traveling-wave ion mobility mass spectrometry. Analytical Chemistry. 91 (18), 12030-12037 (2019).
- Tolmachev, A. V., et al. Characterization of ion dynamics in structures for lossless ion manipulations. Analytical Chemistry. 86 (18), 9162-9168 (2014).
- Arndt, J. R., et al. High-resolution ion-mobility-enabled peptide mapping for high-throughput critical quality attribute monitoring. Journal of the American Society for Mass Spectrometry. 32 (8), 2019-2032 (2021).
- Le Fèvre, A., Dugourd, P., Chirot, F. Exploring conformational landscapes using trap and release tandem ion mobility spectrometry. Analytical Chemistry. 93 (9), 4183-4190 (2021).
- Ohshimo, K., He, X., Ito, R., Misaizu, F. Conformer separation of dibenzo-crown-ether complexes with Na+ and K+ ions studied by cryogenic ion mobility-mass spectrometry. The Journal of Physical Chemistry A. 125 (17), 3718-3725 (2021).
- Purves, R. W., Barnett, D. A., Ells, B., Guevremont, R. Gas-phase conformers of the [M + 2H]2+ ion of bradykinin investigated by combining high-field asymmetric waveform ion mobility spectrometry, hydrogen/deuterium exchange, and energy-loss measurements. Rapid Communications in Mass Spectrometry. 15 (16), 1453-1456 (2001).
- Ujma, J., et al. Cyclic ion mobility mass spectrometry distinguishes anomers and open-ring forms of pentasaccharides. Journal of the American Society for Mass Spectrometry. 30 (6), 1028-1037 (2019).
- Warnke, S., Faleh, A. B., Scutelnic, V., Rizzo, T. R. Separation and identification of glycan anomers using ultrahigh-resolution ion-mobility spectrometry and cryogenic ion spectroscopy. Journal of The American Society for Mass Spectrometry. 30 (11), 2204-2211 (2019).
- Williamson, D. L., Bergman, A. E., Nagy, G. Investigating the structure of α/β carbohydrate linkage isomers as a function of group I metal adduction and degree of polymerization as revealed by cyclic ion mobility separations. Journal of the American Society for Mass Spectrometry. 32 (10), 2573-2582 (2021).
- Myers, O. D., Sumner, S. J., Li, S., Barnes, S., Du, X. One step forward for reducing false positive and false negative compound identifications from mass spectrometry metabolomics data: new algorithms for constructing extracted ion chromatograms and detecting chromatographic peaks. Analytical Chemistry. 89 (17), 8696-8703 (2017).
- Marchand, A., Livet, S., Rosu, F., Gabelica, V. Drift tube ion mobility: how to reconstruct collision cross section distributions from arrival time distributions. Analytical Chemistry. 89 (23), 12674-12681 (2017).
- Davis, D. M., et al. Analysis of ion mobility spectra for mixed vapors using Gaussian deconvolution. Analytica Chimica Acta. 289 (3), 263-272 (1994).
- Polasky, D. A., Dixit, S. M., Fantin, S. M., Ruotolo, B. T. CIUSuite 2: next-generation software for the analysis of gas-phase protein unfolding data. Analytical Chemistry. 91 (4), 3147-3155 (2019).
- Salbo, R., et al. Traveling-wave ion mobility mass spectrometry of protein complexes: accurate calibrated collision cross-sections of human insulin oligomers. Rapid Communications in Mass Spectrometry. 26 (10), 1181-1193 (2012).
- Gelb, A. S., Jarratt, R. E., Huang, Y., Dodds, E. D. A study of calibrant selection in measurement of carbohydrate and peptide ion-neutral collision cross sections by traveling wave ion mobility spectrometry. Analytical Chemistry. 86 (22), 11396-11402 (2014).
- Richardson, K., Langridge, D., Dixit, S. M., Ruotolo, B. T. An improved calibration approach for traveling wave ion mobility spectrometry: robust, high-precision collision cross sections. Analytical Chemistry. 93 (7), 3542-3550 (2021).
재인쇄 및 허가
JoVE'article의 텍스트 или 그림을 다시 사용하시려면 허가 살펴보기
허가 살펴보기더 많은 기사 탐색
This article has been published
Video Coming Soon
Copyright © 2025 MyJoVE Corporation. 판권 소유