需要订阅 JoVE 才能查看此. 登录或开始免费试用。
Method Article
单层石墨烯在冷冻电子显微镜网格中的应用,用于高分辨率结构测定
摘要
在低温电子显微镜(cryoEM)网格中应用支撑层可以增加颗粒密度,限制与空气-水界面的相互作用,减少光束引起的运动,并改善颗粒取向的分布。本文描述了一种用单层石墨烯涂覆冷冻电镜网格以改进冷冻样品制备的稳健方案。
摘要
在低温电子显微镜(cryoEM)中,纯化的大分子被施加到带有多孔碳箔的网格上;然后将分子吸干以除去多余的液体,并迅速冻结在大约20-100nm厚的玻璃冰层中,悬浮在大约1μm宽的箔孔上。使用低温透射电子显微镜对所得样品进行成像,并使用合适的软件进行图像处理后,可以确定近原子分辨率的结构。尽管冷冻电镜已被广泛采用,但样品制备仍然是冷冻电镜工作流程中的一个严重瓶颈,用户经常遇到与样品在悬浮玻璃冰中表现不佳相关的挑战。最近,已经开发出用单个连续石墨烯层修改冷冻电镜网格的方法,石墨烯作为支撑表面,通常增加成像区域中的颗粒密度,并可以减少颗粒与空气-水界面之间的相互作用。在这里,我们提供了将石墨烯应用于冷冻电镜网格的详细方案,并用于快速评估所得网格的相对亲水性。此外,我们还描述了一种基于电磁的方法,通过可视化石墨烯的特征衍射图来确认石墨烯的存在。最后,我们通过使用相对低浓度的纯样品快速重建Cas9复合物的2.7 Å分辨率密度图,证明了这些石墨烯载体的实用性。
引言
单颗粒低温电子显微镜 (cryoEM) 已发展成为一种广泛使用的可视化生物大分子的方法1。在直接电子检测2、3、4、数据采集5 和图像处理算法6、7、8、9、10 的进步推动下,cryoEM 现在能够产生快速增长的大分子数量的近原子分辨率3D 结构 11.此外,通过利用该方法的单分子性质,用户可以从单个样品12,13,14,15中确定多个结构,突出了使用生成的数据来理解异质结构集合16,17的前景。尽管取得了这些进展,但冷冻样本网格制备的瓶颈仍然存在。
为了通过冷冻电镜进行结构表征,生物样品应充分分散在水溶液中,然后必须通过称为玻璃化的过程快速冷冻18,19。目标是捕获悬浮在规则间隔孔上的均匀薄玻璃化冰层中的颗粒,这些孔通常被切割成一层无定形碳。这种图案化的无定形碳箔由带有铜或金支撑棒网的 TEM 网格支撑。在标准工作流程中,在应用样品之前,使用辉光放电等离子体处理使网格具有亲水性。用滤纸吸干多余的液体,使蛋白质溶液在孔上形成一层薄薄的液体膜,在浸入冷冻过程中可以很容易地玻璃化。常见的挑战包括颗粒定位到空气-水界面(AWI)和随后的变性20,21,22或采用优选取向23,24,25,颗粒粘附在碳箔上而不是迁移到孔中,以及孔内颗粒的聚集和聚集26.冰层厚度不均匀是另一个问题;由于电子散射增加,厚冰会导致显微照片中更高水平的背景噪声,而极薄的冰可以排除较大的颗粒27。
为了应对这些挑战,各种薄支撑膜已被用于涂覆网格表面,使颗粒停留在这些支撑物上,理想情况下,避免与空气-水界面的相互作用。石墨烯载体已经显示出巨大的前景,部分原因是它们的高机械强度加上它们最小的散射截面,这减少了支撑层28添加的背景信号。除了对背景噪声的贡献最小外,石墨烯还表现出显着的导电性和导热性29。石墨烯和氧化石墨烯涂层网格已被证明可以产生更高的颗粒密度、更均匀的颗粒分布30,并减少对 AWI22 的定位。此外,石墨烯提供了一个支撑面,可以进一步修改为:1)通过功能化31,32,33调节网格表面的物理化学性质;或 2) 偶联连接剂,促进目标蛋白的亲和纯化 34,35,36。
在本文中,我们修改了用单个均匀的石墨烯30 层涂覆冷冻电镜网格的现有程序。这些修改旨在最大限度地减少整个协议中的网格处理,以提高产量和可重复性。此外,我们还讨论了评估各种紫外线/臭氧处理在使网格在暴跌前具有亲水性的功效的方法。使用石墨烯涂层网格进行冷冻电镜样品制备的这一步骤至关重要,我们发现我们量化所得网格的相对亲水性的简单方法很有用。使用该方案,我们通过与向导RNA和靶DNA复合物生成催化失活的 化脓性 链球菌Cas9的高分辨率3D重建,证明了使用石墨烯包被网格进行结构测定的效用。
研究方案
1. CVD石墨烯的制备
- 如下所述制备石墨烯蚀刻溶液。
- 将 4.6 g 过硫酸铵 (APS) 溶解在 50 mL 烧杯中的 20 mL 分子级水中,形成 1 M 溶液,并用铝箔覆盖。让 APS 在继续执行步骤 1.2 时完全溶解。
- 制备一段用于甲基丙烯酸甲酯(MMA)涂层的CVD石墨烯。小心地切割一块正方形的CVD石墨烯。将方块转移到干净的培养皿中的盖玻片(50 mm x 24 mm)中,并在运输到旋涂机的过程中盖上盖子。
注意:一个 18 mm x 18 mm 的正方形应该产生 25-36 个石墨烯涂层网格。
2. 用MMA涂覆CVD石墨烯
- 将旋涂机设置设置为 60 秒高速旋,转速为 2,500 rpm。小心地将CVD石墨烯放在适当尺寸的卡盘上。
注意:理想情况下,CVD石墨烯将在所选卡盘的边缘延伸1-2毫米,以防止MMA吸入真空系统。 - 按下 Take/Absorb 按钮接合真空泵并将 CVD 石墨烯固定到卡盘上。将MMA涂抹在CVD石墨烯正方形的中心,盖上盖子,然后立即按 下开始/停止 按钮。对于 18 mm x 18 mm 见方的 CVD 石墨烯,40 μL MMA 就足够了。
- 旋转停止后,松开真空泵并用镊子小心地取回 MMA 涂层的 CVD 石墨烯。将CVD石墨烯倒置,使MMA涂层的一面朝下,并将其放回玻璃盖玻片上。
3. 石墨烯背面的等离子体蚀刻
- 将盖玻片上的CVD石墨烯转移到辉光放电器中,并使用平头镊子在25mA下辉光放电30秒。
- 将盖玻片上的CVD石墨烯放回培养皿中,并在运输到铜蚀刻区域时盖上盖子。MMA涂层将保护上部石墨烯层免受等离子体蚀刻。
4. 切割网格大小的MMA涂层CVD石墨烯方块
- 使用两对镊子支撑CVD石墨烯方块。注意 CVD 石墨烯正方形的方向,在连接到镊子时保持 MMA 面朝上 (CRITICAL)。
- 将CVD石墨烯切割成约3mm x 3mm的正方形。在此步骤中使用两组反作用镊子将 CVD 石墨烯正方形正面朝上固定并将其固定到位,并在将其与正方形的其余部分切开后保持 3 mm x 3 mm 正方形的边缘。
5. 从MMA涂层CVD石墨烯中溶解铜基板
- 小心地将每个 3 mm x 3 mm 正方形漂浮在 APS 溶液中。在释放每个方块之前与 APS 溶液的表面接触。倾斜烧杯,使每个正方形可以以浅角度放置在溶液中;这确保了正方形不会下沉。
- 用铝箔盖住烧杯,并在25°C下孵育过夜。
6. 从 APS 中去除 MMA/石墨烯薄膜
- 使用尺寸为 12 mm x 50 mm 的玻璃盖玻片,通过轻轻地将盖玻片垂直插入 APS 然后横向移动盖玻片使其毗邻浮动的 MMA/石墨烯方块,从 APS 中提取 MMA/石墨烯方块。
- 小心地取下盖玻片,并确保正方形在取下时完全粘附在盖玻片的侧面。
- 将MMA /石墨烯方块转移到装有分子级水的干净 50 mL 烧杯中 20 分钟。轻轻地将装有MMA /石墨烯方块的盖玻片垂直插入水中,并确保正方形在与水面相互作用时从盖玻片上脱落。对所有MMA/石墨烯方块重复上述步骤。
7.将石墨烯粘附在网格上
- 使用负动镊子,轻轻地将网格垂直浸入水中,碳面朝向漂浮的 MMA/石墨烯方块。与正方形接触后,小心地移除网格,并确保正方形在移除时完全粘附在栅格的碳侧。当浸没在水中时,尽量减少网格的横向移动,以防止损坏网格方块 (CRITICAL)。
- 将网格放在干净的盖玻片上,MMA /石墨烯面朝上,风干1至2分钟。使用平头镊子将盖玻片石墨烯/ MMA涂层网格转移到设置为130°C的热板上。
- 盖上玻璃培养皿的顶部,孵育20分钟。关火,冷却至室温 1 至 2 分钟。
注意:小心,因为培养皿顶部会非常热。
8.用丙酮溶解MMA
- 将整个盖玻片转移到装有 15 mL 丙酮的培养皿中。孵育 30 分钟。
- 使用干净的玻璃血清移液管,将孵育网格的丙酮转移到废物容器中。使用干净的玻璃血清移液管小心地将 15 mL 新鲜丙酮加入培养皿中。孵育 30 分钟。
- 重复这些洗涤步骤,总共进行 3 次丙酮洗涤。
9.用异丙醇去除残留的丙酮
- 丙酮洗涤 3 次后,除去丙酮并使用干净的玻璃血清移液管替换为 15 mL 异丙醇。孵育 20 分钟。
- 重复 3 次,共洗涤 4 次异丙醇。小心地从异丙醇中取出网格,然后用镊子在干净的盖玻片上风干。
注意:残留的异丙醇会使镊子难以释放网格。在从镊子中释放网格之前,在网格和干净的盖玻片之间接触可以缓解这个问题。 - 通过将带有石墨烯涂层网格的盖玻片转移到设置为100°C的加热板上10分钟来蒸发残留的有机物。冷却至室温,真空存放直至使用。
10. 石墨烯涂层网格的紫外线/臭氧处理
- 使用反作用镊子,轻轻地将网格放入紫外线/臭氧清洁剂的清洁照明区域,石墨烯涂层的一面朝上。
- 滑动关闭照明区域并打开机器。 将时间拨盘转到指定的处理时间,开始对网格进行紫外线/臭氧处理。
注意:处理持续时间是一个可调参数,过度处理可能会损坏电网。Han 等人 30 建议进行 10 分钟的紫外线/臭氧处理,我们也发现 10 分钟的处理就足够了。有关调整此治疗时间的指导,请参阅步骤 12。 - 按照Koh等人37所述的浸入步骤,直接将冷冻电镜样品浸入处理过的网格上。
注:紫外线/臭氧处理后,大气中的碳氢化合物会积聚在网格表面,并增加石墨烯表面的疏水性38,39。为避免这种情况,请立即将经过紫外线/臭氧处理的网格浸入水中。分批处理紫外线/臭氧处理网格可能是有利的,例如,紫外线/臭氧处理六个网格并立即使这六个网格下降,然后紫外线/臭氧处理第二批网格,然后下降第二批。
11. 拍摄衍射图像
- 确保显微镜在建立平行照明的情况下进行良好调整,并将最终散焦设置为-0.2μm。
- 插入荧光屏,光束完全停止。进入衍射模式可清晰地显示衍射光斑。
- 使用CCD相机采集图像,并使用图像分析软件对其进行评估。
注:石墨烯单层产生的最容易观察和识别的衍射斑点是6个斑点,对应于2.13 Å的空间频率。使用测量工具以倒数单位估计从衍射光束中心到这些衍射点之一的距离。值得注意的是 2.13 å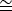 0.47 å-1。
0.47 å-1。
12. 评估网格亲水性
- 准备映像设置。找到手机支架、桌面成像表面、带摄像头的手机、玻璃盖玻片和石蜡膜。此处显示的图像是使用手机支架和桌面成像表面获得的,这些图像使用提供的 .stl 文件进行 3D 打印,从而更容易重复和量化的接触角测量(补充图 1A)。
- 将玻璃盖玻片放在平坦的表面上,然后切下 1 厘米乘 1 厘米见方的石蜡膜并将其放在玻璃盖玻片上。将手机放在手机支架上,调整手机的方向,使相机与玻璃盖玻片在平面内。使用橡皮筋将手机固定在此位置(补充图 1B)。拍摄示例照片以验证相机是否与成像表面对齐。
- 在对石墨烯涂层网格进行紫外线/臭氧处理后,将单个网格放在玻璃盖玻片上的石蜡膜正方形上。确保石墨烯的一面朝上。用移液管将 2 μL 水滴加入网格表面的中心,并立即拍照。
注意:在以下时间重复此步骤:i) 所需的紫外线/臭氧处理间隔以确定足够的处理时间;或ii)紫外线/臭氧处理后所需的时间间隔,以测量处理后网格表面保持其亲水特性的时间。 - 通过将照片导入 ImageJ43 并使用接触角插件来计算照片中的接触角。
13. dCas9复合物数据集的单颗粒分析
注意:本协议中描述的所有图像处理均使用 cryoSPARC 版本 4.2.1 执行。
- 使用“补丁运动校正”和“补丁 CTF 估计”作业对影片进行预处理。使用 Blob 拾取器作业执行颗粒拾取,使用直径范围为 115 Å 至 135 Å 的球形 Blob。
- 使用“从显微照片中提取”作业提取颗粒,使用归一化相关系数 (NCC) 和功率阈值,每张显微照片大约有 200-300 个颗粒。请注意,适当的阈值和由此产生的颗粒计数可能会有所不同,用户应检查一系列显微照片的拣选质量,以确定合适的条件。
- 使用 Ab-initio 重建作业执行多类初始重建,需要三个类。三类中的两类可能含有非Cas9颗粒,包括表面污染物。选择类似于 dCas9 的类进行进一步处理。
注意:可以应用额外的多类从头开始重建或异构细化来进一步细化粒子堆栈。 - 使用选择默认参数的“非均匀细化”作业执行 3D 细化。使用验证 (FSC) 和 ThreeDFSC 作业估计重建的分辨率,并使用最终 3D 优化中的贴图和蒙版。
结果
使用此处概述的设备(图1)和协议(图2)成功制造石墨烯涂层的冷冻电镜网格将导致覆盖箔孔的单层石墨烯,这可以通过其特征衍射图案来证实。为了促进蛋白质吸附到石墨烯表面,可以使用紫外线/臭氧处理通过安装含氧官能团来使表面具有亲水性。然而,空气中的碳氢化合物污染物可以在紫外线/臭氧处理后5分钟内吸附到石墨烯表面,并抵消这种?...
讨论
冷冻电镜样品制备涉及许多技术挑战,大多数工作流程要求研究人员极其小心地手动操作易碎的网格,以避免损坏它们。此外,任何样品对玻璃化的适应性都是不可预测的;颗粒经常与空气-水界面或覆盖网格的固体支撑箔相互作用,这可能导致颗粒采用首选方向或无法进入成像孔,除非施加非常高的蛋白质浓度24。用连续的单层石墨烯覆盖多孔的冷冻电镜网格在改善显微照片上的...
披露声明
作者没有要披露的冲突。
致谢
标本在麻省理工学院的 CryoEM 设施中制备并成像,该设施使用由 Arnold 和 Mabel Beckman 基金会获得的显微镜。接触角成像设备在麻省理工学院大都会创客空间打印。我们感谢 Nieng Yan 和 Yimo Han 的实验室,以及 MIT.nano 的工作人员在整个采用这种方法的过程中给予的支持。我们特别感谢高冠辉博士和Sarah Sterling博士的深刻讨论和反馈。这项工作得到了 NIH 资助 R01-GM144542、5T32-GM007287 和 NSF-CAREER 资助2046778的支持。戴维斯实验室的研究得到了Alfred P. Sloan基金会,James H. Ferry基金会,麻省理工学院J-Clinic和Whitehead家族的支持。
材料
| Name | Company | Catalog Number | Comments |
| 250 mL beaker (3x) | Fisher | 02-555-25B | |
| 50 mL beaker (2x) | Corning | 1000-50 | |
| Acetone | Fisher | A949-4 | |
| Aluminum foil | Fisher | 15-078-292 | |
| Ammonium persulfate | Fisher | (I17874 | |
| Coverslips 50 mm x 24 mm | Mattek | PCS-1.5-5024 | |
| CVD graphene | Graphene Supermarket | CVD-Cu-2x2 | |
| easiGlow discharger | Ted-Pella | 91000S | |
| Ethanol | Millipore-Sigma | 1.11727 | |
| Flat-tip tweezers | Fisher | 50-239-60 | |
| Glass cutter | Grainger | 21UE26 | |
| Glass petri plate and cover | VWR | 75845-544 | |
| Glass serological pipette | Fisher | 13-676-34D | |
| Grid Storage Case | EMS | 71146-02 | |
| Hot plate | Fisher | 07-770-108 | |
| Isopropanol | Sigma | W292907 | |
| Kimwipe | Fisher | 06-666 | |
| Lab scissors | Fisher | 13-806-2 | |
| Methyl-Methacrylate EL-6 | Kayaku | MMA M310006 0500L1GL | |
| Molecular grade water | Corning | 46-000-CM | |
| Negative action tweezers (2x) | Fisher | 50-242-78 | |
| P20 pipette | Rainin | 17014392 | |
| P200 pipette | Rainin | 17008652 | |
| Parafilm | Fisher | 13-374-12 | |
| Pipette tips | Rainin | 30389291 | |
| Quantifoil grids with holey carbon | EMS | Q2100CR1 | |
| Spin coater | SetCas | KW-4A | with chuck SCA-19-23 |
| Straightedge | ULINE | H-6560 | |
| Thermometer | Grainger | 3LRD1 | |
| UV/Ozone cleaner | BioForce | SKU: PC440 | |
| Vacuum desiccator | Thomas Scientific | 1159X11 | |
| Whatman paper | VWR | 28297-216 |
参考文献
- Chua, E. Y. D., et al. cheaper: Recent advances in cryo-electron microscopy. Annu Rev Biochem. 91, 1-32 (2022).
- Bai, X. C., Fernandez, I. S., McMullan, G., Scheres, S. H. Ribosome structures to near-atomic resolution from thirty thousand cryo-EM particles. Elife. 2, 00461 (2013).
- Li, X., et al. Electron counting and beam-induced motion correction enable near-atomic-resolution single-particle cryo-EM. Nat Methods. 10 (6), 584-590 (2013).
- Campbell, M. G., et al. Movies of ice-embedded particles enhance resolution in electron cryo-microscopy. Structure. 20 (11), 1823-1828 (2012).
- Cheng, A., et al. Leginon: New features and applications. Protein Sci. 30 (1), 136-150 (2021).
- Scheres, S. H. RELION: implementation of a Bayesian approach to cryo-EM structure determination. J Struct Biol. 180 (3), 519-530 (2012).
- Punjani, A., Rubinstein, J. L., Fleet, D. J., Brubaker, M. A. cryoSPARC: algorithms for rapid unsupervised cryo-EM structure determination. Nat Methods. 14 (3), 290-296 (2017).
- Tegunov, D., Cramer, P. Real-time cryo-electron microscopy data preprocessing with Warp. Nat Methods. 16 (11), 1146-1152 (2019).
- Grant, T., Rohou, A., Grigorieff, N. cisTEM, user-friendly software for single-particle image processing. Elife. 7, 35383 (2018).
- Bell, J. M., Chen, M., Baldwin, P. R., Ludtke, S. J. High resolution single particle refinement in EMAN2.1. Methods. 100, 25-34 (2016).
- Cheng, Y. Single-particle cryo-EM-How did it get here and where will it go. Science. 361 (6405), 876-880 (2018).
- Kinman, L. F., Powell, B., Zhong, E., Berger, B., Davis, J. H. Uncovering structural ensembles from single particle cryo-EM data using cryoDRGN. Nat Protoc. 18 (2), 319-339 (2022).
- Zhong, E. D., Bepler, T., Berger, B., Davis, J. H. CryoDRGN: reconstruction of heterogeneous cryo-EM structures using neural networks. Nat Methods. 18 (2), 176-185 (2021).
- Chen, M., Ludtke, S. J. Deep learning-based mixed-dimensional Gaussian mixture model for characterizing variability in cryo-EM. Nat Methods. 18 (8), 930-936 (2021).
- Punjani, A., Fleet, D. J. 3D variability analysis: Resolving continuous flexibility and discrete heterogeneity from single particle cryo-EM. J Struct Biol. 213 (2), 107702 (2021).
- Dashti, A., et al. Retrieving functional pathways of biomolecules from single-particle snapshots. Nat Commun. 11 (1), 4734 (2020).
- Sun, J., Kinman, L. F., Jahagirdar, D., Ortega, J., Davis, J. H. KsgA facilitates ribosomal small subunit maturation by proofreading a key structural lesion. Nat Struct Mol Biol. , (2023).
- Dubochet, J., Chang, J. J., Freeman, R., Lepault, J., McDowall, A. W. Frozen aqueous suspensions. Ultramicroscopy. 10 (1-2), 55-61 (1982).
- Dubochet, J. Cryo-EM--the first thirty years. J Microsc. 245 (3), 221-224 (2012).
- Glaeser, R. M., et al. Factors that influence the formation and stability of thin, cryo-EM specimens. Biophys J. 110 (4), 749-755 (2016).
- Glaeser, R. M. Proteins, interfaces, and cryo-Em grids. Curr Opin Colloid Interface Sci. 34, 1-8 (2018).
- D'Imprima, E., et al. Protein denaturation at the air-water interface and how to prevent it. Elife. 8, 42747 (2019).
- Tan, Y. Z., et al. Addressing preferred specimen orientation in single-particle cryo-EM through tilting. Nat Methods. 14 (8), 793-796 (2017).
- Chen, J., Noble, A. J., Kang, J. Y., Darst, S. A. Eliminating effects of particle adsorption to the air/water interface in single-particle cryo-electron microscopy: Bacterial RNA polymerase and CHAPSO. J Struct Biol X. 1, 100005 (2019).
- Noble, A. J., et al. Reducing effects of particle adsorption to the air-water interface in cryo-EM. Nat Methods. 15 (10), 793-795 (2018).
- Drulyte, I., et al. Approaches to altering particle distributions in cryo-electron microscopy sample preparation. Acta Crystallogr D Struct Biol. 74, 560-571 (2018).
- Neselu, K., et al. Measuring the effects of ice thickness on resolution in single particle cryo-EM. J Struct Biol X. 7, 100085 (2023).
- Pantelic, R. S., et al. Graphene: Substrate preparation and introduction. J Struct Biol. 174 (1), 234-238 (2011).
- Geim, A. K., Novoselov, K. S. The rise of graphene. Nat Mater. 6 (3), 183-191 (2007).
- Han, Y., et al. High-yield monolayer graphene grids for near-atomic resolution cryoelectron microscopy. Proc Natl Acad Sci U S A. 117 (2), 1009-1014 (2020).
- Fujita, J., et al. Epoxidized graphene grid for highly efficient high-resolution cryoEM structural analysis. Sci Rep. 13 (1), 2279 (2023).
- Lu, Y., et al. Functionalized graphene grids with various charges for single-particle cryo-EM. Nat Commun. 13 (1), 6718 (2022).
- Naydenova, K., Peet, M. J., Russo, C. J. Multifunctional graphene supports for electron cryomicroscopy. Proc Natl Acad Sci U S A. 116 (24), 11718-11724 (2019).
- Liu, N., et al. Bioactive functionalized monolayer graphene for high-resolution cryo-electron microscopy. J Am Chem Soc. 141 (9), 4016-4025 (2019).
- Benjamin, C. J., et al. Selective capture of histidine-tagged proteins from cell lysates using TEM grids modified with NTA-graphene oxide. Sci Rep. 6, 32500 (2016).
- Wang, F., et al. General and robust covalently linked graphene oxide affinity grids for high-resolution cryo-EM. Proc Natl Acad Sci U S A. 117 (39), 24269-24273 (2020).
- Koh, A., et al. Routine Collection of High-Resolution cryo-EM Datasets Using 200 KV Transmission Electron Microscope. J Vis Exp. (181), (2022).
- Schweizer, P., et al. Mechanical cleaning of graphene using in situ electron microscopy. Nat Commun. 11 (1), 1743 (2020).
- Li, Z., et al. Effect of airborne contaminants on the wettability of supported graphene and graphite. Nat Mater. 12 (10), 925-931 (2013).
- Jinek, M., et al. A programmable dual-RNA-guided DNA endonuclease in adaptive bacterial immunity. Science. 337 (6096), 816-821 (2012).
- Zhu, X., et al. Cryo-EM structures reveal coordinated domain motions that govern DNA cleavage by Cas9. Nat Struct Mol Biol. 26 (8), 679-685 (2019).
- Croll, T. I. ISOLDE: a physically realistic environment for model building into low-resolution electron-density maps. Acta Crystallogr D Struct Biol. 74, 519-530 (2018).
- Schneider, C. A., Rasband, W. S., Eliceiri, K. W. NIH Image to ImageJ: 25 years of image analysis. Nat Methods. 9 (7), 671-675 (2012).
- Prydatko, A. V., Belyaeva, L. A., Jiang, L., Lima, L. M. C., Schneider, G. F. Contact angle measurement of free-standing square-millimeter single-layer graphene. Nat Commun. 9 (1), 4185 (2018).
转载和许可
请求许可使用此 JoVE 文章的文本或图形
请求许可探索更多文章
This article has been published
Video Coming Soon
版权所属 © 2025 MyJoVE 公司版权所有,本公司不涉及任何医疗业务和医疗服务。