JoVE 비디오를 활용하시려면 도서관을 통한 기관 구독이 필요합니다. 전체 비디오를 보시려면 로그인하거나 무료 트라이얼을 시작하세요.
Method Article
Single-Copy Gene Locus Chromatin Purification in Saccharomyces cerevisiae (맥주효모균의 단일 복제 유전자 자리, 염색질 정제)
요약
이 프로토콜은 신진 효모인 맥주효모균(Saccharomyces cerevisiae)에서 네이티브 염색질 맥락에서 관심 있는 단일 복제 유전자 자리를 정제하기 위해 부위 특이적 재조합을 기반으로 하는 유전자좌 특이적 염색질 분리 방법을 제시합니다.
초록
진핵 염색질의 기본 조직 단위는 뉴클레오솜 코어 입자 (NCP)이며, 이는 히스톤 옥타머 주위에 ~ 1.7 배 감싼 DNA로 구성됩니다. 크로마틴은 NCP와 전사 인자, 염색질 리모델링 및 변형 효소를 포함한 수많은 다른 단백질 복합체의 실체로 정의됩니다. 이러한 단백질-DNA 상호 작용이 세포주기의 여러 단계에서 특정 게놈 위치 수준에서 어떻게 조정되는지는 아직 불분명합니다. 이는 주로 현재의 기술적 한계로 인해 이러한 동적 상호 작용의 정확한 측정값을 얻기가 어렵기 때문입니다. 여기서는 부위 특이적 재조합과 효율적인 단일 단계 친화성 정제 프로토콜을 결합하여 네이티브 염색질 상태에서 단일 복제 관심 유전자 자리를 분리하는 개선된 방법을 설명합니다. 이 방법은 게놈 크로마틴에 대한 표적 자리의 강력한 농축을 허용하므로 이 기술은 질량 분석법과 같은 편향되지 않고 체계적인 방식으로 단백질 상호 작용을 식별하고 정량화하기 위한 효과적인 전략이 됩니다. 이러한 조성 분석에 더하여, 이 방법에 의해 정제된 천연 염색질은 뉴클레오솜 위치 지정 및 히스톤 변형에 관한 생체 내 상황을 반영할 가능성이 높으며, 따라서 효모의 거의 모든 게놈 유전자좌에서 유래한 염색질의 추가 구조 및 생화학적 분석에 적합합니다.
서문
진핵생물 게놈을 염색질로 역동적으로 조직하면 DNA가 핵의 한계 내에 맞도록 압축되는 동시에 유전자 발현을 위한 충분한 역학과 조절 인자에 대한 접근성을 보장합니다. 부분적으로, 이 다재다능함은 히스톤 옥타머1 주위에 ~1.7배 감싼 DNA의 147 bp를 가진 핵심 입자를 포함하는 염색질의 기본 단위인 뉴클레오솜에 의해 매개됩니다. 뉴클레오솜은 N- 및 C-말단 히스톤 꼬리에 수많은 히스톤 변이체와 번역 후 변형(PTM)이 있는 구성과 관련하여 매우 역동적인 구조입니다. 또한 진핵 염색질은 전사 인자, DNA 및 RNA 처리 기계, 건축 단백질, 염색질 리모델링 및 변형에 관여하는 효소, 염색질과 관련된 RNA 분자와 같은 다양한 다른 필수 구성 요소와 상호 작용합니다. 전사, 복제 및 복구와 관련된 이러한 중요한 기계는 모두 이러한 과정의 천연 기질 역할을 하는 크로마틴에 대한 접근이 필요합니다. 결과적으로, 이러한 DNA 거래의 기초가 되는 분자 메커니즘을 이해하려면 이러한 기계가 수렴하고 생물학적 반응을 촉진하는 특정 게놈 영역에서 염색질 구조의 집합적 변화를 정확하게 정의해야 합니다.
유전학 및 단백질-단백질 상호 작용 연구를 통해 수많은 염색질 인자를 식별했음에도 불구하고 특정 게놈 부위에서 염색질 상호 작용에 대한 직접적이고 편향되지 않은 포괄적인 분석을 수행하는 것은 중요한 장애물로 남아 있습니다 2,3. 초기에는 게놈의 매우 풍부한 영역(즉, 반복적 유전자좌) 또는 다중 복제 플라스미드만 관련 단백질 4,5,6,7의 질량 분석 식별을 위해 충분한 양과 순도로 분리할 수 있었습니다. 크로마틴화된 DNA에 대한 포획 프로브의 직접 하이브리드화, CRISPR-dCas9 시스템을 사용한 근접 비오틴화 또는 염기서열 특이적 어댑터 단백질을 관심 유전자좌에 결합하는 것을 기반으로 하는 일련의 새로운 접근 방식은 효모 및 포유류 게놈 8,9,10에서 단일 복제 유전자좌의 단백질체를 풀기 시작했습니다. 그러나 이러한 모든 방법은 단백질-DNA 상호 작용을 안정화하기 위해 포름 알데히드 교차 결합과 후속 정제를 위해 염색질을 용해시키기 위해 초음파 처리가 필요합니다. 두 조작 모두 정제된 크로마틴의 후속 구조적 및 기능적 연구 가능성을 배제합니다.
이러한 한계를 극복하기 위해 우리는 이전에 효모11,12에서 표적 염색체 도메인을 추출하기 위해 부위 특이적 재조합을 사용하는 방법론을 고안했습니다. 본질적으로, 관심의 게놈 영역은 Zygosaccharomyces rouxi의 부위 특이적 R-재조합효소에 대한 인식 부위(RS)로 둘러싸여 있으며, 동시에 동일한 영역 내에서 원핵생물 전사 억제제 LexA 단백질(LexA)에 대한 3개의 DNA 결합 부위 그룹을 통합합니다. 효모 세포에는 R-재조합효소의 동시 발현을 위한 발현 카세트와 탠덤 친화성 정제(TAP) 태그에 융합된 LexA 단백질이 포함되어 있습니다. R-재조합효소의 유도 후, 효소는 원형 염색질 도메인의 형태로 염색체에서 표적 영역을 효율적으로 절제합니다. 이 도메인은 LexA DNA 결합 부위와 친화성 지지체에 결합하는 LexA-TAP 어댑터 단백질을 통해 정제할 수 있습니다. 이 방법은 효모 염색체 III13의 선택된 복제 기원을 포함하는 뚜렷한 염색질 도메인을 분리하는 데 최근에 사용되었습니다.
이 생체 외 접근법의 주요 장점 중 하나는 분리된 물질의 기능적 분석이 가능하다는 것입니다. 예를 들어, 이 방법으로 정제된 복제 기원 도메인은 in vitro 복제 분석을 통해 native in vivo 조립 염색질 템플릿으로부터 시험관에서 기원 발화의 효율성을 평가할 수 있습니다. 궁극적으로, 분리된 물질의 생화학적 및 기능적 특성화는 천연 염색질 주형과 함께 정제된 단백질을 사용하여 핵 공정의 재구성을 허용할 수 있습니다. 요약하면, 이 방법론은 특정 염색체 거래를 겪는 특정 게놈 영역의 집합적 구성 및 구조적 염색질 변화를 추적할 수 있기 때문에 염색질 연구에서 흥미로운 길을 열어줍니다.
프로토콜
이 프로토콜에 사용된 모든 재료 및 도구와 관련된 자세한 내용은 재료 표를 참조하십시오. 표 1 에서 사용된 솔루션, 버퍼 및 매체 목록을 참조하십시오.
1. 재조합 효모 균주 구성
- 재조합 적격 효모 균주를 구축하기 위해, SbfI-소화된 플라스미드 K238을 관심 유전자좌(13,14)에 통합된 LexA-결합 부위 및 RS 재조합 부위를 갖는 효모 균주로 형질전환시킨다.
참고: 형질전환된 SbfI 제한 단편에는 상동 재조합에 의한 발현 카세트의 게놈 통합을 위한 효모 염색체 I의 상동 서열과 함께 LexA-TAP 융합 단백질 및 R-재조합효소의 구성적 발현에 필요한 발현 카세트가 포함되어 있습니다(그림 1). - 대조군 균주를 구성하기 위해서는 통합 RS 및 LexA 결합 부위가 없는 동종 효모 균주를 재조합 가능 균주에 사용된 것과 동일한 조건에서 SbfI 분해 K238 플라스미드로 형질전환시킵니다.
- SCD-LEU 한천 플레이트14의 LEU2 선택 마커를 기반으로 유능한 효모 세포를 선택합니다.
2. IgG 항체를 에폭시 활성 마그네틱 비드에 연결
참고: IgG 항체를 다음 발표된 프로토콜11에 따라 에폭시 활성화 마그네틱 비드에 결합합니다.
- 50mL 원뿔형 튜브에 10mL의 50% 아세톤(300mg은 ~5.1 ×10 10 개의 비드에 해당)에 300mg의 에폭시 활성화 비드를 현탁시킵니다. 소용돌이 믹서에서 세게 흔듭니다.
- 비드가 들어 있는 튜브를 820× g 및 4°C에서 2분 동안 원심분리합니다. 상층액을 제거합니다.
- 0.1M 인산나트륨 완충액(pH 7.4) 20mL로 비드를 3회 세척합니다. 2.2단계에서 설명한 대로 원심분리를 통해 각 세척 단계 후에 상층액을 제거합니다.
- 0.1M 인산나트륨 완충액(pH 7.4) 16mL에 비드를 현탁시키고 교잡 오븐에서 실온에서 5분 동안 부드럽게 회전시킵니다.
- 토끼 IgG(100mg)를 7mL의dH2O(최종 농도: 14mg/mL)에 녹입니다.
- IgG 현탁액을 13,000× g 및 4°C에서 10분 동안 원심분리하여 현탁액을 정화합니다.
- 상청액 3.5mL(토끼 IgG 50mg에 해당)를 새 50mL 원뿔형 튜브에 옮깁니다.
- IgG 용액을 0.1M 인산나트륨 완충액(pH 7.4) 9.85mL로 희석한 다음 부드럽게 혼합하여 0.1M 인산나트륨(pH 7.4)에 3M 황산암모늄 6.65mL를 적가합니다.
알림: 염의 국소 농도가 높으면 토끼 IgG가 침전되므로 황산암모늄을 용액에 빠르게 첨가하지 마십시오. - IgG 용액을 820× g 및 4°C에서 3분 동안 원심분리하고 생성된 상층액을 마그네틱 비드 현탁액에 추가합니다.
- 튜브를 하룻밤 동안 또는 30°C에서 최소 18시간 동안 교잡 오븐에서 부드럽게 회전하여 배양합니다.
- 2.2단계에서 설명한 대로 상층액을 제거합니다.
- 20mL의 100mM 글리신-HCl(pH 2.5)로 비드를 세척합니다. IgG 폴리펩티드의 변성을 피하기 위해 단계 2.2에 설명된 대로 용액을 빠르게 제거합니다.
- 20mL 10mM Tris-HCl (pH 8.8)로 비드를 한 번 씻으십시오. 2.2단계에서 설명한 대로 상층액을 흡인합니다.
- 0.1M 트리에틸아민 용액 20mL를 5-10분 동안 부드럽게 회전하여 잔류 반응성 에폭시기 비활성화합니다. 2.2단계에서 설명한 대로 상층액을 제거합니다.
- 20mL의 PBS(pH 7.4)로 비드를 4번 세척하고 부드럽게 회전하여 5분 동안 세척합니다. 각 세척 단계 후 2.2단계에서 설명한 대로 상층액을 제거합니다.
- 0.5% Triton X-100(w/v)으로 20mL의 PBS(pH 7.4)로 비드를 2회 세척하고 교잡 오븐에서 각각 5분, 15분 동안 부드럽게 회전시킵니다. 2.2단계에서 설명한 대로 상층액을 제거합니다.
- 0.02% 아지드화나트륨(w/v)과 함께 16mL의 PBS(pH 7.4)의 최종 부피에 비드를 현탁시킵니다. 사용할 때까지 4°C에서 1mL 부분 표본으로 보관하십시오.
3. 효모 세포 배양 및 수확
- YPD 플레이트의 제어 및 재조합 효모 균주를 5mL의 YPR 배지에 접종하고 30°C 및 200rpm에서 밤새 배양합니다.
- 이 배양액 2mL를 YPR 배지 100mL에 접종하고 30°C 및 200rpm에서 밤새 배양합니다.
- 각 균주에 대해 1,800mL의 오토클레이브 YP 배지와 200mL의 오토클레이브 라피노스 용액(20% w/v)을 2개의 5L 삼각 플라스크(각 균주에 대해 총 4L의 배양 배지, 2개의 플라스크로 나뉜)에 각각 분주합니다.
- 성장하는 효모 세포를 각각의 배지에 OD600 0.2로 접종하고, 약 6시간 동안 또는 세포가 원하는 OD600 1.0에 도달할 때까지 단계 3.1에 설명된 대로 배양합니다. 오염이 없는 세포의 정상적인 성장을 보장하려면 2시간 간격으로 OD를 확인하십시오.
- 200mL의 갈락토오스(20% w/v)를 추가하여 부위 특이적 재조합을 유도합니다.
- 110μL(50ng/mL)의 YMFA(갈락토오스와 동시, 3.5단계)를 첨가하여 G1 단계의 세포를 포획하고 2시간 동안 배양합니다.
참고: 세포에 YMFA를 추가하는 것은 실험 조건과 해결해야 할 생물학적 질문에 따라 다릅니다. 정확하게는, 이 실험을 위해, 세포는 허가된 복제 기원을 가진 균질한 세포 집단을 얻기 위해 G1 단계에서 체포된다; 이 과정에서, pre-replicative 복합체는 S-phase에서 DNA 복제가 시작되기 전에 G1 phase의 기원에 결합합니다. - 셀 현탁액을 1L 원심분리기 버킷으로 옮기고 6,000× g 및 4°C에서 10분 동안 원심분리합니다. 상층액을 버리고, 세포 펠릿을 총 10-15 mL의dH2O로 재현탁시킨다.
- 루어 플러그로 25mL 주사기를 밀봉하고 물을 채운 50mL 원뿔형 튜브 안에 넣습니다. 셀 현탁액을 주사기 어셈블리로 옮기고 실온에서 10분 동안 2,397× g 으로 원심분리합니다. 상층액을 버리십시오.
- 주사기에서 루어 플러그를 제거하고 세포를 액체 질소로 압출하여 세포 "스파게티"를 형성합니다.
참고: 4L의 배양 배지를 사용하면 7-10g의 최종 세포 펠릿의 습윤 중량을 얻을 수 있습니다. - 냉동 셀 스파게티를 50mL 원뿔형 튜브에 옮기고 더 사용할 때까지 -80°C에서 보관합니다.
4. 염색질 궤적 정화
참고: 그림 2 에서 이 유전자좌 특이적 크로마틴 정제 프로토콜과 관련된 단계에 대한 개략적인 개요를 볼 수 있습니다.
- 매번 30초 동안 커피 그라인더를 2번 세게 흔들어 드라이아이스 50-30g을 갈아서 상업용 커피 그라인더를 식힙니다. 식으면 드라이아이스 가루를 버리십시오.
- 냉동 효모 세포 스파게티 3g과 사전 냉각된 커피 그라인더에 ~30-50g의 드라이아이스를 섞습니다.
- 캡과 그라인더 사이의 접합부를 파라필름으로 밀봉하여 밀링 중 효모 세포 분말의 손실을 방지합니다.
- 효모 셀 드라이 아이스 믹스를 매번 30 초 동안 10 회 분쇄하고 각 라운드 사이에 30 초 간격으로 분쇄합니다 (총 시간 예상 : ~ 10 분). 드라이아이스와 셀 파우더가 커피 그라인더 벽에 달라붙는 것을 방지하려면 분쇄하는 동안 커피 그라인더의 측면을 계속 두드리십시오.
- 생성된 효모 세포 드라이아이스 분말을 깨끗하고 건조한 주걱을 사용하여 플라스틱 비커에 옮깁니다.
- 드라이아이스를 증발시키기 위해 비커를 실온에 보관하십시오.
- 드라이아이스가 증발하면 1x 프로테아제 및 인산가수분해효소 억제제(효모 세포 750μL/g)가 포함된 MB 완충액 2.25mL를 효모 세포 분말에 추가합니다.
- 세포-완충액 혼합물을 세게 피펫팅하여 완충액으로 세포가 완전히 현탁되도록 하고 15mL 코니컬 튜브로 옮깁니다.
- 생성된 세포 현탁액(조세포 추출물[CCE])에서 DNA(0.1%) 및 단백질(0.05%) 분석을 위한 샘플을 채취합니다. 추가 처리가 될 때까지 -20°C에서 보관하십시오(섹션 7 참조).
- 세포 현탁액을 결합이 낮은 2mL 반응 튜브로 옮기고 4°C에서 30분 동안 21,130× g 으로 원심분리하여 조세포 용해물에서 세포 파편을 분리합니다.
- 모든 튜브의 상층액을 하나의 15mL 코니컬 튜브에 모읍니다.
- DNA(0.1%) 및 단백질 분석(0.05%)을 위해 상층액(입력[IN])에서 샘플을 채취합니다. 추가 처리가 될 때까지 -20°C에서 보관하십시오(섹션 7 참조).
- 20rpm으로 회전할 때 4°C에서 각각 5분 동안 1x 프로테아제 및 인산가수분해효소 억제제가 포함된 500μL의 차가운 MB 버퍼로 2x 세척하여 500μL의 IgG 결합 마그네틱 비드 슬러리(각 효모 균주)를 평형화합니다. 각 세척 단계 후에 마그네틱 랙을 사용하여 비드에서 상청액을 버리십시오.
- IgG 결합 마그네틱 비드를 500μL의 차가운 MB 완충액에 1x 프로테아제 및 인산가수분해효소 억제제를 넣고 20rpm으로 회전하면서 4°C에서 1시간 동안 배양합니다. 마그네틱 랙을 사용하여 비드에서 상층액을 버립니다.
- 평형 마그네틱 비드 슬러리를 세포 용해물과 혼합하고 4°C에서 2시간 동안 20rpm으로 회전하여 배양합니다.
- 완전한 마그네틱 비드 셀 용해물 현탁액을 결합이 낮은 반응 튜브로 옮깁니다.
- 이제 관심 염색질 고리를 운반하는 마그네틱 비드를 마그네틱 랙을 사용하여 세포 용해물에서 분리합니다.
- 각 튜브의 나머지 플로우 스루(FT)를 새로운 15mL 코니컬 튜브로 옮기고 DNA(0.1%) 및 단백질(0.05%) 분석을 위한 샘플을 채취합니다. 추가 처리가 될 때까지 -20°C에서 보관하십시오(섹션 7 참조).
- 각 튜브의 마그네틱 비드를 300μL의 차가운 MB 버퍼에 매달고 비드를 하나의 반응 튜브에 모읍니다. 750μL의 차가운 MB 완충액과 1x 프로테아제 및 인산가수분해효소 억제제를 각각 10분 동안 4°C에서 20rpm으로 회전하여 5회 세척합니다. 프로테아제 및 인산가수분해효소 억제제 없이 750μL의 저온 MB 완충액으로 최종 세척을 수행합니다.
- 프로테아제 및 인산가수분해효소 억제제 없이 40μL의 차가운 MB 완충액에 비드를 현탁시킵니다.
참고: 용리액의 최종 부피는 예상되는 다운스트림 응용 분야에 따라 조정할 수 있습니다. TEV 용리는 일반적으로 100-300 μL 범위 내에서 효율적으로 작동합니다.
5. TEV 프로테아제 매개 용출
- 비드에서 LexA-CBP 크로마틴 고리 복합체를 방출하려면 열혼합기에서 4°C 및 450rpm에서 밤새 2μL의 6x His-태그 재조합 TEV 프로테아제로 비드를 배양합니다.
- 마그네틱 랙을 사용하여 최종 용리액에서 비드를 분리합니다. 절단된 크로마틴 링이 포함된 용리액을 새로운 1.5mL 반응 튜브로 옮깁니다.
- 튜브를 마그네틱 랙에 다시 보관하여 최종 용리액에서 잔류 비드를 분리합니다.
- 750μL의 저온 AC 버퍼에 비드(TB)를 재현탁시키고 DNA(0.1%) 및 단백질(0.05%) 분석을 위해 샘플을 채취합니다. 추가 처리가 될 때까지 -20°C에서 보관하십시오(섹션 7 참조).
- 최종 용리액(TE)에서 DNA(0.5%) 및 단백질(0.25%) 분석을 위한 샘플을 채취합니다. 추가 처리가 될 때까지 -20°C에서 보관하십시오(섹션 7 참조).
참고: 최종 용리액의 부피가 적기 때문에 DNA 및 단백질 분석을 위해 수집된 샘플의 비율이 증가하여 분석 중에 단백질 및 DNA 함량을 더 잘 표현할 수 있습니다.
6. 변성 용출
- 비드를 750μL의 차가운 AC 버퍼에서 20분 동안 20분 동안 세척합니다.
- 나머지 결합 LexA-크로마틴 복합체를 추출하기 위해 비드에 500μL의 0.5MNH4OH를 첨가하여 변성 용출을 수행하고 실온에서 30분 동안 배양합니다.
- 마그네틱 랙을 사용하여 현탁액에서 비드를 분리하고 용리액을 결합이 적은 반응 튜브로 옮깁니다.
- 6.2단계에서와 같이 비드를 다시 배양하여 용리액의 최대 염색질 위치를 회수합니다.
- 마그네틱 랙을 사용하여 현탁액에서 비드를 분리하고 생성된 용리액을 6.3단계의 용리액이 들어 있는 동일한 튜브에 합칩니다.
- 750μL의 dH2O에 비드(DB)를 재현탁시키고 DNA(0.1%) 및 단백질(0.05%) 분석을 위해 샘플을 채취합니다.
- 최종 용리액(DE)에서 DNA(0.5%) 및 단백질(0.25%) 분석을 위한 샘플을 채취합니다.
7. DNA 및 단백질 분석
- DNA 분석
- 시료 전처리
- DNA 샘플에 100μL의 IRN 완충액을 추가하고 dH2O로 부피를 최종 부피 200μL로 증가시킵니다.
- K071 스파이크인 플라스미드 DNA 1ng을 추가합니다.
- 1μL의 RNAse A(10mg/mL)를 추가하고 37°C에서 1시간 동안 배양합니다.
- 5μL의 proteinase K(10mg/mL)와 10μL의 SDS(20%)를 추가하고 56°C에서 1시간 동안 배양합니다.
- 페놀/클로로포름/이소프로필 알코올 200μL(25:24:1)를 넣고 매번 10초 동안 2번 완전히 소용돌이칩니다.
- 샘플을 21,130× g 에서 7분 동안 원심분리하여 유기상과 수용상을 분리합니다.
- 1.5μL의 글리코겐(5mg/mL)과 2.5x 100% 에탄올이 들어 있는 새 1.5mL 튜브에 상층액을 옮깁니다.
- -20°C에서 최소 2시간, 최대 하룻밤 동안 튜브를 배양하여 DNA를 침전시킵니다.
- 21,130 × g, 4 °C에서 45분 동안 원심분리기 상층액을 버리십시오.
- DNA 펠릿을 재현탁하지 않고 150μL의 70% 에탄올을 첨가하고 4°C에서 21,130× g 에서 10분 동안 다시 원심분리합니다.
- DNA 펠릿을 실온에서 10-15분 동안 건조시키고 40μL의 dH2O에 재현탁시킵니다.
- HpaI 제한 엔도뉴클레아제로 단계 7.1.1.11에서 분리한 DNA를 선형화하기 위해 제한 효소 분해를 수행합니다. 50 μL 반응 혼합물의 경우, 40 μL의 분리된 DNA + 2 μL의 HpaI 효소 + 5 μL의 제한 효소 완충액 + 3 μL의 dH2O를 37°C에서 밤새 배양합니다.
- qPCR 분석
- 제한-소화된 DNA를 1:5 비율로 희석한다(40 μL의dH2O에서 단계 7.1.1.12로부터 수득한 제한-소화된 DNA의 10 μL).
- ARS316 영역, PDC1 및 spike-in plasmid DNA를 위해 설계된 primer pair를 사용합니다.
- 표 2에 제공된 프로그램을 사용하여 qPCR을 실행합니다.
- ARS316 영역과 스파이크인 플라스미드 DNA를 타겟으로 사용하고 PDC1(또는 다른 유전자 또는 게놈 영역)을 참조 유전자좌로 사용하여 상대 정량화로 qPCR 결과를 분석합니다.
- ARS316 및 PDC1 프라이머 상대 정량화 값을 각 샘플에 대해 취한 분획 부피의 백분율로 정규화하여 PDC1에 대한 ARS316 유전자좌 회수율을 평가합니다. 예를 들어, 플로우 스루에 대해 0.1%에 1,000을 곱하고 TEV 용리액에 대해 0.5%에 200을 곱합니다.
- ARS316 및 PDC1 회수율을 스파이크인 플라스미드 DNA 상대 정량 값으로 정규화합니다.
- 방정식 (1)을 사용하여 얻은 상대 정량 목표/참조 값을 평가하여 총 염색질에 대한 ARS316 유전자좌의 농축을 평가합니다.
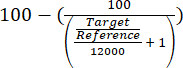 (1)
(1)
- 서던 블롯 분석
- 20μL의 제한 효소 분해 DNA 샘플에 5μL의 겔 로딩 염료를 추가합니다.
- 샘플을 1% 아가로스 겔에서 110V에서 ~3시간 동안 실행합니다.
- 젤을 트레이에 옮기고 20분 동안 부드럽게 흔들면서 디퓨리네이션 용액에 담그십시오.
- 젤을 dH2O로 헹구고 변성 용액에 15분 동안 흔들면서 담그십시오. 변성 용액을 버리십시오.
- 젤을 변성 용액에 15분 동안 담그고 부드럽게 흔듭니다.
- 젤을 dH2O로 헹구고 부드럽게 흔들면서 전사 버퍼로 매번 15분 동안 2번 세척합니다.
- 트레이에 1-1.5L의 전사 버퍼를 채우고 안정적인 플랫폼에 놓습니다.
- 긴 Whatman 종이를 잘라 종이의 양쪽 끝이 전사 버퍼에 적시도록 플랫폼에 놓습니다.
- 포지티브 나일론 멤브레인 한 스트립과 젤 크기와 동일한 Whatman 종이 스트립 4개를 자릅니다.
- 전송 버퍼에 적신 Whatman 용지 두 장을 플랫폼의 놓습니다.
- Whatman 종이 조각 위에 젤을 뒤집어 놓습니다.
- 젤 위에 양극 나일론 멤브레인을 놓고 전사 완충액에 적신 나머지 두 장의 Whatman 종이를 놓습니다. 전송 버퍼로 스택을 젖은 상태로 유지해야 합니다.
- 유리 막대를 사용하여 갇힌 기포를 굴려 제거하십시오.
- 조립된 더미 위에 종이 타월 더미를 놓고 0.5kg의 물체(예: 유리병)를 놓습니다.
- 실온에서 하룻밤 동안 이송할 수 있도록 어셈블리를 그대로 두십시오.
- 이송 후 총 에너지 출력 1,200J/cm2로 멤브레인을 UV 가교합니다.
- ARS316 유전자좌 검출을 위해 참조된 DNA 라벨링 시스템을 사용하여 합성된 방사성 프로브를 사용하여 서던 블롯 하이브리드화를 수행합니다.
알림: 달리 언급되지 않는 한 얼음 위에서 이후의 모든 단계를 수행하십시오. - 저결합 반응 튜브에서 25-40ng의 PCR 단편(프로브)을 19μL의dH2O에 희석하고 95°C에서 5분 동안 배양합니다. 얼음 위에서 즉시 식히십시오.
- 튜브에 500μM dCTP, 500μM dGTP 및 500μM dTTP를 각각 1μL씩 추가합니다.
- 키트와 함께 제공된 무작위 뉴클레오티드 헥사머를 포함하는 완충액 20μL를 추가합니다.
- 방사성 표지된 뉴클레오티드[α-32P] dATP 5μL를 튜브에 추가합니다. 방사능 승인 보호 환경에서 방사능 표지 물질과 관련된 모든 단계를 수행하십시오.
- 1 μL의 Klenow 단편을 첨가하고 단일 가닥 DNA 합성을 위해 37°C에서 열혼합기에서 15분 동안 배양합니다.
- 5μL의 정지 완충액을 추가하여 반응을 중지합니다.
- 크기 배제 컬럼을 1,500× g 에서 2분 동안 원심분리하여 스토리지 버퍼를 제거합니다. 흐름을 버리고 컬럼을 새 튜브에 넣습니다.
- 프로브 혼합물을 컬럼에 통과시켜 통합되지 않은 방사성 뉴클레오티드를 제거합니다. 프로브를 수집하기 위해 1,500× g 에서 30초 동안 원심분리기.
- 150μL의 연어 정자 DNA(1:100)를 추가하여 프로브와 멤브레인의 비특이적 결합을 차단합니다.
- 프로브 혼합물을 95°C에서 5분 동안 배양하여 이중 가닥 DNA를 변성시킵니다.
- 얼음 위에서 몇 초 동안 얼린 다음 500× g 에서 몇 초 동안 원심분리하여 뚜껑에 응축된 물방울을 떨어뜨립니다.
- 교잡 완충액으로 서던 블롯 멤브레인을 회전하면서 5-10분 동안 간단히 세척합니다.
- 회전과 함께 55°C에서 1시간 동안 혼성화 완충액으로 멤브레인을 사전 혼성화합니다. 하이브리드화 버퍼를 삭제합니다.
- 준비된 프로브와 함께 15mL의 신선한 교잡 완충액(55°C에서 예열)을 멤브레인에 추가합니다. 회전하면서 55°C에서 밤새 멤브레인을 배양합니다.
- 교잡 후 세척을 2회 15분 동안 각각 0.3x SSC, 55°C에서 0.1% SDS로 수행합니다.
- 교잡 후 2회 세척을 각각 15분 동안 0.1x SSC, 55°C에서 0.1% SDS로 수행합니다.
- 교잡 후 2회 세척을 각각 15분 동안 0.1x SSC, 1.5°C에서 55% SDS로 수행합니다.
- 혼성화 튜브에서 멤브레인을 제거하고 멤브레인을 최대 3일 동안 형광자 스크린에 노출시켜 필름에 방사성 각인을 얻습니다.
- 인광 레이저 스캐닝 시스템을 사용하여 필름의 이미지를 획득합니다.
- 시료 전처리
- 단백질 분석
- 시료 전처리
- 1 μL의 β-메르캅토에탄올, PAGE LDS 샘플 버퍼(1x) 및 dH2O를 추가하여 모든 단백질 샘플을 최종 부피(조세포 추출물, 투입, 플로우 스루, 비드 및 용출액 샘플의 경우 각각 200μL, 100μL, 100μL, 20μL 및 20μL)로 조정합니다.
- 샘플을 95°C에서 5분 동안 변성시킵니다.
- 웨스턴 블롯 분석
알림: 표준 프로토콜15,16을 사용하여 SDS-PAGE 및 웨스턴 블로팅을 수행합니다.- 각 샘플의 15μL를 1.5mm SDS-PAGE 겔의 각 웰에 로드합니다.
- PAP(1:2,000) 및 LexA(1:1,000) 항체를 사용하여 4°C에서 하룻밤 동안 배양하여 블롯의 면역염색을 수행합니다. 5% 분유/PBST 용액에 희석합니다.
참고: PAP 분석 후, 두 번째 LexA 항체로 면역염색하기 전에 마일드 스트리핑 프로토콜17 을 사용하여 블롯을 스트리핑할 수 있습니다.
- 시료 전처리
결과
~1.4kb ARS316 크로마틴 도메인의 정제는 구성적으로 발현된 LexA-TAP 어댑터 단백질에 의해 매개되었습니다. 음성 대조군으로 사용하기 위해 LexA-TAP을 발현하지만 통합 RS 및 LexA 결합 부위를 포함하지 않는 동종 균주를 사용하여 정제를 수행했습니다. 그림 3 은 ARS316 유전자좌를 표적으로 하는 대조군과 재조합 가능 균주 모두에 대해 수행된 표준 정제 실험의 DNA 분석 결과를 보여...
토론
특정 표적 게놈 영역의 인자 및 염색질 지형을 식별하는 것은 염색질 연구에서 계속해서 주요 과제를 제기하고 있다18. 이 프로토콜은 효모 염색체에서 뚜렷한 염색질 도메인을 특이적으로 절제하고 정제하는 효율적인 시스템을 설명합니다. 우리가 아는 한, 이 단일 단계 정제의 순도와 수율은 유전자좌 특이적 염색질 정제 방법의 많은 한계를 극복하여 다른 관련 없는 게놈 영?...
공개
저자는 공개할 이해 상충이 없습니다.
감사의 말
S.H. 실험실에서의 작업은 SFB1064(프로젝트 ID 213249687), 유럽 연구 위원회(ERC Starting Grant 852798 ConflictResolution) 및 Helmholtz Gesellschaft를 통해 DFG의 지원을 받았습니다.
자료
| Name | Company | Catalog Number | Comments |
| Yeast strains | |||
| Control Strain: MATa; ura3Δ0; leu2Δ0; his3Δ1; met15Δ0; bar1::kanMX4; Chr I 212kb::LEU2 pTEF2-LEXA-TAP pGAL1-10 RecR | Section 1, see references 13 and 14 | ||
| Recombination Strain: MATa; ura3Δ0; leu2Δ0; his3Δ1; met15Δ0; bar1::kanMX4; RS_LEXA_NS-3_ARS316_NS+3_RS; Chr I 212kb::LEU2 pTEF2-LEXA-TAP pGAL1-10 RecR | Section 1, see reference 13 and 14 | ||
| Plasmid | |||
| K238 plasmid | Section 1, see reference 13 Storage: Store at -20 °C | ||
| K071 Spike-in plasmid DNA | Section 7.1, see reference 13 Storage: Store at -20 °C | ||
| Reagents | |||
| Acetone | Carl Roth | 5025.1 | Section 2 Storage: Store at room temperature |
| Ammonium acetate (NH4Ac) | Sigma Aldrich | A7262 | Section 6 and 7.1 Storage: Store at room temperature |
| Ammonium solution (NH4OH) 25% | Merck Millipore | 533003 | Section 6 Storage: Store at room temperature |
| Ammonium sulfate | Santa Cruz | Sc-29085 | Section 2 Storage: Store at room temperature |
| Bacto agar | BD (VWR) | 90000-760 | Section 3 Storage: Store at room temperature |
| Bacto peptone | BD (VWR) | 211820 | Section 3 Storage: Store at room temperature |
| β-Mercaptoethanol | Sigma Aldrich | 07604 | Section 7.2 Storage: Store at 4 °C |
| Chemiluminescent substrate kit | ThermoFisher | 34580 | Section 7.2 Storage: Store at 4 °C |
| Di-Sodium Hydrogen phosphate dodecahydrate | Merck | 1.06579.1000 | Section 2 and 7.1 Storage: Store at room temperature |
| Dithiothreitol (DTT) | ThermoFisher | 15508013 | Section 4 Storage: Store at 4 °C |
| Ethanol | Merck | 100983 | Section 7.1 Storage: Store at room temperature |
| Ethylenediaminetetraacetic acid (EDTA) | Sigma Aldrich | ED | Section 7.1 Storage: Store at room temperature |
| Galactose (20% (w/v) stock) | Sigma Aldrich | G0625-1KG / 5KG | Section 3 Storage: Store at room temperature |
| Gel loading dye (6x) | BioLabs | B7024A | Section 7.1 Storage: Store at -20 °C |
| Glusose | Sigma-Aldrich | G8270 | Section Storage: Store at room temperature |
| Glycine | Carl Roth | .0079.4 | Section 2 Storage: Store at room temperature |
| Glycogen (5 mg/mL) | Invitrogen | AM9510 | Section 7.1 Storage: Store at -20 °C |
| Hydrochloric acid (HCl) | PanReac AppliChem | 182109.1211 | Section 2, 4 and 7.1 Storage: Store at room temperature |
| Magnesium Acetate (MgAc) | Bernd Kraft | 15274.2600/C035 | Section 4 Storage: Store at room temperature |
| Magnesium chloride (MgCl2) | Sigma Aldrich | M8266 | Section 6 Storage: Store at room temperature |
| Nu PAGE LDS sample buffer (4x) | Invitrogen | 2399549 | Section 7.2 Storage: Store at room temperature |
| Phenol/Chloroform/Isoamyl alcohol (25:24:1 v/v) | Invitrogen | 15593-031 | Section 7.1 Storage: Store at 4 °C |
| Potassium chloride (KCl) | Sigma | P9541 | Section 4 Storage: Store at room temperature |
| Radioactively labeled α-32P dATP (3,000 Ci/mmol, 10 mCi/mL) | Hartmann Analytic | SRP-203 | Section 7.1 Storage: Store at 4 °C |
| RadPrime labeling system | ThermoFisher | 18428-011 | Section 7.1 Storage: Store at -20 °C |
| Raffinose (20% (w/v) stock) | SERVA | 34140.03 | Section 3 Storage: Store at room temperature |
| Sodium chloride (NaCl) | Merck | K53710504142 | Section 7.1 Storage: Store at room temperature |
| Sodium citrate (Na3C6H5O7) | Sigma-Aldrich | 71402 | Section 7.1 Storage: Store at room temperature |
| Sodium hydroxide (NaOH) | Sigma Aldrich | S5881 | Section 7.1 Storage: Store at room temperature |
| Sodium n-dodecyl sulfate (SDS) (5% stock (w/v) ) | Alfa Aesar | A11183 | Section 7.1 Storage: Store at room temperature |
| Sodium phosphate monobasic | Sigma-Aldrich | 71496 | Section 2 and 7.1 Storage: Store at room temperature |
| Sodium azide | Santa Cruz Biotechnology | sc-208393 | Section 2 Storage: Store at -20 °C |
| Triethylamine | Sigma Aldrich | 90340 | Section 2 Storage: Store at room temperature |
| Tris base | Chem Cruz | SC-3715B | Section 2 and 4 Storage: Store at room temperature |
| Triton X-100 | Sigma Aldrich | X100 | Section 2 and 4 Storage: Store at room temperature |
| Tween-20 | Bernd Kraft | 18014332 | Section 4 Storage: Store at room temperature |
| Yeast extract | BD (VWR) | 212720 | Section 3 Storage: Store at room temperature |
| Yeast mating factor alpha (1 µg/mL stock ) | Biomol | Y2016.5 | Section 3 Storage: Store at -20 °C |
| Yeast Synthetic Drop-out medium Supplements without LEUCINE | Sigma Aldrich | Y1376 | Section 1, see reference 14 |
| Enzymes | |||
| HpaI restriction enzyme (5,000 U/mL) | NEB | R0105S | Section 7.1 Storage: Store at -20 °C |
| Protease and Phosphatase Inhibitor Cocktail (100x) | ThermoFisher Scientific | 78446 | Section 4 Storage: Store at4 °C |
| Proteinase K (10 mg/mL) | SERVA | 33756 | Section 7.1 Storage: Store at -20 °C |
| RNase A (10 mg/mL) | ThermoFisher | EN0531 | Section 7.1 Storage: Store at -20 °C |
| TEV protease (10000 U/µL) | NEB | P8112S | Section 5 Storage: Store at -20 °C |
| Materials | |||
| BcMag Epoxy-Activated Magnetic Beads | Bioclone Inc. | FC-102 | Section 2 Storage: Store at 4 °C |
| Dry ice | Section 4 | ||
| Low-binding centrifuge tubes 2.0 mL | Eppendorf | 22431102 | Section 4 |
| Microspin G-25 Columns | Cytiva | 27-5325-01 | Section 7.1 Storage: Store at room temperature |
| Parafilm | Merck | P7793 | Section 4 |
| Positive nylon membrane | Biozol | 11MEMP0001 | Section 7.1 Storage: Store at room temperature |
| PVDF transfer membrane | Immobilon-Merck Millipore | IPVH00010 | Section 7.2 Storage: Store at room temperature |
| SDS-PAGE gel 4-12% bis-tris (15 well, 1.5 mm) | Invitrogen | NP0336BOX | Section 7.2 Storage: Store at 4 °C |
| Syringe (25 mL) with luer fitting | Henke Sass Wolf | 4200-000V0 | Section 3 |
| Whatman paper (Grade 3MM CHR Cellulose Western Blotting Paper Sheet) | Cytiva | 3030-917 | Section 7.1 Storage: Store at room temperature |
| Antibodies | |||
| Anti-LexA, rabbit polyclonal IgG, DNA binding region antibody | Merck Millipore | 06-719 | Section 7.2 Storage: Store at -20 °C |
| Goat Anti-Rabbit IgG (H+L), Horseradish peroxidase conjugate | Invitrogen | G21234 | Section 7.2 Storage: Store at -20 °C |
| Peroxidase Anti-Peroxidase (PAP) antibody produced in rabbit for the detection of TAP-tagged proteins | Sigma Aldrich | P1291-500UL | Section 7.2 Storage: Store at -20 °C |
| Rabbit IgG antibodies | Sigma | I5006-100MG | Section 2 Storage: Store at 4 °C |
| Primers (10 µM) | |||
| ARS316: fwd 5'- CGGCATTATCGTACACAACCT, rev 5'- GTTCTTCGTTGCCTACATTTTCT | Section 7.1 | ||
| K071 Spike-in plasmid DNA: fwd: 5'-TTTTCGCTGCTTGTCCTTTT, rev 5'- CATTTTCGTCCTCCCAACAT | Section 7.1 | ||
| PCR fragment from yeast genomic DNA as a template for ARS316 amplification (for southern blot): fwd 5’- AAATTCTGCCCTTGATTCGT rev 5’- TTTGTTTATCTCATCACTAAT | Section 7.1 | ||
| PDC1: fwd 5'- CATGATCAGATGGGGCTTCA, rev 5'-ACCGGTGGTAGCGACTCTGT | Section 7.1 | ||
| Equipment | |||
| Coffee grinder | Gastroback | 42601 | Section 4 |
| Dewar flask | NAL GENE | 4150-2000 | Section 3 |
| DynaMag TM-2 magnetic rack | Invitrogen | 12321D | Section 4, 5 and 6 |
| Hybridization oven | Hybaid Mini10 | Ri418 | Section 2 |
| Microcentrifuge | Eppendorf | 5424R | Section 4 and 7.1 |
| UV-crosslinker | Analytikjena | 95-0174-02 | Section 7.1 |
참고문헌
- Kornberg, R. D., Lorch, Y. Twenty-five years of the nucleosome, fundamental particle of the eukaryote chromosome. Cell. 98 (3), 285-294 (1999).
- Gauchier, M., van Mierlo, G., Vermeulen, M., Déjardin, J. Purification and enrichment of specific chromatin loci. Nature Methods. 17 (4), 380-389 (2020).
- Korthout, T., et al. Decoding the chromatin proteome of a single genomic locus by DNA sequencing. PLoS Biology. 16 (7), e2005542 (2018).
- Antão, J. M., Mason, J. M., Déjardin, J., Kingston, R. E. Protein landscape at Drosophila melanogaster telomere-associated sequence repeats. Molecular and Cellular Biology. 32 (12), 2170-2182 (2012).
- Déjardin, J., Kingston, R. E. Purification of proteins associated with specific genomic loci. Cell. 136 (1), 175-186 (2009).
- Ide, S., Dejardin, J. End-targeting proteomics of isolated chromatin segments of a mammalian ribosomal RNA gene promoter. Nature Communications. 6, 6674 (2015).
- Unnikrishnan, A., Gafken, P. R., Tsukiyama, T. Dynamic changes in histone acetylation regulate origins of DNA replication. Nature Structural & Molecular Biology. 17 (4), 430 (2010).
- Buxton, K. E., et al. Elucidating protein-DNA interactions in human alphoid chromatin via hybridization capture and mass spectrometry. Journal of Proteome Research. 16 (9), 3433-3442 (2017).
- Kennedy-Darling, J., et al. Discovery of chromatin-associated proteins via sequence-specific capture and mass spectrometric protein identification in Saccharomyces cerevisiae. Journal of Proteome Research. 13 (8), 3810-3825 (2014).
- Liu, S. J., et al. CRISPRi-based genome-scale identification of functional long noncoding RNA loci in human cells. Science. 355, 7111 (2017).
- Hamperl, S., et al. Purification of specific chromatin domains from single-copy gene loci in Saccharomyces cerevisiae. Functional Analysis of DNA and Chromatin. 1094, 329-341 (2014).
- Hamperl, S., et al. Compositional and structural analysis of selected chromosomal domains from Saccharomyces cerevisiae. Nucleic Acids Research. 42 (1), 2 (2014).
- Weiβ, M. Single-copy locus proteomics of early- and late-firing DNA replication origins identifies a role of Ask1/DASH complex in replication timing control. Cell Reports. 42 (2), 112045 (2023).
- Gietz, R. D., Schiestl, R. H. High-efficiency yeast transformation using the LiAc/SS carrier DNA/PEG method. Nature Protocols. 2 (1), 31-34 (2007).
- Laemmli, U. K. Cleavage of structural proteins during the assembly of the head of bacteriophage T4. Nature. 227 (5259), 680-685 (1970).
- Towbin, H., Staehelin, T., Gordon, J. Electrophoretic transfer of proteins from polyacrylamide gels to nitrocellulose sheets: procedure and some applications. Proceedings of the National Academy of Sciences of the United States of America. 76 (9), 4350-4354 (1979).
- Western blot membrane stripping for restaining protocol. Abcam Available from: https://www.abcam.com/protocols/western-blot-membrane-stripping-for-restaining-protocol (2023)
- Vermeulen, M., Déjardin, J. Locus-specific chromatin isolation. Nature Reviews. Molecular Cell Biology. 21 (5), 249-250 (2020).
재인쇄 및 허가
JoVE'article의 텍스트 или 그림을 다시 사용하시려면 허가 살펴보기
허가 살펴보기This article has been published
Video Coming Soon
Copyright © 2025 MyJoVE Corporation. 판권 소유